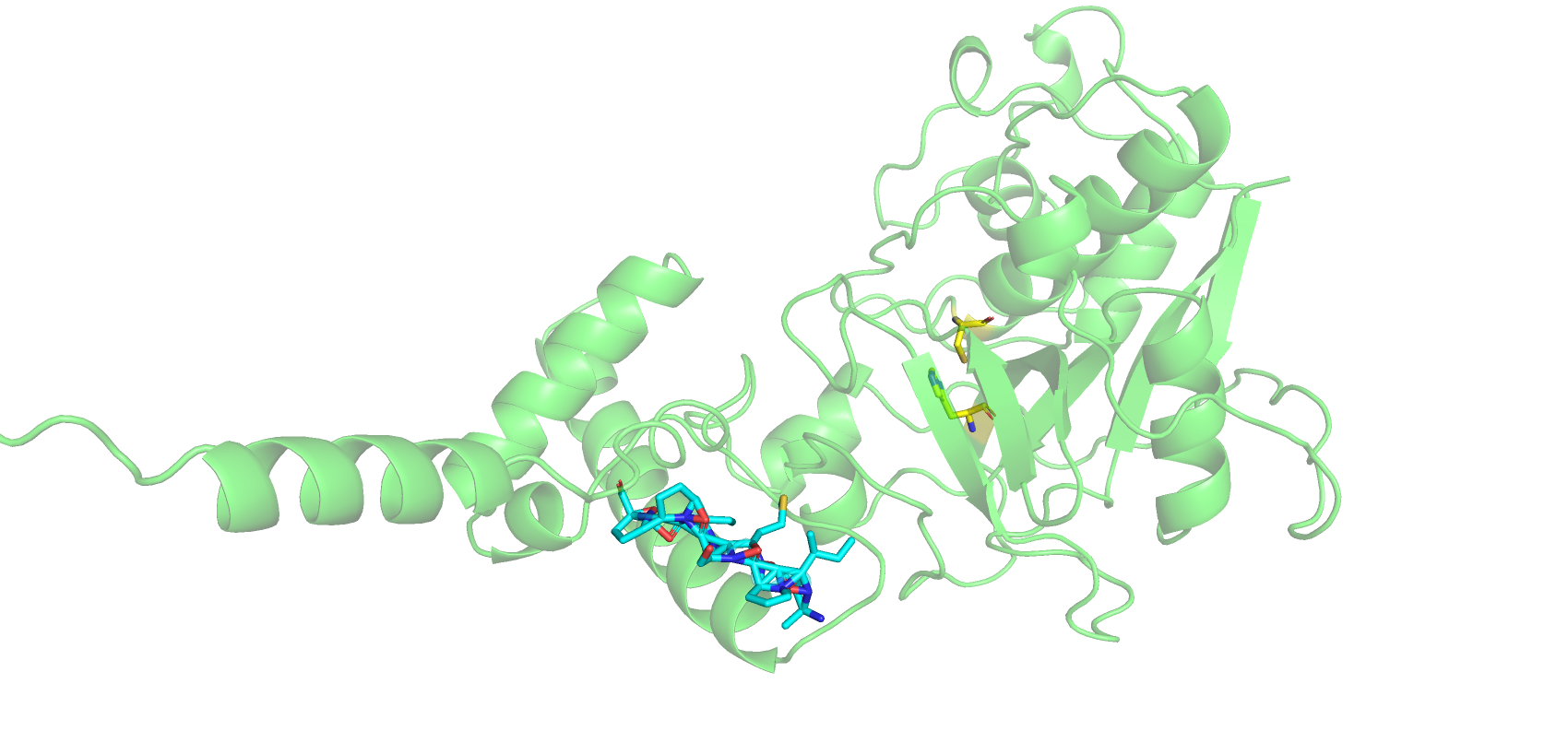
В данном задании было проведено моделирование комплекса папаина и олигопептидного субстрата AIPMSIPP с помощью сервиса AlphaFold2.
Для начала было проведено моделирование субстрата и фермента с его N-концевым пропептидом и сигнальным пептидом. Пропептид препрофермента предотвращает преждевременное связывание активного центра с субстратом. Каталитическая диада папаина состоит из диады Cys-25 и His-159 (Источник: Handbook of Proteolytic Enzymes (Third Edition), pp.1858-1861, chapter 419).

Как видно, связывание в активном центре не произошло, а структура лиганда очень неточная ("месиво" из аминокислот). Возможно, AlphaFold2 неточно предсказывает местоположение лиганда в белке. Также на качество модели могло повлиять наличие участков с 1 по 133 аминокислотный остаток.
Теперь проведем моделирование без участка последовательности 1-133 и сравним результат с предыдущим и с 6TCX.
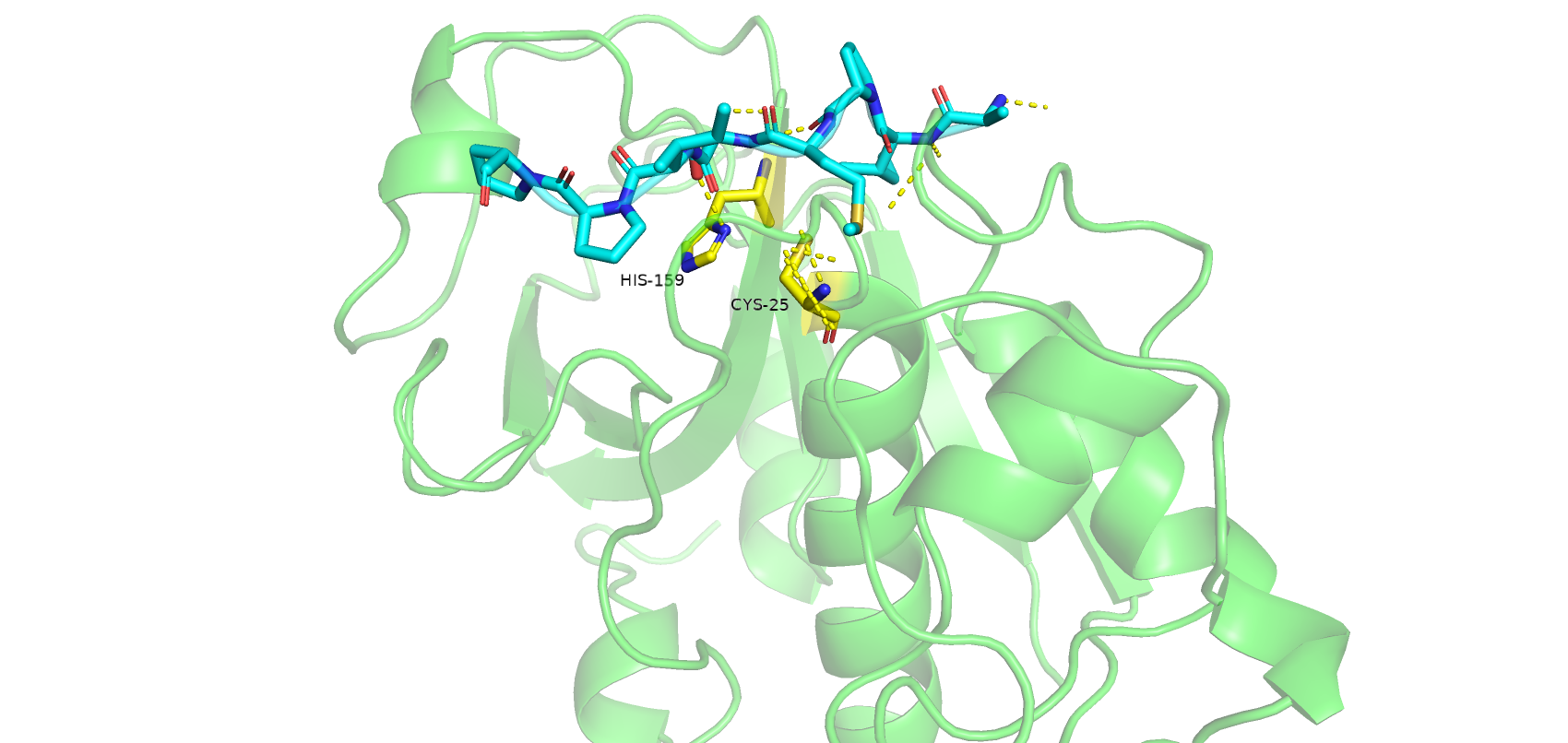
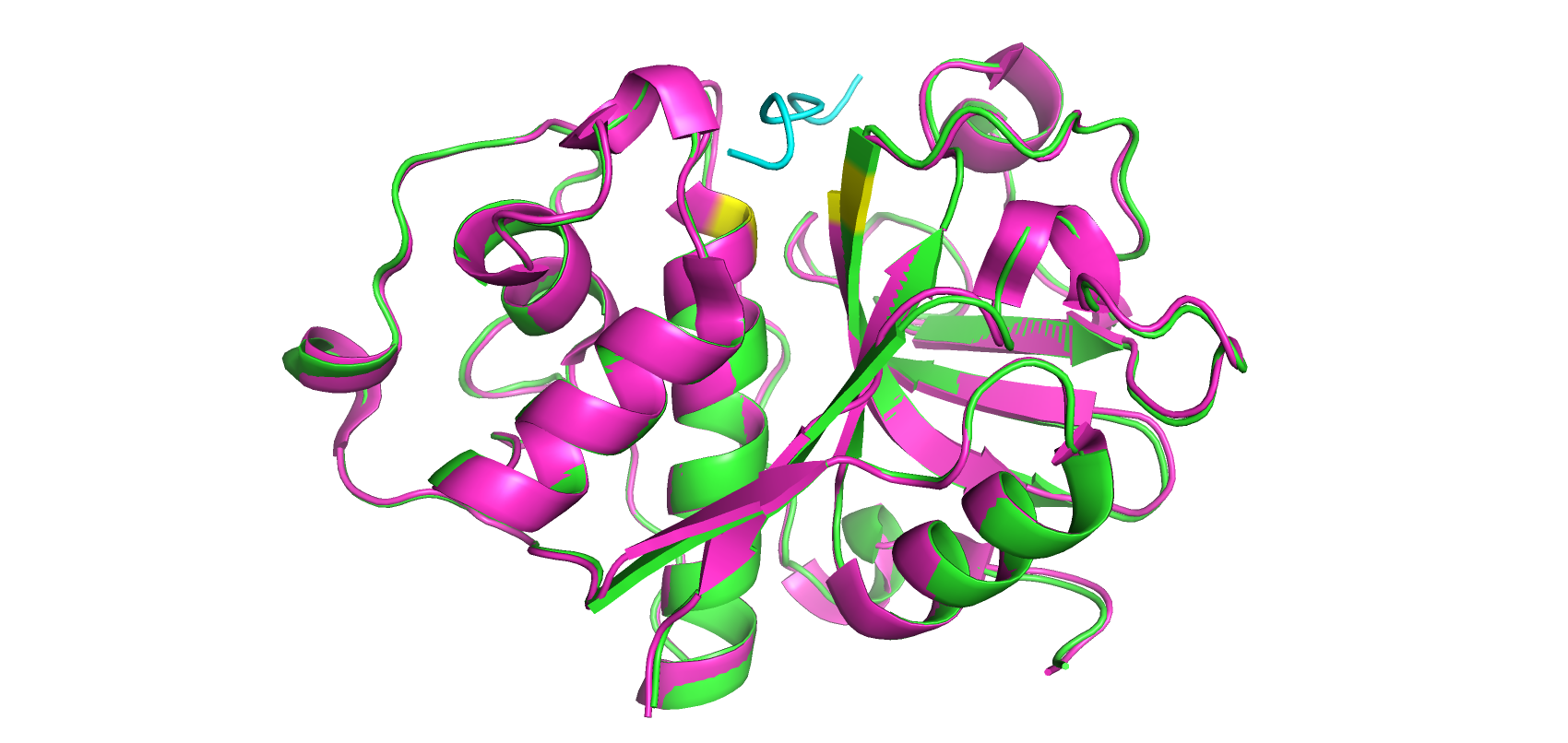
В этот раз связывание произошло гораздо более успешно. Лиганд взаимодействует с His-159 из каталитической диады и находится в месте связывания лиганда (щель между двумя доменами). Однако Cys-25 находится относительно далеко от олигопептида, а сама структура лиганда все равно остается неточной (достаточно посмотреть на концевые остатки пролинов). При сравнении полученной модели и 6TCX из PDB не было найдено существенных различий, что показывает неплохую предсказательную способность сервиса.
Таким образом, в итоге AlphaFold2 удалось достаточно неплохо предсказать структуру комплекса фермент-субстрат. Лиганд расположился вблизи реального кармана связывания, а структура самого фермента была точна. Однако по полученной информации сложно судить о взаимодействиях в активном центре и структуре связанного лиганда. Поэтому, возможно, не следует использовать данный сервис для исследования, например, механизма реакций, а удобно его применять для исследования новых ферментов.
Ссылка на архив1 (первое моделирование), и на архив2 (второе моделирование).
Назад