Blast
- Задание 1. Определение таксономии и функции нуклеотидной последовательности.
Для определения таксономии моей последовательности я запустил megablast c параметрами по умолчанию. Лучшие находки выдачи представлены на Рисунке 1. Далее я выбрал несколько находок с лучшими параметрами E-value, покрытия, идентичности и построил их множественное выравнивание с моей последовательностью (Рисунок 3). Как мне кажется, внутри рода Gammarus замен относительно query меньше, при этом есть участки, где у рода стоит один нуклеотид в конкретной позиции, а у других видов - нет. Таким же образом род Hyppolyte отличается от остальных. Род Hyppolyte имеет с родом Gammarus первый общий таксон - подкласс Eumalacostraca. Тут стоит отметить, что ген оказался очень консервативен, раз в выдаче мы имеем выдачи с высокими параметрами для разных порядков. Также я посмотрел на Blast tree view для выдачи в 500 находок, и там моя последовательность точно находится в кладе амфипод, соседствуя с гаммарусами (Рисунок 4). Можно было бы отнести мою последовательность и к семейству Gammaridae и к роду Gammarus, но в поисках по семейству других родов не найдено, чтобы было с чем сравнить. Я считаю, принадлежность последовательности однозначно можно установить следующим образом: Eukaryota; Metazoa; Ecdysozoa; Arthropoda; Crustacea; Malacostraca; Amphipoda.
Для определения функции последовательности я провел blastx, лучшие находки на Рисунке 2. Видно, что находки с лучшим весом принадлежат совсем не амфиподам, но это можно объяснить тем, что у лучших находок больше покрытие и , следовательно, больший вес, чем у тех же гаммарусов. Функция последовательности - гистон h3, один из коровых гистонов, формирующих нуклеосому. Это можно установить и из нуклеотидного бласта, и из белкового. Еще раз отмечу, что белок оказался очень консервативен - выравнивание нуклеотидных последовательностей с неродственными организмами дает очень высокую (до 100%) идентичность. Значит, большинство нуклеотидных замен не влияют на аминоксилотную последовательность и являются синонимичными.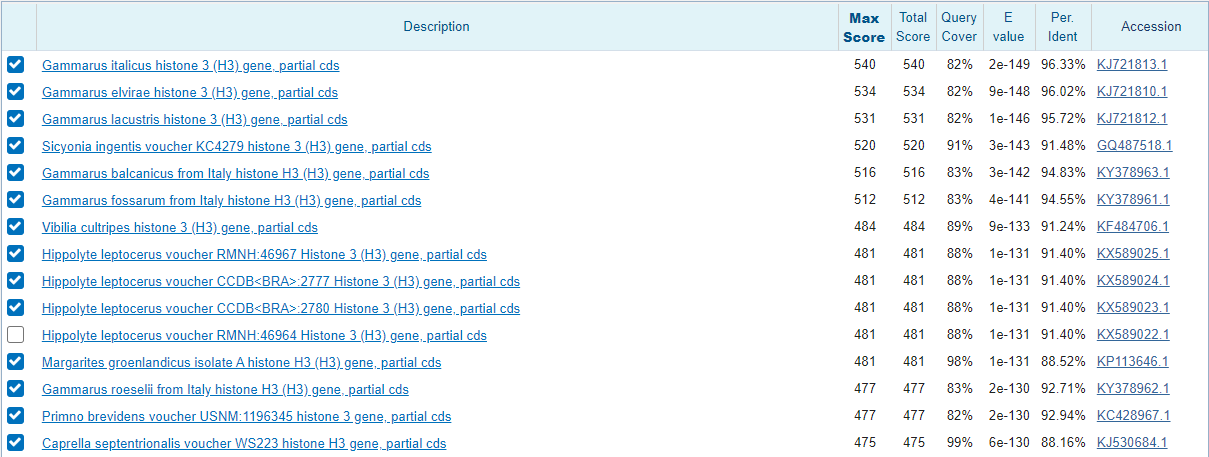
Рисунок 1. Выдача megablast.
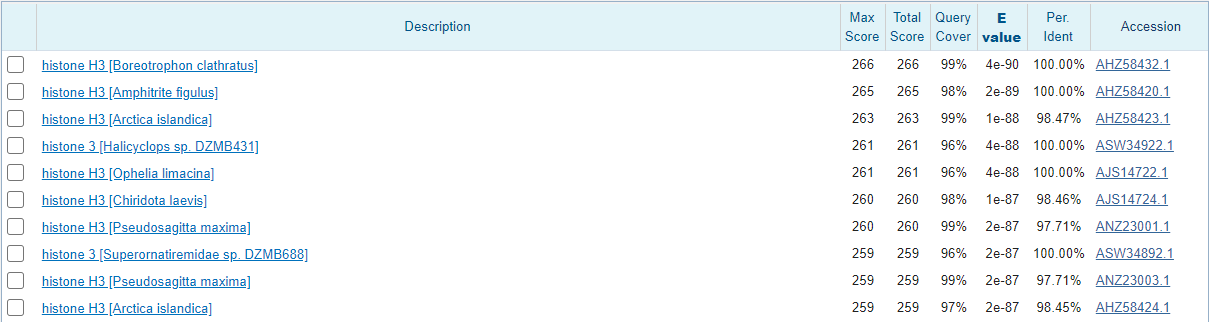
Рисунок 2. Выдача blstx.

Рисунок 3. Выравнивание выдачи megablast.
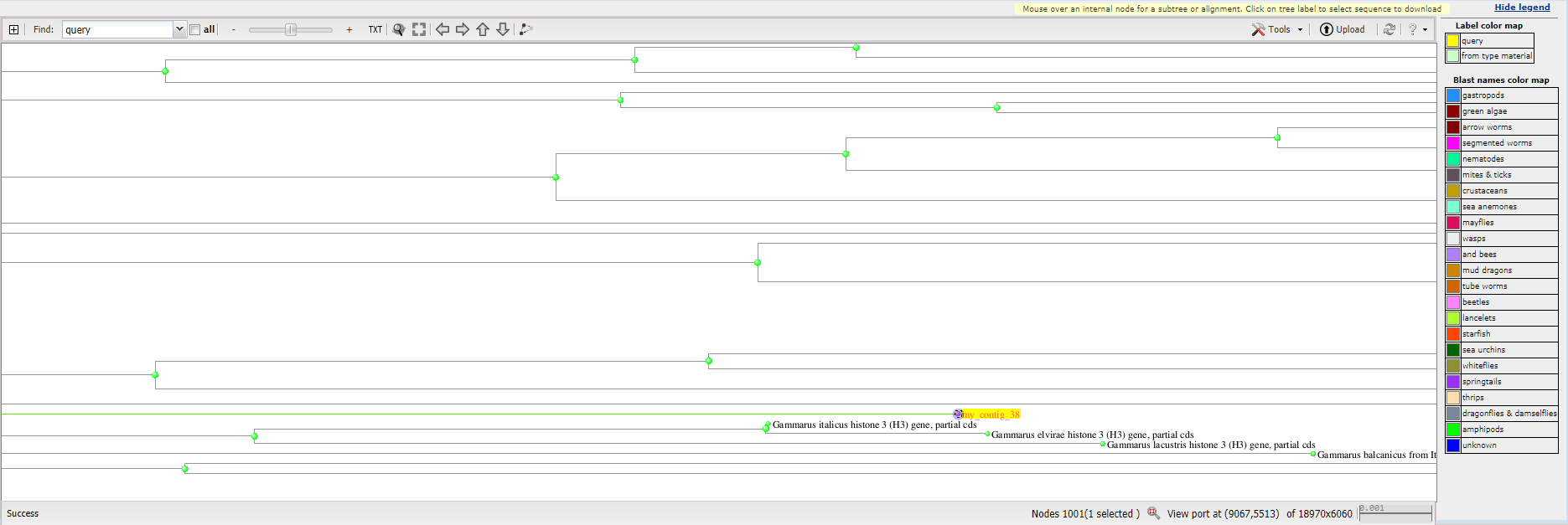
Рисунок 4. Дерево находок.
- Задание 2. Сравнение выдачи разных вариантов запуска blast
В этом задании нужно было сравнить выдачу нескольких вариантов запуска blast (megablast, blastn, sensetive blastn) для последовательности из предыдущего задания и для одного CDS вируса из предыдущего практикума. Я выбрал эту. Запуски я проводил с параметрами по умолчанию, кроме: для всех поставил выдачу 1000, для чувствительного blast длину слова 7 и Match/Mismatch Scores "1,-1". Также я сузил область поиска, оставив/исключив некоторые таксоны (Рисунок 5 и Рисунок 6).
Запуски алгоритмов для консенсуса демонстрируют следующие различия, например: megablast не находит последовательность на Рисунке 7, так как в ней нет слова длиной 28. Blastn с длиной слова 11 ее находит. Выдача обычного нуклеотидного бласта и нуклеотидного отличается, напимер, порядком находок, так как уменьшение штрафа за мисматч увеличивает вес выравнивания (Рисунки 8 и 9).
Для вирусов результаты несколько интереснее. Для всех трех поисков в результаты попали в соновном полные геномы. Megablast дает 4 находки среди родственных вирусов со 100% захватом query и хорошей идентичностью - возможно гомологи исходной cds. Оба запуска blastn дают большое количество находок, однако все c низким query covery. Видимо, это отдельные участки похожих последовательностей. Приведу пример последовательности, найденной чувствительным бластом (выравнивание на Рисунке 10). Снова видно, что длина слова 11 у обычного blastn недостаточна, чтобы обнаружить такую находку.
В целом можно отметить, что изменение длины слова сказывается на количестве находок по базам данных, меньше длина - больше шансов найти такое слово и больше результатов. Изменение Match/Mismatch Scores, из того что я мог заметить, меняет ранжировку результатов алгоритмом, разрешая больше мисматчей, чем в случае по умолчанию.
Рисунок 5. Поиск для консенсуса.
Рисунок 6. Поиск для CDS вируса.
Консенсус Вирус megablast 26 4 blastn 64 245 sens. blastn 68 709 Таблица 1. Полученные находки.
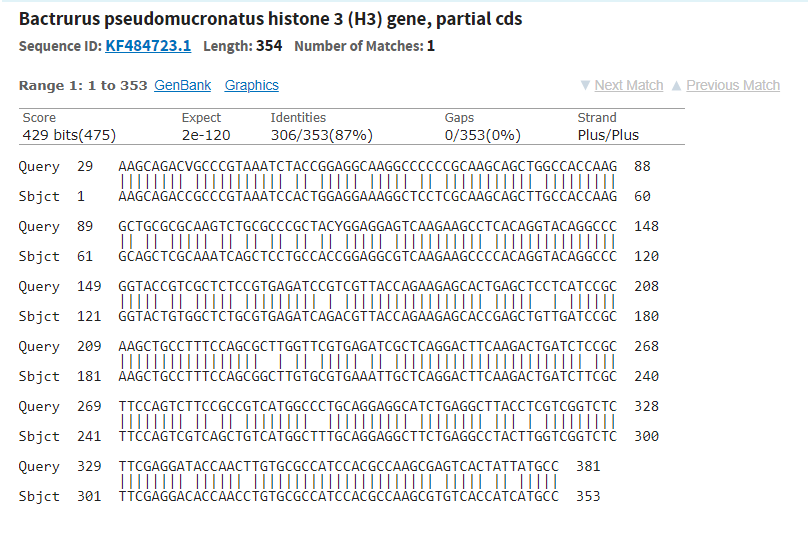
Рисунок 7. Выравнивание, megablast не нашел.
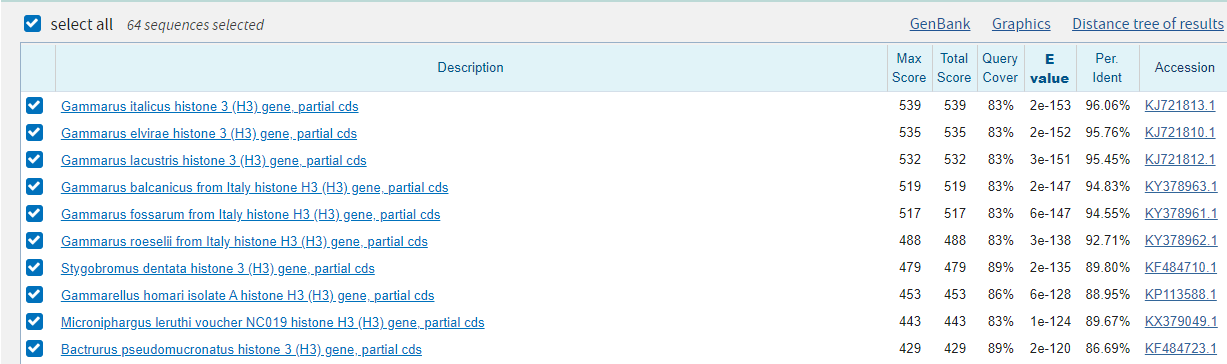
Рисунок 8. Находки blastn по умолчанию.
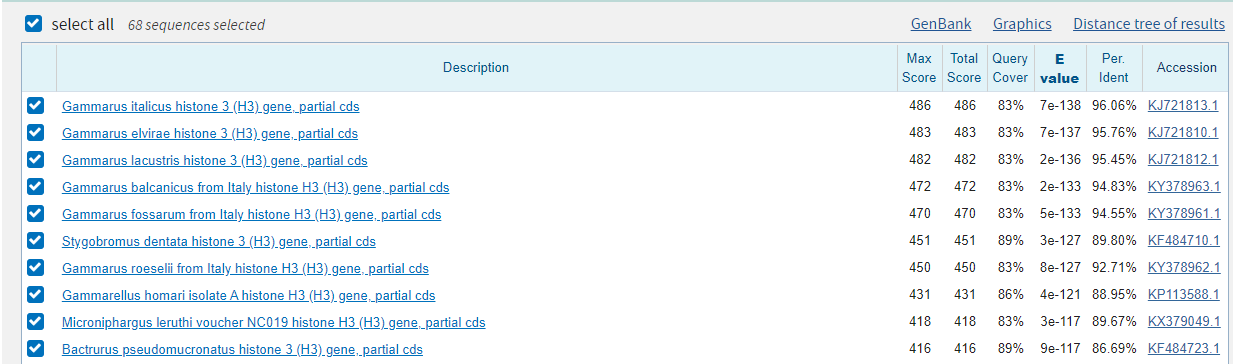
Рисунок 9. Находки blastn чувствительного.
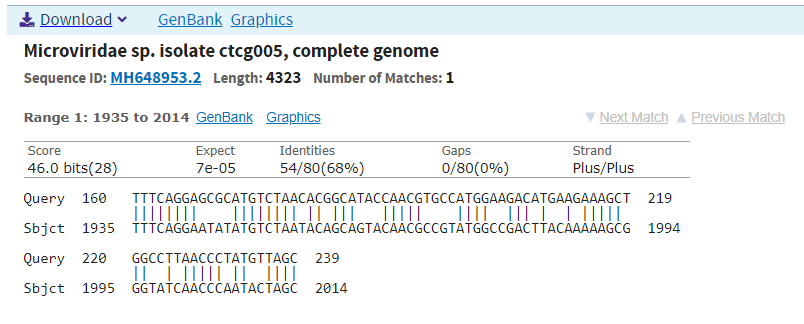
Рисунок 10. Находки blastn чувствительного.
- Задание 3. Поиск белков в геноме.
В это задании нужно было найти гомологи белков с известной функции в неаннотированном геноме Amoeboaphelidium protococcarum. Я выбрал следующие три белка для поиска:
Гистон H3 мыши - белок, учавствующий в образовании нуклеосомы и отвечающий за компактизацию ДНК
Актин мыши - глобулярный белок, образующий скоратительные милофиламенты.
Аконитазу мыши - фермент из гласса лиаз, катализирующий превращение цитрата в изоцитрат в цикле Кребса.
Поиск белков я проводил так: искал в NCBI Protein по названию в All Fields (напр. Histone h3) и Organizm - Mus musculus.
Далее я запустил tblastn на kodomo, предварительно создав базу X5.fasta в своей директории. Я также использовал таблицу генетического кода, указанную в записях GenBank о Amoeboaphelidium protococcarum.makeblastdb -in X5.fasta -dbtype nucl tblastn -query histone_H3.fasta -db_gencode 6 -db X5.fasta -out histone.res tblastn -query aconitase.fasta -db_gencode 6 -db X5.fasta -out aconitase.res tblastn -query actin.fasta -db_gencode 6 -db X5.fasta -out actin.res
Найдены совпадения: гистон актин аконитаза. Считаю результат для каждого белка положительным. Покрытие во всех случаях больше 95%. Не самая высокая идентичность для аконитазы, но в выравнивании много идентичных длинных участков. Согласно записи в GenBank, на участках 95 - 505 и 587 - 735 находятся домены. Примерно в этих участках выравнивания (приведено ниже) прослеживается большая гомологичность.
Белок Достоверных находок Большее E-value Меньший вес Меньшая идентичность Гистон 3 5е-78 254 95 Актин 3 0.00 735 92 Аконитаза 2 0.00 1101 70 Таблица 2. Результаты tblastn.
Query 28 QRAKVAMSHFEPSEYIRYDLLEKNINIVRKRLNRPLTLSEKIVYGHLDDPANQEIERGKT 87 Q KV M++ E ++YI Y +E N+ IVR RL RPLTLSEKIVYGHLDD NQEI+RG++ Sbjct 75347 QLNKVMMNNLEKNQYINYKRIEDNLKIVRDRLQRPLTLSEKIVYGHLDDAKNQEIKRGQS 75526 Query 88 YLRLRPDRVAMQDATAQMAMLQFISSGLPKVAVPSTIHCDHLIEAQVGGEKDLRRAKDIN 147 YLRLRPDRVA QDATAQMA+LQF+S+G+P VAVPST+HCDHLIEAQVGGEKDL RAKDIN Sbjct 75527 YLRLRPDRVACQDATAQMALLQFMSAGMPTVAVPSTVHCDHLIEAQVGGEKDLARAKDIN 75706 Query 148 QEVYNFLATAGAKYGVGFWRPGSGIIHQIILENYAYPGVLLIGTDSHTPNggglggicig 207 +EVY+FL++A AKYG+GFW+PG GIIHQIILENYA+PG L+IGTDSHTPN GGLG + +G Sbjct 75707 KEVYDFLSSACAKYGLGFWKPGGGIIHQIILENYAFPGGLMIGTDSHTPNAGGLGMVAVG 75886 Query 208 vggADAVDVMAGIPWELKCPKVIGVKLTGSLSGWTSPKDVILKVAGILTVKGGTGAIVEY 267 VGGADAVDVMA IPWELKCP VIGVKLTG +SGWTS KDVILKVAGILTVKGGTGAIVEY Sbjct 75887 VGGADAVDVMADIPWELKCPNVIGVKLTGKMSGWTSAKDVILKVAGILTVKGGTGAIVEY 76066 Query 268 HGPGVDSISCTGMATICNMGAEIGATTSVFPYNHRMKKYLSKTGRTDIANLAEEFKDHLV 327 GPGVDS+SCTGMATICNMGAEIGATTS+FP+N RM YL+ T R IA + +F +L Sbjct 76067 FGPGVDSLSCTGMATICNMGAEIGATTSLFPFNSRMADYLNATKRPYIAEASRKFAHNLR 76246 Query 328 PDPGCQYDQVIEINLNELKPHINGPFTPDLAHPVADVGTVAEKEGWPLDIRVGLIGSCTN 387 D G +YDQVIEI+L++L+P+INGPFTPDLA P++ VA+K WP +++V LIGSCTN Sbjct 76247 ADEGAKYDQVIEIDLSKLEPYINGPFTPDLATPLSQFAEVAQKNNWPTELKVALIGSCTN 76426 Query 388 SSYEDMGRSAAVAKQALAHGLKCKSQFTITPGSEQIRATIERDGYAQILRDVGGIVLANA 447 SSYEDM RSA +AKQAL GLK KSQFTITPGSEQIRATIERDG ++L D GG+VLANA Sbjct 76427 SSYEDMDRSANLAKQALDAGLKVKSQFTITPGSEQIRATIERDGQMEVLTDAGGVVLANA 76606 Query 448 CGPCIGQWDRKDIKKGEKNTIVTSYNRNFTGRNDANPETHAFVTSPEIVTALAIAGTLKF 507 CGPCIGQWDRKD+KKGEKN+I+TSYNRNFTGRNDANP THAFV SPE+VTA+A G L+F Sbjct 76607 CGPCIGQWDRKDVKKGEKNSIITSYNRNFTGRNDANPATHAFVASPELVTAMAFGGDLRF 76786 Query 508 NPETDFLTGKDGKKFKLEAPDADELPRSDFDPGQDTYQHPPKDSSGQRVDVSPTSQRLQL 567 NP D L KDGK FK P ELP +DPGQ+TYQ PP+ + +V V P S RLQ Sbjct 76787 NPAKDQLKTKDGKPFKFREPSGHELPARGYDPGQNTYQPPPEQRANVQVVVDPKSNRLQK 76966 Query 568 LEPFDKWDGKDLEDLQILIKVKGKCTTDHISAAGPWLKFRGHLDNISNNLLIGAINIENG 627 L PF K++ KD DL ILIKVKGKCTTDHISAAGPWLK+RGHLDNISNN+LIGAINIEN Sbjct 76967 LTPFPKFNRKDPTDLPILIKVKGKCTTDHISAAGPWLKYRGHLDNISNNMLIGAINIENN 77146 Query 628 KANSVRNAVTQEFGPVPDTARYYKKHGIRWVVIGDENYGEGSSREHAALEPRHLGGRAII 687 KAN V+N + ++ VP AR YKK+G+ WVVIGD+NYGEGSSREHAALE RHLGG AII Sbjct 77147 KANEVKNVLNGKYDAVPAVARDYKKNGVGWVVIGDQNYGEGSSREHAALEVRHLGGVAII 77326 Query 688 TKSFARIHETNLKKQGLLPLTFADPSDYNKIHPVDKLTIQGLKDFAPGKPLKCVIKHPNG 747 KSFARIHETNLKKQG+LPLTFA+ +DY+KI P D++T++G+ APGKP+ +K +G Sbjct 77327 VKSFARIHETNLKKQGMLPLTFANAADYDKIDPTDRVTLKGVSTLAPGKPVTMQVKKASG 77506 Query 748 TQETILLNHTFNETQIEWFRAGSALNRM 775 I LNHTFNE Q+EWF+AGSALN M Sbjct 77507 KTVDIPLNHTFNENQLEWFKAGSALNAM 77590 - Задание 4. Поиск гена в контиге.
Для выполнения этого задания я выбрал скэффолд длиной 25140 нуклеотидов из сборки (Беркут) из предыдущего практикума. Я провел blastx со следующими параметрами (Рисунок 11). Лучшие результаты на Рисунке 12. Со 100% идентичностью и полным покрытием выравнивается ген olfactory receptor 10A7-like того же вида, что и в сборке. Также хорошо (80% идентичность, более 95% покрытие) выравнивается ген olfactory receptor 10A2 Калипты Анны - птицы из семейства колибри. Оба эти гена - обонятельные рецепторы. Это разные белки, но, видимо, трансмембранные участки у них похожи. Ниже приведено выравнивание с геном Беркута. По выравниванию с геном Беркута определим примерные координаты гена в этом скэффолде: 18996 - 19988.
Query 18996 MGPVEEMKPGNQKVTTHFLLLGFAFHGKmqllffmlisimflailiGNSLIVMITTIDPV 19175 MGPVEEMKPGNQKVTTHFLLLGFAFHGKMQLLFFMLISIMFLAILIGNSLIVMITTIDPV Sbjct 1 MGPVEEMKPGNQKVTTHFLLLGFAFHGKMQLLFFMLISIMFLAILIGNSLIVMITTIDPV 60 Query 19176 LHTPMYYFLKNLALTEICYSLSLVHKMLAIFLVERKNNSFTACALQLNCIILFVTCEHFL 19355 LHTPMYYFLKNLALTEICYSLSLVHKMLAIFLVERKNNSFTACALQLNCIILFVTCEHFL Sbjct 61 LHTPMYYFLKNLALTEICYSLSLVHKMLAIFLVERKNNSFTACALQLNCIILFVTCEHFL 120 Query 19356 LGAMAYDQQAAICHPLHYATMMNRDRCFKMAIGSWLSGVPVALGFTTWLFTLPFCGRNTV 19535 LGAMAYDQQAAICHPLHYATMMNRDRCFKMAIGSWLSGVPVALGFTTWLFTLPFCGRNTV Sbjct 121 LGAMAYDQQAAICHPLHYATMMNRDRCFKMAIGSWLSGVPVALGFTTWLFTLPFCGRNTV 180 Query 19536 NHFFCDVSPVLKLVCADTALFELLIFIAIVIVMIPFSLTGISYLCITHAVLQISSAVGQR 19715 NHFFCDVSPVLKLVCADTALFELLIFIAIVIVMIPFSLTGISYLCITHAVLQISSAVGQR Sbjct 181 NHFFCDVSPVLKLVCADTALFELLIFIAIVIVMIPFSLTGISYLCITHAVLQISSAVGQR 240 Query 19716 RAFSTCAAHLVVVTLFYSTTGIIHLQPKSSISSNMKKMVSLSYTVVTPMLDPIIYSLRNQ 19895 RAFSTCAAHLVVVTLFYSTTGIIHLQPKSSISSNMKKMVSLSYTVVTPMLDPIIYSLRNQ Sbjct 241 RAFSTCAAHLVVVTLFYSTTGIIHLQPKSSISSNMKKMVSLSYTVVTPMLDPIIYSLRNQ 300 Query 19896 EVKQSLRRCIDRCLLRKQMAFFSSIQVMDSL 19988 EVKQSLRRCIDRCLLRKQMAFFSSIQVMDSL Sbjct 301 EVKQSLRRCIDRCLLRKQMAFFSSIQVMDSL 331
Рисунок 11. Параметры blastx.
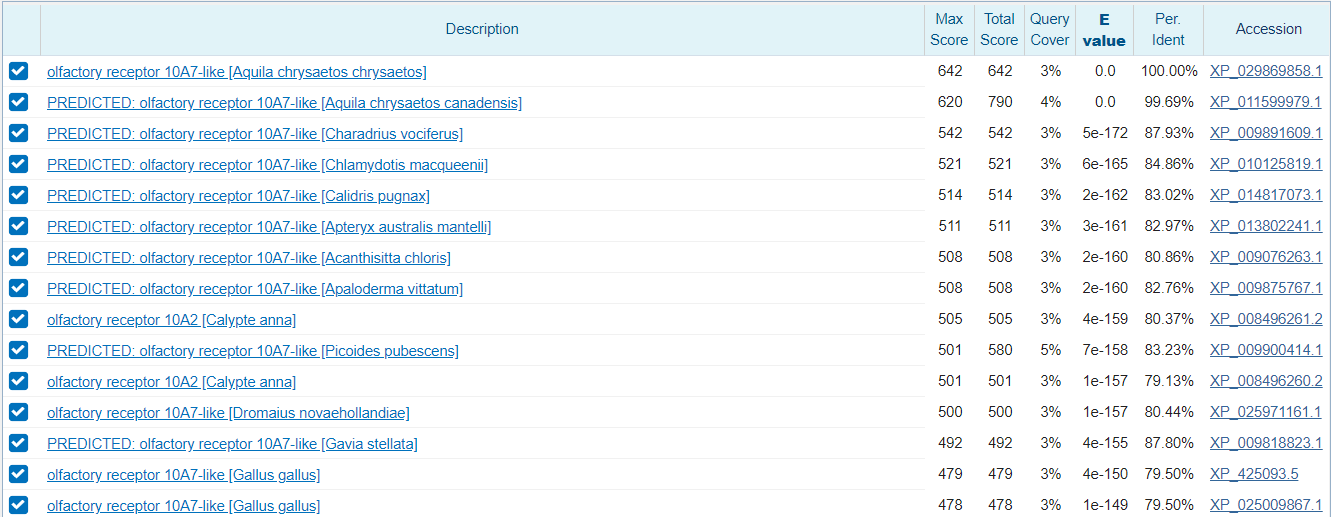
Рисунок 12. Выдача blastx.