С помощью программы Rasmol определили несколько важных параметров, необходимых для исследования неизвестной ДНК.
| A-форма | B-форма | Файл dna30.pdb | ||
| Тип спирали | Правая | Правая | Правая | |
| Шаг спирали | 28.028 | 33.752 | 33.347 | |
| Число оснований на виток |
11 | 10 | 10 | |
| Ширина большой бороздки | 16.808 | 17.216 | 17.315(от фосфата 5 основания цепи В) | 17.009(от фосфата 6 основания цепи В) |
| Ширина малой бороздки | 7.985 | 11.694 | 13.238(от фосфата 1основания цепи А) | 13.949(от фосфата 2 основания цепи А) |
Проанализируем полученную таблицу.
Сначала мы исследовали две формы ДНК: А и В. Можно сказать, что эти формы сходны по типу спирали,
но отличаются по шагу, числу оснований в витке, ширине бороздок. Кроме того следует заметить, что в
форме А глубина большой бороздки больше, чем радиус всей спирали. Это приводит к возникновению отверстия,
которое видно, если смотреть с торца. Такое различие в структуре порождается различием в геометрии остова
ДНК, а именно в стерике сахара: в А-форме атом С3' находится вне плоскости кольца дезоксирибозы (3' -
эндо конформация), а в В-форме - атом С2' (2' - эндо конформация)(более подробный разбор следует далее).
Важно заметить, что ширины малой и большой бороздок не изменяется от одного нуклеотидного остатка к
другому.
Теперь взглянем на исследуемую ДНК (dna30).
| A-форма | B-форма | dna30 |
Заметим очень интересный факт, при измерении величины борозд исследуемой dna30 расстояние меняется от остатка к остатку, в то время как у А- и В- форм такого не наблюдается. Это говорит о том, что fiber строит "идеальные" цепи, а структура dna30, полученная экспериментальным путем учитывает взаимодействия ДНК с другими соединениями, учитывает действие внешних природных факторов. Поэтому, скорее всего, структура dna30 отображена более реально.
К этим всем исследованиям добавим еще одно, очень интересное, связанное с формированием спирали той или иной формы Обратим внимание на строение остова всех трёх структур, для этого выделим один нуклеотидный остаток для каждой структуры.
| А-форма | B-форма | dna30 |
Как видно из картинок, сделанных с помощью Rasmol, в цикле дезоксирибозы у разных форм наблюдается разное расположение атомов:
Программа find_pair, торсионные углы.
Сначала для каждого файла со структурами
запустили программы find_pair и analyze: Изображение стопочных структур с помощью pdb2img
find_pair -t XXXX.pdb stdout | analyze, где XXXX- имя файла.
Получили среди многих файлов нужные для рассмотрения XXXX.out
В них в поле Main chain and chi torsion angles нашли значения торсионных углов.
Note:
alpha: O3'(i-1)-P-O5'-C5'
beta: P-O5'-C5'-C4'
gamma: O5'-C5'-C4'-C3'
delta: C5'-C4'-C3'-O3'
epsilon: C4'-C3'-O3'-P(i+1)
zeta: C3'-O3'-P(i+1)-O5'(i+1)
chi for pyrimidines(Y): O4'-C1'-N1-C2
chi for purines(R): O4'-C1'-N9-C4
Из данных таблиц видно, что у А- и В- форм ДНК углы alpha, beta, gamma, epsilon примерно сходны. У dna30
также данные углы такие же. А вот углы delta, zeta, chi расходятся довольно значительно у А- и В- форм.
dna30 по этим угам близка к В-форме. Это еще раз доказывает близость этих структур.Значения торсионных углов A-форма B-форма
Strand I
base alpha beta gamma delta epsilon zeta chi
1 G --- 174.8 41.7 79.0 -147.8 -75.1 -157.2
2 A -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
3 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
4 C -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
5 G -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
6 A -51.7 174.8 41.7 79.0 -147.8 -75.1 -157.2
7 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
8 C -51.7 174.8 41.7 79.0 -147.8 -75.0 -157.2
9 G -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
10 A -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
11 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
12 C -51.7 174.8 41.7 79.1 -147.7 -75.1 -157.2
13 G -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
14 A -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
15 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
16 C -51.7 174.8 41.7 79.1 --- --- -157.2
Strand II
base alpha beta gamma delta epsilon zeta chi
1 C -51.7 174.8 41.7 79.0 --- --- -157.2
2 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
3 A -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
4 G -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
5 C -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
6 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
7 A -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
8 G -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
9 C -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
10 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
11 A -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
12 G -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
13 C -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
14 T -51.7 174.8 41.7 79.1 -147.8 -75.1 -157.2
15 A -51.7 174.8 41.7 79.0 -147.8 -75.1 -157.2
16 G --- 174.8 41.7 79.1 -147.7 -75.1 -157.2
Strand I
base alpha beta gamma delta epsilon zeta chi
1 G --- 136.4 31.1 143.4 -140.8 -160.5 -98.0
2 A -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
3 T -29.9 136.3 31.1 143.3 -140.8 -160.5 -97.9
4 C -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
5 G -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
6 A -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
7 T -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
8 C -29.9 136.3 31.1 143.3 -140.8 -160.5 -97.9
9 G -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
10 A -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
11 T -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
12 C -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
13 G -29.9 136.3 31.1 143.3 -140.8 -160.5 -98.0
14 A -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
15 T -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
16 C -29.9 136.4 31.1 143.4 --- --- -98.0
Strand II
base alpha beta gamma delta epsilon zeta chi
1 C -29.9 136.4 31.1 143.4 --- --- -98.0
2 T -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
3 A -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
4 G -29.9 136.3 31.1 143.3 -140.8 -160.5 -98.0
5 C -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
6 T -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
7 A -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
8 G -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
9 C -29.9 136.3 31.1 143.3 -140.8 -160.5 -97.9
10 T -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
11 A -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
12 G -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
13 C -29.9 136.4 31.1 143.4 -140.8 -160.5 -98.0
14 T -29.9 136.3 31.1 143.3 -140.8 -160.5 -97.9
15 A -29.9 136.3 31.2 143.3 -140.8 -160.5 -98.0
16 G --- 136.4 31.1 143.4 -140.8 -160.5 -98.0
dna30
Strand I
base alpha beta gamma delta epsilon zeta chi
1 A --- --- 175.9 139.2 172.7 -97.2 -108.0
2 C -60.5 -168.7 51.6 138.8 -166.6 -96.6 -105.8
3 C -52.9 172.7 34.8 120.4 -176.8 -93.0 -109.8
4 G -60.3 174.8 50.1 137.1 -148.8 -169.7 -92.7
5 A -48.3 149.6 46.2 142.2 -172.2 -86.1 -111.6
6 C -63.9 175.5 47.0 110.5 -174.8 -85.3 -119.9
7 G -61.4 172.7 46.2 112.1 176.9 -91.9 -115.0
8 T -54.9 176.4 45.2 115.6 178.3 -90.5 -117.1
9 C -53.6 162.9 48.2 86.2 -166.4 -83.6 -141.6
10 G -56.6 177.6 57.4 140.1 -178.9 -93.2 -107.5
11 G -68.4 -175.3 48.7 119.0 178.6 -87.7 -116.0
12 T -72.3 173.7 58.5 84.9 --- --- -137.5
Strand II
base alpha beta gamma delta epsilon zeta chi
1 T -72.0 173.8 51.7 83.4 --- --- -136.7
2 G -57.6 -177.5 32.5 138.1 -179.2 -91.4 -104.7
3 G -64.4 154.4 43.3 146.4 -170.2 -106.8 -100.0
4 C -60.3 171.9 40.2 141.0 -129.4 -178.4 -81.9
5 T -57.9 -175.7 49.4 132.3 -168.6 -90.7 -108.3
6 G -73.5 141.4 39.5 132.3 -176.3 -100.7 -113.3
7 C -66.5 172.6 38.7 138.1 -96.5 169.9 -88.6
8 A -55.7 175.8 46.0 140.7 -162.8 -87.8 -116.3
9 G -75.3 173.2 48.1 135.6 -171.1 -134.7 -98.2
10 C -54.7 163.3 48.0 117.8 -164.8 -84.0 -120.7
11 C -68.8 178.3 55.2 124.3 -160.4 -112.9 -111.3
12 A --- --- -175.2 148.2 -177.3 -83.8 -109.3
Стопочные структуры для А-формы Вид с торца Вид сбоку 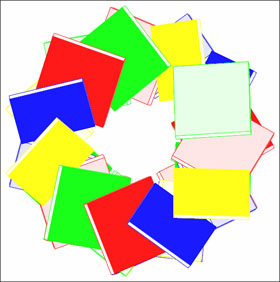

Стопочные структуры для B-формы Вид с торца Вид сбоку 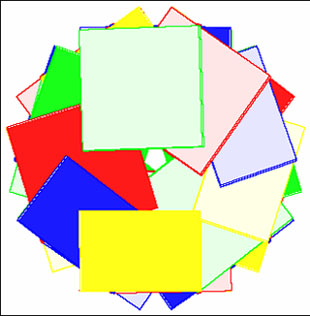
Стопочные структуры для dna30 Вид с торца Вид сбоку 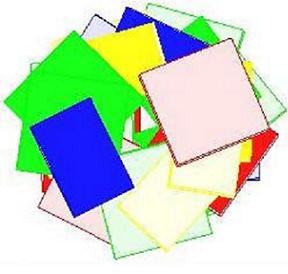
Все полученные изображения еще раз доказывают большое сходство dna30 и В-формы ДНК.
©Ивин Юрий