G C C G A G G U A G C U C A G U U G G U A G A G C A U G C G A C U G A A A A U C G C A G U G U C C G C G G U U C G A U U
Команды для получения изображения в Rasmol:
background white restrict RNA wireframe off backbone 250 define helix1 1-7:C,66-72:C select helix1 color red define helix2 49-53:C,61-65:C select helix2 color green define helix3 39-44:C,26-31:C select helix3 color grey define helix4 10-13:C,22-25:C select helix4 color blue select phosphorus and G1 label G1 color black select phosphorus and A76 label A76 color black |
Анализ структуры с помощью Rasmoll.
- С помощью Rasmoll были найдены внеспиральные стекинг-взаимодействия:
Вне спиралей между плоскостями оснований возникат взаимодействия(стекинг), которые приводят к образованию одноцепочечной спирали. - Cвязи между основаниями, не сводящиеся к Уотсон-Криковскому взаимодействию комплементарных оснований:
44 G — A 26
14 A — U 8
15 G — C 48
16 A — U 59
18 G — U 55
73 A — C 74
45 U — A 8 - Спирали в данной тРНК являются двухцепочечными. На виток приходится 11 пар оснований. Кроме того если смотреть с торца, в спирали есть отверстие. Следовательно спираль тРНК близка по структуре к А-форме ДНК.
Вводимая нуклеотидная последовательность:trna.fasta
Штраф за гэп [12]: 12
Минимальный значение порога [50]:10 (при выборе 15, 20 или 50 программа выравнивание не находит)
Значение основания (канонической пары) [3]:3
Значение неканонической пары("несоответствие") [-4]:enter
Выходной файл : outfile.inv
SEQUENCE: Score 21: 7/7 (100%) matches, 0 gaps
1 gccgagg 7
|||||||
72 cggctcc 66
Полученное выравнивание соотносится по составу с первой спиралью, указанной программой find_pair. Einverted, по-видимому, не учитывает неканонические взаимодействия, поэтому эта программа не показала другие спирали, в которых присутствуют такие взаимодействия.
Программа mfold.
mfold SEQ=trna1.fasta
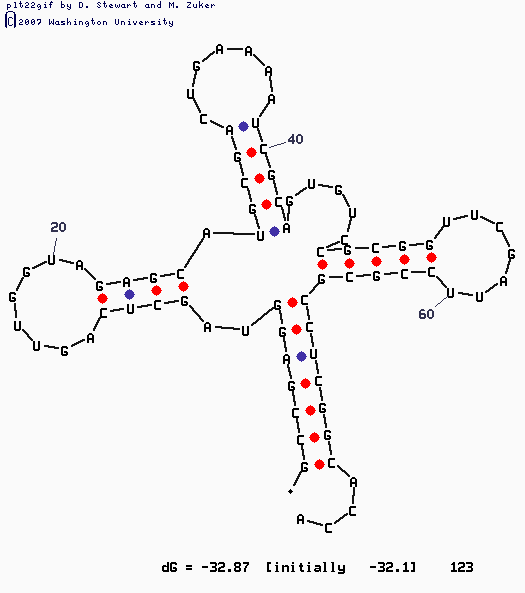 |
На данной картинке представлена структура тРНК, полученная программой mfold. Эта структура очень сходна с той, которая получена с помощью find_pair(те же самые спирали). Отличие состоит в том, что mfold не учитывает неканонические взаимодействия между основаниями, поэтому структура построена без учета них. Эта структура получена под номером 1. |