Алгоритмы (окончание). Укоренение. Сравнение деревьев. Бутстрэп
Реконструкция дерева по нуклеотидным последовательностям
Для организмов из пердыдущих двух практикумов, за исключением Ostrinia nubilalis и Tetrodontophora bielanensis, было построено дерево по нуклеотидным последовательностям 12S рРНК. Последовательности были получены из GenBank, и перед построением дерева были выровнены программой muscle. Дерево строилось программой fastme, с помощью модели Тамуры-Неи (TN93). Она рассчитывает эволюционное расстояние между последовательностями, учитывая разные частоты четырёх нуклеотидов (A, C, G, T) и раздельные скорости для двух типов транзиций (между пуринами A↔G и между пиримидинами C↔T) относительно общего уровня трансверсий. Приминялась опция -r, так как в выравнивании было немало гэпов (вероятнее всего из-за не слишком близкого родства выбранных организмов).
fastme -i 12S.phy -o 12S.tree -dT -r
Получилось следующее дерево:
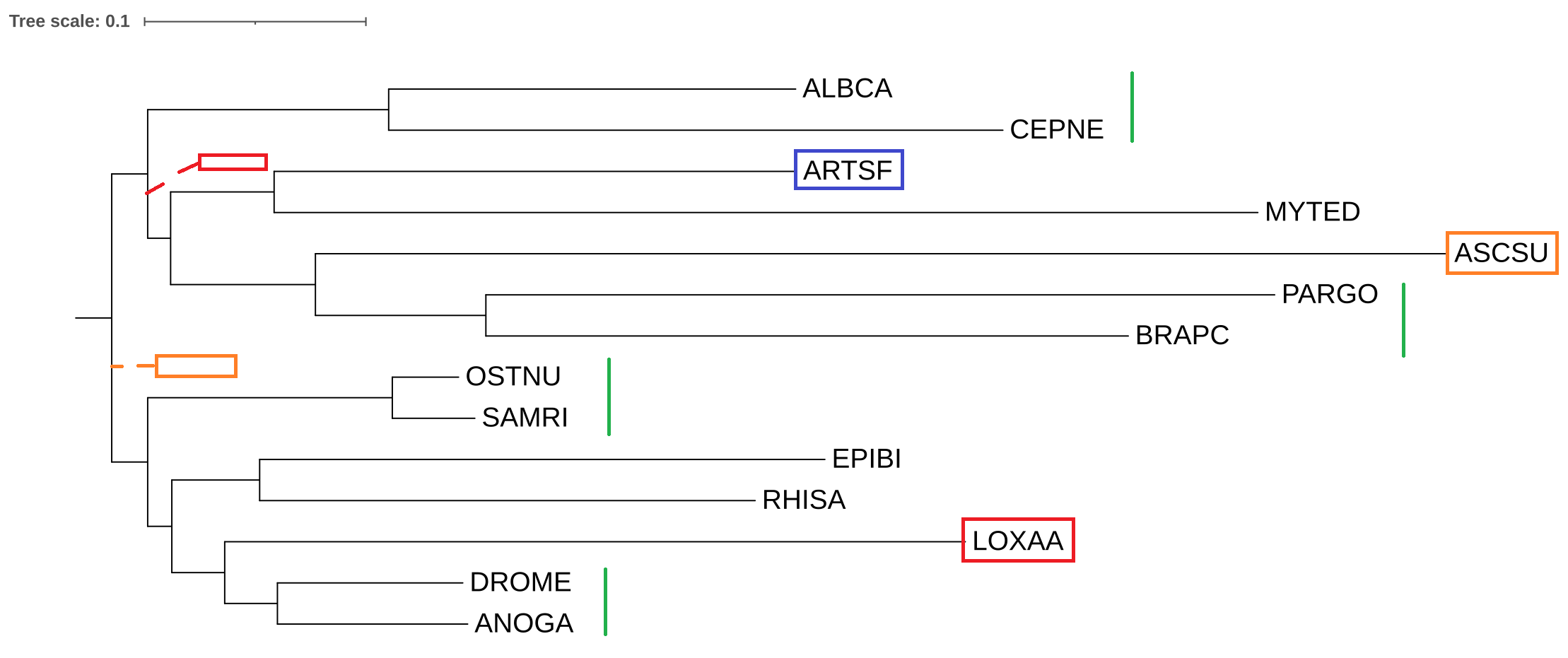
Дерево получилось неплозим, но многие организмы были правильно расположены только по парам. Однако многие организмы в нём расположены не совсем правильно. Много где перепутаны порядки ответвления. Деревья построенные по цитохрому б (хотя бы одно) были лучше по моему мнению.
Укоренение во внешнюю группу
Далее было решено укоренить дерево построенное по цитохрому б с помощью модели MtREV, воспользовавшись организмом из внешней (не первичноротые) группы. Я выбрал миногу: Petromyzon marinus. Проделал шаги как в предыдущем практикуме и получил следующее дерево:
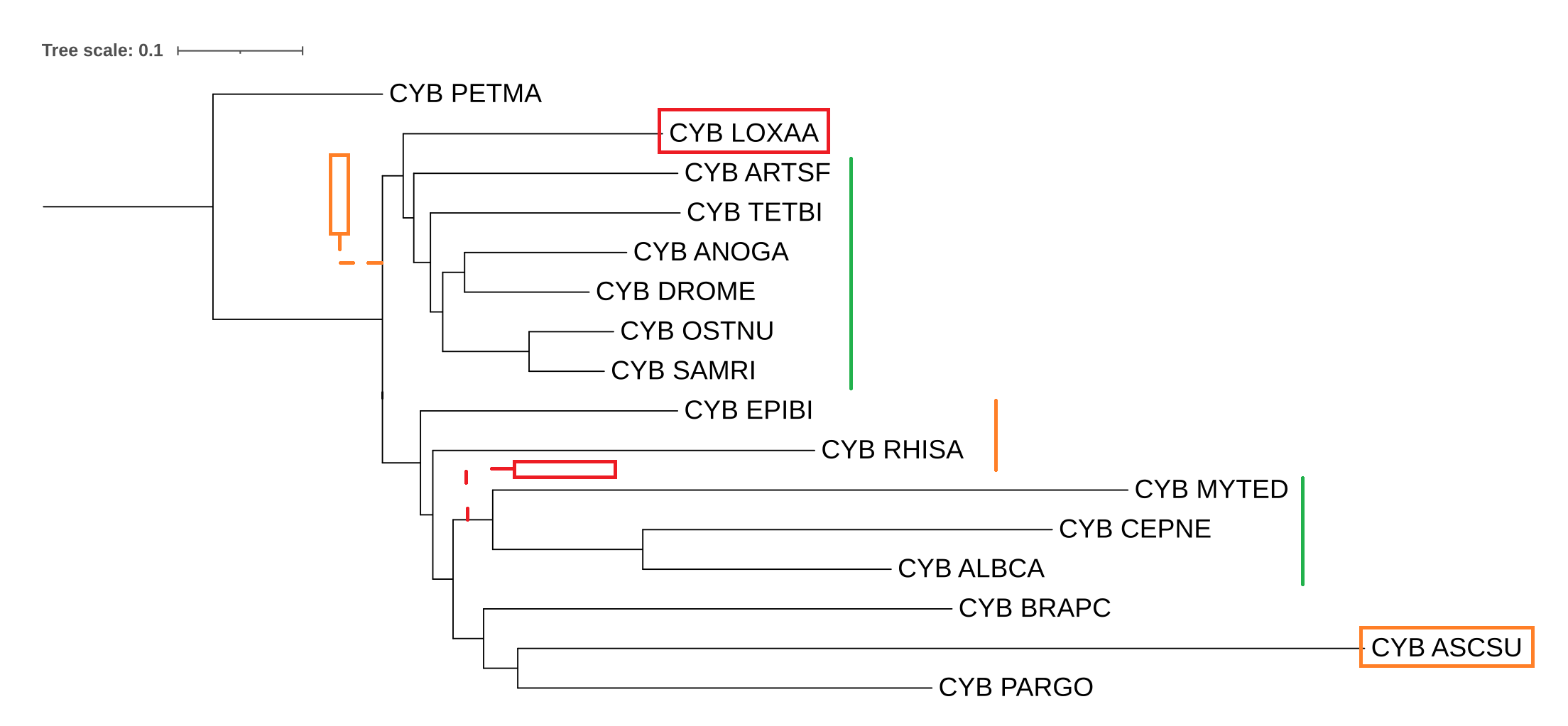
Полученное таким способом дерево получилось довольно неплохим. Есть большие клады, которые оказались там где надо на дереве.
Бутстреп
Для дерева полученного в задании выше (с внешней группой) было решено сделать 100 реплик бутстрепа. Для этого к уже известной команде fastme была дополнительно дописана опция "-b 100". Был получен следующий результат:
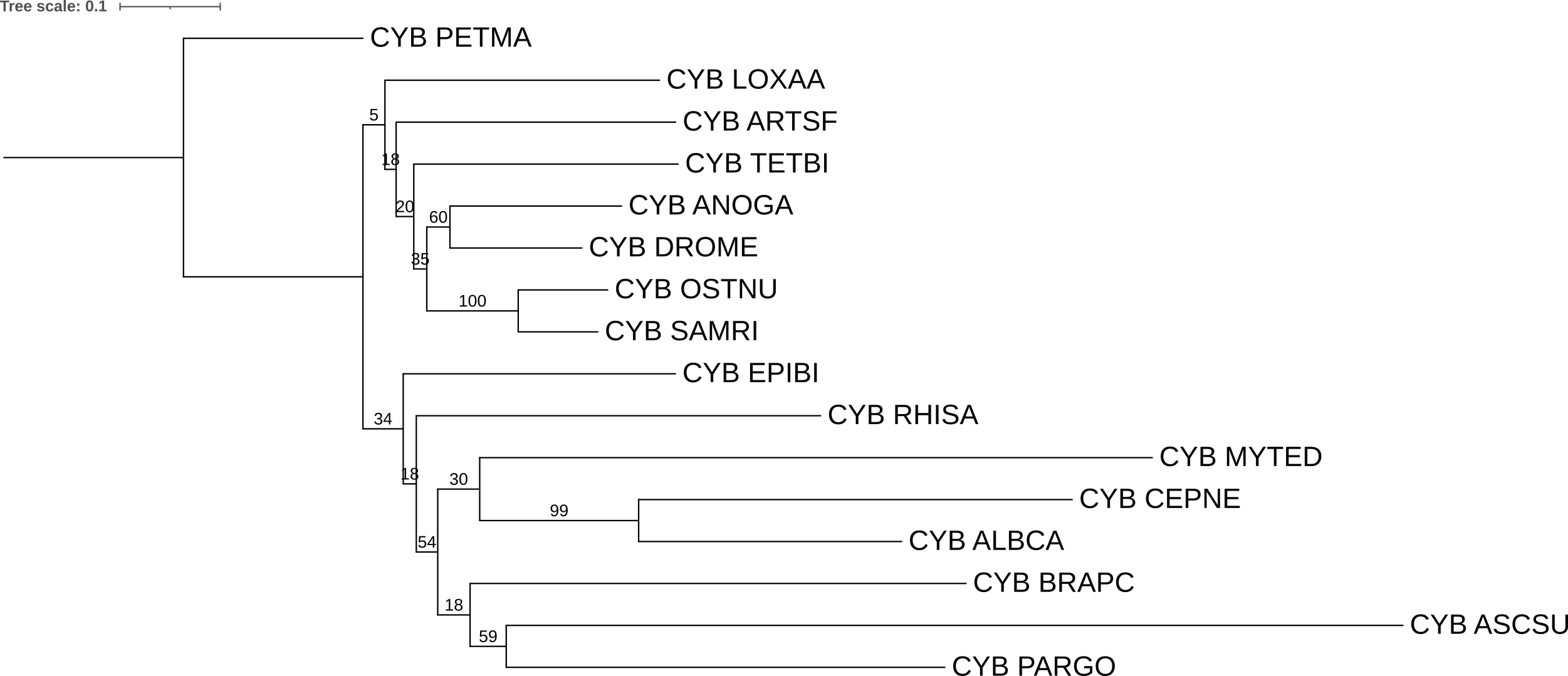
Можно увидеть, что некоторые клады получались очень часто и они на самом деле и являются правильными. Есть странность в верхней ветке, где ветвь образующая самую большую правильную кладу имеет значние 18. LOXAA действительно неправдобадобно располгается на дереве, что и показал данный анализ. Однако неоднозначная ситуация с ASCSU, который оказался не в той базальной кладе, но ветвь имеет значение 59.