Поиск гомологов белка CLPX_ECOLI
Гомологи данного белка я искал в 7 бакетриях: Bartonella henselae (BARHE), Bordetella pertussis (BORPE), Brucella suis biovar 1 (BRUSU), Burkholderia mallei (BURMA), Saccharophagus degradans (SACD2), Serratia proteamaculans (SERP5), Shewanella denitrificans (SHEDO).
Были скачаны протеомы этих бактерий, объединены в один файл database.fa и была создана база данных:
makeblastdb -in database.fa -dbtype prot
Также была скачена последовательность белка CLPX_ECOLI. Далее был произведён поиск гомологов с помощью blastp:
blastp -query P0A6H1.fasta -db database.fa -evalue 0.0001 -outfmt 7 -out out.txt
Список наxодок blast в файле.
Дальше были отобраны нужные белки (ura.fa) из протеомов и сделано выравнивание:
muscle -align ura.fa -output aligned_ura.fa
Далее выравнивание было переведено в другой формат и было построено дерево с помощью программы IQTree:
iqtree -s ura.phy -B 1000
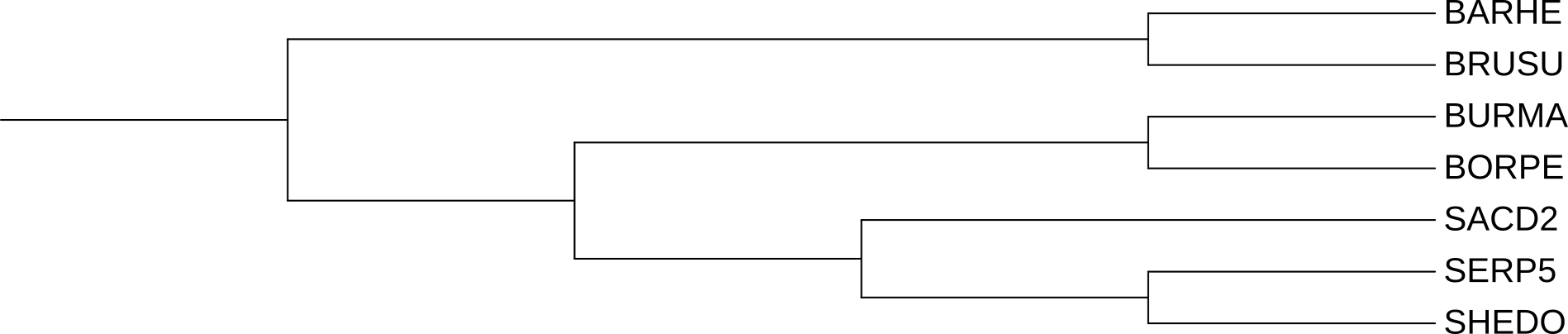
Было получено дерево (рис. 1). Скобочная формула.
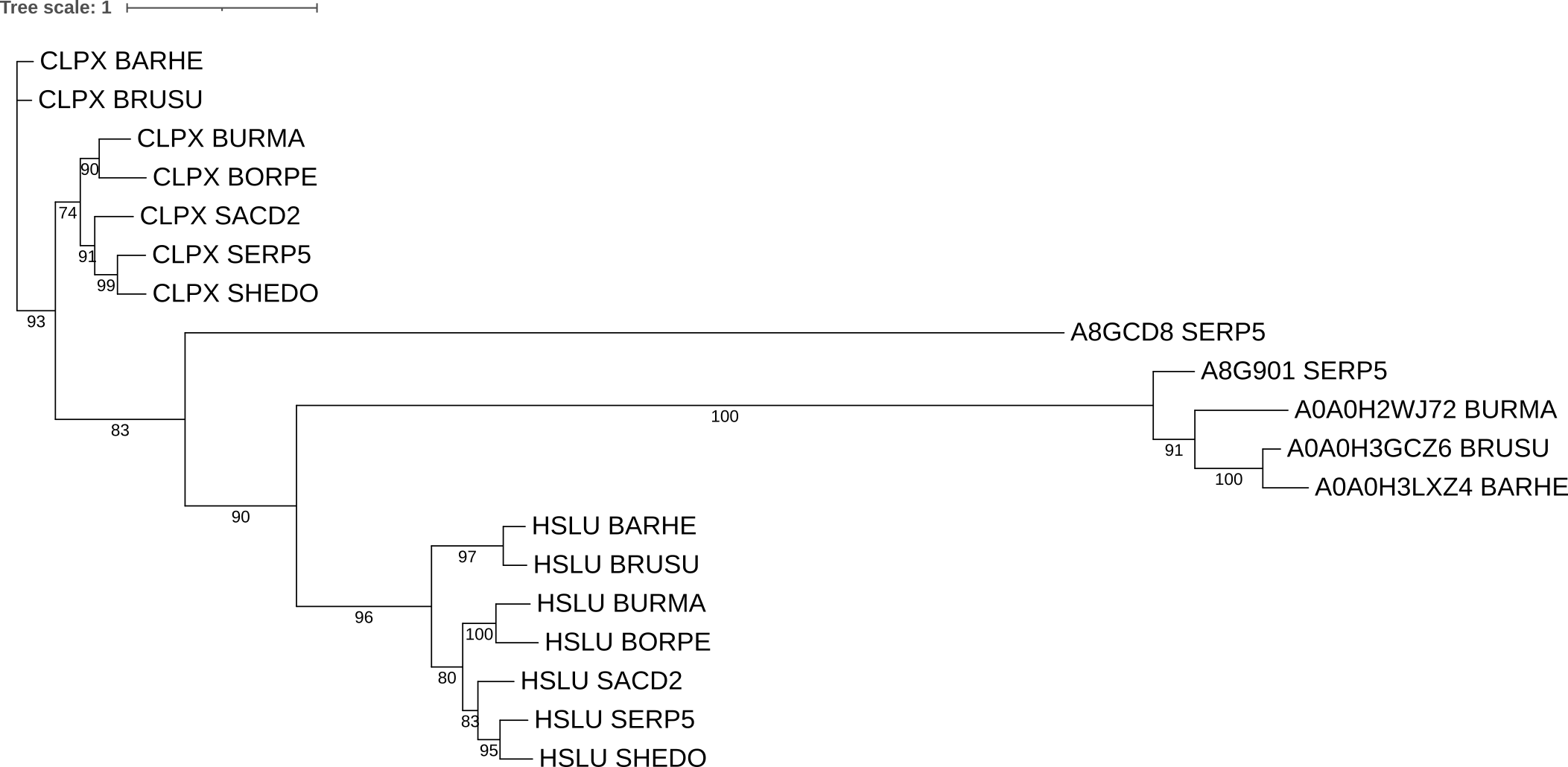
Далее дерево было укоренено в среднюю точку (рис. 2).
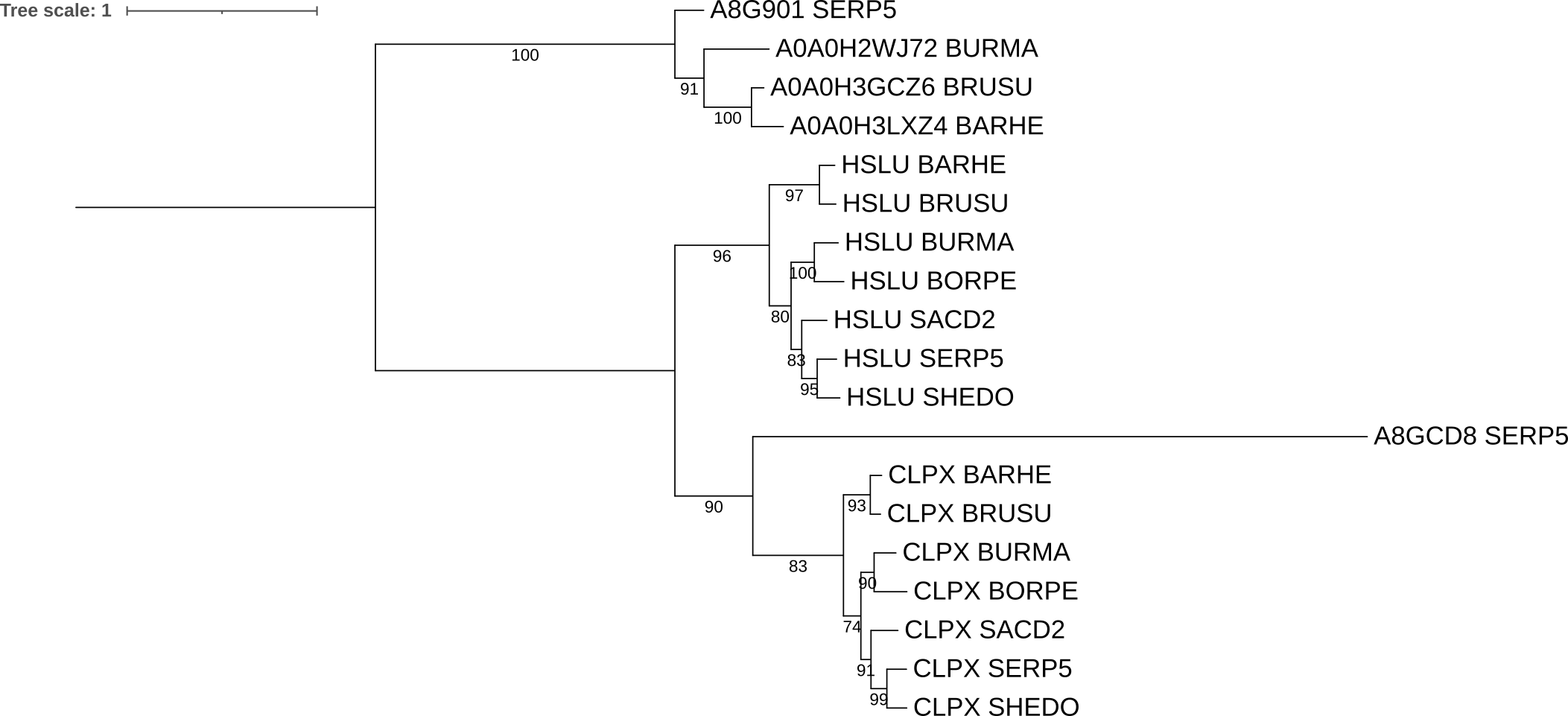
Два гомологичных белка будем называть ортологами, если они: а) из разных организмов; б) разделение их общего предка на линии, ведущие к ним, произошло в результате видообразования. Два гомологичных белка из одного организма будем называть паралогами.
Ниже представлены 3 пары ортологов:
- HSLU_BARHE - HSLU_BRUSU
- CLPX_BURMA - CLPX_BORPE
- A0A0H3GCZ6_BRUSU - A0A0H3LXZ4_BARHE
И 3 пары паралогов:
- HSLU_SERP5 - CLPX_SERP5
- HSLU_BURMA - CLPX_BURMA
- A0A0H3GCZ6_BRUSU - CLPX_BRUSU
Далее дерево было редактировано. Были покрашены ортологические группы в разные цвета (рис. 3), а ткаже эти группы были схлопнуты (рис. 4).
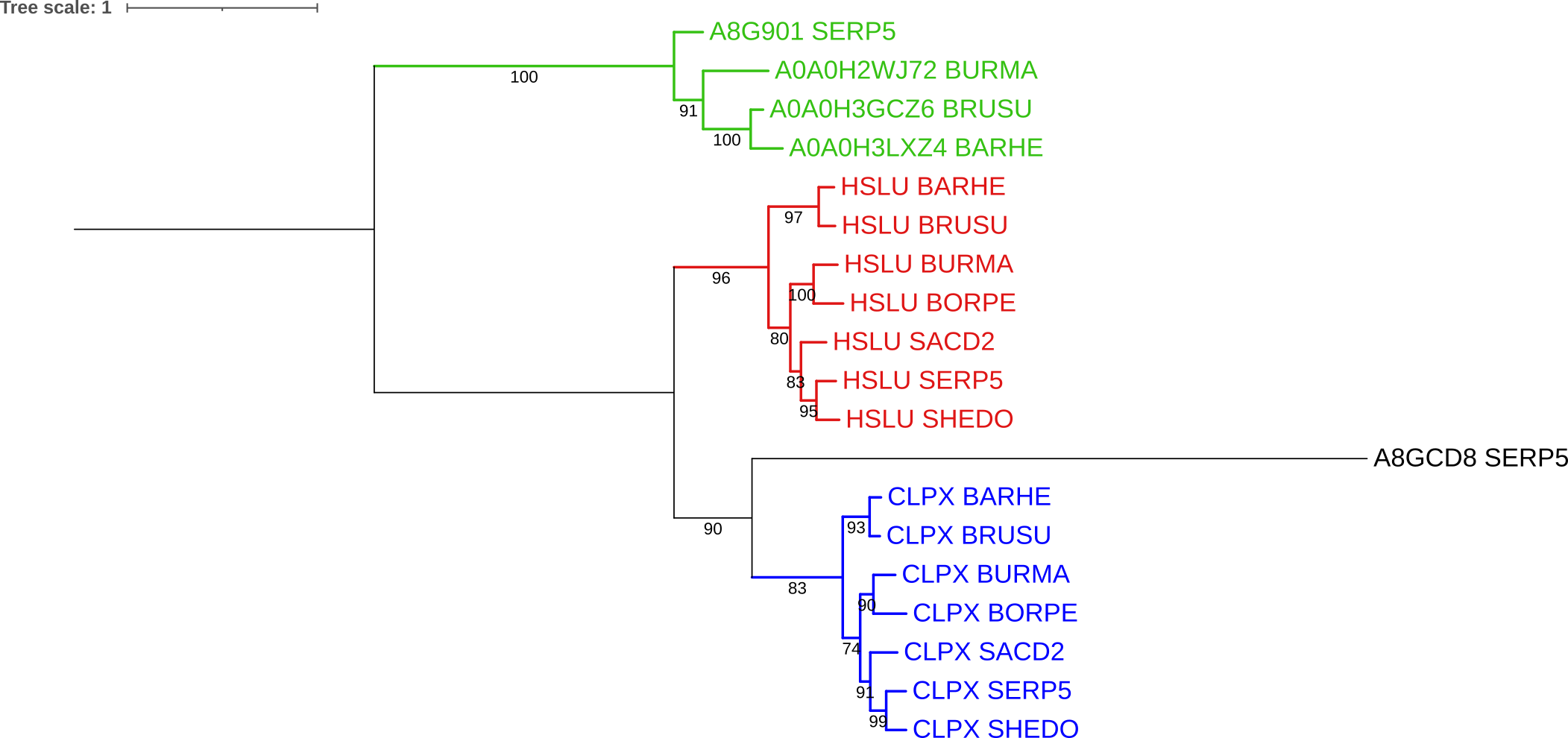
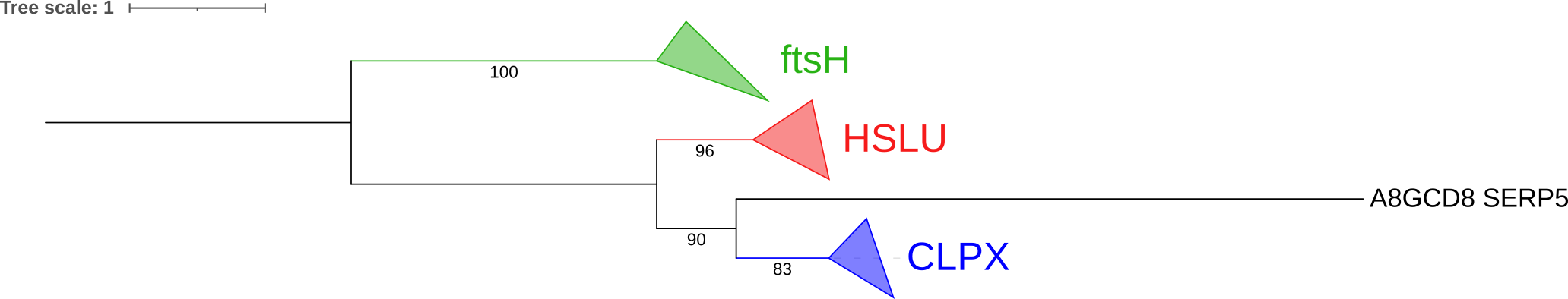
За верную филогению взята та, что представлена на рис. 5.