Результат построения дерева в Python выдал неукорененное дерево, поэтому скобочная модель была загружена в MEGA, которая, в свою очередь, выдала укорененное дерево:
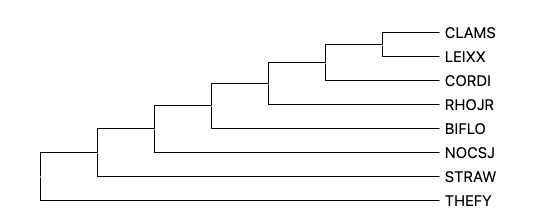
Нетривиальные ветви, которые выделяют некоторые таксоны¶
{CLAMS, LEIXX} vs {CORDI, RHOJR, BIFLO, NOCSJ, STRAW, THEFY} - Microbacteriaceae
Судя по картинке из MEGA, такая нетривиальная ветвь только одна. Однако картинка из питона и NCBI Taxonomy говорят, что есть еще одна нетривиальная ветвь:
{CORDI, RHOJR} vs {CLAMS, LEIXX, BIFLO, NOCSJ, STRAW, THEFY} - Corynebacteriales
Малое количество нетривиальных ветвей, которые выделяют таксоны свидетельствуют о том, что некоторые бактерии достаточно далеки друг от друга по таксономии.