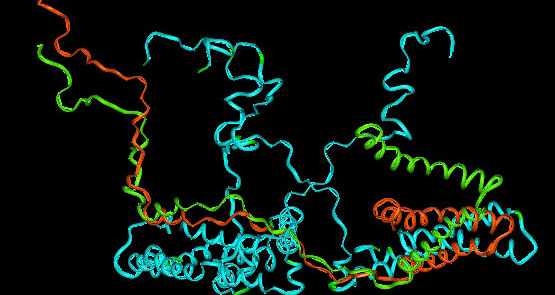
С помощью сервиса PDBeFold было найдено 2 гомолога белка 4QLX (61.6 3eo7:A и 48,9 2ymv:A). Поиск осуществлялся по доменам (оказалось наиболее оптимально, порог 70). В таблице 1 представлена краткая характеристика найденных гомологов. На рисунке 1 изображено наложение структур гомологов на структуру 4qlx.
Таблица 1. Информация о структурных гомологах енон-редуктазы бактерии Lactobacillus plantarum.

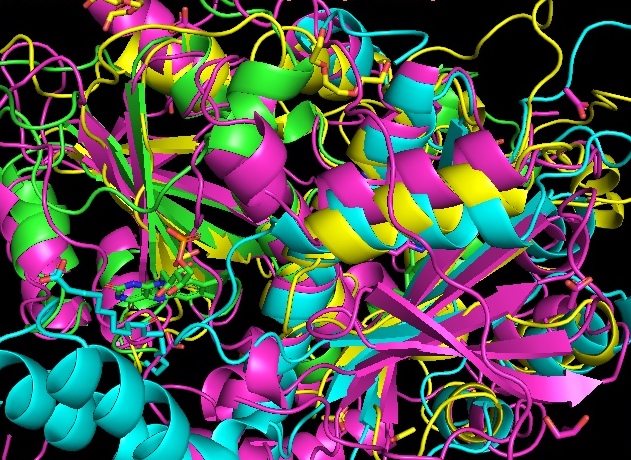
Рис.1 Совмещение структурных гомологов енон-редуктазы бактерии Lactobacillus plantarum
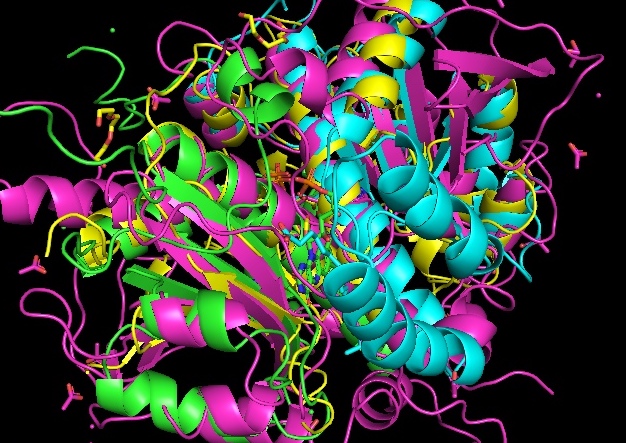
Рис.2 Совмещение структурных гомологов енон-редуктазы бактерии Lactobacillus plantarum
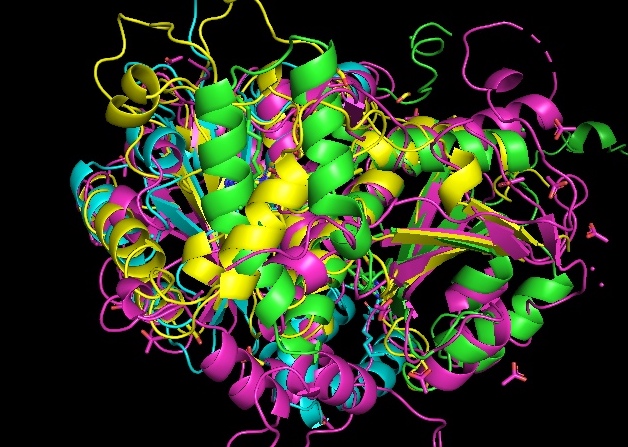
Рис.3 Совмещение структурных гомологов енон-редуктазы бактерии Lactobacillus plantarum
Структуры не очень хорошо совпадают - особенно петли, есть проблемы с альфа-спиралями (рис.2), лучше всех, как мне кажется, совпадают бета-листы.
Как можно заметить из рис.1-3, 3e07 (фиолетовый) и оригинал (зеленый) плохо совпали.
Далее требовалось сравнить структурное выравнивание (Рис. 4) и выравнивание по последовательностям (Рис. 5). Последнее я строила с помощью алгоритма Muscle.

Рис.4 Структурное выравнивание (сверху) и выравнивание с помощью программы Muscle (снизу)
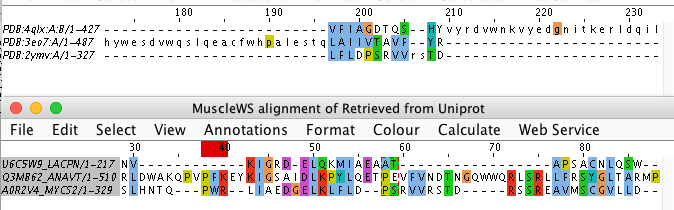
Рис.5 Структурное выравнивание (сверху) и выравнивание с помощью программы Muscle (снизу)
Выравнивания различаются между собой. Однако продемонстрировать конкретное различие было довольно трудно, так как, во-первых, длины белков в fasta-файле со структурным выравниванием и в структурах, подгружаемых в PyMOL, различаются. Это сильно осложнило поиск "интересующих мест" на самих структурах. Далее, большинство несовпадений находятся в начале или конце выравниваний, где структуры слишком различаются, поэтому нельзя сделать вывод о том, какое выравнивание более правильное. Еще один осложняющий фактор - наличие нерасшифрованных участков в структурах (особенно в исходной), они как раз часто оказываются в местах несовпадений выравниваний.
Как видно из рис.4, один и тот же участок выравнялся совершенно по-разному. С другой стороны на рис.5 видно, что в позиции 199 в верхнем выравнивании в 3ео7 и нижней последовательности совпадают буквы, однако не совпадает контекст, кроме того верхняя последовательность тоже по-другому выровнена. Посмотрим на структурах участок с рис.4. Из рис.6 видно, что хорошо совмещены в этом участке только розовая и желтая цепи (это А цепь белка 4QLX и 3EO7, L42 отображен сферами), что и отражено в структурном выравнивании - то есть по этому участку оно "более правильное". Хотя, как было сказано выше - их сравнивать вообще странно.

Рис.6 Демонстрация одного из участков в PyMol
© Yuliia Preobrazhenskaya, 2015-2016