Практикум 4
Составление списка гомологичных белков, включающих паралоги
Я выбрала 7 бактерий: PARDP, PASMU, POLAQ, PROMH, PSEAE, PSEMY, RHIME и ROSDO. С помощью BLAST нашла в этих организмах достоверные гомологи белка CLPX_ECOLI. Выдача BLAST (20 находок):
Score E
Sequences producing significant alignments: (Bits) Value
sp|B4EU54|CLPX_PROMH ATP-dependent Clp protease ATP-binding subun... 769 0.0
sp|A4XTZ6|CLPX_PSEMY ATP-dependent Clp protease ATP-binding subun... 658 0.0
sp|Q9I2U0|CLPX_PSEAE ATP-dependent Clp protease ATP-binding subun... 654 0.0
sp|A4SXD7|CLPX_POLAQ ATP-dependent Clp protease ATP-binding subun... 613 0.0
sp|P57981|CLPX_PASMU ATP-dependent Clp protease ATP-binding subun... 612 0.0
sp|Q92QQ2|CLPX_RHIME ATP-dependent Clp protease ATP-binding subun... 596 0.0
sp|Q165G0|CLPX_ROSDO ATP-dependent Clp protease ATP-binding subun... 582 0.0
sp|A1B1H7|CLPX_PARDP ATP-dependent Clp protease ATP-binding subun... 580 0.0
sp|A1B5T0|HSLU_PARDP ATP-dependent protease ATPase subunit HslU O... 103 4e-24
sp|B4F171|HSLU_PROMH ATP-dependent protease ATPase subunit HslU O... 96.7 1e-21
sp|Q9HUC5|HSLU_PSEAE ATP-dependent protease ATPase subunit HslU O... 95.9 2e-21
sp|Q16CY2|HSLU_ROSDO ATP-dependent protease ATPase subunit HslU O... 93.6 1e-20
sp|A4XPN6|HSLU_PSEMY ATP-dependent protease ATPase subunit HslU O... 93.2 1e-20
sp|P57968|HSLU_PASMU ATP-dependent protease ATPase subunit HslU O... 93.2 1e-20
sp|Q92TA7|HSLU_RHIME ATP-dependent protease ATPase subunit HslU O... 92.8 1e-20
tr|A1B8N4|A1B8N4_PARDP ATP-dependent Clp protease, ATP-binding su... 50.1 2e-06
tr|B4F2B3|B4F2B3_PROMH ATP-dependent zinc metalloprotease FtsH OS... 46.6 2e-05
sp|Q168A2|RUVB_ROSDO Holliday junction branch migration complex s... 45.4 3e-05
tr|Q92M98|Q92M98_RHIME ATP-dependent zinc metalloprotease FtsH OS... 45.4 4e-05
tr|A1AZV8|A1AZV8_PARDP ATP-dependent zinc metalloprotease FtsH OS... 44.3 9e-05
Реконструкция и визуализация
Последовательности находок я поместила в fasta-файл и отредактировала их названия, оставив только ID. (Последовательности CLPX_PSEMY, HSLU_PSEMY, A1B8N4_PARDP, B4F2B3_PROMH, Q92M98_RHIME, A1AZV8_PARDP найдены не были). Далее провела выравнивание с помощью muscle и реконструировала дерево программой iqtree
Формула дерева в формате Newick

Рис. 1. Изображение дерева с выделенными ортологическими группами.
Примеры пар паралогов: CLPX_PSEAE и HSLU_PSEAE, CLPX_ROSDO и HSLU_ROSDO, CLPX_RHIME и HSLU_RHIME.
Примеры пар ортологов: CLPX_POLAQ и CLPX_PASMU, CLPX_RHIME и CLPX_PASMU, HSLU_PROMH и HSLU_ROSDO.
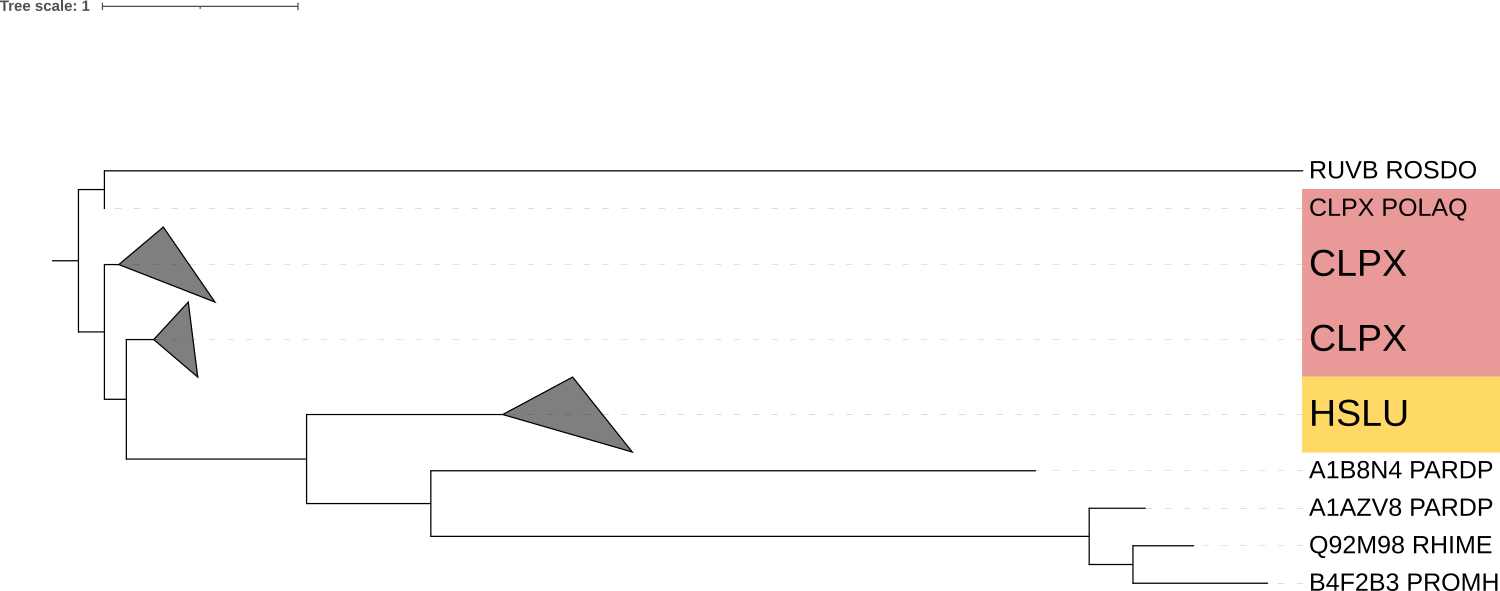
Рис. 2. Изображение дерева со свернутой ортологической группой.
- Описание каждой ортологической группы
CLPX
Не удалось полностью свернуть, так как представители группы не находятся на одной общей ветке. Реконструировано правильно.
HSLU
Нет бактерии POLAQ, остальное правильно.