АННОТАЦИЯ
Данный обзор посвящен анализу генома термофильной бактерии Thermomicrobium roseum DSM 5159, имеющей многочисленные приспособления к обитанию в экстремальных условиях. Были изучены распределения длин белков в протеоме, GC-состава CDS, а также содержание элементов различных типов на “+” и “-” цепях.
1. ВВЕДЕНИЕ
Thermomicrobium roseum DSM 5159 — чрезвычайно термофильная палочковидная неподвижная грамотрицательная бактерия, первоначально выделенная из горячего источника Тодустул-Спринг в Йеллоустонском национальном парке. Оптимально растет при температуре 70–75°С и рН 8,2–8,5, классифицируется как облигатно аэробный гетеротроф. Её мембрана полностью состоит из длинноцепочечных 1,2-диолов, а клеточная стенка — из белков, богатых пролином, глутаматом, глицином и аланином. Подобное строение покровов обеспечивает устойчивость к экстремальным условиям [1].
Геном бактерии включает кольцевую хромосому и мегаплазмиду, на которой расположен набор генов жгутикового аппарата и хемотаксиса - это первый известный пример полной жгутиковой системы, закодированной на плазмиде, что также является адаптацией к условиям обитания. Кроме того, T. roseum - единственный термофил, окисляющий CO [1] .
Таксономическая принадлежность Thermomicrobium roseum DSM 5159:
Домен: Bacteria
Филум: Pseudomonas
Класс: Thermomicrobia
Порядок: Thermomicrobiales
Семейство: Thermomicrobiaceae
Род: Thermomicrobium
Вид: Thermomicrobium roseum
Штамм: DSM 5159
2. МАТЕРИАЛЫ И МЕТОДЫ
В работе использовались таблица особенностей генома (см. S1), а также последовательности репликонов и кодирующих последовательностей (см. S2) Thermomicrobium roseum DSM 5159 (геномная сборка GCF_000021685.1 (см. S9)).
Для обработки данных применялись базовые методы анализа таблиц, расчет статистических показателей и построение гистограмм в Google Sheets.
3. РЕЗУЛЬТАТЫ
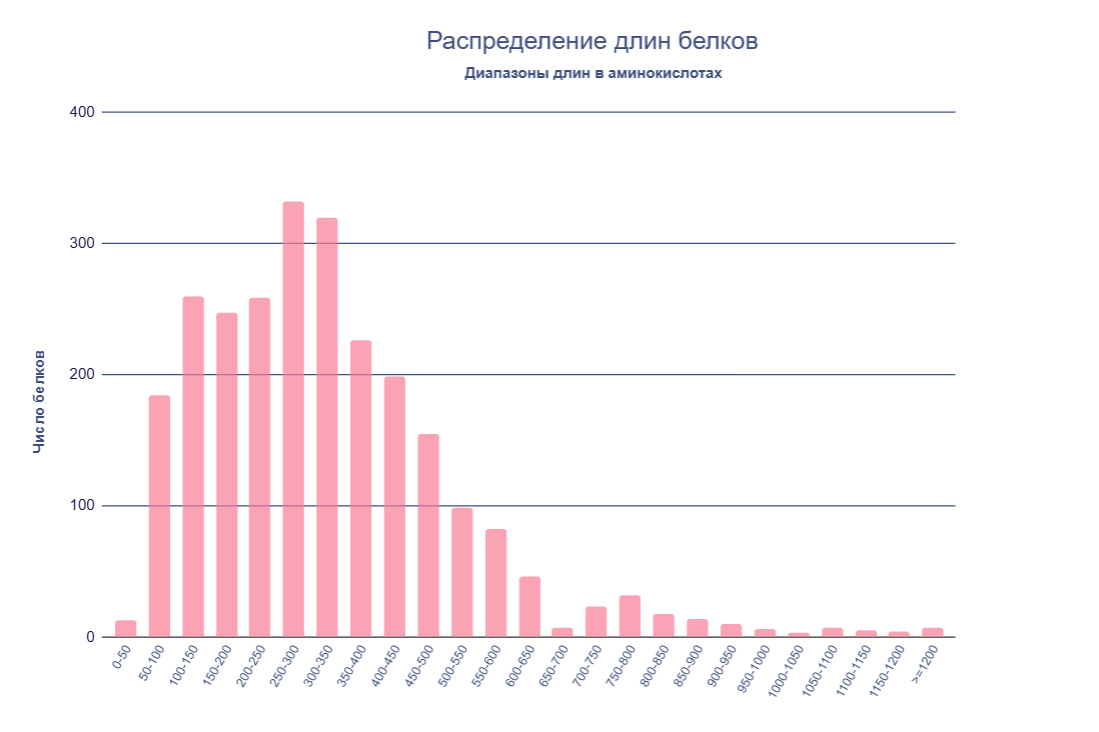
1. Гистограмма длин белков бактерии Thermomicrobium roseum DSM 5159
Из анализа длин 2584 белков протеома Thermomicrobium roseum DSM 5159 видно, что чаще всего встречаются белки длиной 250-300 аминокислотных остатков (см. Рис. 1) — на этот диапазон приходится пик распределения. Также оказалось, что 84,55% всех белков имеют длину от 50 до 500 аминокислот, то есть большая часть протеома состоит из сравнительно коротких и средних по размеру белков, что типично для бактерий. Кроме того на гистограмме наблюдается “хвост” из небольшого числа длинных белков (см. S3).
Рассчитанные статистические показатели тоже демонстрируют, что длины белков распределены довольно равномерно, без сильных выбросов: среднее значение длины составляет 329 а.о., медиана — 299 а.о., мода — 334 а.о. (см. S3).
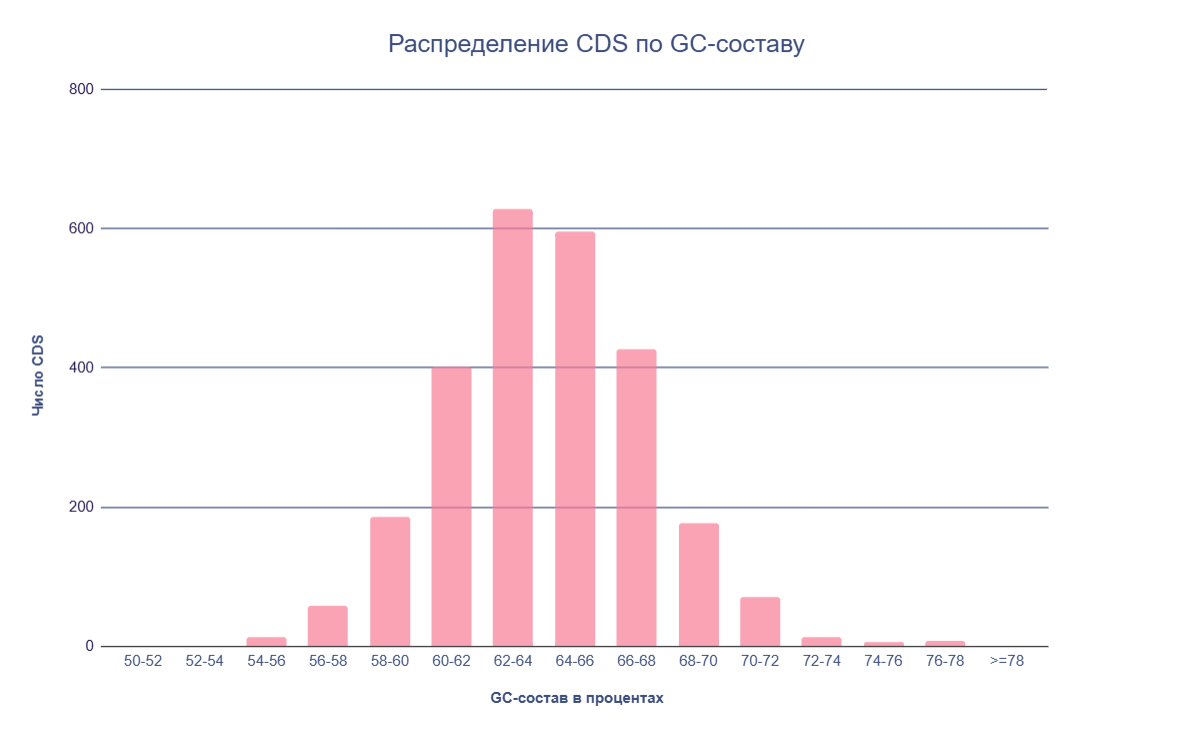
2. Гистограмма GC-состава CDS бактерии Thermomicrobium roseum DSM 5159
| GC-состав | Количество CDS (шт) | Количество CDS (%) |
|---|---|---|
| меньше 50% | 0 | 0,00 |
| от 50% до 60% | 259 | 10,03 |
| от 60% до 70% | 2229 | 86,30 |
| от 70% до 80% | 95 | 3,68 |
| больше 80% | 0 | 0,00 |
Анализ распределения GC-состава CDS Thermomicrobium roseum DSM 5159 показал, что геном отличается выраженным смещением в сторону высоких значений GC (см Рис.2). Среднее значение GC% составило 64,05%, медиана — 64%, а мода — 66,67%, что демонстрирует одинаково высокий уровень GC среди большинства генов (см. S4).
Данную тенденцию подтверждает распределение по интервалам: 86,3% CDS находятся в диапазоне 60–70% GC, и ещё 3,68% — в диапазоне 70–80% GC. Гены с содержанием GC ниже 50% и выше 80% отсутствуют (см. Таблица 1). Такое узкое и сильно смещенное распределение GC указывает на структурную и эволюционную стабильность генома (см. S5).
3. Содержание элементов различных типов на "+" и "-" цепях хромосомы и плазмиды Thermomicrobium roseum DSM 5159
Как было сказано ранее, геном Thermomicrobium roseum DSM 5159 состоит из двух кольцевых элементов. В настоящем исследовании было проанализировано распределение генов различных типов между комплементарными цепями хромосомы и мегаплазмиды (см. S6, S7). В анализ включены белок-кодирующие гены, псевдогены и гены, кодирующие основные виды РНК (см. Таблицы 2, 3).
| цепи плазмиды | вид гена | |||||
|---|---|---|---|---|---|---|
| белок-кодирующий | псевдоген | ген рРНК | ген SRP_РНК | ген тмРНК | ген тРНК | |
| "+" цепь | 400 | 7 | 0 | 0 | 0 | 1 |
| "-" цепь | 397 | 4 | 3 | 0 | 0 | 2 |
| цепи хромосомы | вид гена | |||||
|---|---|---|---|---|---|---|
| белок-кодирующий | псевдоген | ген рРНК | ген SRP_РНК | ген тмРНК | ген тРНК | |
| "+" цепь | 819 | 8 | 0 | 1 | 1 | 28 |
| "-" цепь | 940 | 8 | 3 | 0 | 0 | 18 |
Выяснилось, что белок-кодирующие гены на хромосоме распределены по + и - цепям неравномерно, что, вероятно, связано с согласованием направления репликации и транскрипции у бактерий. В мегаплазмиде такой асимметрии не наблюдается [2].
Оба репликона, по всей видимости, содержат по одному оперону рРНК, однако мегаплазмида кодирует только 3 из 49 тРНК и не содержит генов тмRNA и SRP RNA, отвечающих за контроль качества белков и их доставку к мембране.
СОПРОВОДИТЕЛЬНЫЕ МАТЕРИАЛЫ
CDS from genome of Thermomicrobium roseum DSM 5159
S1. Лист “Feature table” таблицы “Feature table”
S2. Лист “cds” таблицы “CDS from genome of Thermomicrobium roseum DSM 5159”
S3. Лист “prot_lengths_hist” таблицы “CDS from genome of Thermomicrobium roseum DSM 5159”
S4. Лист “gc_hist” таблицы “CDS from genome of Thermomicrobium roseum DSM 5159”
S5. Лист “gc” таблицы “CDS from genome of Thermomicrobium roseum DSM 5159”
S6. Лист “plasmid” таблицы “Feature table”
S7. Лист “chromosome” таблицы “Feature table”
S8. NCBI Taxonomy: Thermomicrobium roseum DSM 5159. NCBI:txid500: https://www.ncbi.nlm.nih.gov/Taxonomy/Browser/wwwtax.cgi?mode=Info&id=500
S9. National Center for Biotechnology Information (NCBI). Genome assembly GCF_000021685.1. https://www.ncbi.nlm.nih.gov/assembly/GCF_000021685.1
СПИСОК ЛИТЕРАТУРЫ
[1] Wu D, Raymond J, Wu M, Chatterji S, Ren Q, Graham JE, et al. (2009) Complete Genome Sequence of the Aerobic CO-Oxidizing Thermophile Thermomicrobium roseum. PLoS ONE 4(1): e4207. https://doi.org/10.1371/journal.pone.0004207
[2] Zhaoqian Liu, Jingtong Feng, Bin Yu, Qin Ma, Bingqiang Liu, The functional determinants in the organization of bacterial genomes, Briefings in Bioinformatics, Volume 22, Issue 3, May 2021, bbaa172, https://doi.org/10.1093/bib/bbaa172