1. Выбор и описание семейства доменов
Для проведения анализа из списка Pfam был выбран домен TEA (PF01285). Описание его характеристик приведено в таблице 1.
TEA-домены – это ДНК-связывающие участки протяженностью от 66 до 68 аминокислот, названные в честь двух белков: TEF-1 и AbaA. Благодаря своей компактной структуре, они обеспечивают высокую точность распознавания ДНК-мишеней внутри клетки. В частности, TEA-домены играют важную роль в одном из ключевых сигнальных путей – Hippo. Он отвечает за пролиферацию и дифференцировку клеток, а также регулирует размер органов. Большинство белков содержат только один TEA домен (обычно в N-концевой части). Домены этого семейства встречаются только у эукариот и имеют трёхспиральную глобулярную укладку типа «helix-turn-helix» (HTH), но с необычным удлинённым C-концом. Так же внутри домена есть участок для связывания с коактиваторами транскрипции YAP/TAZ (участники пути Hippo).
| AC pfam | PF01285 |
| ID pfam | TEA/ATTS domain |
| #SEED | 33 |
| #All | 10k |
| #SW | 25 |
| #architectures | 69 |
| #3D | 5 |
| Taxonomy | #eukaryota: 9584 #archaea: 0 #bacteria: 0 |
2. Описание выравнивания белковых доменов (seed)
Описание выравнивания приведено в таблице 2. Ознакомиться с ним можно, скачав файл с проектом Jalview по ссылке.
| Выравнивание seed | 119 колонок, 33 последовательности |
| Максимальный достоверный блок, включающий ВСЕ последовательности (МДБ-all) | 108-116* |
| 100% консервативные колонки в МДБ-all | 108:Q, 111:S, 114:Q |
| Максимальный достоверный блок, включающий НЕ ВСЕ последовательности (МДБ-notAll) | колонки 100-117 (последовательности 24-33) |
| 100% консервативные колонки в МДБ-notAll | 100:T, 101:G, 104:R, 107:K, 108:Q, 111:S, 112:R, 114:Q, 116:L, 117:R |
| Участок без достоверных подблоков | колонки 50-68 |
*Для выделения МДБ-all было найдено 2 подходящих участка одинаковой длины: 76-84 и 108-116. Работа проводилась с участком 108-116, так как в нем больше 100% консервативных колонок.
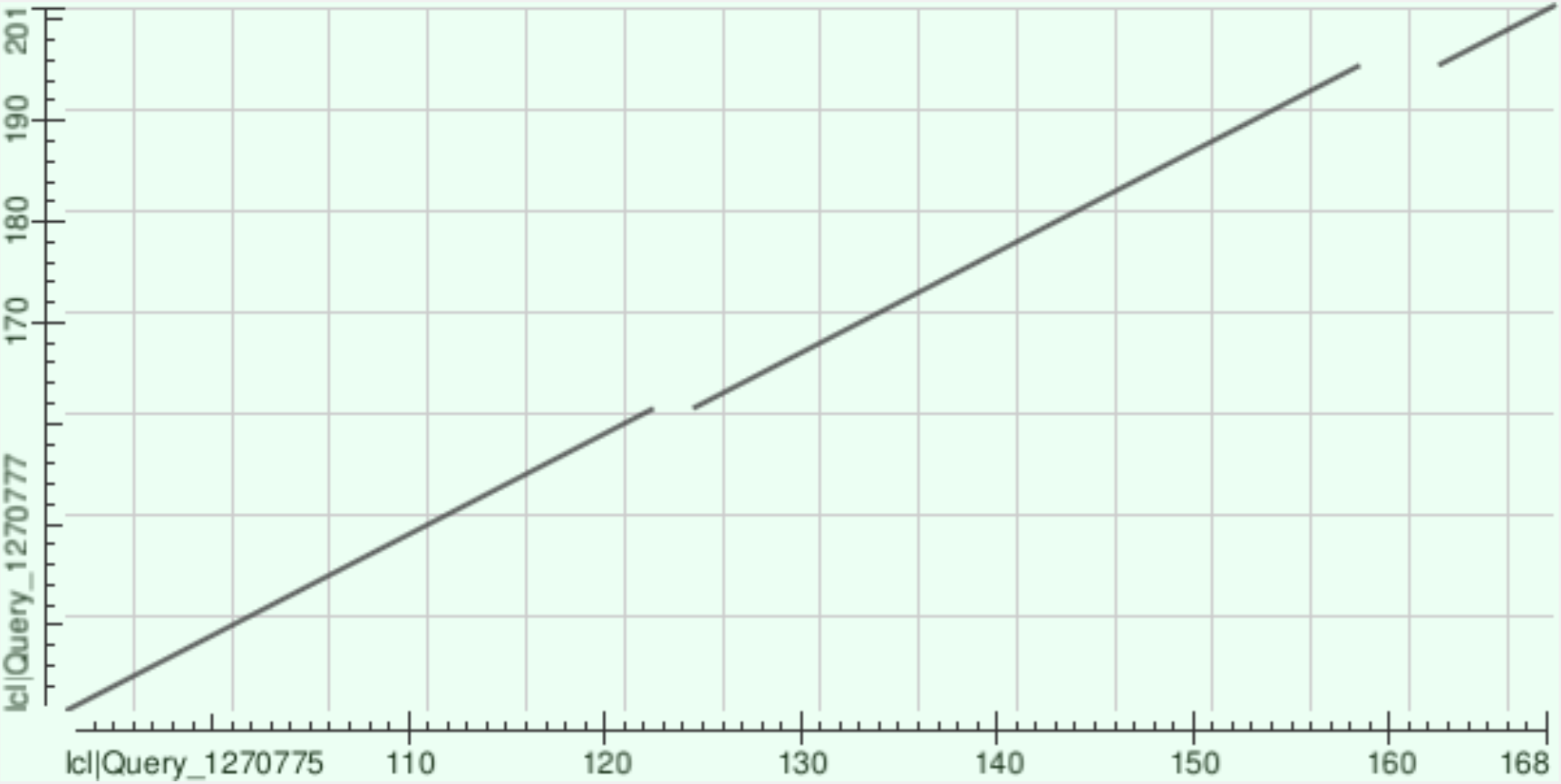
3. Построение карты локального сходства (dotplot)
Для построения dotplot были выбраны два белка с разной доменной архитектурой, содержащие домен TEA (см. Таблица 3).
| Доменная архитектура 1 | PF01285-PF17725 |
| Белок с архитектурой 1 | P30052 |
| Доменная архитектура 2 | PF01285 |
| Белок с архитектурой 2 | P18412 |
Полученная карта локального сходства белков P30052 (содержит TEA- и YBD-домены) и P18412 (содержит только TEA-домен) указывает на гомологию последовательностей: видна четкая диагональ с двумя разрывами, которые соответствуют делециям или инсерциям, произошедшим в ходе эволюции.