Практикум №8. Нуклеотидный BLAST
Поиск δ-субъединицу АТФ-синтазы
В данном задании исследовался геном и протеом коралла Acropora millepora.
С помощью текстового поиска в файле протеома была найдена последовательность δ-субъединицы АТФ-синтазы. В качестве запроса были заданы слова "subunit delta".
Файл с последовательностью белка atpase_sub_delta.fasta
Далее белок был найден в NCBI Protein Database, откуда был взят идентификатор нуклеотидной записи, к которой относится ген, кодирующий данный белок: NC_058079.1
Данная запись предаставляет собой 14 хромосому Acropora millepora, на которой был найден ген, кодирующий δ-субъединицу АТФ-синтазы: LOC14961338
Файл с последовательностью гена и его окружением nucleotide_seq_atpase.fasta
Координаты гена: 4438820-4443480

Рис 1. Окружение гена.
Применение различных алгоритмов BLAST для фрагмента ДНК
Так как Acropora millepora не относится ни к первичноротым животным, ни ко вторичноротым животным, то для дальнейшего анализа было выбрано произвольное семейство Кошачих (Felidae).
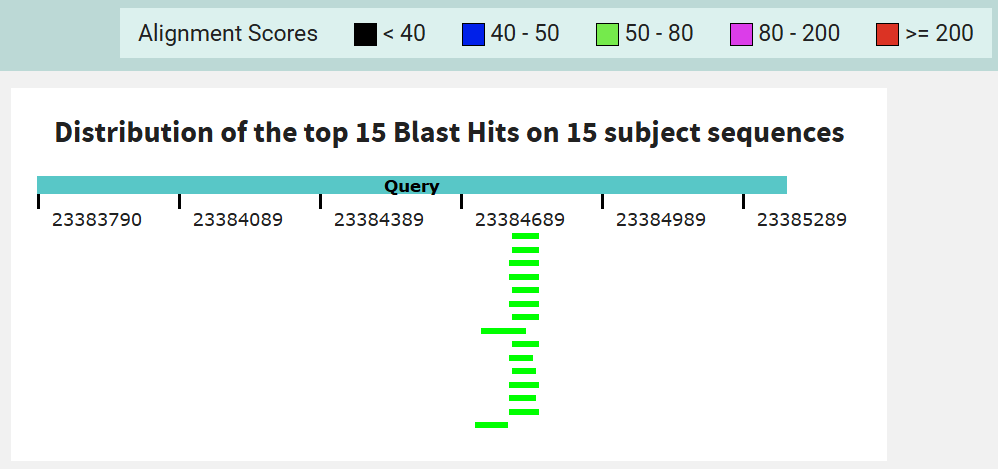
Рис 2. При поиске с помощью blastn на вход подавался fasta-файл с последовательностью гена δ-субъединицы АТФ-синтазы. При этом megablast не использовался ввиду наличия большого расхождения псоледовательностей, из-за чего выдача была бы путой. В качестве базы данных для поиска была выбрана refseq_genomes. В параметрах алгоритма была указана минимальная длина слова 7. В результате было найдено 15 записей.
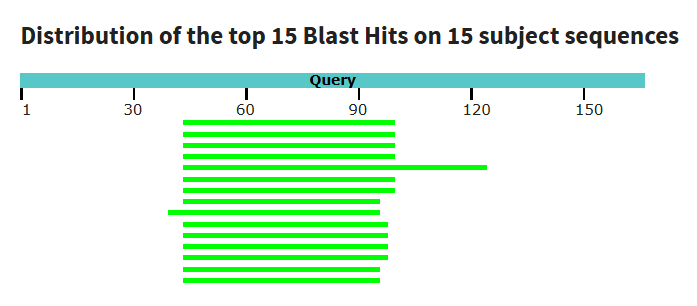
Рис 3. Поиск проводился по базе данных refseq_genomes. Была указана длина слова 5, так как достоверных находок оказалось достаточное количество. Была использована программа tblastn вместо tblastx, так как имеет меньшее время работы. Обнаружено 15 соответствий, что говорит о наличии в гене δ-субъединицы АТФ-синтазы консерватиных участков.
Поиск в геноме Acropora millepora генов основных рибосомальных РНК по далёкому гомологу
Для поиска гомологов последовательности генома Acropora millepora были проиндексированы с помощью локального BLAST:
makeblastdb -in GCF_013753865.1_Amil_v2.1_genomic.fna -dbtype nucl -out Amil_DB
Поиск гомологов 16S и 23S рРНК у E. coli по базе данных Acropora millepora производился с помощь алгоритма blastn:
blastn -task blastn -query 16S_rRNA_ecoli.txt -db Amil_DB -out 16s_pr8.out -evalue 0.01 -outfmt 7
blastn -task blastn -query 23S_rRNA_ecoli.txt -db Amil_DB -out 23s_pr8.out -evalue 0.01 -outfmt 7
Ниже представленны файлы выдачи отдельно для каждой рРНК:
В результате локального поиска с помощью алгоритма blastn для 16S рРНК было найдено 14 хитов, которые имели значение E-value меньше 0.01. Для 23S рРНК было найдено 33 хита. Все хиты были выровнены на прямой цепи.
Все хиты 23S рРНК обладали достаточно низким E-value. Можно заметить, что процент идентичности был тем меньше, чем короче было выравнивание.
Для визуализации локального поиск BLAST были построены схемы выравнивания 6 участков для гомолога NW_025322990.1, соответствующих участкам 23S рРНК.
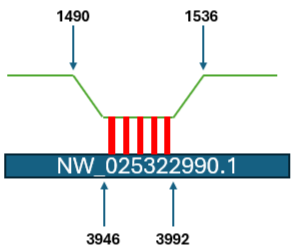
Рис 4. Визуализация участка выравнивания 23S рРНК E.Coli на геном Acropora millepora.
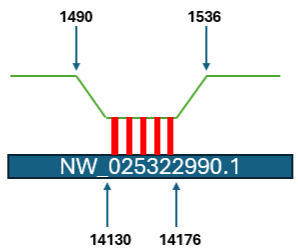
Рис 5. Визуализация участка выравнивания 23S рРНК E.Coli на геном Acropora millepora.
Из рис 4. и рис. 5. видно, что одни и те же 3 участка 23S рРНК E.Coli выравнялись на 2 разных места на NW_025322990.1
Это говорит, что в геноме Acropora millepora нашлось 2 повтора генов 23S рРНК.
Построение карты локального сходства участков двух схожих геномов
Для построения карты локального сходства были выбраны хромосомные сборки из геномов бактерий Bacillus subtilis и Bacillus licheniformis. Построение осуществлялось с помощью алгоритмов megablast, blastn и tblastx.
Выбор организмов из одного рода был обусловлен необходимостью сильного сходства между сравниваемыми последовательностями.
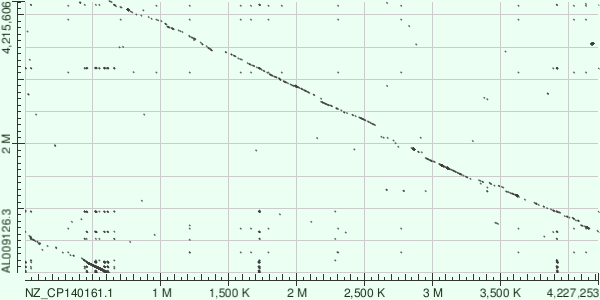
Рис 6. Карта локального сходства хромосом Bacillus subtilis и Bacillus licheniformis, построенная с помощью алгоритма megablast.
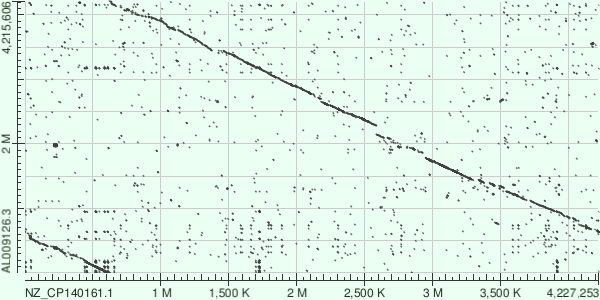
Рис 7. Карта локального сходства хромосом Bacillus subtilis и Bacillus licheniformis, построенная с помощью алгоритма blastn.