Практикум 2
Cравнительный анализ канонической ДНК и стеблей тРНК
Задание 1. Построение структур ДНК
С помощью программы fiber были построены модели A, B, Z форм ДНК. Команды:
fiber -seq=GATC -rep=5 -a gatc-a.pdb
fiber -seq=GATC -rep=5 -b gatc-b.pdb
fiber -seq=GATC -rep=5 -z gatc-z.pdb
Файлы с полученными структурами: A-форма, B-форма, Z-форма
Задание 2. Анализ цепей ДНК
Я выбрала А-форму экспериментальной ДНК. В её модели определила положение атомов 5 гуанина относильно большой и малой бороздок
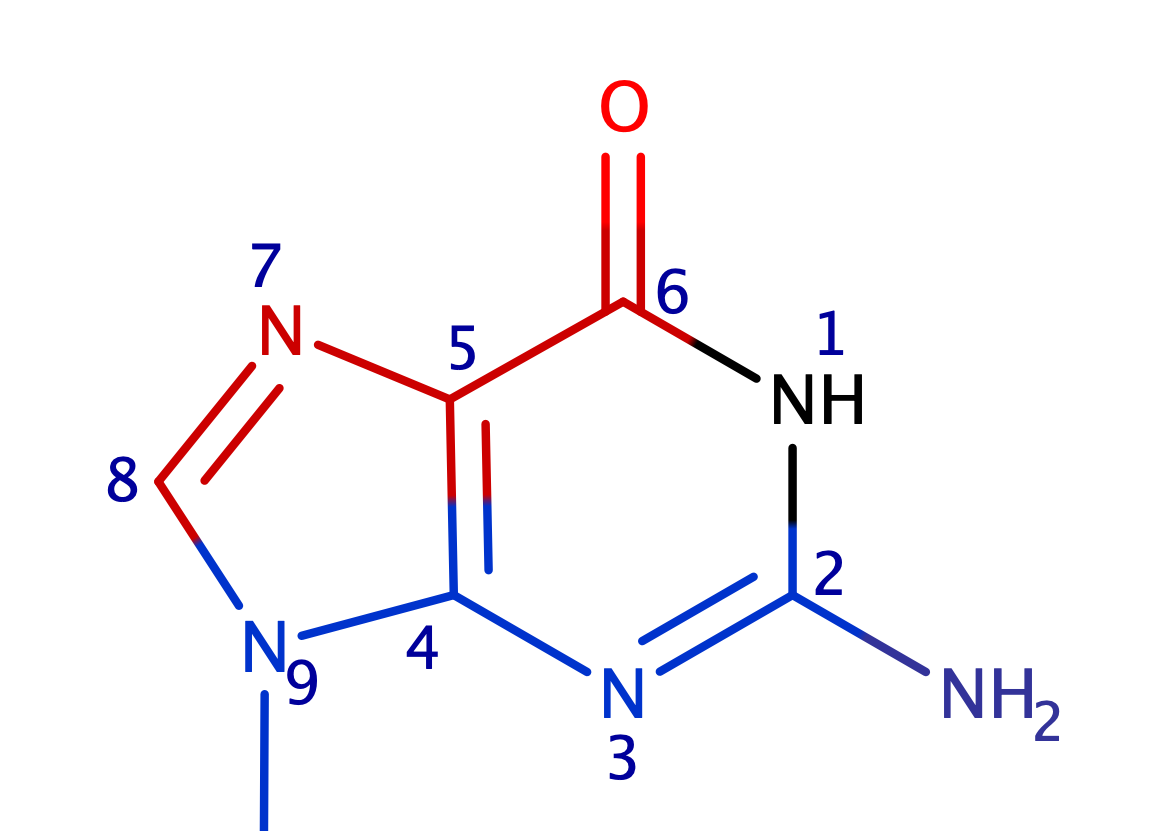
В сторону большой бороздки: G5.N2, G5.N3, G5.C4, G5.N9, G5.C2
В сторону малой бороздки: G5.N7, G5.C5, G5.C6, G5.O6, G5.C8
С помощью раздела Measurment были получены основные характеристики трёх спиралей
| А-форма | В-форма | Z-форма | |
|---|---|---|---|
| Тип спирали | Правая | Правая | Левая |
| Шаг спирали, Å | 25.4 | 31.8 | 26.2 |
| Число оснований на виток | 11 | 10 | 12 |
| Ширина большой бороздки, Å | 17.0 (A/DT-7--B/DG-37) | 17.9 (A/DG-5--B/DC-32) | 23.5 (A/DC-2--B/DC-14) |
| Ширина малой бороздки, Å | 9.6 (B/DT-27--A/DT-7) | 13.1 (B/DC-32--A/DC-12) | 8.5 (B/DG-15--A/DG-9) |
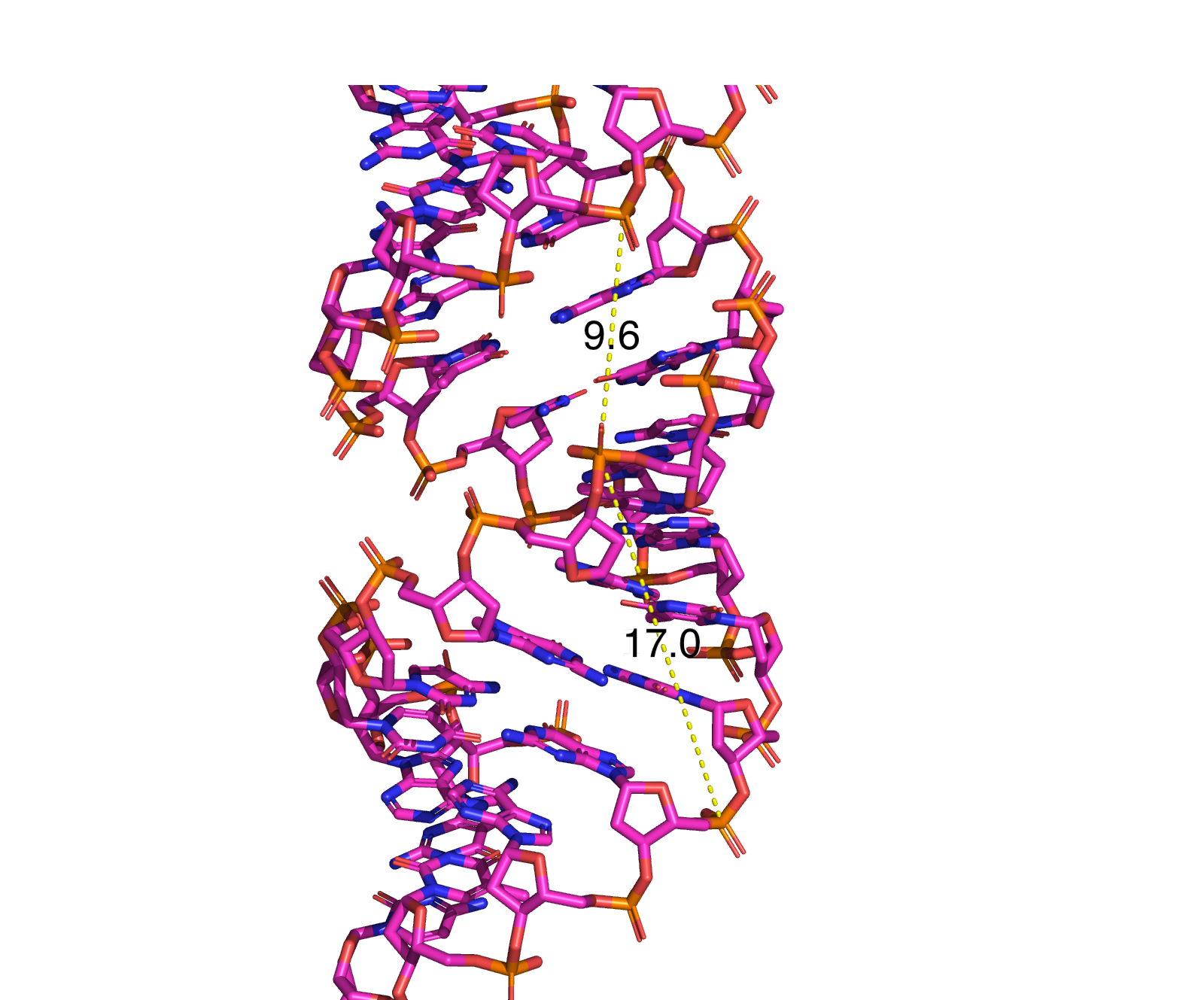
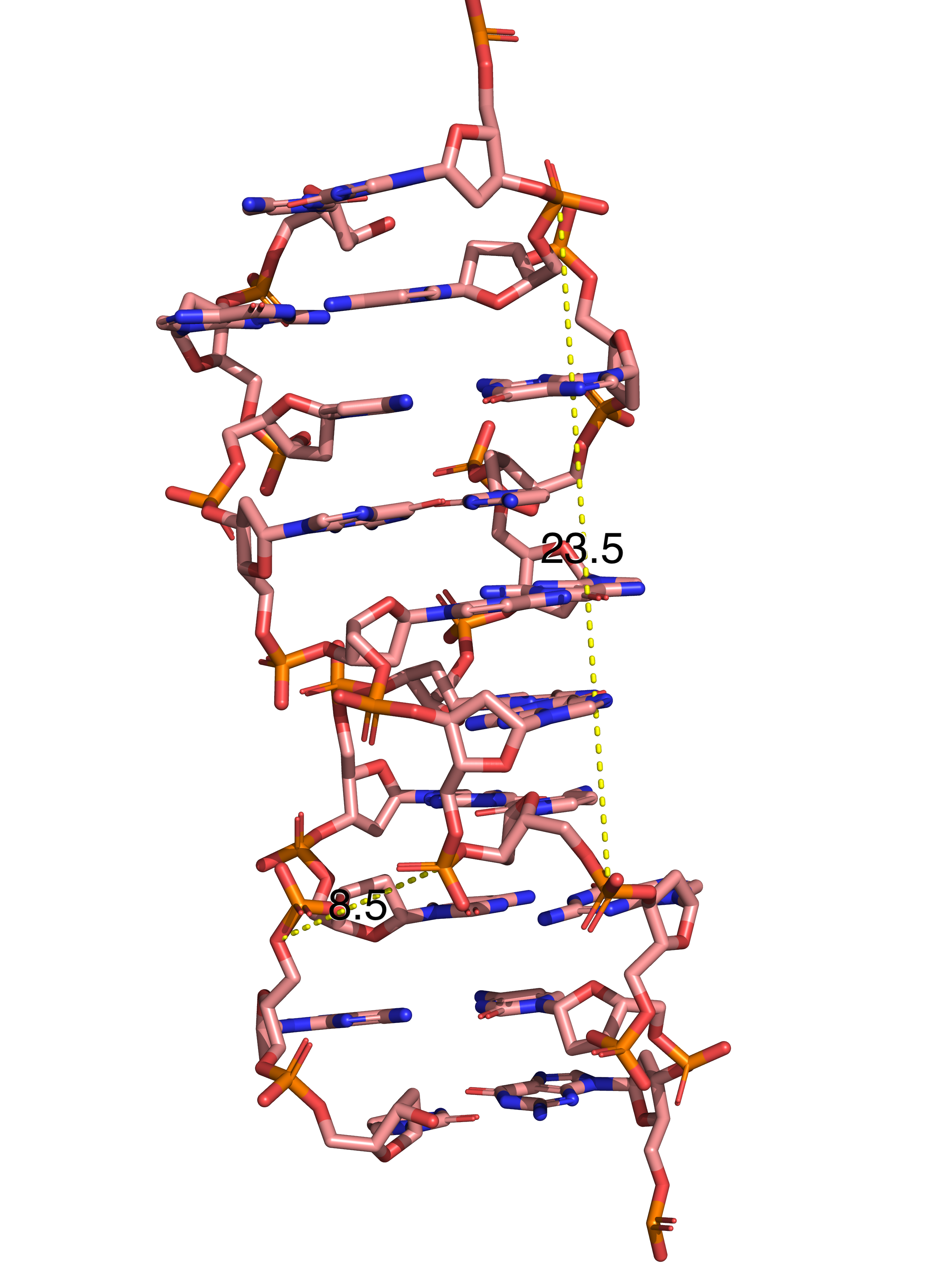
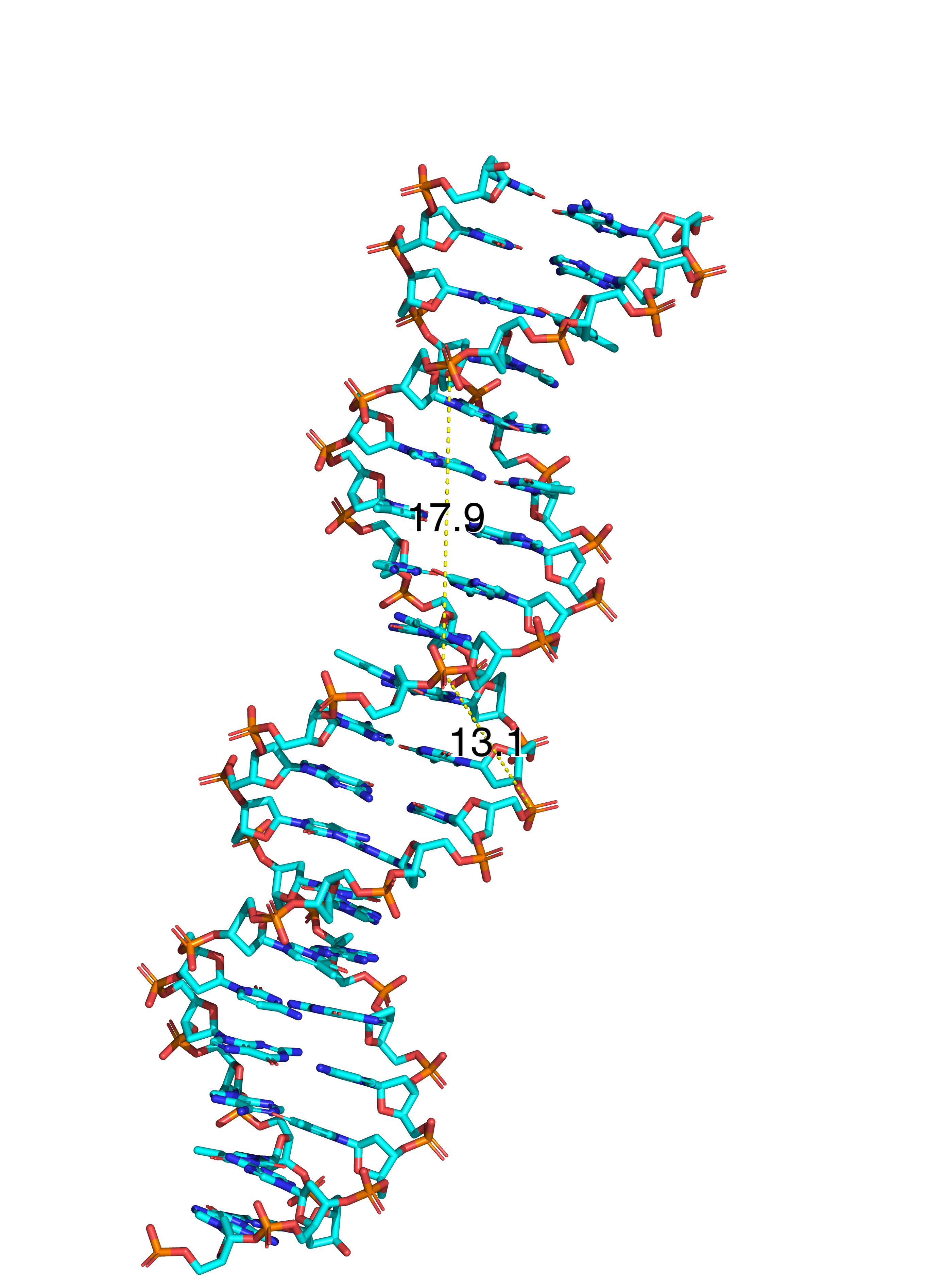
Задание 3. Структура РНК
Структура РНК, предоставленная мне, имеет PDB ID: 1eiy. При помощи команд:
1) wget "https://files.rcsb.org/download/1eiy.pdb" -O "1eiy.pdb"
2) remediator --old ''1eiy.pdb'' > ''1eiy_old.pdb
3) find_pair -t 1eiy_old.pdb stdout | analyze
Был получен файл, который содержит основную информацию. В разделе "RMSD of the bases (----- for WC bp, + for isolated bp, x for helix change)" можно найти основную информацию о стеблях, неканонических парах оснований и дополнительных водородных связях

Номера нуклеотидов, образующих стебли: 1-7 и 72-66, 49-53 и 65-61, 39-44 и 31-26, 10-13 и 25-22
Строка внизу таблицы: "Note: This structure contains 7[7] non-Watson-Crick base-pairs.", указывает на то, что содержится 7 неканонических пар:
• 44_G-**--A_26
• 14_A-**--U_8
• 15_G-**+-C_48
• 16_U-**+-U_59
• 18_G-**+-U_55
• 73_A-**+-C_74
• 45_U-**--A_9
Дополнительные водородные связи:
• 14_A-U_8
• 15_G-C_48
• 16_U-U_59
• 18_G-U_55
• 19_G-C_56
• 73_A-C_74
• 45_U-A_9