Описание доменной архитектуры белка QUEC_BACSU в соответствии с банком Pfam
В табл. 1 представлено описание доменной архитектуры белка.

| |||||
| Пояснения к схеме. | |||||
| № | Pfam AC | Pfam ID | Полное название семейства доменов | Положение в последовательности белка QUEC_BACSU | Клан |
| 1 | PF06508 | QueC | Семейство названо по названию конечного продукта метаболического пути квеуозина и катализирует первую его стадию | 5-212 | Относится к клану HUP, содержащего 26 семейств |
Табл. 1. Сведения о доменной струтуре белка QUEC_BACSU.
Некоторые данные о домене QueC
- Домен входит в 14 архитектур.
- Для всех белков, содержащих домен, известна последовательность.
- Для 2 белков определена пространственная структура.
- Ссылка на выравнивание
- Выравнивание содержит много гомологичных участков, что подтверждает гомологию (внутри домена)
Описание частоты встречаемости разных доменов одной архитектуры по отдельности
Для этой задачи я выбрал архитектуру E8PLB5_THESS, содержащую 2 домена: ATP_bind_3 и QueC. Ее изображение приведено на рис. 1.

Рис. 1. Архитектура E8PLB5_THESS. Сведения о встречаемости доменов представлены в табл. 2 (ATP_bind_3) и табл. 3 (QueC).
Таксон Количество белков с доменом ATP_bind_3. Эукариоты Зеленые растения 38 Грибы 132 Животные 80 Остальные эукариоты 54 Археи 146 Бактерии 4350 Вирусы 9 Табл. 2. Встречаемость домена ATP_bind_3 среди разных таксонов.
Таксон Количество белков с доменом QueC. Эукариоты Зеленые растения 3 Грибы 0 Животные 2 Остальные эукариоты 1 Археи 135 Бактерии 2832 Вирусы 12 Табл. 3. Встречаемость домена QueC среди разных таксонов.
Из таблиц видно, что оба домена значительно более распространены среди бактерий нежели среди остальных таксонов. В то же время домен ATP_bind_3 является в целом более распространенным, чем QueC.Сравнение описания мотивов в разных БД семейств по данным InterPro.
На рис. 2 представлена разметка мотивов белка в InterPro.
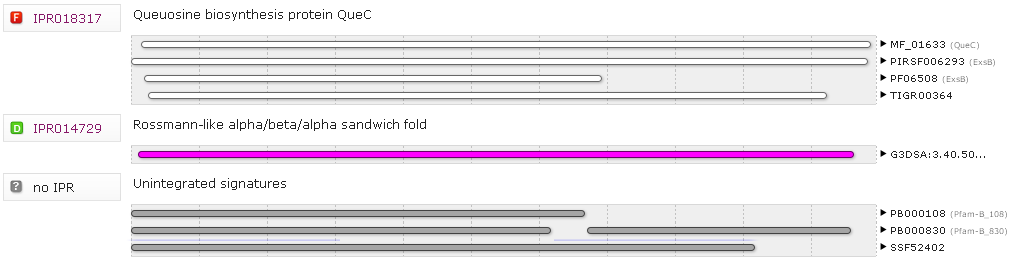
Рис. 2. Разметка мотивов белка QueC в InterPro.
Самый короткий мотив называется PF06508 (ExsB) и содержится в Pfam.
Самый длинный мотив называется PIRSF006293 (ExsB) и содержится в PIRSF.
В InterPro интегрирована одна запись - Domain IPR014729; Rossmann-like alpha/beta/alpha sandwich fold.