Для построения филогенетических реконструкций использовались последовательности гена митохондриальной 12S рРНК выбранных животных. Список животных был изменён по сравнению с предыдущими реконструкциями (см. п.р. №1, п.р. №2) в связи с отсутствием в базе данных ENA требуемых последовательностей. Так, Sorex saussurei был заменён на Sorex unguiculatus (SORUN), Akodon orophilus - на Akodon montensis (AKOMN), Ctenodactylus vali - на Ctenodactylus gundi (CTEGU), а от Massoutiera mzabi пришлось отказаться совсем из-за отсутствия в ENA нужной последовательности даже для ближайших родственников этого организма.
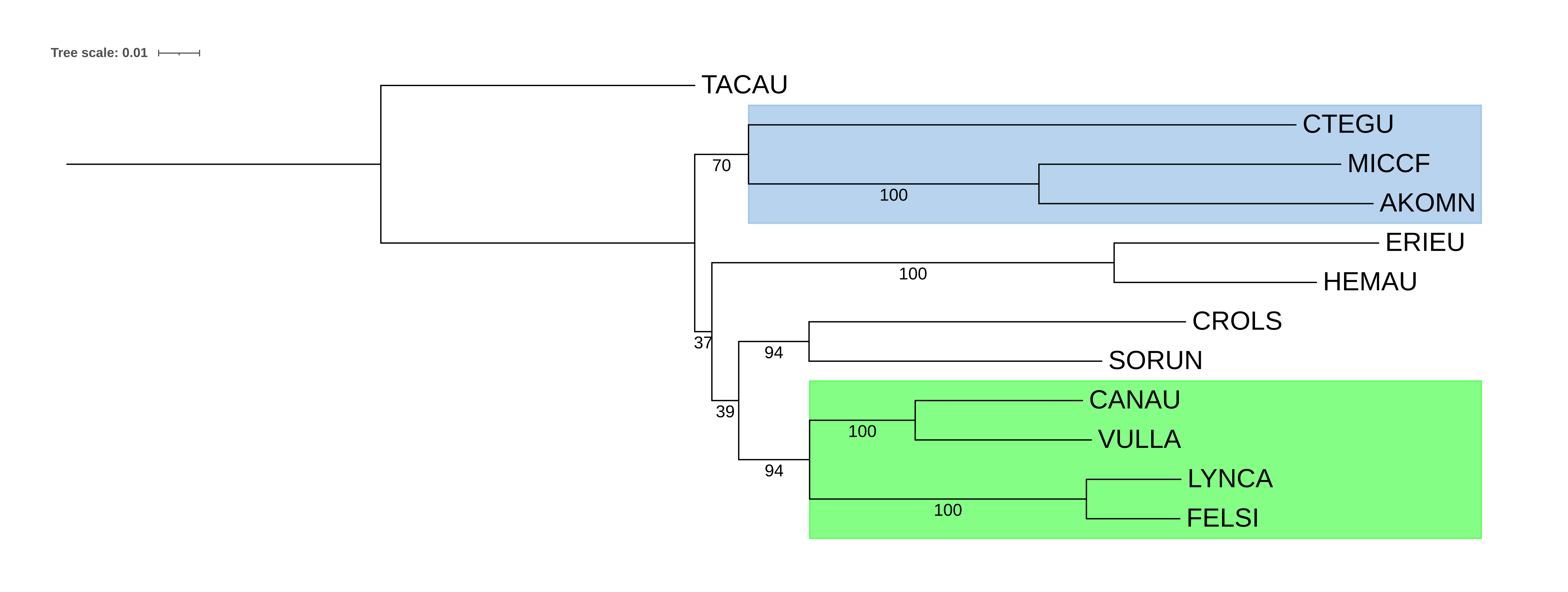
С помощью программы iqtree по полученным последовательностям было построено дерево (см. рис. 1). В нём, как и в предыдущих работах, правильно выделены клады, соответствующие семействам, клада, соответствующая отряду Хищные, но остальные клады не соответствуют современным представлениям таксономии. Единственное отличие по топологии от филогенетической реконструкции, созданной по последовательности цитохрома B (см. п.р. №2), - теперь клада, соответствующая семейству Ежовые, стала сестринской к кладе, соответствующей семейству Хомяковые (и, соответственно, теперь семейство Гребнепалые стало сестринским к описанной паре). Это не соответствует таксономии.

Для построения следующих деревьев использовалась программа fastme с эволюционной моделью F84. В качестве внешней группы был выбран Tachyglossus aculeatus (отр. Однопроходные) (TACAU). При укоренении полученного дерева в ветвь, ведущую к внешней группе, выявилась клада, соответствующая отр. Грызуны (см. рис. 2). Клады, соответствующей отр. Насекомоядные, не сформировалось, но представители этого отряда теперь оказались ближе к отр. Хищные. В этом смысле новое дерево оказалось ближе к данным таксономии.
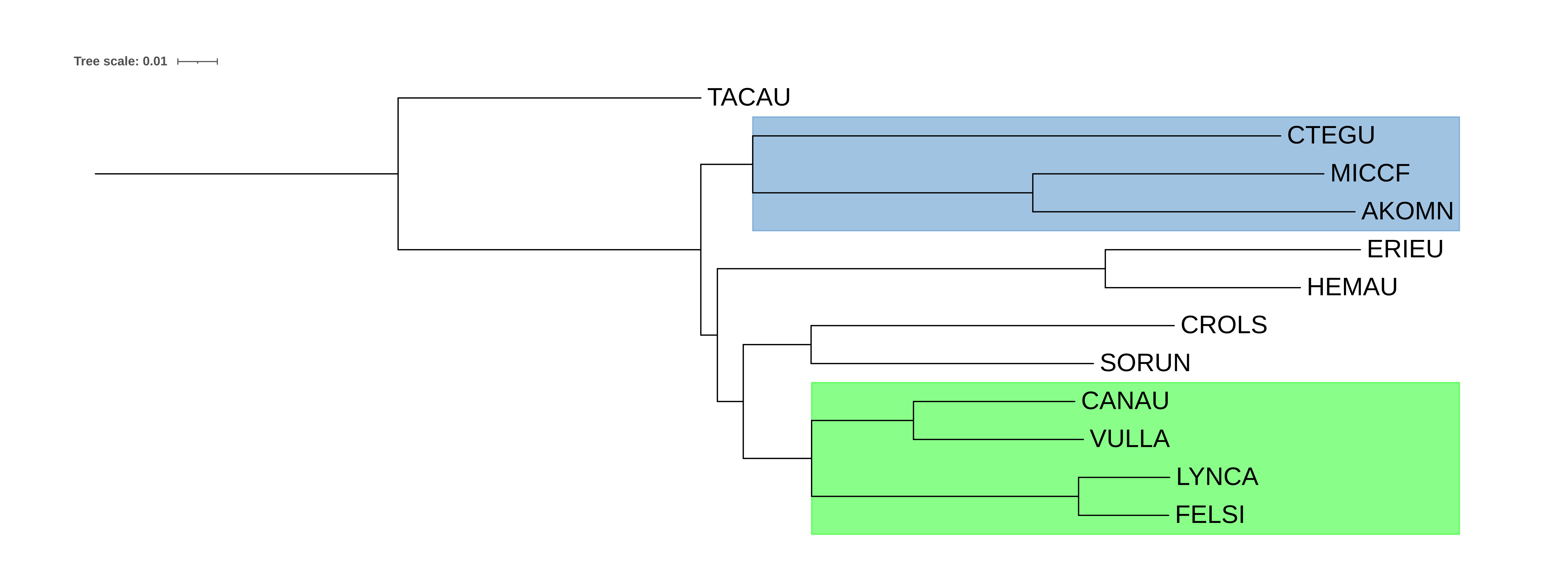
На основе тех же данных было построено дерево с применением bootstrap (см. рис. 3). Топология дерева не изменилась, а полученные числа поддержки коррелируют с соответствием ветвей таксономии: все ветви, поддерживающие клады, соответствующие таксономии, имеют большую поддержку, чем ветви, поддерживающие таксономически неправильные клады.