Исследование белка Ribulose bisphosphate carboxylase large chain(AC O85040).
Введение
Название белка большая цепь рибулозобисфосфаткарбоксилазы
Halothiobacillus neapolitanus-бактерия в которой был обнаружен исследуемый белок.Эта бактерия облигатный хемоавтотроф, использующий для получения энергии сульфиды.В лабораторных условиях хорошо растет на тиосульфате и тетратионате.Штамм этой бактерии был выделен из древнего природного источника, богатого сульфидами[1].
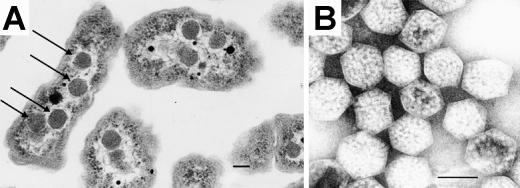
Электронные микрофотографии карбоксисом H. neapolitanus (А) Электронная микрофотография тонких срезов клеток H. neapolitanus с карбоксисомами внутри. В одной из показанных ячеек стрелками выделены видимые карбоксисомы. (B) Отрицательно окрашенное изображение интактных карбоксисом, выделенных из H. neapolitanus. Длинна черты =100нм [2]RuBisCO -фермент катализирующий реакцию фиксации углекислого газа к сахару- рибулозо-1,5-бифосфату. Этот фермент встречается и у растений и у бактерий(в частности у Halothiobacillus neapolitanus).У бактерий он входит в состав структур называемых карбоксисомами[3].
3D структуры
Есть информация о 2-х записяхв PDB с 3D структурами исследуемого в этом исследовании белка:
- 1SVD Сделанна с помощью X-ray, разрешение 1.80 Å
- 6UEW Сделанна с помощью X-ray, разрешение 2.40 Å
Изучение кластеров
- UniRef100
- representative: Ribulose bisphosphate carboxylase large chain:O85040
- seed:Ribulose bisphosphate carboxylase large chain
- UniRef90
- representative: Ribulose bisphosphate carboxylase large chain:O85040
- seed : Ribulose bisphosphate carboxylase large chain, CsoS2 N-peptide fusion
- UniRef50
- representative: Ribulose bisphosphate carboxylase large chain:O85040
- seed : Ribulose-1,5-bisphosphate carboxylase/oxygenaselarge subunit
representative во всех кластерах является белок исследуемый в этом практикуме. В UniRef100 всего два белка один в swiss-prot другой в TrEMBL. В UniRef90 21 белок(на 01.09.2022) из которых в swiss-prot только 2 , в TrEMBL 15 , остальные 4 в Uniparc. В UniRef50 4 570 белков, но в swiss-prot всего 40, 4 335 в TrEMBL 9 219 и 195 в Uniparc
- UniRef100
Запросы
Файл с запросами и количеством выданных файлах.- В первом запросе я искал белок Ribulose bisphosphate carboxylase large chain в организмах отличных от Halothiobacillus neapolitanus.
- Во втором запросе я искал белки такого же семейства как и Ribulose bisphosphate carboxylase large chain в пределах рода Halothiobacillus
- В третьем запросе я искал белок Ribulose bisphosphate carboxylase large chain у эукариот(Eukaryota)
- В четвертом запросе я искал фермент из той же классификации что и Ribulose bisphosphate carboxylase large chain среди вторичноротых животных.И как ни странно нашелся 1 результат из автоматической базы данных TrEMBL.Такой белок(AC: A0A822IMI4) был найден у лягушки.Очевидно это невозможно.И действительно его уровень существования 4 т.е. он предсказанный.
Скачивание протеомов и минианализ
Протеом моей бактерии Halothiobacillus neapolitanus был скачен командой(команда для новой версии сайта):wget 'https://rest.uniprot.org/uniprotkb/stream?compressed=true&download=true&format=txt&query=%28proteome%3AUP000009102%29' -O UP000009102.swiss.gz
Протеом Escherichia coli был скачен командой:wget 'https://rest.uniprot.org/uniprotkb/stream?compressed=true&download=true&format=txt&query=%28proteome%3AUP000000625%29' -O UP000000625.swiss.gz
Протеом Halothiobacillus neapolitanus с ID UP000009102 в базе данных swiss-prot имеет 19 белков в TrEMBL 2335 .CPD:Standard BUSCO в норме.Протеом Escherichia coli UP000000625 всего состоит из 4448 белков из которых целых 4400 находятся в swiss-prot. CPD: standart, BUSCO в норме.
Сравнение протеомов
Трансмембранные белки
Количество трансмембранных белков в протеоме Escherichia coli (UP000000625) нашел по запросу в Uniprot :
(ftlen_transmem:[* TO *]) AND (proteome:UP000000625)Количество трансмембранных белков в протеоме Halothiobacillus neapolitanus (UP000009102) нашел по запросу в Uniprot :
(ftlen_transmem:[* TO *]) AND (proteome:UP000009102)Результат: у Escherichia coli 957 трансмембранных белков, у Halothiobacillus neapolitanus 426
Ферменты
Количество ферментов в протеоме Escherichia coli (UP000000625) нашел по запросу в Uniprot :
(proteome:UP000000625) AND (ec:*)Количество ферментов в протеоме Halothiobacillus neapolitanus (UP000009102) нашел по запросу в Uniprot :
(proteome:UP000009102) AND (ec:*)Результат: у ecoli 1695 ферментов, у Halothiobacillus neapolitanus 638
Лиазы
Количество лиаз в протеоме ecoli (UP000000625) нашел по запросу в Uniprot :
(proteome:UP000000625) AND (ec:4.*)Количество лиаз в протеоме Halothiobacillus neapolitanus (UP000009102) нашел по запросу в Uniprot :
(proteome:UP000009102) AND (ec:4.*)Результат: у Escherichia coli 168 лиаз, у Halothiobacillus neapolitanus 65
Все ли белки начинаются с метеонина?
Я скачал протеомы в формате фаста этими командами .Далее испозьзовал Скрипт для получения ответа на вопрос:
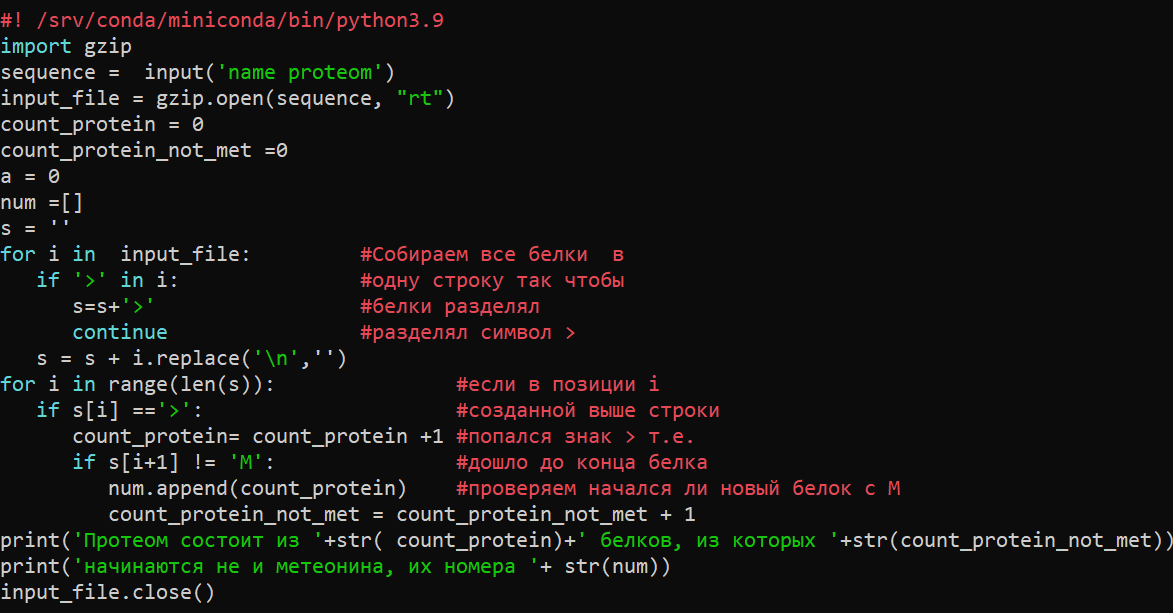
По результатам его работы я получил что в обоих протеомах нет белка который начинается не с метеонина.
Распространенные ключевые слова
Для получения самых распространенных слов я воспользовался командой:
zgrep ^KW Proteome_ID.swiss.gz |cut -d ' ' -f4- | tr -d '.'|tr '\n' ';' |tr ';' '\n' | cut -d '{' -f 1 |cut -d '}' -f 2 |sort |uniq -c |sort -rn > topProteome_IDВ итоге я получил 2 файла с топ 10 слов для протеомов: ecoli (UP000000625) и Halothiobacillus neapolitanus (UP000009102)
Первое место в обоих протеомах занимает Referenceproteome, что ожидаемо т.к. они из референсных протеомов.Далее у Escherichia coli второе место занимает 3D-structure, что опять же не увдивительно, ведь эта бактерия модельный объкт, ее активно изучили.А вот 3D-structure у Halothiobacillus neapolitanus в топ 10 не вошел.Что говорит о не слишком высокой степени изучения этой бактерии.
Список литературы
- 1. Wood AP, Woodall CA, Kelly DP. Halothiobacillus neapolitanus strain OSWA isolated from "The Old Sulphur Well" at Harrogate (Yorkshire, England). Syst Appl Microbiol. 2005 Oct;28(8):746-8. doi: 10.1016/j.syapm.2005.05.013. PMID: 16261864.
- 2. Tsai Y, Sawaya MR, Cannon GC, Cai F, Williams EB, Heinhorst S, Kerfeld CA, Yeates TO. Structural analysis of CsoS1A and the protein shell of the Halothiobacillus neapolitanus carboxysome. PLoS Biol. 2007 Jun;5(6):e144. doi: 10.1371/journal.pbio.0050144. PMID: 17518518; PMCID: PMC1872035.
- 3. Wheatley NM, Sundberg CD, Gidaniyan SD, Cascio D, Yeates TO. Structure and identification of a pterin dehydratase-like protein as a ribulose-bisphosphate carboxylase/oxygenase (RuBisCO) assembly factor in the α-carboxysome. J Biol Chem. 2014 Mar 14;289(11):7973-81. doi: 10.1074/jbc.M113.531236. Epub 2014 Jan 23. PMID: 24459150; PMCID: PMC3953307.