Практикум 3. Построение и анализ дерева, содержащего паралоги.
В первом Практикуме мы строили филогенетическое древо восьми бактерий,
руководствуясь древом, приведённым в тексте задания. Теперь же нам предстоит реконструировать филогенетическое
древо. Для этого нам понадобится составленное в прошло практикуме древо и новое древо, построенное по последовательностям
белка энолазы (CLPX_ECOLI).
Выбранные мной белки отображены в Таблице 1.
| Название |
Мнемоника |
Таксономия |
| Bradyrhizobium diazoefficiens |
BRADU |
| Rhizobium etli |
RHIEC |
| Burkholderia cenocepacia |
BURCA |
| Neisseria meningitidis |
NEIMA |
| Enterobacter sp. 638 |
ENT38 |
| Salmonella typhimurium |
SALTY |
| Pasteurella multocida |
PASMU |
| Proteus mirabilis |
PROMH |
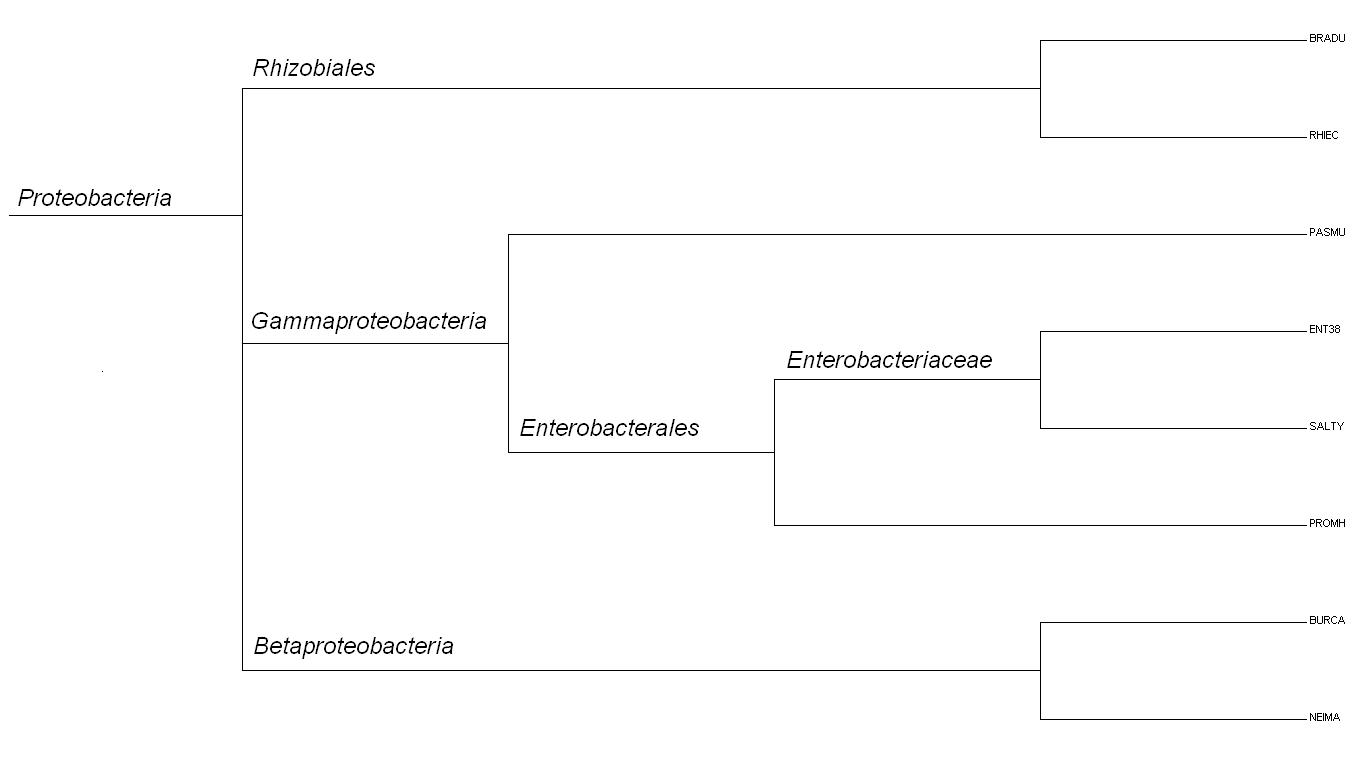
Далее в отчете приведено уже представленное ранее в Практикуме 1 изображние дерева, полученного с помощью
программы Mega (Рис.1):
Рис.1 Изображение дерева, полученное с помощью программы Mega
Потом с помощью программы blastp в геномах выбранных мной прокариот были найдены гомологи белка CLPX_ECOLI.
(Сначала с помощью программы
cat *fasta >> pr3.fasta я собрала необходимые мне белки в один файл, после чего программой
makeblastdb -in pr3.fasta -dbtype prot из полученного файла была собрана база данных,
в которой я программной
blastp -evalue 0.001 -query CLPX_ECOLI.fasta -db pr3.fasta > out.fasta нашла гомологи белка).
Результат выполнения программы можно посмотреть
здесь.
Список гомологичных белков и их функции:
CLPX_SALTY --- ATP-dependent Clp protease ATP-binding subunit
CLPX_ENT38 --- ATP-dependent Clp protease ATP-binding subunit
CLPX_PROMH --- ATP-dependent Clp protease ATP-binding subunit
CLPX_BURCA --- ATP-dependent Clp protease ATP-binding subunit
CLPX_PASMU --- ATP-dependent Clp protease ATP-binding subunit
CLPX_RHIEC --- ATP-dependent Clp protease ATP-binding subunit
CLPX_BRADU --- ATP-dependent Clp protease ATP-binding subunit
CLPX_NEIMA --- ATP-dependent Clp protease ATP-binding subunit
HSLU_PROMH --- ATP-dependent protease ATPase subunit HslU
HSLU_RHIEC --- ATP-dependent protease ATPase subunit HslU
HSLU_PASMU --- ATP-dependent protease ATPase subunit HslU
HSLU_ENT38 --- ATP-dependent protease ATPase subunit HslU
HSLU_BRADU --- ATP-dependent protease ATPase subunit HslU
HSLU_SALTY --- ATP-dependent protease ATPase subunit HslU
HSLU_BURCA --- ATP-dependent protease ATPase subunit HslU
B4F2B3_PROMH --- ATP-dependent zinc metalloprotease FtsH
A4WEY9_ENT38 --- ATP-dependent zinc metalloprotease FtsH
FTSH_SALTY --- ATP-dependent zinc metalloprotease FtsH
RUVB_BRADU --- Holliday junction ATP-dependent DNA helicasa
Q2K4M2_RHIEC --- ATP-dependent zinc metalloprotease FtsH
Q8KKT3_RHIEC --- Probable ATPase (ATP-binding) protein
A0A0H2XMS5_BURCA --- ATP-dependent zinc metalloprotea
H7C810_BRADU --- ATP-dependent zinc metalloprotease FtsH
Q9CNJ2_PASMU --- ATP-dependent zinc metalloprotease FtsH
RUVB_NEIMA --- Holliday junction ATP-dependent DNA helicasa
YIFB_SALTY --- Uncharacterized protein YifB
C помощью программы MEGA я получила реконструированное филогенетическое древо, представленное на Рис.2.
Рис.2 Изображение дерева, полученное с помощью программы Mega

С первого взгляда видны две больших ортологичных группы белков:
CLPX и HSLU. Белки обоих групп являются гомологами и являются результатом процесса видообразования.
Можно также предположить, что белки CLPX и HSLU в каждом из организмов являются паралогами, произошедшими во время дупликации.
Кроме того можно заметить отдельную группу, состоящую всего из двух белков, RUVB. Возможно, они также ортологичны друг к другу.
На Главную страницу
На страницу Семестра
