Для данного практикума использовалась оксидаза, анализируемая в практикумах этого семестра с PDB ID = 1w07.
Были найдены 4 структурных гомолога рассматриваемого белка, а именно цепи А (т.к. он гомодимер). Был использован поиск по сходству структур в PDBeFold. Были отобораны структуры разных белков с RMSD между 0,8 и 2,5 и длиной выравнивания более 50% от длины исследуемого белка.
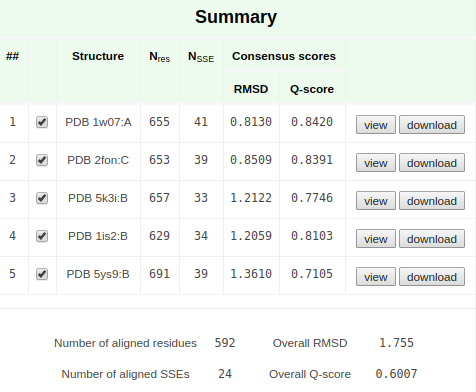
Summary по выдаче можно посмотреть на рис. 1 , выравнивание вторичных структур на рис. 2, и статистику по структурам на рис. 3

Рис 1. Summary выдачи PDBeFold

Рис 2. Выравнивание вторичных структур по выдаче PDBeFold
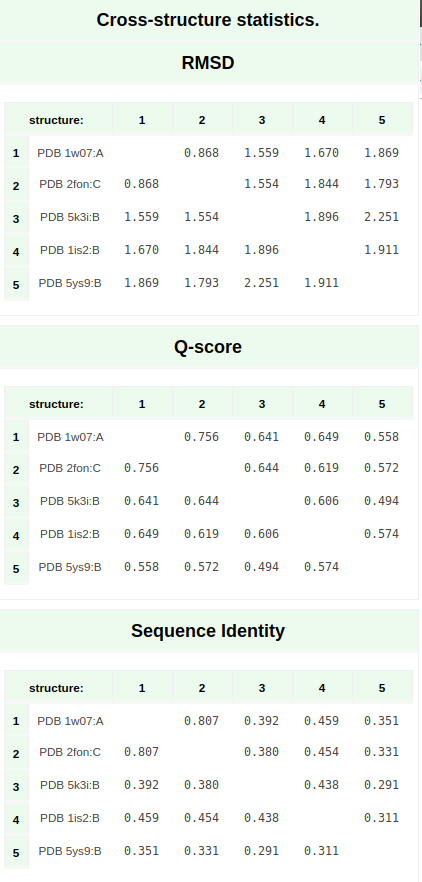
Рис 3. Статистика выдачи PDBeFold
Как можно выдеть на рис. 4 структуры совмещены довольно неплохо.
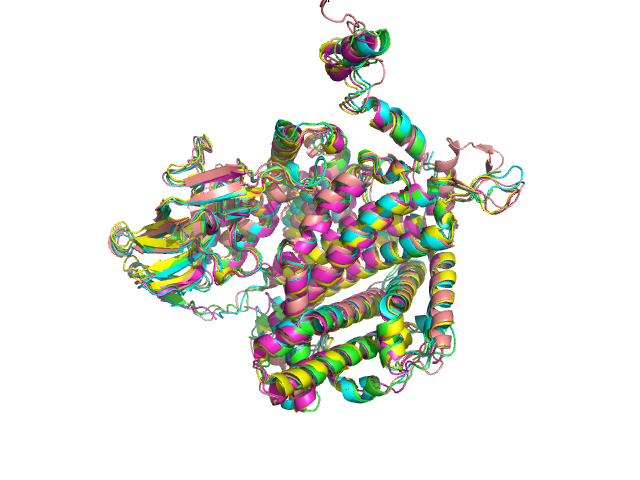
Рис 4. Совмещенные структуры 1w07 и его гомологов по выдаче PDBeFold
Также можно скачать выравнивание последовательностей, полученно по выдаче PDBeFold и выравнивание последовательностей, полученное в Jalview с помощью Muscle. Эти же выравнивания представлены на рис. 5 и 6. Как можно видеть, в целом они неплохо совпадают.

Рис 5. Выравнивание, построенное по структурам

Рис 6. Выравнивание, построенное Muscle
На рис. 7 показано выбранное место, где эти выравниваания отличаются. Как можно видеть, последовательность 5k3i в выравнивании по структуре смещена на 1 остаток вправо, из-за чего 61ом столбце теряется полная консервативность по пролину. Мне кажется, в этом случае Muscle строит более правильное выравнивание. К тем более, как можно видеть на рис. 8 это место находится в районе петель и непредставляет собой консервативной вторичной структуры.
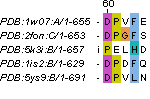 |
 |
Рис 7. Выравнивание, полуенное по структурам (слева) и с помощью Muscle (справа).
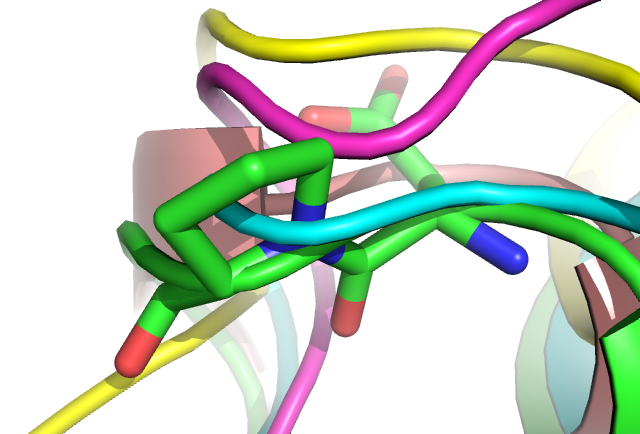
Рис 8. Изображение совмещенных структур в отличающемся остатке