Филогенетическая реконструкция белка цитохрома B
Объект исследования: аминокислотные последовательности белка CYB (цитохром B), животных из прака 1.
Выравнивание: получено алгоритмом MUSCLE, с помощью программы Jalview. Выравнивание.fasta
Укоренение: деревья укоренены в ветвь, отделяющую воробьинообразных от трубконосых.
1. Дерево по таксономии.
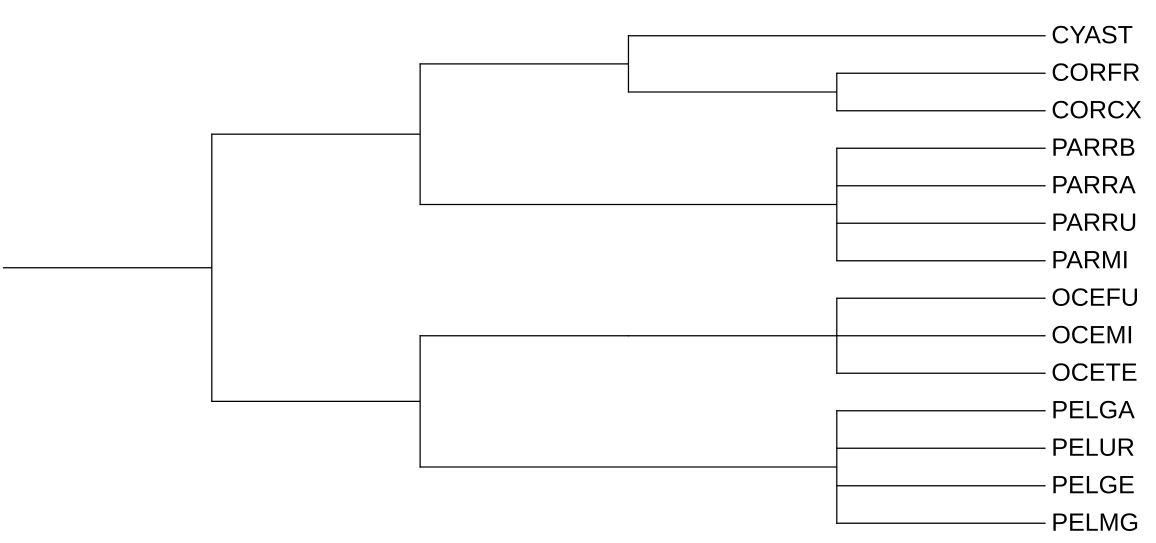
Рис 1. Дерево видов по таксономическанным данным NCBI.
2. Реконструкция программами FastME и IQ-TREE
Для оценки расстояний использовались две модели:
- p-distance:считает долю замененных аминокислот без учета специфики мутаций.
- MtREV:матрица замен для митохондриальных белков, учитывает специфику мутаций

Рис 2. Программа FastME. Алгоритм: Minimum Evolution. Модель: p-distance
Ошибки: Род Corvus реконструирован неверно - CORFR попал в одну группу с сойкой CYAST. В роду Pelecanoides пара PELMG и PELGE оказалась разделена другими видами.

Рис 3. Программа FastME. Алгоритм: Minimum Evolution. Модель: MtREV
Ошибки: Топология полностью совпадает с результатом p-distance. Смена модели не помогла исправить неточности в родах Corvus и Pelecanoides.
Реконструкция методом Maximum Likelihood
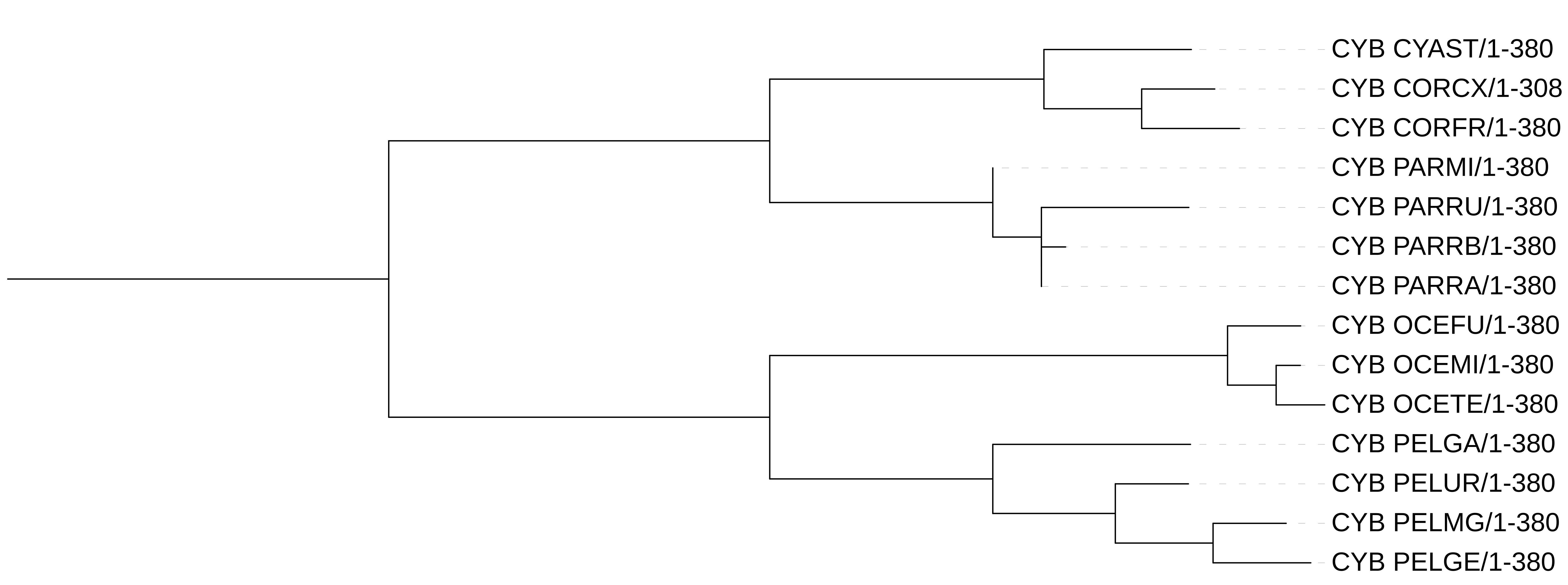
Рис 4. Программа IQ-TREE. Алгоритм: Maximum Likelihood. Модель: Auto
Анализ: Это дерево наиболее точно повторяет эталон. Оно правильно объединило воронов (CORCX и CORFR). В роду ныряющих буревестников оно верно восстановило ожидаемые пары видов: (PELGE + PELMG) и (PELGA + PELUR).
Выводы
Для белка CYB метод максимального правдоподобия в IQ-TREE показал лучший результат. Методы в FastME ошиблись в определении близости видов внутри родов, не сумев правильно сгруппировать пары в роду Pelecanoides и род Corvus.
Источник таксономии: IOC World Bird List (v14.1), Order Procellariiformes.