Общая информация о структуре представлена на этой странице сайта. Загрузим нашу структуру и покажем ее через cartoon. Уберем все лишнее, чтобы изображение выглядело чище. Сделаем фон белым:
fetch 2CX1
remove solvent
show cartoon, all
bg white
Выделим гетероатомы (молекулы TLA и MSE), переименуем выборки в названия соответствующих молекул, покажем их с помощью sticks, покрасим в условные цвета атомов (углерод выкрасим в бирюзовый):
select TLA, resn TLA
select MSE, resn MSE
show sticks, TLA
color atomic, TLA
util.cba(5,"TLA",_self=cmd)
util.cba(5,"MSE",_self=cmd)
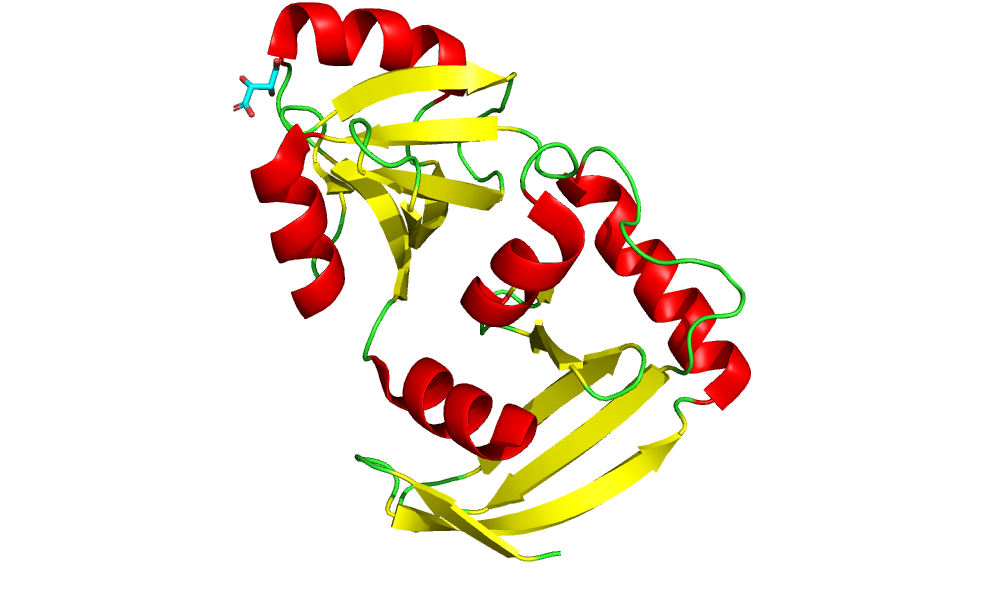
В структуре присутствует одна полимерная цепь А. Оставим цвет таким же. В биологической единице также одна цепь (то есть белок APE0525 функционирует как мономер). Биологическая единица не отличается от асимметричной.
Структура представлена на рис.1

Покрасим альфа-спирали вторичной структуры в красный, бета-листы в желтый (рис. 2):
color red, ss h
color yellow, ss s
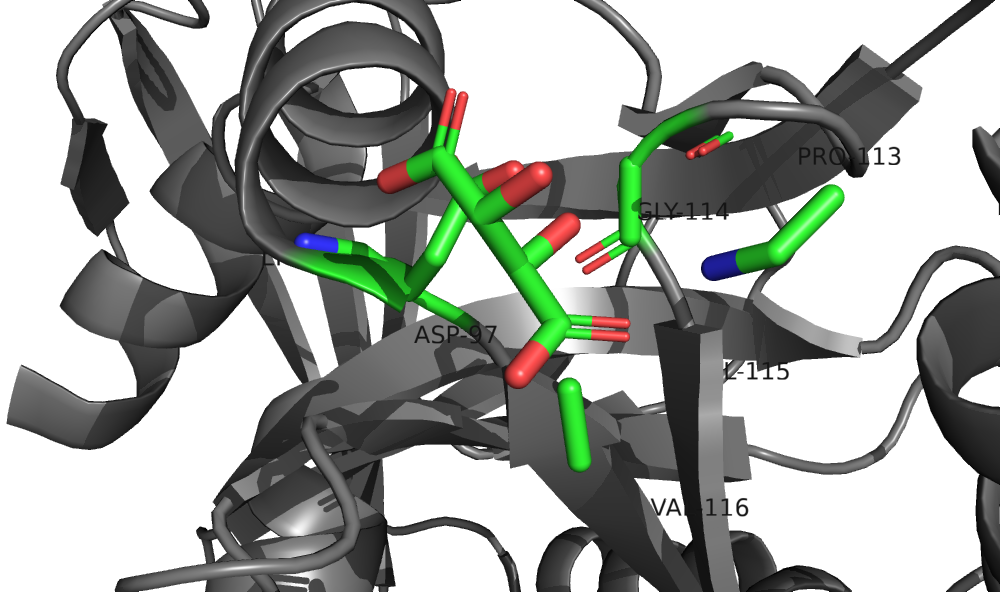
В структуре присутствует 2 типа малых молекул: L(+)-Винная кислота (TLA), селенометионин (MSE). Покажем аминокислотные остатки белка на расстоянии до 5 ангстрем от молекулы селенометионина. Назовем выборку neighbours.
select neighbours, all within 5 of MSE
Выкрасим всю структуру в серый, а лиганд и его окружение по классическим цветам:
color grey, all
util.cba(33,"neighbours",_self=cmd)
util.cba(33,"TLA",_self=cmd)
Назовем все аминокислоты в выборке neighbour, подпишем их номера:
label neighbours
Результат представлен на рис.3.