Практикум 2. Филогенетическая реконструкция и сравнение деревьев
Создадим выравнивание последовательностей цитохромов B из выбранных в предыдущем практикуме животных (выравнивания находятся в файле cyb-alignment.fasta).
Далее тремя способами реконструируем филогенетическое дерево и визуализируем их в iTOL:
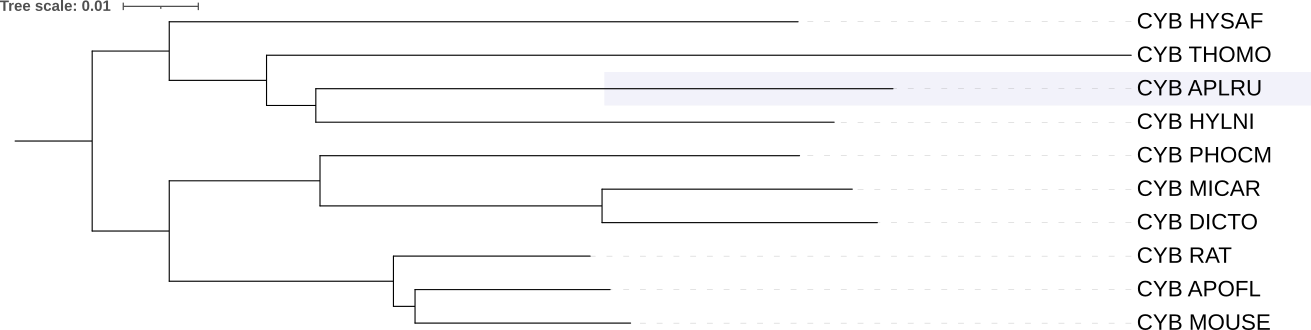

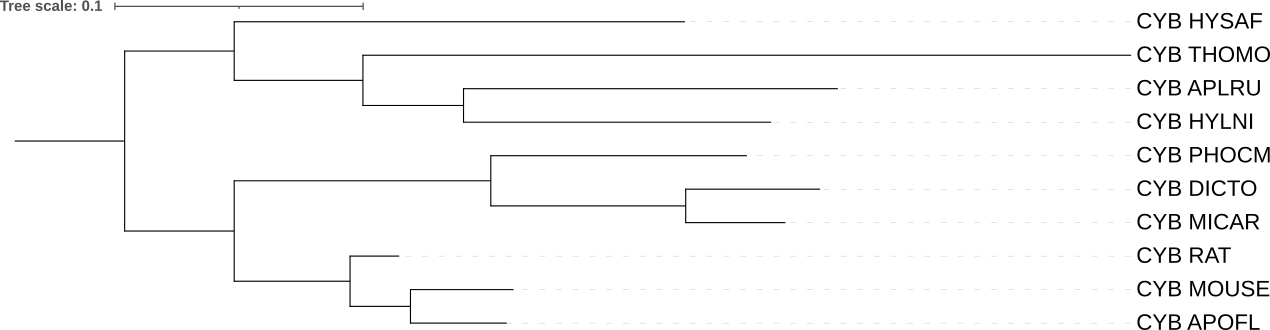
Деревья были укоренены в ветвь, которая отделяет 4 листа (HYSAF, THOMO, HYLNI, APLRU) от остальных листьев. Деревья получились абсолютно идентичными, только в реконструкции с помощью iqtree длина ветвей короче.
Сравним полученные деревья с деревом видов
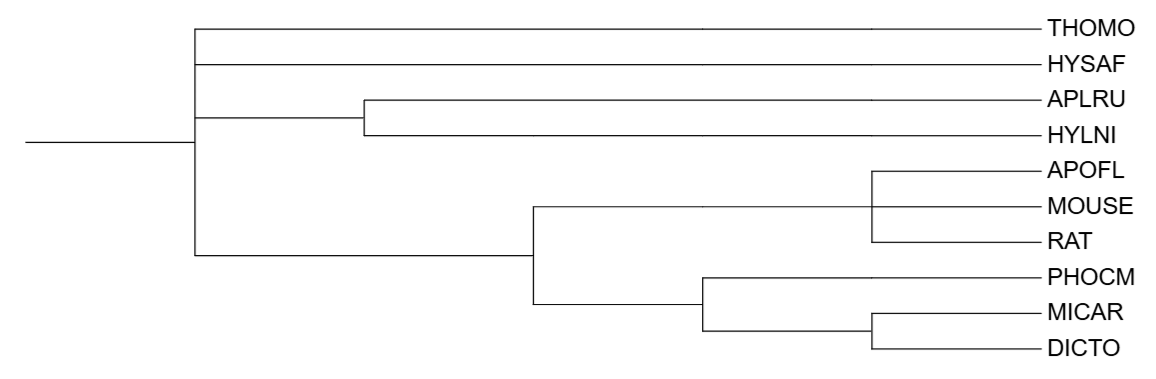
Реконструированные деревья и дерево видов имеют идентичную топологию на уровне крупных клад.
На реконструированных деревьях появились дополнительные клады, которые в таксономии отсутствуют из-за неразрешенностей (политомий):
1) На дереве видов клада {RAT, MOUSE, APOFL} представлена как политомия, на реконструированных деревьях эта клада разрешена как (RAT, (APOFL, MOUSE)), что не противоречит таксономии, а лишь уточняет её.
2) На реконструированных деревьях появилась клада {THOMO, APLRU, HYLNI}. Вид THOMO (гофер) теперь включён в одну кладу с APLRU и HYLNI (белкообразные), которые в таксономии выходили из общего узла независимо.
3) Новая клада {HYSAF, THOMO, APLRU, HYLNI}: группа, объединяющая дикобраза - HYSAF1 со всеми остальными не мышеобразными грызунами.
Единственное отличие между деревом видов и реконструированными деревьями заключается в разрешении политомий, поэтому ошибочно отсутствующих или присутствующих групп в данном случае нет.