Практикум 3. Укоренение. Сравнение деревьев. Бутстрэп
Реконструкция дерева по нуклеотидным последовательностям
Для выбранных животных реконструируем дерево по последовательностям малой РНК митохондриальных рибосом (12S rRNA).
Митходриальный геном был найден не для всех видов, поэтому для этих организмов были взяты ближайшие к ним виды:
1. Для Microtus arvalis был взят Microtus obscurus. Мнемоника: 9RODE
2. Для Phodopus campbelli - Phodopus sungorus. Мнемоника: PHOSU
3. Для Hystrix africaeaustralis - Hystrix indica. Мнемоника: 9HYST
4. Для Thomomys monticola ближайщий родственник Thomomys bottae, но в EMBL файле для него не было координат для 12S rRNA, только join(JAVLKH010000001.1:1..17079), поэтому был взят родственник из другого рода Geomys pinetis. Мнемоника: GEOPI
5. Для Aplodontia rufa тоже не нашлись родственники того же рода, поэтому для построения дерева был взят Sciurus vulgaris. Мнемоника: SCIVU
Далее последовательности были выравнены и записаны в файл 12S_rRNA_alignment.fasta. Потом перезаписали файл в формат phy и реконструировали дерево программой IQ-Tree. На дереве первое название ветви - это новая мнемоника, второе - старая. В качестве внешней группы был выбран GEOPI-THOMO.

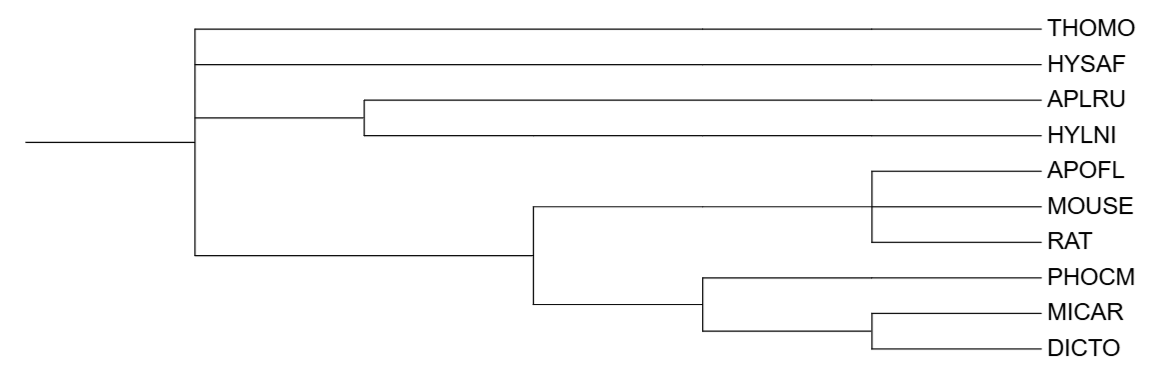
При сравнении реконструированного дерева с деревом видов видно, что внутренняя топология групп не изменилась. Группа HYLNI + APLRU (беличьи) остается монофилетичной и является сестринской по отношению к большой группе мышеобразных. Также сохранилось четкое разделение на две подгруппы: «мышиные» (APOFL, MOUSE, RAT) и «хомяковые/полевки» (PHOCM, MICAR, DICTO). Укоренение по ветви GEOPI-THOMO (Гофер) является биологически верным в рамках данного набора данных, так как согласно систематике, THOMO (подотряд Castorimorpha) является одним из наиболее удаленным от остальных видов (которые относятся к подотрядам Sciuromorpha и Myomorpha). К тому же ветвь к THOMO длинная. Это подтверждает, что последовательность 12S rRNA этого вида сильно отличается от остальных, что характерно для хорошей внешней группы.
Теперь повторим филогенетическую реконструкцию программой fastme, использовав 100 реплик бутстрепа. В качестве внешней группы для укоренения - GEOPI-THOMO.

При сравнении реконструированного дерева со 100 репликами бутстрепа с деревом видов так же видно, что основная структура сохранилась, но есть локальные изменения внутри групп. Группа APLRU + HYLNI (беличьи) реконструирована идеально с поддержкой 100. Разделение на две большие ветви (мышиные и хомяковые) также подтверждено поддержкой 100. В группе «хомяковых» топология (PHOCM внешняя к MICAR + DICTO) совпадает с деревом видов, но здесь поддержка 50 и это самый слабый узел на дереве. Хотя ветвь и совпала с эталоном, FastME не уверен в этом результате на данных для 12S rRNA. Узел (APOFL + RAT), поддержка 78; на дереве видов этот узел неразрешен. Поддержка 78 считается умеренной, тем не менее в 22% реплик бутстрепа программа видела другую картину (скорее всего ту, где крыса с мышью вместе).