Практикум 4. Реконструкции филогении
В данном практикуме необходимо было найти в протеомах отобранных 7 бактерий достоверные гомологи белка CLPX_ECOLI (ATP-связывающую субъединицу ATP-зависимой Clp протеазы Escherichia coli) с помощью программы blastp с поогом на E-value 0,0001.
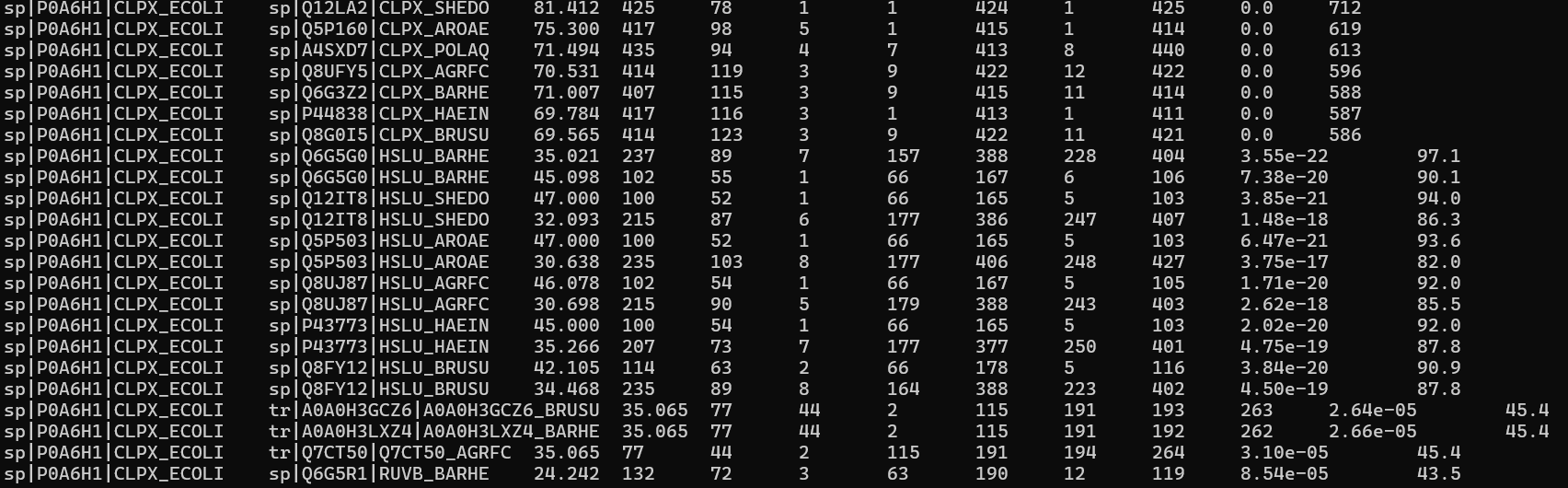
Далее для отобранных последовательностей с помощью программы fastme с эволюционной моделью MtREV и 100 репликами бутстрепа было реконструировано филогенетическое дерево.

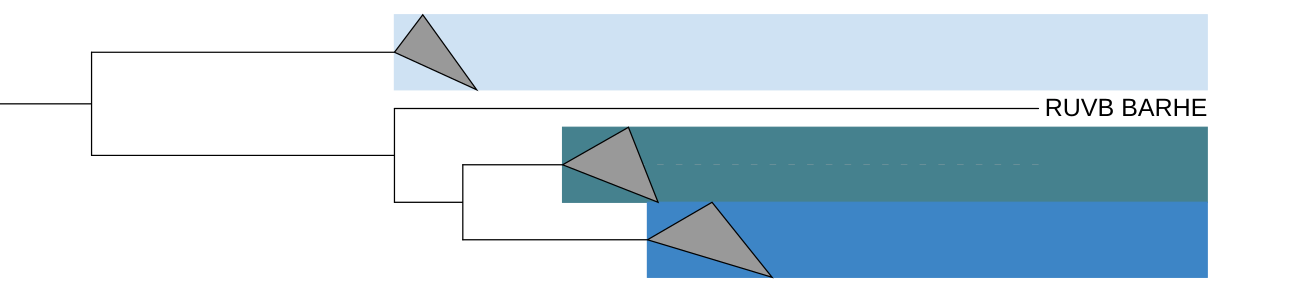
Три пары паралогов: белки из одного организма, появившиеся в результате дупликации гена в прошлом
1. CLPX_BARHE и HSLU_BARHE
2. CLPX_AGRFC и HSLU_AGRFC
3. CLPX_BRUSU и HSLU_BRUSU
Также паралогами будут, например, CLPX_BARHE и RUVB_BARHE, так как они гомологичны, но выполняют разные функции в одной клетке.
Три пары ортологов: один и тот же белок в разных организмах, разделившийся в момент расхождения видов
1. CLPX_BARHE и CLPX_BRUSU
2. HSLU_HAEIN и HSLU_SHEDO
3. CLPX_HAEIN и CLPX_SHEDO
Видно, что дерево сначала делится на функциональные группы (ClpX отдельно, HslU отдельно). Это говорит о том, что дупликация, создавшая эти два семейства, произошла гораздо раньше, чем разделились виды бактерий. Группу RUVB_BARHE можно охарактеризовать как высокодивергентного удаленного гомолога. Хотя RuvB, ClpX и HslU относятся к одному суперсемейству АТФаз, их функции в клетке кардинально различаются:
ClpX и HslU — это шапероны/анфолдазы, которые участвуют в деградации белков
RuvB — это ДНК-хеликаза, участвующая в рекомбинации и репарации ДНК.
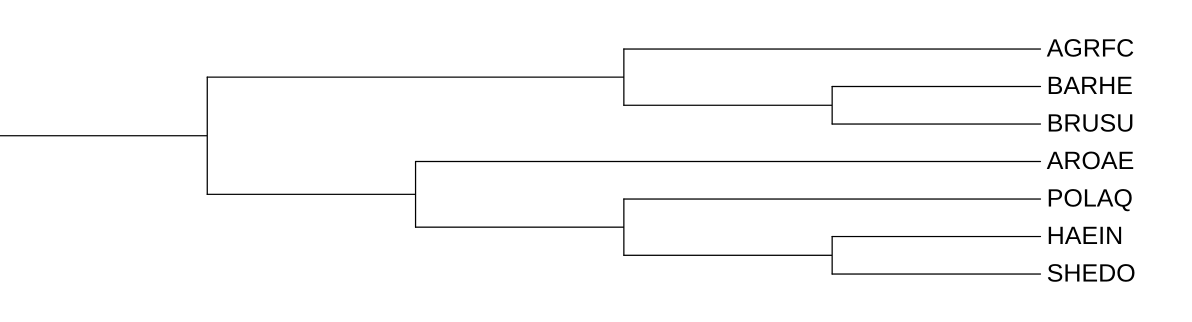
Сравнение реконструированной филогении ортологической группы с филогенией бактерий.
1. Группа HslU:
Ветвь {BARHE, BRUSU}: Полное совпадение. На дереве таксономии это сестринские виды.
Ветвь {BARHE, BRUSU, AGRFC}: Полное совпадение.
Ветвь {HAEIN, SHEDO}: Полное совпадение.
Ветвь {HAEIN, SHEDO, AROAE}: это правильная ветвь, хотя в ней и нет POLAQ.
1. Группа ClpX:
Ветвь {BARHE, BRUSU, AGRFC}: Совпадает с таксономией (клада Альфа-бактерий).
Ветвь {HAEIN, SHEDO}: Совпадает (клада Гамма-бактерий).
Ветвь {HAEIN, SHEDO, AROAE}: Противоречие. На дереве гомологов белок AROAE оказывается ближе к гамма-бактериям, чем POLAQ. Однако на дереве таксономии именно POLAQ должен быть ближе к ним.
1. Верхний кластер:
Ветвь {BARHE, AGRFC}: Противоречие. На дереве гомологов BARHE и AGRFC — ближайшие родственники. Но на дереве таксономии BARHE должен быть в паре с BRUSU.