| На главную |
|
Мои проекты | Ссылки | Обо мне | Мои заметки |
Эволюционные домены 2
Построение филогенетического дерева по выравниванию представителей домена, полученного в практикуме 9
Доменные архитектуры:
1 - однодоменная с YscJ_FliF (PF01514) с 1128 последовательностями,
2 - двухдоменная с YscJ_FliF (PF01514) и YscJ_FliF_C (ID PF08345) доменами.
Сравниваемые таксоны - это порядки: Aeromonadales - ae, Enterobacteriales - en, Alteromonadales - al, Vibrionales - vi, Oceanospirillales - oc, Pseudomonadales - ps, Xanthomonadales - xa.
Используем для работы полученную в 9м практикуме таблицу Excel.
Добавим к именам всех последовательностей спереди коды архитектуры и таксона. Получаю выравнивание taxonomy.fasta.
Проведем бутстреп-анализ для построения дерева, используя 2 метода из доступных в программе MEGA. Беру число реплик равное 100.
Гипотеза молекулярных часов удобна для оценок времен дивергенции видов и построения филогенетических деревьев, но может быть не точной. Приведу анализ с её использованием и не используя её.
Метод Neighbor-Joining строит неукоренённое дерево (Но его можно укоренить вручную), взвешивает длины ветвей и не предполагает использование молекулярных часов.
Метод UPGMA (Unweighted Pair Group Method with Arithmetic Mean) строит укоренённое ультраметрическое дерево и является наиболее оптимальным из использующих молекулярные часы.
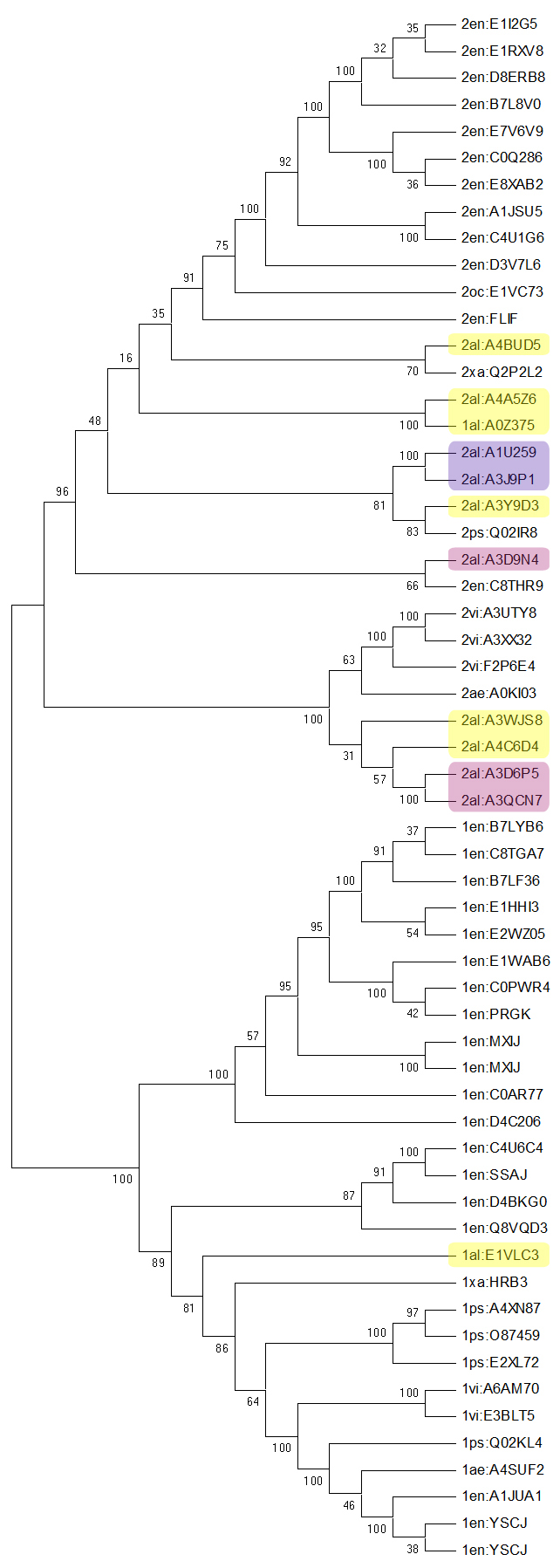
Деревья, полученные с помощью Neighbor-Joining и UPGMA соответственно:
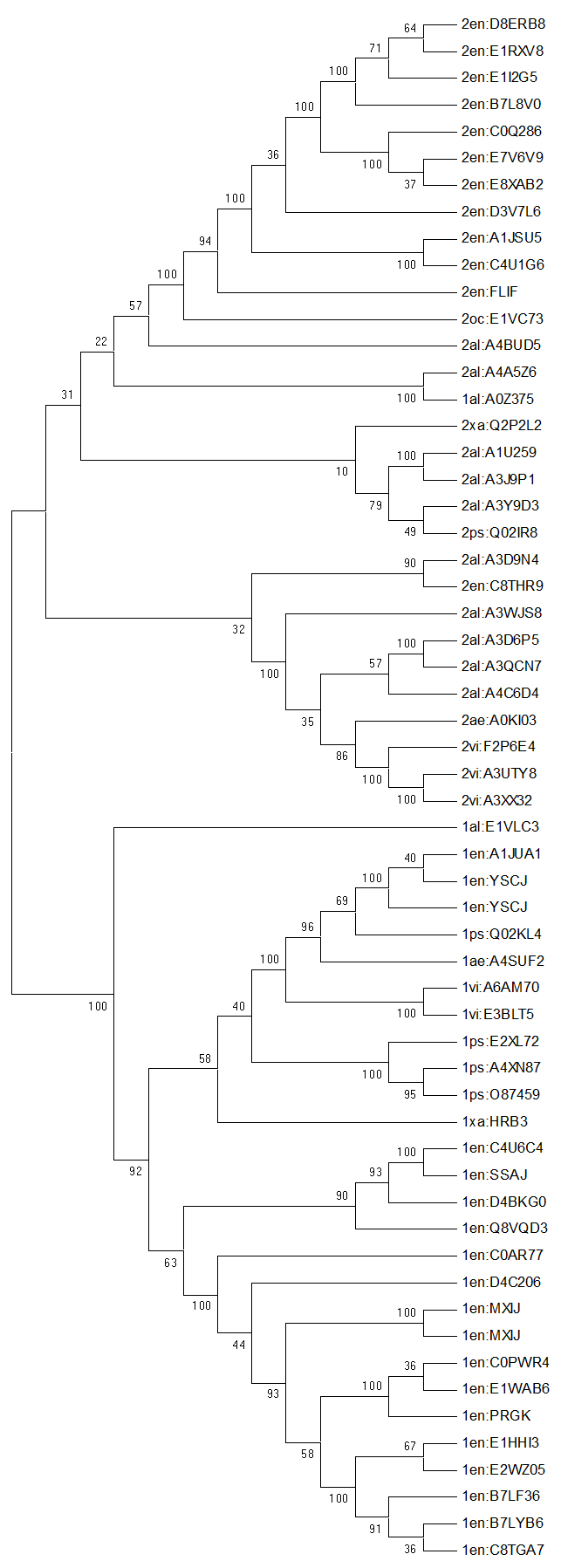
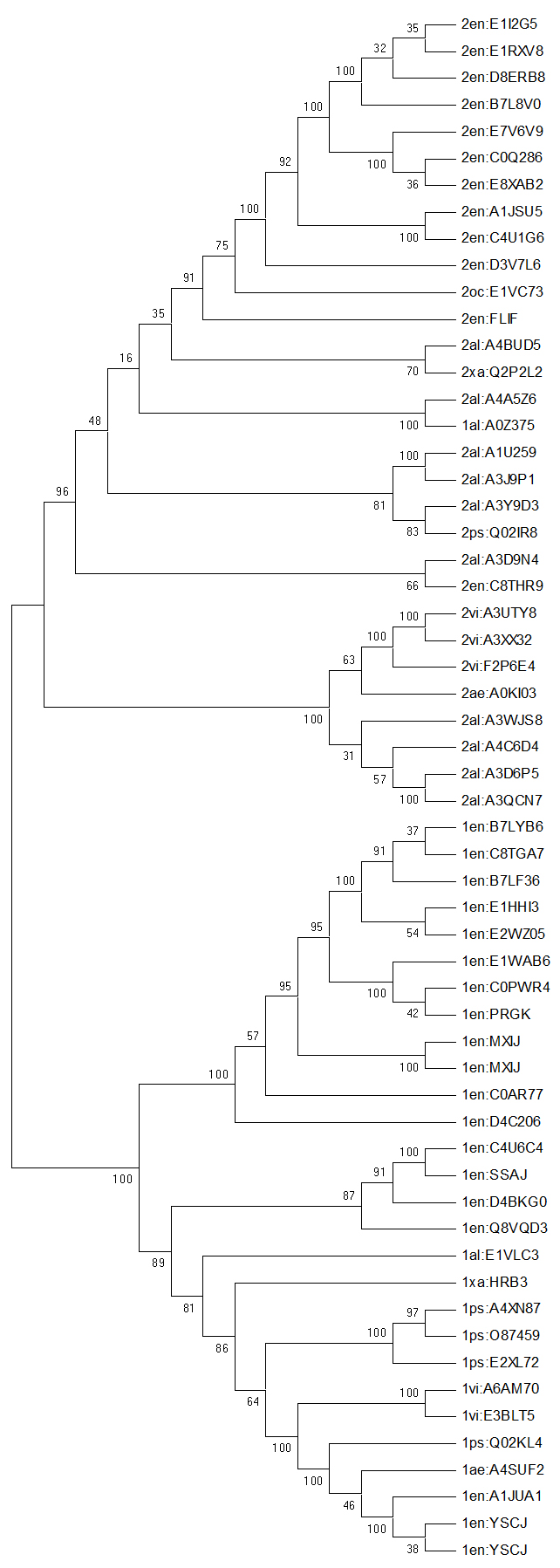
Использовала бутстреп-анализ, потому что он удобен предоставлением информации о достоверности построения ветвей. Правильные ветви имеют высокую поддержку. Чем число ближе к 100, тем правильнее ветвь.
Верхние клады деревьев представлены последовательностями с двухдоменной архитектурой (за одним исключением), нижние - с однодоменной. На дереве, построенном с UPGMA (справа), поддержка первых ветвей верхней клады выше, чем на дереве, полученном с Neighbor-Joining.
Использовала программу визуализации деревьев - . Получилась картинка с обращенным порядком клад. Клада из организмов с однодоменной архитектурой окрашена красным, с двудоменной - синим. Названия таксонов, встречающихся более двух раз, выделены цветом. Левое дерево - Neighbor-Joining, правое - UPGMA.
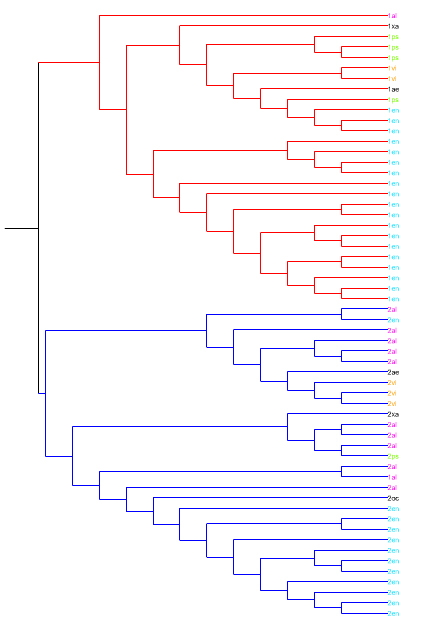
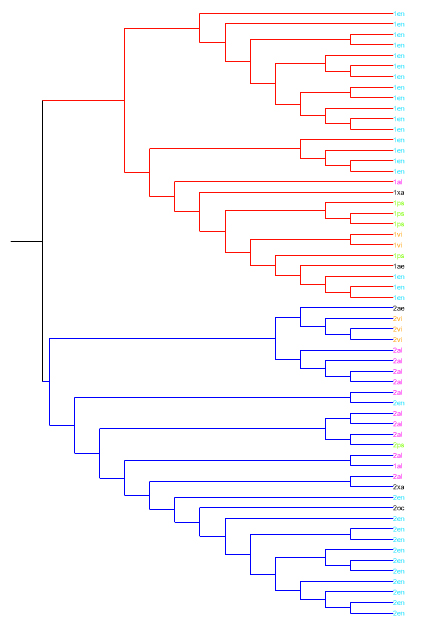
Ссылки на файлы со скобочной структурой: nj.nwk, upgma.nwk.
Выводы о возможном пути эволюции доменной архитектуры, включающей исследуемый домен
По дереву видно, что первая и вторая архитектуры относительно обособлены друг от друга, но не обособлены поо составу организмов. Вероятно, что в ходе эволюции не было четкого разделения порядков на организмы с первой (однодоменная с YscJ_FliF (PF01514)) - красная клада и организмы со второй (двухдоменная с YscJ_FliF (PF01514) и YscJ_FliF_C (ID PF08345)) архитектурой - синяя клада.Возможно, это связано с тем, что у организмов разных порядков события приобретения нового домена или потери старого происходили независимо. Первая архитектура наиболее характерна для Enterobacteriales, вторая чаще встречается у Alteromonadales. Для остальных порядков архитектуры характерны в одинаковой степени (возможно, из-за малого числа представителей данных таксонов, входящих в состав выборки для построения дерева).
На примере Alteromonadales - al можно рассмотреть эволюцию внутри порядка. Ниже изображены полученные бутстрэп-анализом деревья UPGMA: слева - приведенное выше дерево для всех выбранных последовательностей, справа - построенное на основе выравнивания для порядка Alteromonadales.
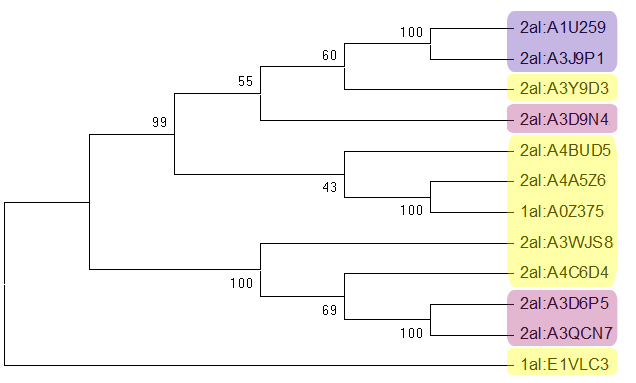
Порядок Alteromonadales включат в себя несколько семейств, из которых на построенных деревьях представлены Alteromonadaceae, Idiomarinaceae и Shewanellaceae.
Семейство Shewanellaceae - наиболее молодое. Большинство представителей имеет вторую архитектуру.
Семейство представлено последовательностями A3D6P5, A3D9N4 (Shewanella baltica) и A3QCN7 (Shewanella loihica) - выделены розовым. Мне показалось странным, что последовательности одного вида и даже штамма A3D6P5 и A3D9N4 получились далеко друг от друга, но их последовательности, действительно, значительно отличаются. A3D6P5 и A3QCN7 же представляют один лист , хотя известно, что Shewanella loihica - более древний вид.
Представители семейства Alteromonadaceae выделены фиолетовым, Idiomarinaceae - желтым. При этом два представителя Idiomarinaceae имеют белки, относящиеся к первой архитектуре.
Деревья, которые сравнивались с полученными данными, в большинстве были построены на основе анализа рРНК. Скорее всего, сравнения последовательностей белка моего домен недостачно для получения филогении класса гаммапротеобактерий, и тем более его порядков. Зато можно проследить разделение на организмы, в которых домен входит в первую или вторую архитектуру.