1
Ознакомление с программой Muscle
Невыровненные последовательности в GeneDoc выглядят так (показаны частично, полная картинка здесь):
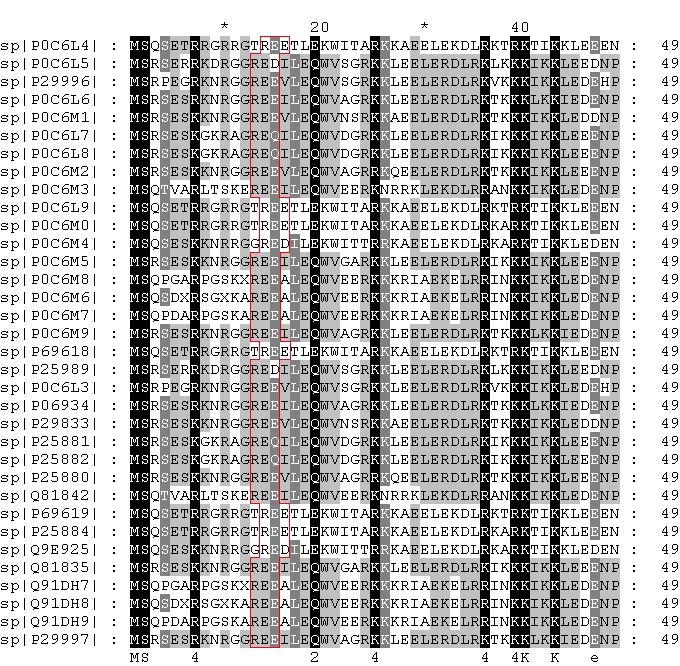
Мы можем определить вероятное расположение пробелов в выравнивании на глаз. Например, на приведенном выше рисунке красным отмечены повторяющиеся во всех последовательностях группы REE (в некоторых последовательностях последний а.о. варьирует, но это не имеет значения). В большинстве последовательностей эти группы располагаются одинаково, но в некоторых они сдвинуты на один а.о. вправо, следовательно, в остальных последовательностях при выравнивании перед этой группой появится пробел.
Теперь выровняем последовательности при помощи программы muscle, выполнив команду
muscle -in delta.fasta -out delta_aligned.fasta
Мы получили выравнивание в fasta-формате, оно находится в файле delta_aligned.fasta. Мы можем импортировать его в GeneDoc (последовательности показаны частично, полная картинка здесь):

Мы видим, что совпадений стало гораздо больше, причем для этого не понадобилось вставлять много гэпов: всего один гэп как раз в том месте, которое мы обнаружили в еще невыровненных последовательностях. Кроме того, после выравнивания изменился порядок последовательностей.
2
Выравнивание набора гомологов своего белка
| Идентификатор | E-value | Идентичность (% совпавших а.о.) |
Сходство (% положительных замен) |
| OTC_SALTI | 3e-180 | 89% | 95% |
| OTC_YERP3 | 6e-164 | 79% | 89% |
| OTC_VIBHB | 2e-136 | 68% | 84% |
| OTC_PSEPK | 3e-47 | 35% | 51% |
| OTCC_STRRT | 2e-95 | 53% | 70% |
| OTC_STAES | 3e-112 | 57% | 74% |
fasta-формат
формат .msf

| Позиции выравнивания | Позиции OTC1_ECOLI |
| 8-25 | 7-24 |
| 44-64 | 43-63 |
| 83-110 | 82-109 |
| 124-142 | 123-141 |
| 159-175 | 158-174 |
| 230-240 | 229-239 |
| 270-278 | 269-277 |
| 315-333 | 314-332 |
Большое количество гэпов в первой строке выравнивания (последовательность OTC_PSEPK) вполне может быть объяснено тем, что этот белок произошел путем множества делеций либо вставок из общего предка всех рассмотренных белков. То же можно сказать и о второй последовательности (OTCC_STRRT), которая в данном выравнивании содержит меньшее число гэпов.
Похоже, не несут биологического смысла позиции выравнивания с 334 по 341 (последние, туда входят лишь 2 а.о. из OTC1_ECOLI: 333 и 334) для первых трех последовательностей. У них длины "хвостов" и их состав существенно различаются. Возможно, эти концевые участки не несут никакой функциональной нагрузки. Тем не менее, у белков OTC_YERP3, OTC1_ECOLI и OTC_SALTI даже здесь наблюдается сходство, что также подтверждает их гомологичность.
3*
Другие программы множественного выравнивания
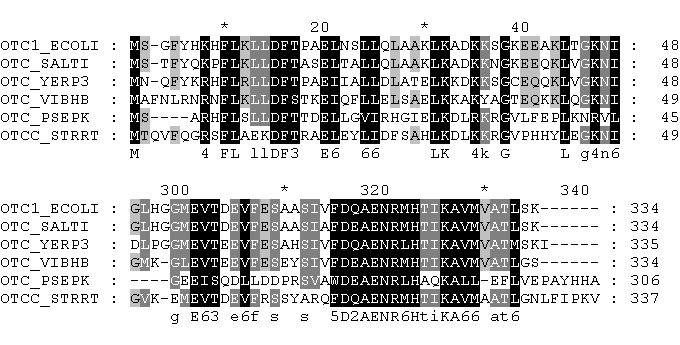
Выравнивание из edialign также отличается от двух остальных только началом и концом. В начале программа так же, как и mafft, выровняла метионины, но по-другому расположила аминокислотные остатки между этими метионинами и первой консервативной позицией (8-я, соответствует 7-й позиции OTC1_ECOLI). Эти изменения ничего не значат, так как биологического смысла этот участок как не нес, так и не несет. Конечный участок, также не имеющий биологического смысла для OTC_VIBHB, OTC_PSEPK и OTCC_STRRT, здесь такой же, как и в выравнивании, полученном muscle.
Начало и конец выравнивания из edialign показаны на рисунке ниже.
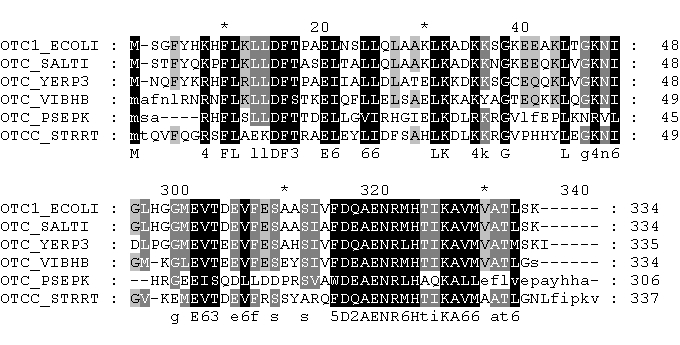
4*
Знакомство с некоторыми программами обработки множественных выравниваний
к проектам
на главную