Занятие 8. Ферменты и метаболические пути
1. Код фермента
Изучаемый фермент OTC1_ECOLI имеет EC 2.1.3.3. Расшифровка этого кода по пунктам такова:2 - transferases (трансферазы), переносят группы атомов с одного субстрата (донора) на другой (акцептор),
2.1 - transferring one-carbon groups (переносчики групп, в состав которых входит один атом углерода),
2.1.3 - Carboxy- and Carbamoyltransferases (карбокси- и карбамоилтрансферазы), осуществляют перенос карбоксильных и карбамоил-групп
(-СООН, -CONH2),
2.1.3.3 - ornithine carbamoyltransferase (орнитинкарбамоилтрансфераза).
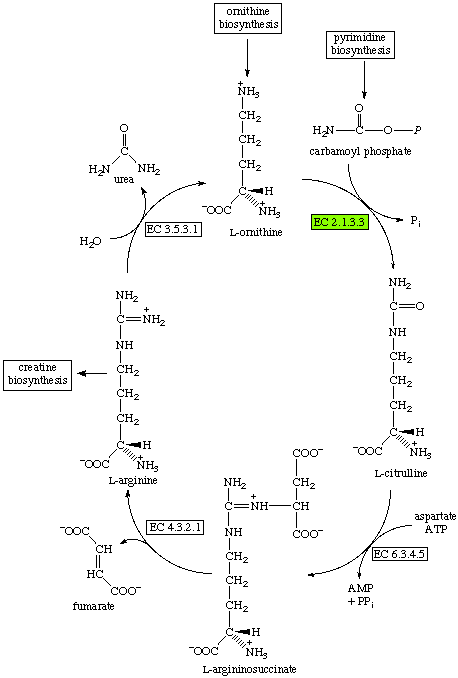
Фермент катализирует реакцию образования L-орнитина, в результате которой образуются L-цитруллин и фосфат:
carbamoyl phosphate + L-ornithine = phosphate + L-citrullineЭта реакция является частью биосинтеза аргинина:
2. Метаболические пути с участием фермента
Имя локуса гена исследуемого фермента - b4254. В БД KEGG по этому имени (eco:b4254) найдем нужный ген.С этим геном ассоциированы два идентификатора метаболических путей:
| eco00330 | Arginine and proline metabolism (метаболизм аргинина и пролина), | |
| eco01100 | Metabolic pathways (метаболические пути). |
Графическая карта метаболизма аргинина и пролина сохранена в файле eco00330.jpg. Изучаемый фермент на ней отмечен стрелкой.
3. Поиск структурных формул соединений в БД KEGG LIGAND
Была найдена информация о следующих соединениях:- Рибулозо-5-фосфат (найдено 2 энантиомера)
- ФАД
| KEGG ID | Русское название | Английское название | Структурная формула |
| C00199 | D-рибулозо-5-фосфат | D-Ribulose 5-phosphate | 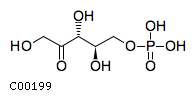 |
| C01101 | L-рибулозо-5-фосфат | L-Ribulose 5-phosphate | 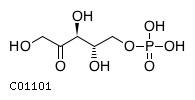 |
| C00016 | ФАД, флавинадениндинуклеотид | FAD; Flavin adenine dinucleotide | 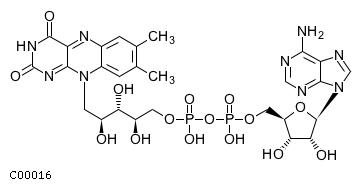 |
4. Поиск метаболического пути между заданными веществами в БД KEGG PATHWAY
Метаболический путь между рибулозо-5-фосфатом и ФАД существует только в случае D-рибулозо-5-фосфата.Выбранная цепочка ферментативных реакций:
путь: метаболизм рибофлавина,
цепочка: рибулозо-5-фосфат → ФАД. Содержит 5 стадий.
Карта этого пути: map00740.png. Интермедиаты (C15556, C04332, C00255, C00061) отмечены желтым, исходное вещество (рибулозо-5-фосфат) - красным, конечное (ФАД) - зеленым.
5. Сравнение метаболических путей у разных организмов
Для того, чтобы определить возможность найденного в упр.4 метаболического пути у разных организмов, будем переводить общую карту пути (Reference map) в режимы, соответствующие этим организмам. Результаты будем заносить в таблицу:| Организм | Возможна ли цепочка реакций (да/нет/неизвестно) |
Обоснование |
| Escherichia coli K-12 MG1655 | да (посмотреть карту) | имеются все необходимые ферменты |
| Archaeoglobus fulgidus | нет | неизвестны гены некоторых ферментов (2.5.1.9 - рибофлавинсинтаза, катализирует 3-ю стадию, и 2.7.7.2 - ФАД-синтаза, катализирует 5-ю стадию) |
| Arabidopsis thaliana | нет | отсутствует фермент 2.7.7.2 - ФАД-синтаза |
| Homo sapiens | нет | неизвестны гены некоторых ферментов (4.1.99.12 - 3,4-дигидрокси-2-бутанон-4-фосфат-синтаза, катализирует 1-ю стадию, 2.5.1.9 - рибофлавинсинтаза, катализирует 3-ю стадию, а также катализирующий 2-ю стадию фермент с кодом ЕС 2.5.1, относящийся к трансферазам арильных и алкильных групп, содержащих больше одного атома углерода) |
6. Сравнение ферментов из далеких организмов
Код ЕС 2.7.6.1 ассоциирован с рибозо-фосфат-дифосфокиназами - ферментами, переносящими пирофосфат от АТФ на рибозо-5-фосфат. Для того, чтобы правильно найти в SRS белки с таким ЕС, использование маски необязательно, т.к. не существует EC 2.7.6.10, 2.7.6.11 и т.д. Для нахождения белков археи Archaeoglobus fulgidus и человека с заданным ЕС, был составлен следующий запрос:([uniprot-ECNumber:2.7.6.1] & ([uniprot-ID:*_HUMAN*] | [uniprot-ID:*_ARCFU*]))По этому запросу было найдено 10 последовательностей. После отсеивания повторяющихся последовательностей при помощи ссылок на UniRef100 имеем 9 разных последовательностей ферментов с ЕС 2.7.6.1: 7 у человека и 2 у археи. Все найденные белки имеют схожую доменную организацию - представляют из себя единственный домен с идентификатором PFAM PF00156:
|
|
Для дальнейшей работы выберем по одной последовательности из каждого организма: KPRS1_ARCFU из археи и PRPS1_HUMAN из человека.
Чтобы определить процент совпадения последовательностей гомологичных доменов этих ферментов, при помощи seqret вырежем их из последовательностей белков и выравняем с помощью needle. Полученный файл с выравниванием: aln.needle.
Процент идентичности доменов составляет 28,2% (31/110). Для человека и археи такое большое расхождение вполне ожидаемо.
Далее воспользуемся инструментами KEGG, чтобы найти для выбранного человеческого белка лучшего ортолога из архей, а для архейного - лучшего ортолога у эукариот.
Фермент KPRS1_ARCFU кодируется геном prsA-1 и имеет KEGG ID AF0589. Фермент PRPS1_HUMAN кодируется геном PRPS1 и имеет KEGG ID 5631. Для каждого из ферментов был найден лучший ортолог из соответствующей по заданию группы:
Лучший ортолог из эукариот для KPRS1_ARCFU:
имя гена - PKH_122800,
организм - Plasmodium knowlesi (малярийный плазмодий, вызывающий малярию у макак),
функция - фосфорибозилпирофосфатсинтаза (рибозо-фосфат-пирофосфокиназа),
идентичность - 31,1%.
Лучший ортолог из архей для PRPS1_HUMAN:
имя гена - MTH784,
организм - Methanobacterium thermoautotrophicum,
функция - рибозо-фосфат-пирофосфокиназа,
идентичность - 36,3%.
Несмотря на то, что идентичность последовательностей ортологов у таких далеких организмов, как эукариоты и археи, мала (всего лишь около 30%), белки все же сохранили свою функцию и доменную организацию и участвуют в одних и тех же метаболических путях. Интересно, что лучший ортолог для белка археи принадлежит плазмодию - не самому высокоорганизованному из эукариот.
Назад