Занятие 6.
I. Исследование доменной структуры конкретного белка
1. Доменная структура белка OTC1_ECOLI по данным Pfam
Cхема из Pfam: |
|||||
| Пояснения к схеме |
|||||
| № | Pfam AC | Pfam ID | Полное название семейства домена | Положение в последовательности белка OTC1_ECOLI | Клан |
| 1. | PF02729 | OTCace_N | Аспартат/орнитинкарбамоилтрансфераза, карбамоилфосфатсвязывающий домен | 7-148 | - |
| 2. | PF00185 | OTCace | Аспартат/орнитинкарбамоилтрансфераза, аспартат/орнитин-связывающий домен | 155-331 | - |
2. Выравнивание-затравка (seed) для N-концевого домена (OTCace_N)
Выравнивание в формате msf было сохранено в файле PF02729_seed.msf.3. Сравнение описания доменной структуры в Pfam с описаниями в других БД
По идентификатору UniProt белка OTC1_ECOLI найдем описание всех подписей, интегрированных в БД InterPro. Наиболее интересная из найденных подписей (InterPro ID IPR006130) приведена на рисунке ниже (черного цвета) вместе с подписями Pfam (фиолетовые):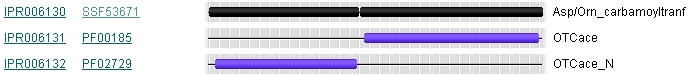
Подпись IPR006130 получена из БД SuperFamily. В отличие от подписей Pfam, описывающих два разных домена, здесь мы видим один повторяющийся домен. Расположение этих копий соответствует расположению доменов Pfam (1-150 и 152-334, границы доменов Pfam приведены в таблице в п.1).
Можно сделать вывод, что в процессе эволюции произошла дупликация участка последовательности, которая привела к образованию двух отдельных доменов.
4. Сопоставление доменной и 3D структур белка OTC1_ECOLI
C помощью Jmol на сайте Pfam получим изображение 3D-структуры исследуемого белка (PDB-идентификатор 1akm). Из трех идентичных цепей была выбрана цепь А. На изображении хорошо видно, что структурные домены соответствуют доменам Pfam: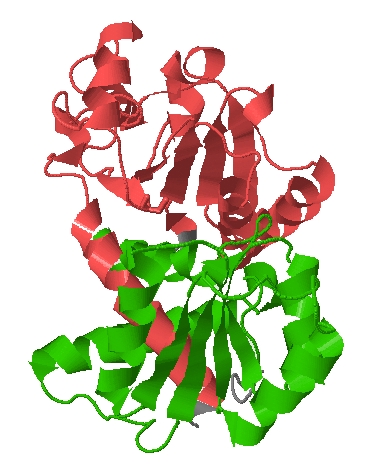
Структурные домены и домены Pfam совпадают практически полностью, за исключением альфа-цепочечных участков, с помощью которых структурные домены соединяются между собой.
Кроме того, можно заметить, что структуры двух доменов Pfam очень похожи: у обоих имеется по четыре бета-слоя в центре, сходное пространственное расположение альфа-цепей и т.д. Это сходство также подтверждает гипотезу о происхождении этих доменов в результате удвоения последовательности.
II. Исследование эволюции отдельных доменов
1. Представленность исследуемых доменов в организмах разных видов
Домен OTCace_N (PF02729) представлен в организмах 1031 вида, OTCace (PF00185) - у 1030 видов. Похоже, что эти домены мало встречаются по отдельности.Рассмотрим подробнее распространенность N-концевого (карбамоилфосфатсвязывающего) домена.
|
Таксон
|
Количество белков с доменом PF02729
|
|
| Эукариоты | Зеленые растения | 56 |
| Грибы | 125 | |
| Животные | 75 | |
| Остальные эукариоты | 42 | |
| Бактерии | 3265 | |
| Археи | 162 | |
Домен присутствует у представителей всех перечисленных в таблице таксонов. Чаще всего он встречается у бактерий, сравнительно широко распространен у эукариот, причем больше всего представлен у грибов, и меньше - у зеленых растений. У архей этот домен встречается приблизительно в два раза реже, чем у эукариот.
2. Встречаемость исследуемых доменов в разных белках Escherichia coli K12
Рассмотрим, в скольких еще белках, помимо OTC1_ECOLI, встречаются исследуемые домены в этой бактерии (в таблице OTC1_ECOLI также учтен):| № | PFAM ID | Количество белков в Escherichia coli (strain K12) |
| 1. | PF02729 | 4 |
| 2. | PF00185 | 4 |
Все найденные белки содержат оба изучаемых домена и имеют ту же доменную организацию, что и OTC1_ECOLI.
3. Примеры доменных перестроек
Два исследуемых домена практически всегда присутствуют вместе и в той же последовательности, что и в белке OTC1_ECOLI. Тем не менее, встречаются и интересные примеры доменных перестроек.1) Домен PF02729 (OTCace_N) может присутствовать и в одиночку. Правда, большая часть таких последовательностей - это фрагменты или гипотетические белки, так что судить о вероятности такой перестройки сложно.
B5J2X0_9RHOB (гипотетический):

Он может присутствовать не только на N-конце, но и внутри последовательности:
Q60504_9RODE (фрагмент):

Этот домен также может удваиваться, хоть и не полностью:
B0XH91_CULQU:

2) Домен PF00185 (OTCace) также может содержаться в последовательности в одиночку
Q84FS7_BACFO:

либо в паре с каким-то еще доменом, кроме OTCace_N, при этом находясь c С-конца:
C2KFS9_9LACO:

Помимо перестроек, в которых домены PF02729 и PF00185 присутствуют по отдельности, также есть перестройки, в которых эти домены расположены в паре, но разделены аминокислотным участком. Тем не менее, порядок доменов не меняется (OTCace_N всегда ближе к N-концу):
A8WNQ4_CAEBR:

(на изображении показан только С-конец)
Назад