1. Введение в PyMOL
1. Работа с записью 1KMY банка PDB
При помощи командыget_pdb 1kmyполучен PDB-файл 1KMY.pdb.
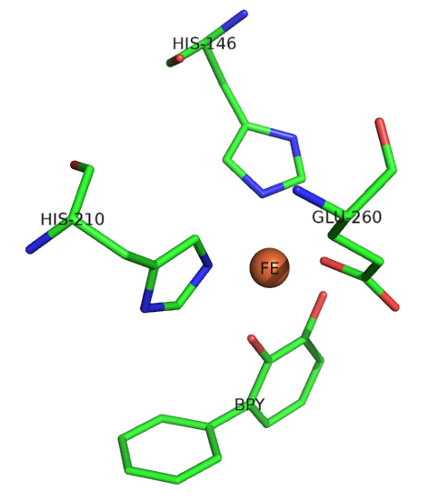
В структуре присутствует ион железа (указан в поле HETATM PDB-файла). Его окрестность включает в себя остатки гистидина (His146, His210) и глутаминовой кислоты (Glu260). Кроме того, с ионом связан координационными связями лиганд бифенил-2,3-диол (BPY):
2.1. Работа с записью 5RXN банка PDB
Файл с записью: 5RXN.pdb. Структура расшифрована в 1984 году, расширение - 1,2 Å.Рассмотрим все остатки треонина в структуре. Их три: Thr5, Thr7, Thr28.
Боковая цепь треонина содержит асимметрический атом углерода (СВ). Благодаря этому она обладает зеркальной симметрией. Ниже приведены изображения всех трёх треонинов, СB-атом выделен, подписана его конфигурация по R-S номенклатуре (Кана-Ингольда-Прелога). Водород при СВ атоме на этих изображениях не виден (направлен назад).
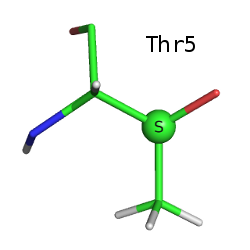
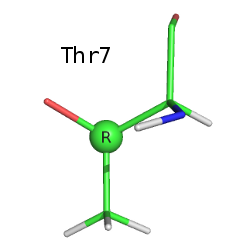
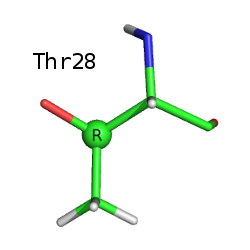
Как видим, боковая цепь Thr5 зеркально симметрична боковым цепям Thr7 и Thr28 (наблюдается энантиомерия).
По СА-атому все остатки имеют (R)-конфигурацию:
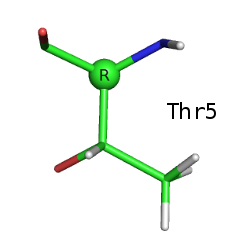
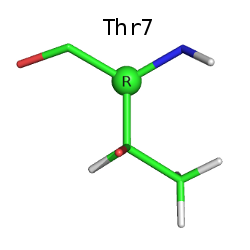
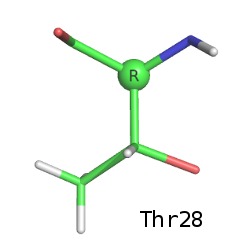
Если использовать DL-номенклатуру, то Thr7 и Thr28 являются L,D-изомерами, а Thr5 - L,L-изомером.
В поле REMARK никаких сведений об исследуемых остатках нет.
2.2. Работа с записью 1DLP банка PDB
Файл с записью: 1DLP.pdb. Структура расшифрована в 1999 году, расширение - 3,3 Å. Файл содержит информацию о 6 полипептидных цепях.Необходимо изучить остатки 136 цепи A и 167 цепи С. Поле REMARK содержит следующую информацию об этих остатках:
REMARK 480 ZERO OCCUPANCY ATOM REMARK 480 THE FOLLOWING RESIDUES HAVE ATOMS MODELED WITH ZERO REMARK 480 OCCUPANCY. THE LOCATION AND PROPERTIES OF THESE ATOMS REMARK 480 MAY NOT BE RELIABLE. (M=MODEL NUMBER; RES=RESIDUE NAME; REMARK 480 C=CHAIN IDENTIFIER; SSEQ=SEQUENCE NUMBER; I=INSERTION CODE): REMARK 480 M RES C SSEQI ATOMS REMARK 480 ASN A 136 CG OD1 ND2 REMARK 480 ARG C 167 CB CG CD NE CZ NH1 NH2 REMARK 500 THE FOLLOWING ATOMS ARE IN CLOSE CONTACT. REMARK 500 ATM1 RES C SSEQI ATM2 RES C SSEQI DISTANCE REMARK 500 N ASP A 97 ND2 ASN A 136 2.16 REMARK 500 O ARG C 167 N ASP C 169 2.17 REMARK 500 THE STEREOCHEMICAL PARAMETERS OF THE FOLLOWING RESIDUES REMARK 500 HAVE VALUES WHICH DEVIATE FROM EXPECTED VALUES BY MORE REMARK 500 THAN 6*RMSD (M=MODEL NUMBER; RES=RESIDUE NAME; C=CHAIN REMARK 500 IDENTIFIER; SSEQ=SEQUENCE NUMBER; I=INSERTION CODE). REMARK 500 M RES CSSEQI ATM1 RES CSSEQI ATM2 DEVIATION REMARK 500 ASN A 136 CB ASN A 136 CG -0.550 REMARK 500 TORSION ANGLES OUTSIDE THE EXPECTED RAMACHANDRAN REGIONS: REMARK 500 (M=MODEL NUMBER; RES=RESIDUE NAME; C=CHAIN IDENTIFIER; REMARK 500 SSEQ=SEQUENCE NUMBER; I=INSERTION CODE). REMARK 500 ARG C 167 106.55 116.09 REMARK 500 THE FOLLOWING RESIDUES HAVE A PSEUDO PLANARITY REMARK 500 TORSION, C(I) - CA(I) - N(I+1) - O(I), GREATER REMARK 500 10.0 DEGREES. (M=MODEL NUMBER; RES=RESIDUE NAME; REMARK 500 C=CHAIN IDENTIFIER; SSEQ=SEQUENCE NUMBER; REMARK 500 I=INSERTION CODE). REMARK 500 M RES CSSEQI ANGLE REMARK 500 ASN A 136 -10.12 REMARK 500 ARG C 167 11.70Сначала рассмотрим Asn136, цепь А:
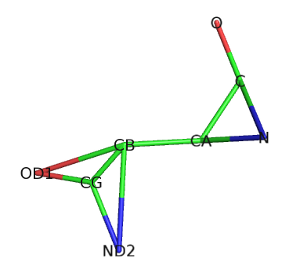
Этот остаток аспарагина содержит три не характерных для него связи: C-N, CB-ND2 и CB-OD1. В поле REMARK указано, что расположение и свойства атомов СG, OD1 и ND2 могут являться неточными, а стереохимические параметры атомов СВ и CG сильно отличаются от ожидаемых.
Кроме того, ND2 находится очень близко к атому N остатка Asp97 той же цепи. Расстояние между ними составляет всего 2,16 Å.
В остове Arg167 цепи С также имеется необычная связь C-N:
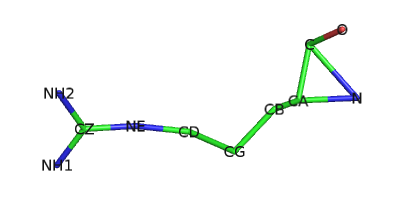
В поле REMARK отмечено, что для многих атомов этого остатка координаты и свойства также могут быть неточны, однако атомы остова (где как раз и присутствует нетривиальная связь) в список ненадёжных атомов не попали. Также указано, что торсионные углы Arg167 не совпадают с ожидаемыми (находятся в запрещённых областях карты Рамачандрана).
Таким образом, наличие необычных связей (т.е. сильно сближенных атомов), возможно, обусловлено ошибками при построении модели, а в настоящей белковой молекуле этих связей может и не присутствовать.
2.3. Работа с записью 2B5A банка PDB
Файл с записью: 2B5A.pdb. Структура расшифрована в 2005 году, расширение - 1,54 Å. Файл содержит информацию о 4 идентичных полипептидных цепях.Необходимо изучить остатки глутамина-21 всех четырёх цепей. В поле REMARK эти остатки не упоминаются.
В цепях А, В и D эти остатки выглядят одинаково и привычно, а у Gln21 цепи С есть сразу две боковые цепи (на изображении для сравнения приведён ещё и Gln21 цепи D):
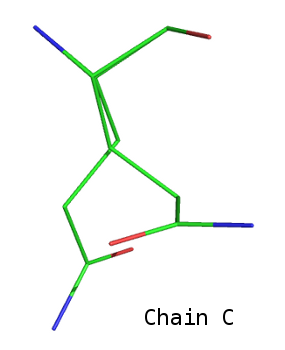
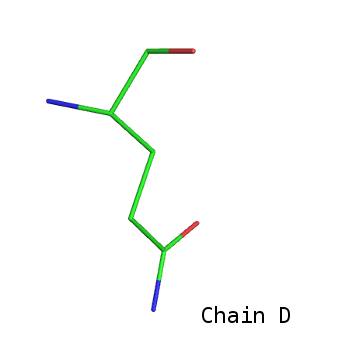
Здесь мы имеем случай, когда аминокислотный остаток в кристалле присутствует в двух альтернативных конформациях. Атомы, соответствующие отдельным конформациям, помечены буквами А и В, например, CDA и СDB. В поле ATOM можно увидеть, что коэффициент заполнения делится пополам между этими конформациями:
ATOM 1405 CA AGLN C 21 19.364 32.425 32.992 0.50 19.11 C ATOM 1406 CA BGLN C 21 19.326 32.397 33.057 0.50 20.53 C ATOM 1409 CB AGLN C 21 17.931 32.039 33.379 0.50 20.64 C ATOM 1410 CB BGLN C 21 17.973 31.950 33.643 0.50 22.06 C ATOM 1411 CG AGLN C 21 17.034 33.216 33.781 0.50 20.74 C ATOM 1412 CG BGLN C 21 16.993 31.438 32.609 0.50 23.71 C ATOM 1413 CD AGLN C 21 17.055 34.359 32.789 0.50 24.73 C ATOM 1414 CD BGLN C 21 15.641 31.013 33.167 0.50 26.46 C ATOM 1415 OE1AGLN C 21 17.097 34.149 31.567 0.50 20.63 O ATOM 1416 OE1BGLN C 21 15.470 30.787 34.370 0.50 32.44 O ATOM 1417 NE2AGLN C 21 17.048 35.589 33.309 0.50 17.33 N ATOM 1418 NE2BGLN C 21 14.666 30.890 32.270 0.50 27.89 N
2.4. Работа с записью 7GPB банка PDB
Файл с записью: 7GPB.pdb. Структура расшифрована в 1990 году, расширение - 2,9 Å. Файл содержит информацию о 4 идентичных полипептидных цепях.Изучим остатки Trp67 этих цепей. Ароматическая система этих триптофанов не является плоской. Сильнее всего угол между плоскостями колец выражен у триптофана цепи D:
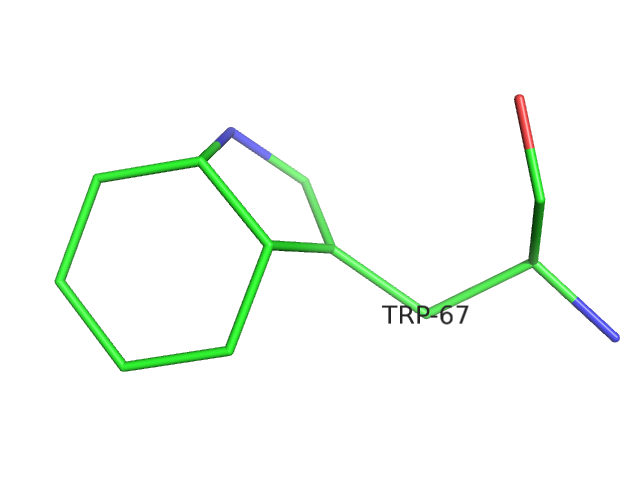
В поле REMARK об этом ничего не сказано. Скорее всего, при уточнении модели не было учтено то, что ароматическая система триптофана должна быть плоской.
3. Создание скрипта для PyMOL
При помощи скрипта trp67.pml можно получить изображение остатка Trp67 цепи D для задания 2.4. Текст скрипта:load 7GPB.pdb bg_color white hide all select trpd, byres d/67/ show lines, trpd zoom trpd orient trpd set line_width, 3 label n. cb & trpd, "%s-%s" % (resn, resi) set label_size, 25 ray png trp67.png |
Чтобы запустить скрипт, в командной строке PyMOL нужно ввести
@trp67.pml(если скрипт находится в активной директории). Результатом работы скрипта является изображение trp67.png, которое создаётся в активной директории.
Назад