1. Общая характеристика семейства PF00172 (Zn_clus)
Семейство белков Zn₂Cys₆ (грибные транскрипционные регуляторы)
- Ключевая особенность: N-концевой ДНК-связывающий домен, богатый цистеином.
- Структура: бинуклеарный Zn-кластер — два атома цинка, связанные шестью остатками цистеина.
- Распространение: характерны для грибов, встречаются у многих регуляторных белков.
- Регулируемые процессы: метаболизм аминокислот (аргинин, пролин, лейцин), утилизация сахаров (мальтоза, галактоза), обмен пиримидинов, катаболизм амидов и ГАМК, использование хината.
- Механизм: Zn-кластер стабилизирует структуру домена, обеспечивая точное узнавание и связывание с ДНК.
- Данные структур: известны для свободного состояния и в комплексе с ДНК.
2. Детальная структура и таксономия домена Zn_clus
Структура
Домен складывается в короткий пучок из двух α-спиралей. В основании — два иона цинка, координированных шестью цистеинами (отсюда название Zn₂Cys₆). Одна из спиралей (обычно первая) длиннее — это распознающая спираль. Она встраивается в большой желоб ДНК, и именно её аминокислоты определяют, на какой сайт белок сядет.
Функции
Сам по себе Zn_clus — это только ДНК-связывающий модуль. Однако почти всегда он идёт в связке с другими доменами: димеризационными доменами (лейциновая молния или длинный α-спиральный линкер) и регуляторными доменами (куда приходят сигнальные молекулы — метаболиты, гем и т.д.). Благодаря модульной конструкции одно семейство (один Zn_clus) управляет разными процессами.
Таксономия
Рисунок 1. Таксономия семейства PF00172
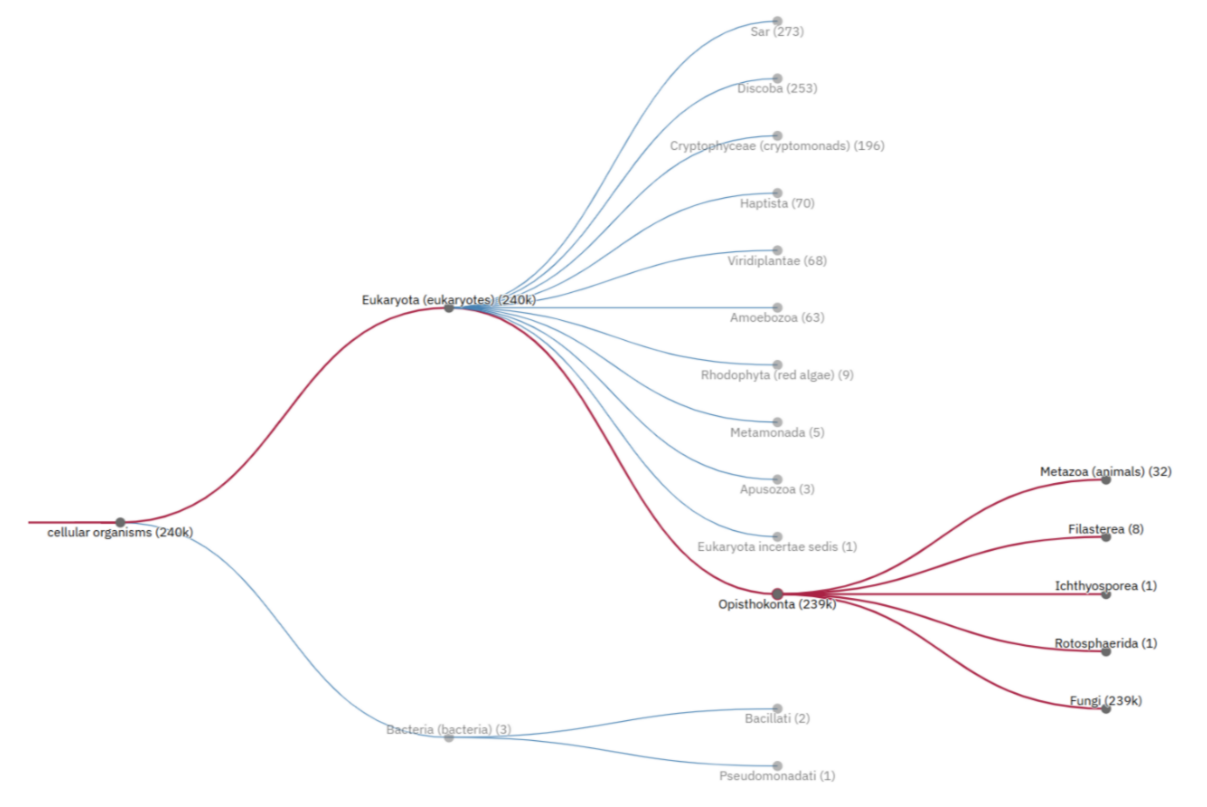
Рисунок 2. Распространенность среди грибных таксонов семейства PF00172.
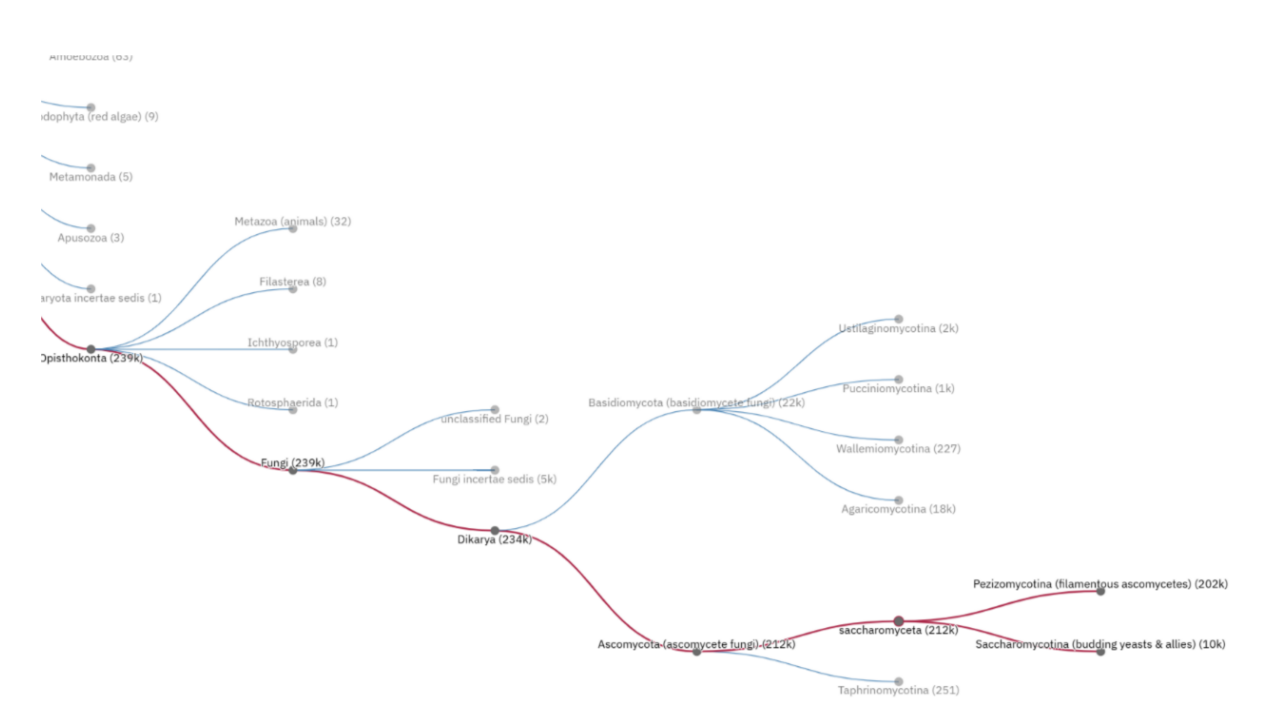
Подавляющее большинство (≈99%) последовательностей домена Zn_clus принадлежит царству Fungi (грибы). Домен является маркерным для грибов.
- Ascomycota (сумчатые) — основная масса: дрожжи, аспергиллы, пенициллы.
- Basidiomycota (базидиальные) — значительная часть: шампиньоны, криптококки.
- Mucoromycota и другие базальные грибы — небольшое число.
- Единичные находки в других царствах (растения, животные, бактерии) — скорее всего, артефакты аннотации или контаминация.
Ключевой вывод: Домен Zn_clus — таксономический маркер грибов.
| Поле | Информация | Комментарии | Пояснения |
|---|---|---|---|
| AC pfam | PF00172 | — | — |
| ID pfam | Zn_clus | Короткое название домена | — |
| #SEED | 28 | Число последовательностей в выравнивании SEED | Вручную отобранные последовательности. |
| #All | ~238 000 | Число всех белков с доменом семейства | Включает полные и частичные последовательности. |
| #SW | ~440 | Число белков с доменом в SwissProt (reviewed) | Только вручную аннотированные. |
| #architectures | ~2 639 | Число разных доменных архитектур | Различные комбинации Zn_clus с другими доменами. |
| #3D | ~38 | Число доменов с известной 3D-структурой | Включая свободные и в комплексе с ДНК. |
| #eukaryota | ~237 997 | Подавляющее большинство | Почти все принадлежат царству Fungi (грибы) |
| #archaea | 0 | Не обнаружено | Домен отсутствует у архей |
| #bacteria | ~3 | Единичные находки | Скорее всего, артефакты аннотации или контаминация |
3. Выравнивание seed домена PF00172 в JalView
Max_Conserved_Block (максимальный блок достоверного выравнивания)
Максимальный блок достоверного выравнивания, включающий фрагменты из всех 28 последовательностей seed-набора без пропусков, находится в позициях 6–13 (по нумерации Jalview). Длина блока составляет 8 аминокислотных колонок. Данный участок содержит высококонсервативный цистеиновый мотив, в котором два цистеина строго фиксированы и разделены ровно 6 любыми аминокислотными остатками.
Partial_Block (блок, включающий фрагменты не из всех последовательностей)
Partial_Block расположен в позициях 24-31 выравнивания. Данный фрагмент соответствует вариабельной петле между цистеинами C4 и C5 + 4 колонки. Из выравнивания исключена 12 последовательность ALCR_EMENI (есть вставки, которые образуют длинные индели в остальных последовательностях)
Non_Homologous_Region (участок без достоверного выравнивания)
Негомологичный регион максимальной длины расположен в позициях 43-53. В этом участке наблюдаются множественные пропуски, очень низкая консервативность. Выравнивание в данной области не может считаться достоверным и не отражает эволюционные связи между последовательностями. Структурно этот регион соответствует C-концевой области домена Zn_clus, расположенной за пределами цинк-связывающего кластера.
| Параметр | Информация | Комментарии |
|---|---|---|
| Выравнивание seed | 28 последовательностей, 52 колонки | Seed-набор Pfam, загружен через Jalview |
| МДБ-all | 6–13 | Длина 8 колонок, цистеиновый мотив |
| 100% консервативные колонки в МДБ-all | 6:C, 13:C | Цистеин (C) у всех 28 последовательностей |
| МДБ-notAll | 24-31, 27 последовательностей | Вариабельная петля между цистеинами + 4 колонки |
| 100% консервативные колонки в МДБ-notAll | 24:С, 27:С | Консервативность частичная |
| Non_Homologous_Region | 43-53 | C-концевая область. Множественные пропуски, низкая консервативность |
4. Dotplot двух последовательностей с разной доменной архитектурой
| Параметр | Информация | Комментарии |
|---|---|---|
| Доменная архитектура 1 | Zn_clus (PF00172) + Gal4_middle (PF01767) | Регуляторный домен, характерный для GAL4-подобных белков |
| Белок с архитектурой 1 | GAL4_YEAST (P04386) | Транскрипционный активатор генов метаболизма галактозы |
| Доменная архитектура 2 | Zn_clus (PF00172) + Leu_zip (PF07716) + fungal_TF_MHR (PF11939) | Лейциновая молния (димеризация) + большой регуляторный домен |
| Белок с архитектурой 2 | PUT3_YEAST (P25502) | Транскрипционный активатор генов метаболизма пролина |
Оба белка относятся к грибным транскрипционным регуляторам и содержат ДНК-связывающий домен Zn_clus (PF00172). Однако их C-концевые регуляторные области различаются: у GAL4_YEAST это домен Gal4_middle, отвечающий за активацию транскрипции в ответ на галактозу, а у PUT3_YEAST — лейциновая молния (Leu_zip) для димеризации и большой регуляторный домен fungal_TF_MHR, участвующий в ответе на пролин. Эти различия в архитектуре обусловливают разную функциональную специализацию белков.
Dotplot (NCBI BLAST)
Dotplot построен с помощью NCBI BLASTp (Aligner two or more sequences).
Рисунок 3. Точечная диаграмма (dotplot) для GAL4_YEAST и PUT3_YEAST.
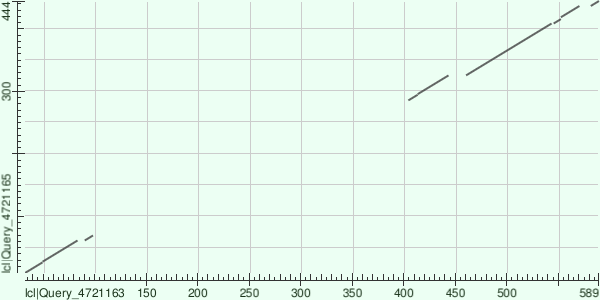
Интерпретация: Наличие диагональной линии в начале указывает на высокую гомологию N-концевых участков, что соответствует общей функциональной роли в связывании ДНК. Локальное выравнивание также присутствует в С-концевом регионе, правда не настолько гомологичное как предыдущее. Отсутствие диагонали после ~70 аминокислот подтверждает независимую эволюцию регуляторных доменов.
Отчёт по практикуму 11 | Мисюрёва Анастасия | 2026