Совмещение структур
Для выполнения данного задания была выбрана субъединица А алкоголь дегидрогеназы (PDB ID:
1TEH).
Был произведен поиск по сходству структур в PDBeFold, который выдал 448 находок. Из этих структур были выбраны четыре, удовлетворяющие
следующим требованиям: значение RSMD = 0.8-2.5, длина выравнивания превышает 50% длины белка.
В Таблице 1 представлены значения основных метрик для выбранного белка и гомологов.
Я пробовал искать гомологов еще для четырех других белков. Это самое интересное, что нашлось.
Таблица 1. Показатели сходства структурных гомологов 1TEH
| PDB ID | RMSD | % seq |
|---|---|---|
| 4dlb | 0.97 | 67 |
| 1p0c | 1.17 | 59 |
| 1u3v | 1.24 | 63 |
| 1hso | 1.26 | 64 |
Для выбранных структур было получено множественное выравнивание с исходной структурой со следующими характеристиками:
Количество выровненных остатков: 360;
Количество элементов вторичной структуры: 28;
Общий RMSD: 1.009;
Общий Q-score: 0.8258.
Также был получен файл с совмещенными структурами и выравнивание вторичных структур:
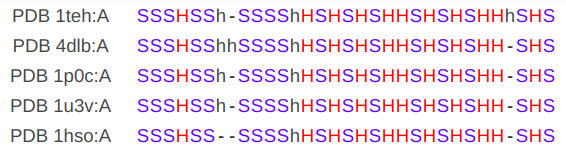 |
Совмещение структур показано на рисунке 2.
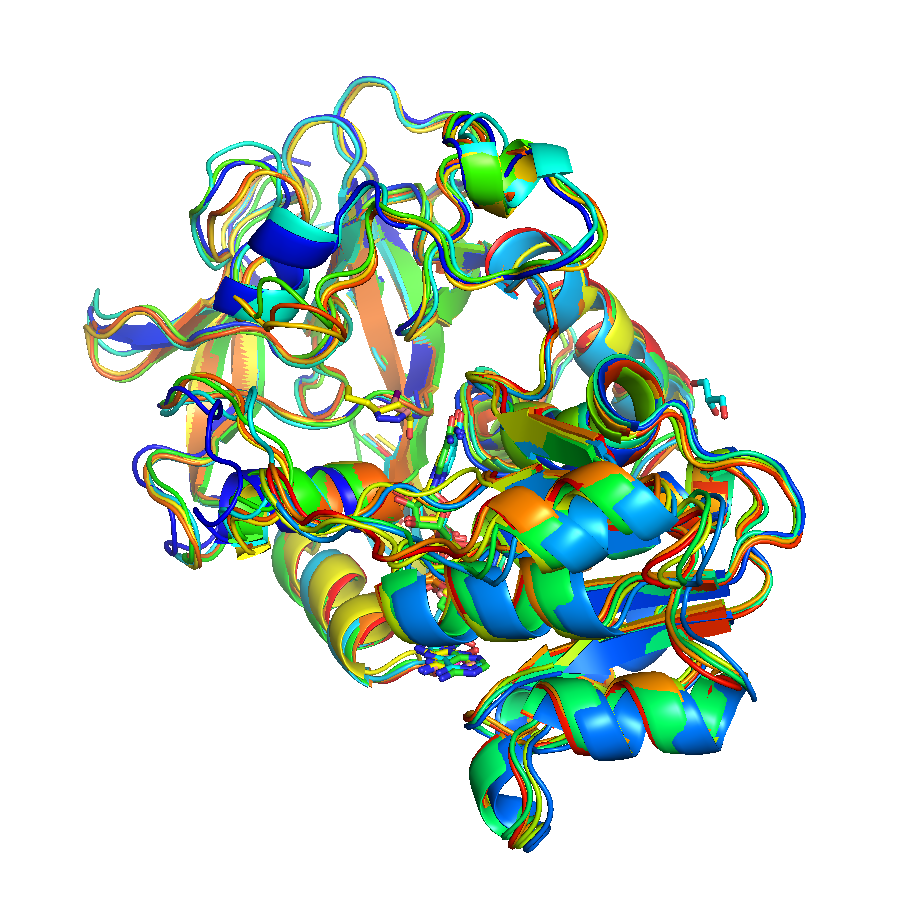 |
Анализ выравнивания
Полученное по структуре множественное выравнивание было сопоставлено с выравниванием, полученным с помощью алгоритма clustalo. В целом, выравнивания оказались похожи. Было найдено несколько мест, в которых построенное по структуре выравнивание оказалось более правитльным. На рисунке 3 показаны фрагменты выравниваний, а рисунок 4 демонстрирует фрагмент структур, образованных данными аминокислотами.

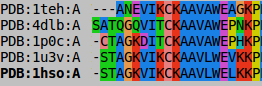
|
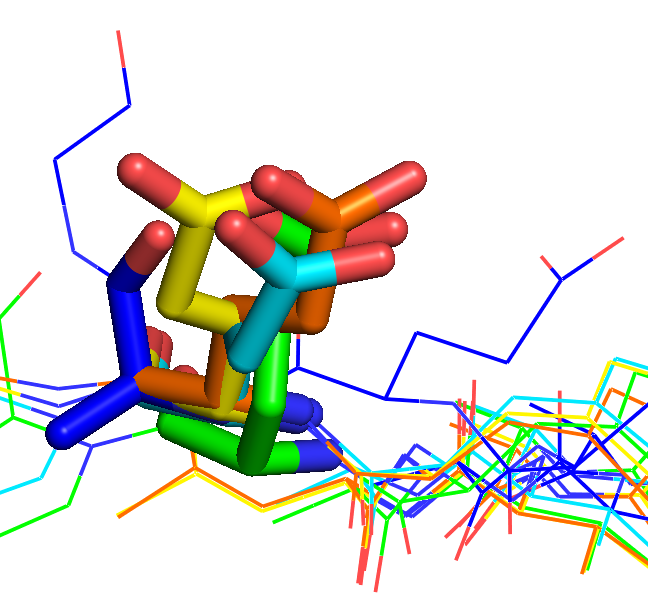 |
Общие выводы
Из рисунка 4 видно, что построенное по структуре выравнивание лучше отражает реальную картину. Раньше я всегда использовал
только выравнивания последовательностей и считал, что прирост качества при использовании структур будет незначительным. Однако из рассмотренного примера понтно,
что построенное по структуре выравнивание в трех местах оказалось более качественным.
Думаю, в научной работе целесообразно использовать
именно такие выравнивания, если имеются соответствующие структуры, а для быстрых прикидок достаточно обычных выравниваний последовательностей.
