
На главную страницу
На главную страницу второго семестра
Рассмотрено эталонное множественное выравнивание семейства доменов PF08501, полученное из БД Smart. Выбраны 5 последовательностей из разных организмов.
|
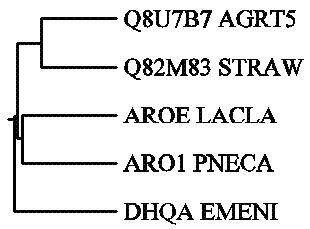
(((Q8U7B7_AGRT5:26.5, Q82M83_STRAW:26.5):34.75, (AROE_LACLA:33.0, ARO1_PNECA:33.0):34.75):36.15, DHQA_EMENI:36.15);Для визуализации дерева использованы программы из Online-версии пакета Phylip: drawtree и drawgram.
| drawtree | drawgram |
 |
 |
Программа drawgram строит укорененное дерево. Корень находится между наиболее
отдаленными последовательностями. Длину ветвей сложно сравниванить,то есть дерево
отражает только ход эволюци (в идеале).
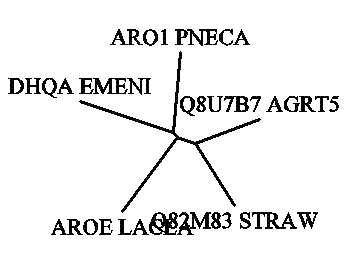
Программа drawtree строит неукорененное дерево. Но длина ветвей различна, и дерево
показывает сходство последовательностей.
Рассмотрим организмы, содержащие данные последовательности:
| Белок | Организм | Царство |
| AROE_LACLA | Streptococcus lactis | Bacteria |
| DHQA_EMENI | Aspergillus nidulans | Fungi |
| ARO1_PNECA | Pneumocystis carinii | Fungi |
| Q8U7B7_AGRT5 | Agrobacterium tumefaciens | Bacteria |
| Q82M83_STRAW | Streptomyces avermitilis | Bacteria |
Таким образом, ход эволюции, отраженный вторым деревом (укорененным), неправдоподобен
(по дереву, от общего предка образовались эукариотическая последовательность и группа
эукариотических и прокариотических последовательностей, которая затем делится на две группы:
прокариотическая и смешанная, то есть грибы образовывались несколько раз независимо).
Поэтому первое изображение лучше отражает мое представление о дереве (его проще объяснить, так
как оно не предлагает строгий путь эволюции).
Заметим, что рассмотренные последовательности – не ортологи, и поэтому могут не отражать ход эволюции организмов.
Таким образом, наиболее вероятный ход эволюции последовательностей:
От гипотетического предка образовались два паралога. Отодного из них произошли последовательности
AROE_LACLA (Fungi) и ARO1_PNECA (Bacteria) и DHQA_EMENI (Fungi). От другой ветви
образовались прокариотические последовательности Q8U7B7_AGRT5 и Q82M83_STRAW.
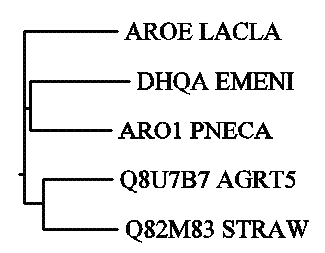
( AROE_LACLA:0.33873, ( DHQA_EMENI:0.35999, ARO1_PNECA:0.29433) :0.02257, ( Q8U7B7_AGRT5:0.25152, Q82M83_STRAW:0.27121) :0.06858);
| drawtree | drawgram |
 |
 |
Заметим, что второе изображение не несет никакого смысла, так как использованный метод не
позволяет строить укорененной дерево.
Полученное дерево в целом сходно с деревом, построенным с помощью алгоритма UPGMA.
В обоих деревьях три последовательности образуются примерно в одно время. Однако второе дерево
можно интерпретировать иначе.
Получаем сценарий эволюции:
От общего предка произошли две гипотетические последовательности, которые дали начало
двум группам последовательностей. Первая группа включает две эукариотические (Fungi/Ascomycota)
последовательности: ARO1_PNECA и DHQA_EMENI. Вторая группа – прокариотические
последовательности, причем сначали от общей ветви отделилась AROE_LACLA, а затем разделились
Q8U7B7_AGRT5 и Q82M83_STRAW.
Последовательность AROE_LACLA отделяется от общей прокариотической группы очень рано,
сразу после образования эукариотической и прокариотической группы. Дерево похоже на звездное.
Возможно, именно поэтому два алгоритма дали разный результат.