На главную страницу
На главную страницу четвертого семестра
Классификация функций. Коды ферментов.
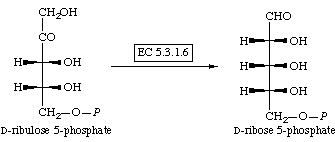
Заданный код фермента (точнее, код катализируемой им реакции) 5.3.1.6.
Расшифровка кода по номенклатуре IUPAC:
|
5.*.*.* |
Изомеразы – ферменты, катализирующие изменения одной молекулы |
|
5.3.*.* |
Внутримолекулярные оксидоредуктазы – катализируют внутримолекулярные
окислительно-восстановительные реакции |
|
5.3.1.* |
преобразования сахаров – альдоз в кетозы
и наоборот |
|
5.3.1.6 |
Рибозо-5-фосфатизомераза (подробнее – D-рибоза-5-фосфат альдозо-кетозо-изомераза) |
Катализируемая реакция:
С помощью SRS в UniProt найдены все белки с данным кодом из организмов кишечной палочки Escherichia
coli K-12, археи Methanococcus jannaschii и человека Homo sapiens:
((([uniprot-ID:*_Ecoli*] | [uniprot-ID:*_Human*]) | [uniprot-ID:*_Metja*]) & [uniprot-Description:5.3.1.6*])
Найдено 5 записей, 4 из них содержат по одному домену (Pfam). У
Escherichia coli K-12 присутствуют рибоза-5-фосфат изомеразы двух типов (A и B), у остальных – тлько A. A2UCW0_ECOLI в БД Pfam отсутствует.
Сравнение доменной структуры ферментов из далеких организмов
| |
UniProt ID |
UniProt AC |
Имя гена |
Первый домен |
Идентификатор Pfam |
Положение в последовательности |
| 1 |
RPIA_ECOLI |
P0A7Z0
P27252
Q2M9S8 |
RPIA |
PF06026
Ribose 5-phosphate isomerase |

47 – 215 |
| 2 |
RPIB_ECOLI |
P37351
O32564
Q2M6L3 |
RPIB |
PF02502
Ribose/galactose isomerase |

62 – 142 |
| 3 |
RPIA_HUMAN |
P49247
Q96BJ6 |
RPIA |
PF06026
Ribose 5-phosphate isomerase |

52 – 229 |
| 4 |
RPIA_METJA |
Q58998 |
RPIA |
PF06026
Ribose 5-phosphate isomerase |

50 – 222 |
| 5 |
A2UCW0_ECOLI |
A2UCW0 |
--- |
--- |
--- |
Далее, оценим сходство последовательностей аминокислот в гомологичных доменах. Для этого используем программу
ClustalW (встроенную в SRS версию).
Получено выравнивание (красным выделены белки, содержащие домен PF06026, последний белок, хотя и
выполняет такую же функцию,
по-видимому, не гомологичен остальным):
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
2 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
4 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
6 |
0 |
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
s |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
l |
|
|
|
|
|
|
|
i |
|
|
d |
G |
a |
d |
e |
|
|
|
|
|
|
|
|
i |
k |
G |
g |
G |
|
|
|
t |
|
e |
K |
i |
|
|
|
|
|
|
| R |
P |
I |
A |
_ |
E |
C |
O |
L |
I |
|
: |
|
E |
G |
A |
V |
S |
S |
S |
D |
A |
S |
T |
E |
K |
L |
K |
S |
L |
G |
I |
H |
V |
F |
D |
L |
N |
E |
V |
D |
S |
L |
G |
I |
Y |
V |
D |
G |
A |
D |
E |
I |
N |
G |
H |
. |
M |
Q |
M |
I |
K |
G |
G |
G |
A |
A |
L |
T |
R |
E |
K |
I |
|
: |
|
|
5 |
9 |
| R |
P |
I |
A |
_ |
H |
U |
M |
A |
N |
|
: |
|
L |
V |
C |
I |
P |
T |
S |
F |
Q |
A |
R |
Q |
L |
I |
L |
Q |
Y |
G |
L |
T |
L |
S |
D |
L |
D |
R |
H |
P |
E |
I |
D |
L |
A |
I |
D |
G |
A |
D |
E |
V |
D |
A |
D |
. |
L |
N |
L |
I |
K |
G |
G |
G |
G |
C |
L |
T |
Q |
E |
K |
I |
|
: |
|
|
5 |
9 |
| R |
P |
I |
A |
_ |
M |
E |
T |
J |
A |
|
: |
|
V |
F |
G |
I |
P |
T |
S |
F |
E |
A |
K |
M |
L |
A |
M |
Q |
Y |
E |
I |
P |
L |
V |
T |
L |
D |
E |
Y |
. |
D |
V |
D |
I |
A |
F |
D |
G |
A |
D |
E |
V |
E |
E |
T |
T |
L |
F |
L |
I |
K |
G |
G |
G |
G |
C |
H |
T |
Q |
E |
K |
I |
|
: |
|
|
5 |
9 |
| R |
P |
I |
B |
_ |
E |
C |
O |
L |
I |
|
: |
|
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
G |
I |
L |
I |
C |
G |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
T |
G |
V |
G |
I |
S |
I |
A |
A |
N |
K |
F |
|
: |
|
|
1 |
8 |
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
8 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
0 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
2 |
0 |
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
a |
|
|
f |
|
|
|
|
d |
|
s |
k |
|
|
|
|
L |
g |
|
|
|
|
|
|
|
p |
|
e |
V |
i |
p |
|
a |
|
|
|
V |
|
r |
|
l |
|
|
|
|
g |
g |
|
|
|
|
r |
|
|
|
|
|
|
|
|
|
|
| R |
P |
I |
A |
_ |
E |
C |
O |
L |
I |
|
: |
|
I |
A |
S |
V |
A |
E |
K |
F |
I |
C |
I |
A |
D |
A |
S |
K |
Q |
V |
D |
I |
L |
G |
K |
F |
P |
L |
. |
. |
. |
P |
V |
E |
V |
I |
P |
M |
A |
R |
S |
A |
V |
A |
R |
Q |
L |
V |
. |
K |
L |
G |
G |
R |
P |
E |
Y |
R |
Q |
G |
. |
. |
|
: |
|
1 |
1 |
3 |
| R |
P |
I |
A |
_ |
H |
U |
M |
A |
N |
|
: |
|
V |
A |
G |
Y |
A |
S |
R |
F |
I |
V |
I |
A |
D |
F |
R |
K |
D |
S |
K |
N |
L |
G |
D |
Q |
W |
H |
K |
G |
I |
P |
I |
E |
V |
I |
P |
M |
A |
Y |
V |
P |
V |
S |
R |
A |
V |
S |
Q |
K |
F |
G |
G |
V |
V |
E |
L |
R |
M |
A |
V |
N |
|
: |
|
1 |
1 |
9 |
| R |
P |
I |
A |
_ |
M |
E |
T |
J |
A |
|
: |
|
V |
D |
Y |
N |
A |
N |
E |
F |
V |
V |
L |
V |
D |
E |
S |
K |
L |
V |
K |
K |
L |
G |
E |
K |
F |
P |
. |
. |
I |
P |
V |
E |
V |
I |
P |
S |
A |
Y |
R |
V |
V |
I |
R |
A |
L |
S |
. |
E |
M |
G |
G |
E |
A |
V |
I |
R |
L |
G |
D |
R |
|
: |
|
1 |
1 |
6 |
| R |
P |
I |
B |
_ |
E |
C |
O |
L |
I |
|
: |
|
A |
G |
. |
. |
I |
R |
A |
V |
V |
C |
S |
E |
P |
Y |
S |
. |
. |
. |
A |
Q |
L |
S |
R |
Q |
H |
N |
. |
. |
. |
D |
T |
N |
V |
L |
A |
F |
G |
S |
R |
V |
V |
G |
L |
E |
L |
A |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
|
: |
|
|
5 |
6 |
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
4 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
6 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
8 |
0 |
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
v |
|
t |
d |
n |
g |
n |
|
I |
|
D |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
i |
|
|
I |
p |
g |
v |
v |
|
|
g |
|
f |
|
|
|
|
|
|
|
|
|
|
g |
|
|
|
g |
|
|
|
|
|
|
|
|
| R |
P |
I |
A |
_ |
E |
C |
O |
L |
I |
|
: |
|
. |
. |
. |
. |
V |
V |
T |
D |
N |
G |
N |
V |
I |
L |
D |
V |
H |
G |
M |
E |
I |
L |
D |
P |
I |
A |
M |
E |
N |
A |
I |
N |
A |
I |
P |
G |
V |
V |
T |
V |
G |
L |
F |
A |
N |
R |
G |
A |
D |
V |
A |
L |
I |
G |
T |
P |
D |
G |
V |
K |
|
: |
|
1 |
6 |
9 |
| R |
P |
I |
A |
_ |
H |
U |
M |
A |
N |
|
: |
|
K |
A |
G |
P |
V |
V |
T |
D |
N |
G |
N |
F |
I |
L |
D |
W |
K |
F |
D |
R |
V |
H |
K |
W |
S |
E |
V |
N |
T |
A |
I |
K |
M |
I |
P |
G |
V |
V |
D |
T |
G |
L |
F |
I |
N |
. |
M |
A |
E |
R |
V |
Y |
F |
G |
M |
Q |
D |
G |
S |
V |
|
: |
|
1 |
7 |
8 |
| R |
P |
I |
A |
_ |
M |
E |
T |
J |
A |
|
: |
|
K |
R |
G |
P |
V |
I |
T |
D |
N |
G |
N |
M |
I |
I |
D |
V |
F |
M |
N |
. |
I |
D |
D |
A |
I |
E |
L |
E |
K |
E |
I |
N |
N |
I |
P |
G |
V |
V |
E |
N |
G |
I |
F |
T |
. |
. |
K |
V |
D |
K |
V |
L |
V |
G |
T |
K |
K |
G |
V |
K |
|
: |
|
1 |
7 |
3 |
| R |
P |
I |
B |
_ |
E |
C |
O |
L |
I |
|
: |
|
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
K |
M |
I |
V |
D |
A |
W |
L |
G |
A |
Q |
Y |
E |
G |
G |
R |
H |
Q |
Q |
R |
V |
E |
A |
I |
T |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
. |
|
: |
|
|
8 |
1 |
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
Приведенное выравнивание доказывает, что домены действительно негомологичны,
и, возможно, механизм катализа принципиально разный.
Поэтому приведемвыравнивание гомологичных доменов:
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
2 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
4 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
6 |
0 |
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
6 |
|
3 |
S |
|
|
|
|
|
|
|
|
|
|
|
6 |
|
6 |
|
|
L |
1 |
|
|
|
|
6 |
|
6 |
|
|
D |
G |
A |
D |
E |
6 |
|
|
|
|
6 |
|
6 |
I |
K |
G |
G |
G |
|
|
|
T |
|
E |
K |
I |
|
|
|
|
|
|
| R |
P |
I |
A |
_ |
E |
C |
O |
L |
I |
|
: |
|
E |
G |
A |
V |
S |
S |
S |
D |
A |
S |
T |
E |
K |
L |
K |
S |
L |
G |
I |
H |
V |
F |
D |
L |
N |
E |
V |
D |
S |
L |
G |
I |
Y |
V |
D |
G |
A |
D |
E |
I |
N |
G |
H |
. |
M |
Q |
M |
I |
K |
G |
G |
G |
A |
A |
L |
T |
R |
E |
K |
I |
|
: |
|
|
5 |
9 |
| R |
P |
I |
A |
_ |
H |
U |
M |
A |
N |
|
: |
|
L |
V |
C |
I |
P |
T |
S |
F |
Q |
A |
R |
Q |
L |
I |
L |
Q |
Y |
G |
L |
T |
L |
S |
D |
L |
D |
R |
H |
P |
E |
I |
D |
L |
A |
I |
D |
G |
A |
D |
E |
V |
D |
A |
D |
. |
L |
N |
L |
I |
K |
G |
G |
G |
G |
C |
L |
T |
Q |
E |
K |
I |
|
: |
|
|
5 |
9 |
| R |
P |
I |
A |
_ |
M |
E |
T |
J |
A |
|
: |
|
V |
F |
G |
I |
P |
T |
S |
F |
E |
A |
K |
M |
L |
A |
M |
Q |
Y |
E |
I |
P |
L |
V |
T |
L |
D |
E |
Y |
. |
D |
V |
D |
I |
A |
F |
D |
G |
A |
D |
E |
V |
E |
E |
T |
T |
L |
F |
L |
I |
K |
G |
G |
G |
G |
C |
H |
T |
Q |
E |
K |
I |
|
: |
|
|
5 |
9 |
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
|
8 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
0 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
2 |
0 |
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
6 |
|
|
|
A |
|
|
F |
6 |
|
6 |
|
D |
|
|
K |
|
|
|
|
L |
G |
|
|
|
|
|
|
|
P |
6 |
E |
V |
I |
P |
|
A |
|
|
|
V |
|
R |
|
6 |
|
|
|
|
G |
G |
|
|
|
|
R |
|
|
|
|
|
|
|
|
|
|
| R |
P |
I |
A |
_ |
E |
C |
O |
L |
I |
|
: |
|
I |
A |
S |
V |
A |
E |
K |
F |
I |
C |
I |
A |
D |
A |
S |
K |
Q |
V |
D |
I |
L |
G |
K |
F |
P |
L |
. |
. |
. |
P |
V |
E |
V |
I |
P |
M |
A |
R |
S |
A |
V |
A |
R |
Q |
L |
V |
. |
K |
L |
G |
G |
R |
P |
E |
Y |
R |
Q |
G |
. |
. |
|
: |
|
1 |
1 |
3 |
| R |
P |
I |
A |
_ |
H |
U |
M |
A |
N |
|
: |
|
V |
A |
G |
Y |
A |
S |
R |
F |
I |
V |
I |
A |
D |
F |
R |
K |
D |
S |
K |
N |
L |
G |
D |
Q |
W |
H |
K |
G |
I |
P |
I |
E |
V |
I |
P |
M |
A |
Y |
V |
P |
V |
S |
R |
A |
V |
S |
Q |
K |
F |
G |
G |
V |
V |
E |
L |
R |
M |
A |
V |
N |
|
: |
|
1 |
1 |
9 |
| R |
P |
I |
A |
_ |
M |
E |
T |
J |
A |
|
: |
|
V |
D |
Y |
N |
A |
N |
E |
F |
V |
V |
L |
V |
D |
E |
S |
K |
L |
V |
K |
K |
L |
G |
E |
K |
F |
P |
. |
. |
I |
P |
V |
E |
V |
I |
P |
S |
A |
Y |
R |
V |
V |
I |
R |
A |
L |
S |
. |
E |
M |
G |
G |
E |
A |
V |
I |
R |
L |
G |
D |
R |
|
: |
|
1 |
1 |
6 |
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
4 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
6 |
0 |
|
|
|
|
|
|
|
|
|
* |
|
|
|
|
|
|
|
1 |
8 |
0 |
|
|
|
|
|
|
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
V |
6 |
T |
D |
N |
G |
N |
|
I |
6 |
D |
|
|
|
|
|
6 |
|
|
|
|
|
6 |
|
|
|
I |
|
|
I |
P |
G |
V |
V |
|
|
G |
6 |
F |
|
|
|
|
|
|
|
|
|
|
G |
|
|
|
G |
|
|
|
|
|
|
|
|
| R |
P |
I |
A |
_ |
E |
C |
O |
L |
I |
|
: |
|
. |
. |
. |
. |
V |
V |
T |
D |
N |
G |
N |
V |
I |
L |
D |
V |
H |
G |
M |
E |
I |
L |
D |
P |
I |
A |
M |
E |
N |
A |
I |
N |
A |
I |
P |
G |
V |
V |
T |
V |
G |
L |
F |
A |
N |
R |
G |
A |
D |
V |
A |
L |
I |
G |
T |
P |
D |
G |
V |
K |
|
: |
|
1 |
6 |
9 |
| R |
P |
I |
A |
_ |
H |
U |
M |
A |
N |
|
: |
|
K |
A |
G |
P |
V |
V |
T |
D |
N |
G |
N |
F |
I |
L |
D |
W |
K |
F |
D |
R |
V |
H |
K |
W |
S |
E |
V |
N |
T |
A |
I |
K |
M |
I |
P |
G |
V |
V |
D |
T |
G |
L |
F |
I |
N |
. |
M |
A |
E |
R |
V |
Y |
F |
G |
M |
Q |
D |
G |
S |
V |
|
: |
|
1 |
7 |
8 |
| R |
P |
I |
A |
_ |
M |
E |
T |
J |
A |
|
: |
|
K |
R |
G |
P |
V |
I |
T |
D |
N |
G |
N |
M |
I |
I |
D |
V |
F |
M |
N |
. |
I |
D |
D |
A |
I |
E |
L |
E |
K |
E |
I |
N |
N |
I |
P |
G |
V |
V |
E |
N |
G |
I |
F |
T |
. |
. |
K |
V |
D |
K |
V |
L |
V |
G |
T |
K |
K |
G |
V |
K |
|
: |
|
1 |
7 |
3 |
| |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
Матрица попарной идентичности (получена с помощью программы
GeneDoc):
RPIA_ECOLI RPIA_HUMAN RPIA_METJA RPIB_ECOLI
RPIA_ECOLI 100% 37% 39% 9%
RPIA_HUMAN 100% 45% 6%
RPIA_METJA 100% 9%
RPIB_ECOLI 100%
|
Итак, видно, что домен из RPIB_ECOLI сильно отличается от других, и, скорее всего, негомологичен им. Домены из
трех других белков похожи. Высокий процент идентичности и большое число замен на "схожие" остатки соответствует тому, что
функции этих белков (доменов) из разных организмов совпадают.
©Семенюк Павел