Реконструкция и визуализация находок
Полученные с помощью blastp находки были помещены в файл all.fasta, хранящий только ID белков-гомологов и соответствующие им последовательности. Далее этот набор был выравнен с помощью mafft:
mafft --auto all.fasta > aln.fasta
и по выравниванию реконструировалось дерево найденных гомологов с числом реплик бутстрепа 1488:
iqtree -s aln.fasta -bb 1488.
Ссылка на файл дерева (./aln.fasta(1).treefile)
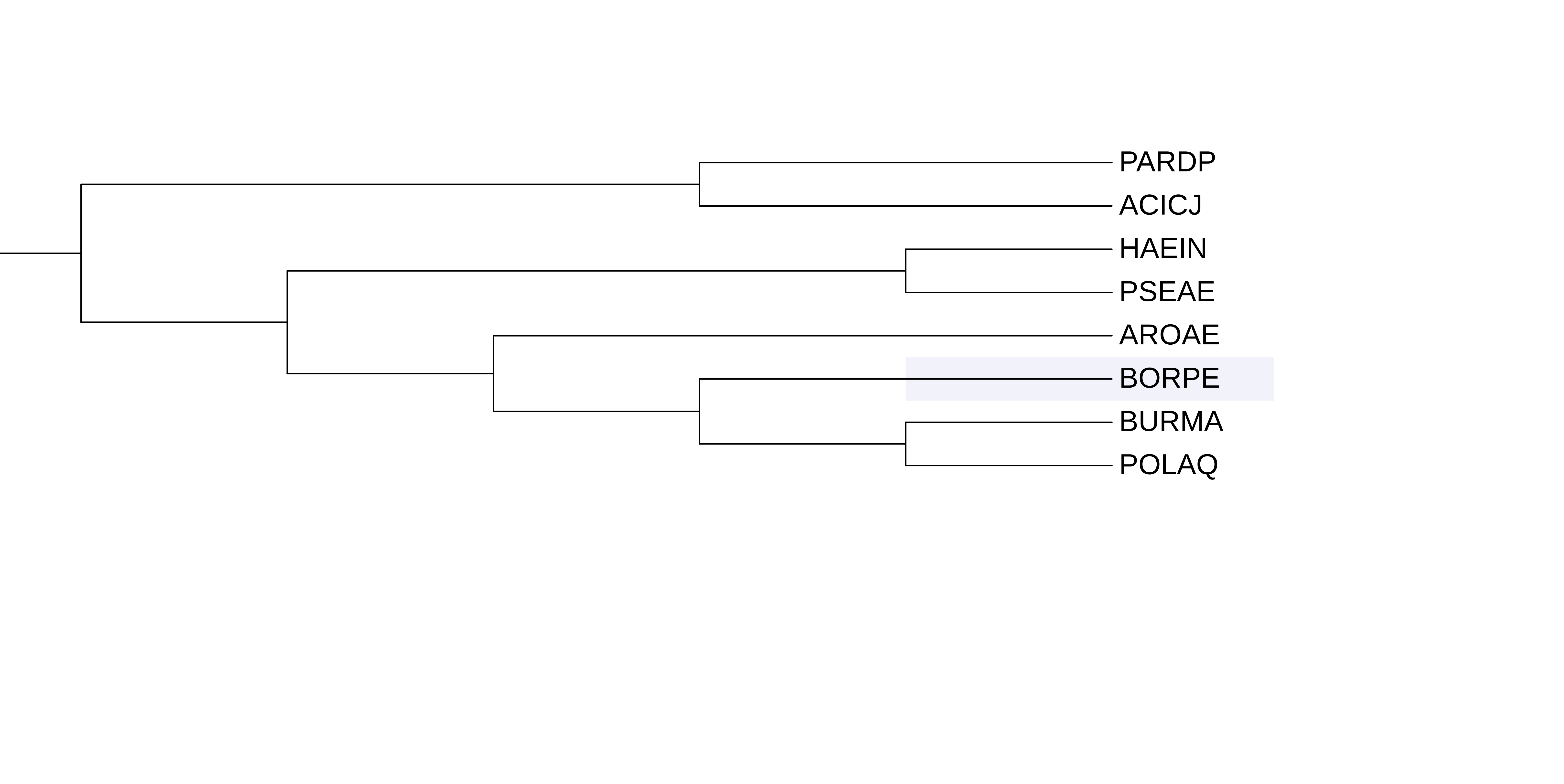
Дерево строилось программой iqtree и midpoint укоренено в ITOL. Разными цветами покрашены разные ортологические группы. A1B8N4_PARDP не вошел ни в одну ортологическую группу, потому и не покрашен.
Три пары ортологов: CLPX_BURMA и CLPX_AROAE, CLPX_ACICJ и CLPX_PARDP, CLPX_HAEIN и CLPX_ACICJ. Три пары паралогов: (HSLU/CLPX)_PARDP, (HSLU/CLPX)_AROAE, (HSLU/CLPX)_BURMA.
Красным треугольником обозначена ортологическая группа белка CLPX, состоящая из белков из организмов POLAQ, BURMA, AROAE, BORPE, PSEAE, HAEIN, ACICJ, PARDP. Зелёным треугольником обозначена клада, состоящая из ортологичных белков А5FYD7 из АCICJ и HSLU из PSEAE, HAEIN, PARDP, AROAE, BURMA, BORPE.
Зелёная клада: не соответствует правильной филогении. Ветви, ведущие к белкам из HAEIN и PSEAЕ не исходят из одного узла. Однако отбросив это, все остальные ветви реконструированы правильно. Красная клада: тоже нет. Ветви к BURMA и AROAE не должны исходить из одного узла, а к HAEIN и PSEAE из разных.
Вывод: деревья видов и деревья, отражающие эволюцию ортогрупп, различаются и далеко не всегда их можно приравнивать друг к другу.
.png)
.png)