| Для данного задания была выбрана структура 1DUP. Для поиска гидрофобных кластеров был использован CluD. |
| Изменяемыми параметрами являлись:порог расстояния и порог размера кластера. |
| В начале при пороге дистанции в 5.4А и параметром не показывать кластеры менее трех атомов было найдено 6 кластеров. |
| 2 кластера состоят из 6 атомов, а один кластер состоит из 227 атомов. |
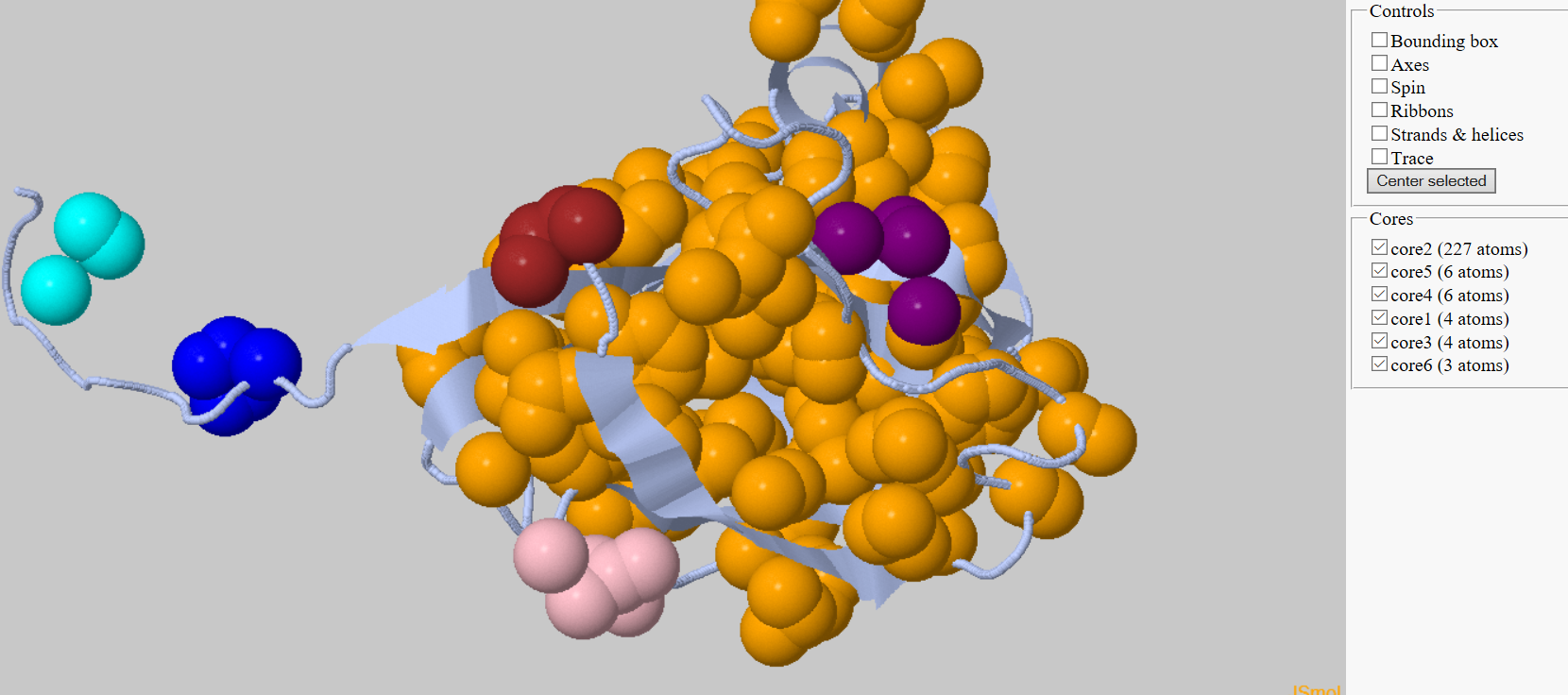 |
| Рис 1, кластеризацмя в 1DUP при параметраз 5.4А и 3
|
| При изменении порога дистанции до 5 ангстрем было найдено 8 кластеров. |
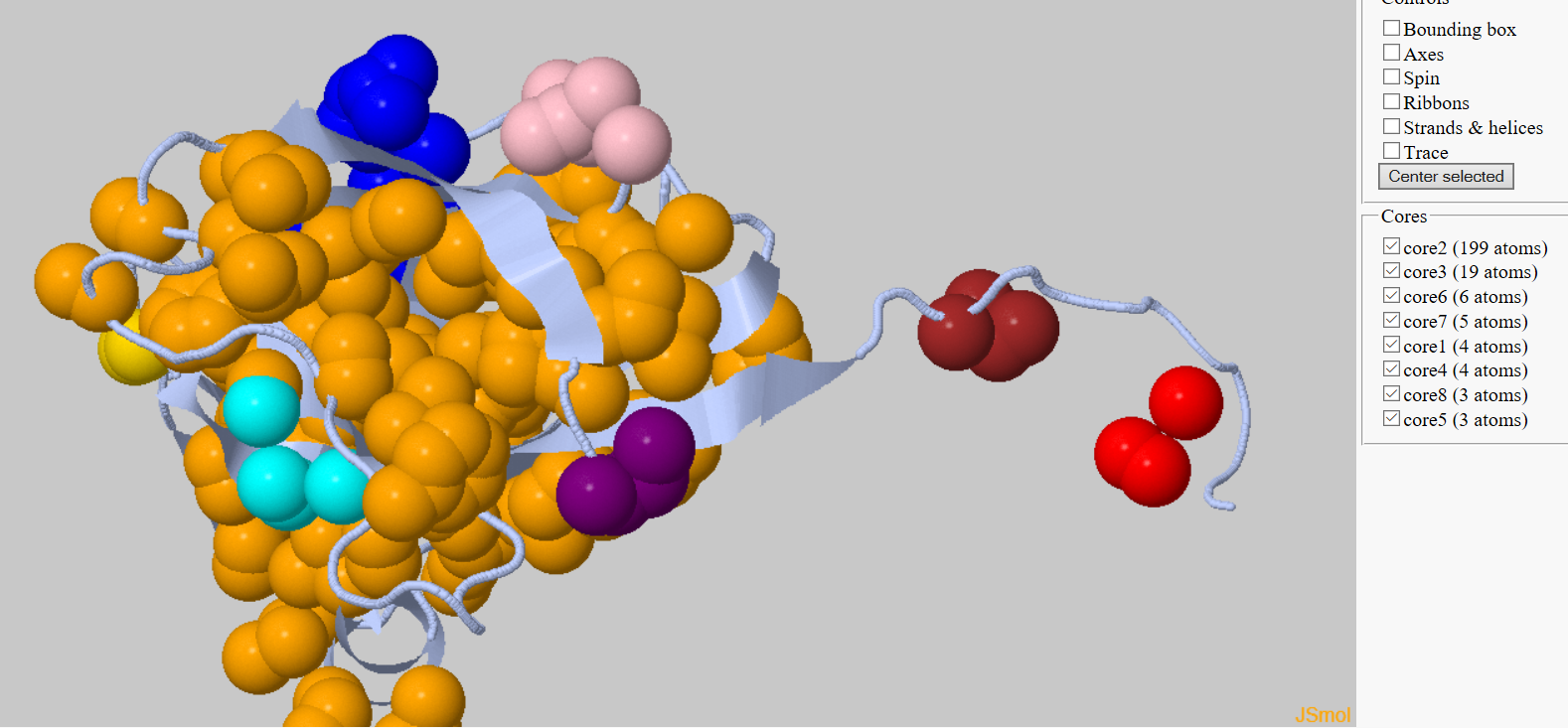 |
| Рис 2, кластеризацмя в 1DUP при параметрах 6А и 3. |
| Уменьшение порога дистанции приводит к тому, что крупные кластеры распадаются на более мелкие, а увеличение - наоборот, приводит к объединению кластеров. |
| При варьировании условий можно добиться того, что гидрофобные кластеры будут покрывать всю поверхность белка. |
| Наиболее оптимальными являются исходные параметры. |
| Гидрофобные кластеры в структуре комплекса белка с ДНК |
| Для данного задания был выбран белок TATА связывающий белок 1TGH (TATA BINDING PROTEIN (TBP)). Для него был призведен поиск гидрофобных кластеров в структуре. |
| При запуске с исходными параметрами 5.4А и >3 атома было найдено 5 кластеров, принадлежащих белку, где один из кластеров принадлежит ДНК. |
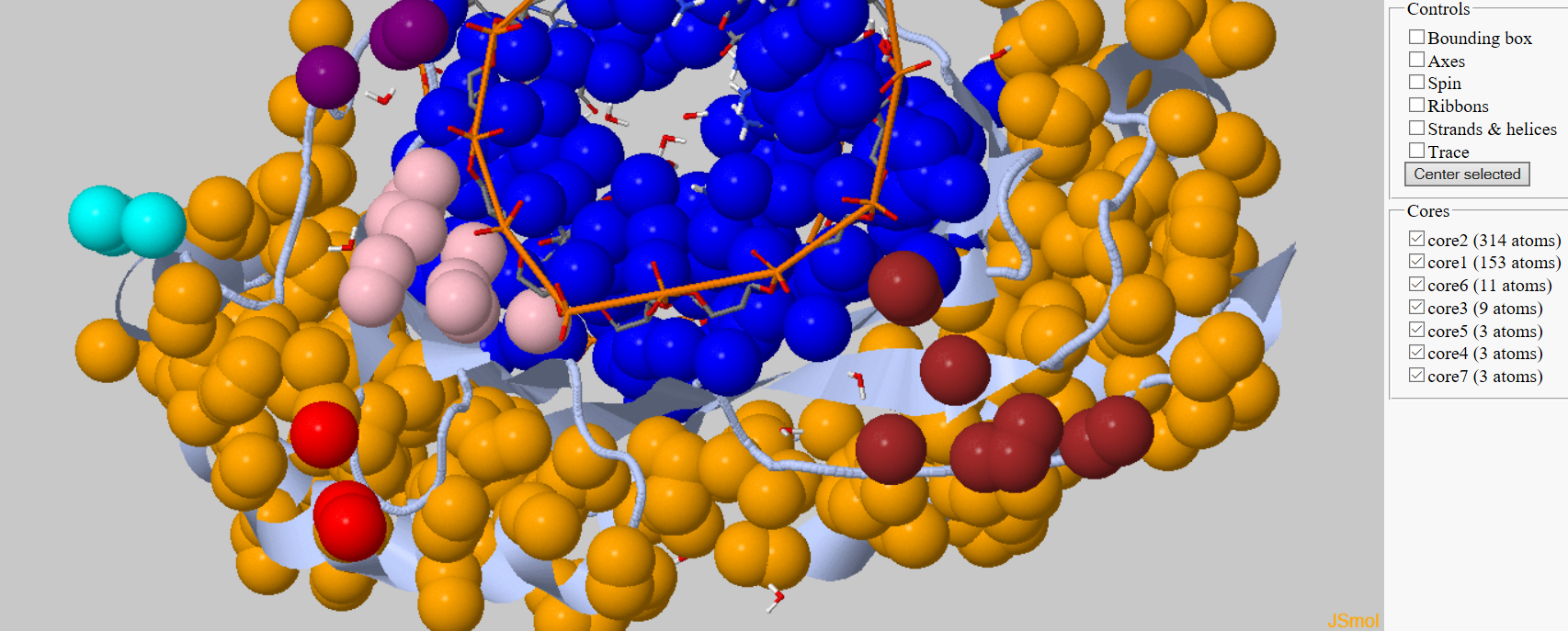 |
| Рис 3, кластеризация в 1TGH c параметрами 5А и 3. |
| При выставлении параметров 6А - кластер ДНК объединяется с кластером белка в один, что не является верным. При уменьшении порога кластер ДНК разбивается на несколько, |
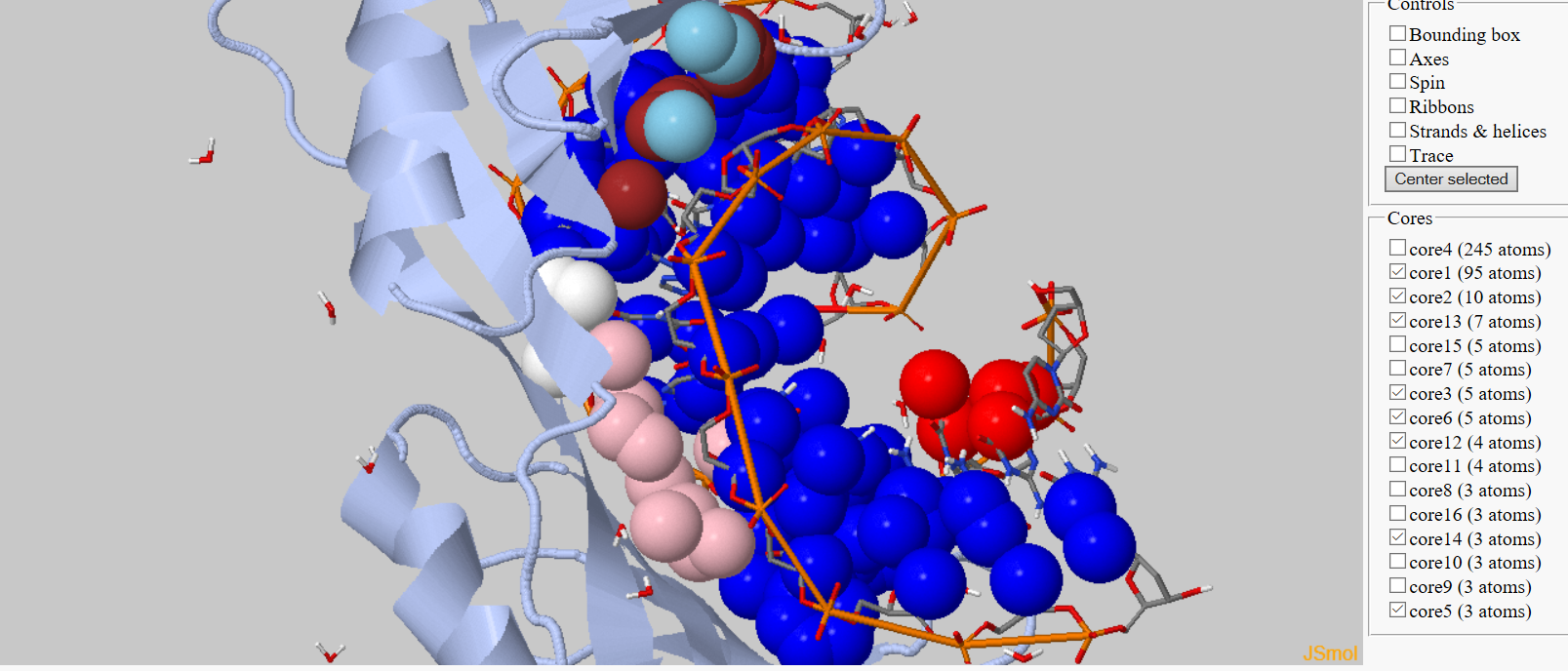 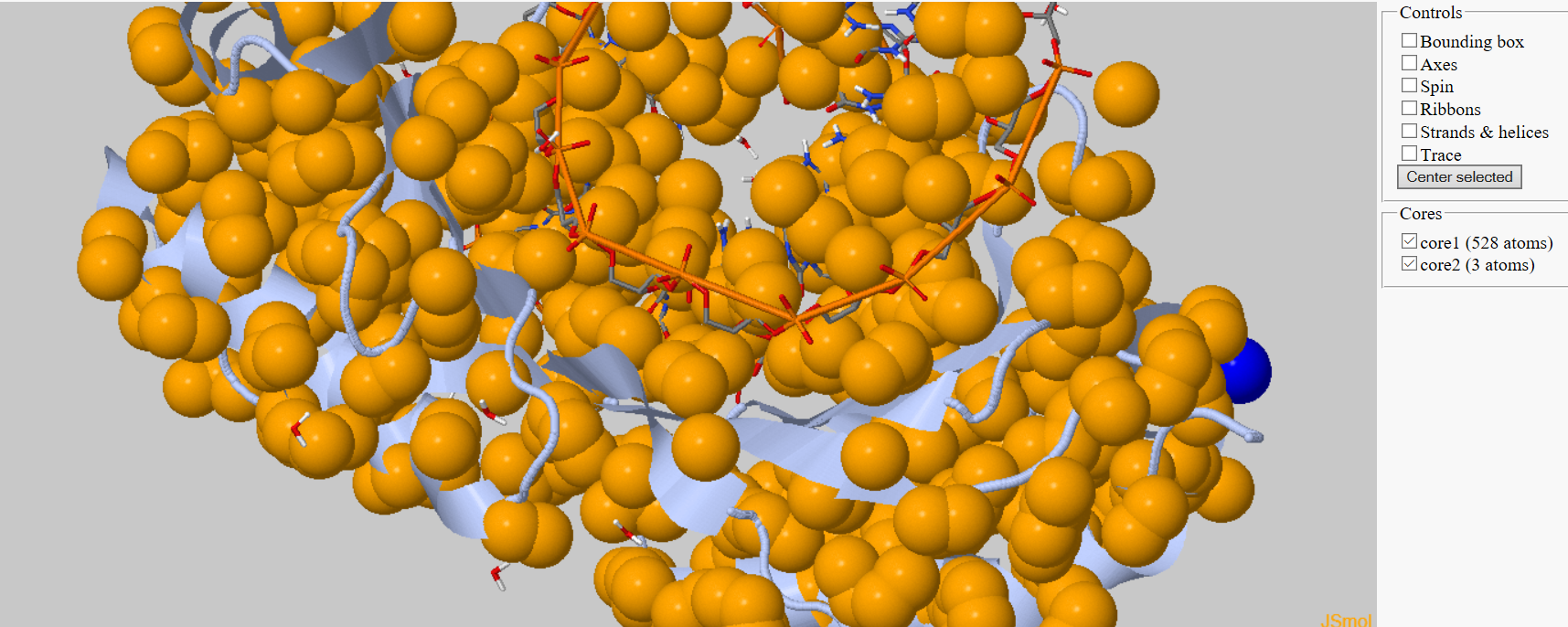 |
| Рис 3, кластеризация в 1TGH c параметрами 4,8А и 3 слева и 6А и 3 справа. |
| Таким образом, оптимальным является запуск с исходными параметрами. Белок содержит гидрофобные кластеры для взаимодействия с ДНК. |









