Банки белковых последовательностей. UniProt.
В этом практикуме ведется работа с UniProt - открытой базой данных белковых последовательностей.
Цель практикума состоит в том, чтобы описать данный белок с разных сторон, используя UniProt и другие источники. Также освоить возможности базы данных (расширенный поиск, истории записи, формат).
INSDC CDS (идентификатор автоматической трансляции из нуклеотидного архива) моего белка - CAA46911.1
Описание бактерии
Предоставленный для анализа белок встречается у бактерии Paraburkholderia xenovorans (штамм LB400)
Таксономическая линия
cellular organisms › Bacteria › Proteobacteria › Betaproteobacteria › Burkholderiales › Burkholderiaceae › Paraburkholderia › Paraburkholderia xenovorans
Грам-отрицательная, стержневидная, подвижная, мезофильная, неспорообразующая. Производимое соединение - бифенилдиоксигеназа.
Геном
Seq. accession number - 36873.6
Assembly level (bp) - full
GC-content 62.6 mol%
Экологическая биотехнология и безопасность
Одной из актуальных проблем современности является загрязнение окружающей среды производственными токсичными соединениями - ароматическими, полиароматическими и их хлорпроизводными LB400 относится к штамму-диструктуру полихлорированных бифенилов (ПХБ), которая утилизирует соединения в аэробных условиях, без накопления токсичных метаболитов. Аэробная биодеградация ПХБ обычно включает два кластера генов, первый отвечает за их превращение в хлорбензоаты и хлорированные алифатические кислоты, верхний путь бифенила, а второй отвечает за дальнейшую минерализацию хлорбензоатов и алифатических кислот, нижний путь бифенила.
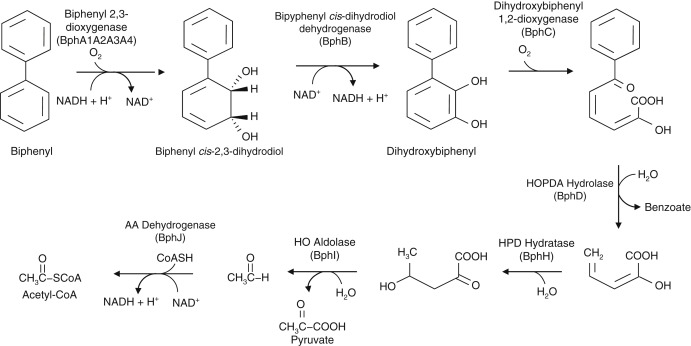
Описание белка
Данные, полученные из UniProt
| UniProtKB | UniProt ID | UniProt AC | DE | DR | SQ |
| Swiss-Prot | BPHD_PARXL | P47229; Q13FU1; | RecName: 2-hyoxy-6-oxo-6-phenylhexa-2,4-dienoate hyolase | EMBL; X66123; CAA46911.1; -; Genomic_DNA. | Длина-286 AA; Масса-32030 MW; |
| Short name: HOPDA hydrolase | EMBL; CP000272; ABE37048.1; -; Genomic_DNA. | ||||
| Alternative name(s): 2,6-dioxo-6-phenylhexa-3-enoate hydrolase |
PDB |
Функция
Катализирует необычный гидролиз связи CC 2-гидрокси-6-оксо-6-фенилгекса-2,4-диеновой кислоты (HOPDA) с образованием бензойной кислоты и 2-гидрокси-2,4-пентадиеновой кислоты (HPD).Метоболический путь
Разложение бифенила, часть деградации ксенобиотиков. Этот белок участвует в стадии 4 подпути, который синтезирует 2-гидрокси-2,4-пентадиеноат и бензоат из бифенила. Молекулярная функция: Сериновая Гидролаза. Биологический процесс: Катаболизм ароматических углеводородов.Структура
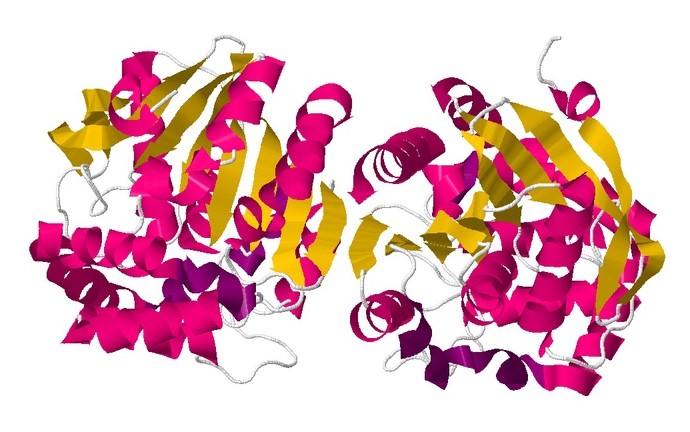
Индификатор в PDB 2OG1
Длина последовательности 286 a.o., молекула состоит из двух цепей A,B и представляет собой гомодимер.
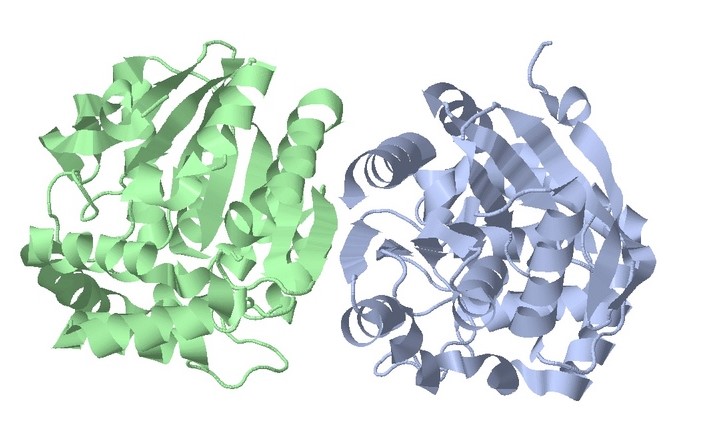
Содержит три лиганда:
1) SO4 (Сульфат-ион)
2) GOl (Глицерол)
3) EOH (Этиловый спирт)
Активный центр фермента составляют глицины в 42..43 позициях. Чтобы лучше разобраться с особенностями строения белка, полезно изучить ключи FT.
Ключи таблицы локальных особенностей (Feature Table)
Все примеры приведены для белка HOPDA, INSDC CDS - CAB50343.1
Chain- cтепень полипептидной цепи в зрелом белке. В Swiss-Prot присутствует:
• Для белков, которые не подвергаются процессингу (тех, для которых последовательность зрелого белка соответствует транслированной последовательности кДНК), ЦЕПЬ охватывает всю последовательность белка:
• Для процессированных белков он описывает зрелую часть белка после удаления препротеиновых частей, таких как пропептиды и сигнальные последовательности:
HOPDA - фермент прокариотического огрганизма, следовательно он не процессируется, что подтверждается данными из UniProt.
| FT | CHAIN | 1..286 |
| FT | /note="2-hydroxy-6-oxo-6-phenylhexa-2,4-dienoate hydrolase" | |
| FT | /id="PRO_0000207052" |
REGION - протяженность интересующей области в последовательности.
42-43 аминокислотный остаток связываются ссубстратом, составляя активный центр фермента:
| FT | REGION | 42..43 |
| FT | /note="Substrate binding" |
ACT SITE - аминокислоты, участвующие в активности фермента.
256 аминокислота является акцептором протона:
| FT | ACT_SITE | 256 |
| FT | /note="Proton acceptor" |
BINDING - сайт связывания для любой химической группы (кофермент, простетическая группа и т. Д.). Химическая природа группы указана в поле описания. В примере 180 а.о. связывается с субстратом
SITE- любой интересный сайт с одной аминокислотой в последовательности, который не определяется другим функциональным ключом. Это также может относиться к аминокислотной связи, которая представлена положениями двух фланкирующих аминокислот.
112 a.o. обеспечивает стабилизацию переходного состояние фермента:
| FT | SITE | 112 |
| FT | /note="Transition state stabilizer" |
MUTAGEN - сайт, экспериментально измененный мутагенезом.
| FT | MUTAGEN | 112 |
| FT | /note="S->A: Catalyzes the tautomerisation of HOPDA. | |
| FT | Extremely low hydrolase activity; when associated with A-265." | |
| FT | MUTAGEN | 265 |
| FT | /note="H->A: Unable to catalyze the tautomerisation of HOPDA. | |
| FT | Extremely low hydrolase activity; when associated with A-112." | |
| FT | /evidence="ECO:0000269|PubMed:17442675" |
Сеансы поиска в Uniprot
Для поиска целевого белка в других организмах, в таксономически близких оргазмах, белков со схожими последовательностями можно провести расширенный поиск по базам UniProtKB или UniRef.
Поиск осуществлялся через базу UniprotKB.Поск по названию:
Текст запроса: name:2-hydroxy-6-oxo-6-phenylhexa-2 4-dienoate hydrolase
Количество находок в Swiss-Prot - 10, в TrEMBLE - 1,431.
В разделе Popular organisms можно посмотреть организмы у которых встречается данный фермент:Mycobacterium tuberculosis, Paraburkholderia xenovorans, Pseudomonas furukawaii, Pseudomonas sp.. Все организмы являются прокариотами, примечательно, что для многих из них существование белка выведено из гомологии, но не подтверждено на белковом или нуклеотидном уровне.
Поск по названию и организму:
Текст запроса: name:"2-hydroxy-6-oxo-6-phenylhexa-2 4-dienoate hydrolase" organism:"paraburkholderia xenovorans strain lb400"
Количество находок в Swiss-Prot - 1, в TrEMBLE - 0.
Поиск по названию и ключевым словам:
Текст запроса: database:(type:pdb) keyword:"aromatic hydrocarbons catabolism"
Количество находок в Swiss-Prot - 117, в TrEMBLE - 35. Организмы: Bacillus subtilis, E. coli, human, mouse. Целевой белок выводится на 12 строке таблицы результатов
Поиск по таксономии:
Текст запроса: name:"2-hydroxy-6-oxo-6-phenylhexa-2 4-dienoate hydrolase" taxonomy:burkholderiaceae
Количество находок в Swiss-Prot - 2, в TrEMBLE - 56.
Только для Paraburkholderia xenovorans (strain LB400) существование белка подтверждено на белковом уровне, для семи бактерий оно выведено из гомологии (Burkholderia cepacia (Pseudomonas cepacia); Burkholderia sp. TSN101), для всех остальных предсказано.
Текст запроса: name:"2-hydroxy-6-oxo-6-phenylhexa-2 4-dienoate hydrolase" taxonomy:burkholderiales
Количество находок в Swiss-Prot - 5, в TrEMBLE - 123. Самым популярным организмом в этом запросе оказалась Comamonas testosteroni
Текст запроса: name:"2-hydroxy-6-oxo-6-phenylhexa-2 4-dienoate hydrolase" taxonomy:betaproteobacteria
Количество находок в Swiss-Prot - 5, в TrEMBLE - 135.
Текст запроса: name:"2-hydroxy-6-oxo-6-phenylhexa-2 4-dienoate hydrolase" taxonomy:proteobacteria
Количество находок в Swiss-Prot - 8, в TrEMBLE - 456.
Во всех запросах с тегом OS в таблице результатов на первой позиции выводиться paraburkholderia xenovorans strain lb400
Поиск, осуществляемый через UniRef.
Белки со сходной последовательностью объединяются в кластеры, представленные в UniRef. В кластеры UniRef100 входят последовательности идентичные на 100%. Чтобы войти в UniRef90, последовательности должны перекрываться хотя бы на 80% и иметь идентичность от 90%. Если последовательности перекрываются на 80%, но идентичны на 50%, то они попадают в UniRef50.
| ID | Название | Размер |
|---|---|---|
| UniRef50_P47229 | Cluster: 2-hydroxy-6-oxo-6-phenylhexa-2,4-dienoate hydrolase | 2136 |
| UniRef90_P47229 | Cluster: 2-hydroxy-6-oxo-6-phenylhexa-2,4-dienoate hydrolase | 31 |
| UniRef100_P47229 | Cluster: 2-hydroxy-6-oxo-6-phenylhexa-2,4-dienoate hydrolase | 2 |
История записей
История записей включает 135 версий, самая первая занесена в Uniprot 01.02.1996 года
В ходе сравнения первой и последней записи в UniProt были установлены следующие закономерности:
1. Значительные различия в систематике:Версия 1:
Bacteria; Proteobacteria; Betaproteobacteria; Burkholderiales; Burkholderiaceae; Paraburkholderia, Paraburkholderia xenovorans (strain LB400).Версия 135:
PROKARYOTA; GRACILICUTES; SCOTOBACTERIA; AEROBIC RODS AND COCCI; PSEUDOMONADACEAE, BURKHOLDERIA CEPACIA (PSEUDOMONAS CEPACIA), strain LB400.2. Добавлено намного больше комментариев относительно функции данного белка - фермента, путей метаболических, кинетических параметров, ингибиторов.
3. Методом рентгеноструктурного анализа были проанализированы особенности вторичной структуры фермента (большое количество записей в PDB). Также в последней версии описаны структурные особенности – субстрат-связывающие регионы, стабилизаторы переходного состояния, акцепторы протонов. Известны мутации. В первой версии отмечен только активный сайт (112).PDB записи появляются в 44 версии от 11-13-2007.
4. Можно заметить, что при сравнении аминокислотной последовательности, различий не было обнаружено. Но в более новой появляется показатель достоверности существования белка PE=1.
<Сравнение протеомов> В качестве модельного организма будет взята Escherichia coli. Во-первых, данная бактерия - хорощо изученный модельный организм, во-вторых, она также как и Paraburkholderia Грам-отрицательная, неспорообразующая, мезофильная бактерия.| Escherichia coli | Paraburkholderia xenovorans (strain LB400) | |
|---|---|---|
| ID протеома | UP000000625 | UP000001817 |
| Количество белков | 4392 | 8591 |
| В том числе из Swiss-Prot | 4389 | 440 |
| группа | текст запроса (на примере E. coli) | Escherichia coli | Paraburkholderia xenovorans (strain LB400) |
|---|---|---|---|
| Трансмембранные белки | annotation:(type:transmem) AND organism:"Escherichia coli (strain K12) [83333]" AND proteome:up000000625 | 946 (~21,5%) | 1533 (~17,84%) |
| Ферменты | ec:* AND organism:"Escherichia coli (strain K12) [83333]" AND proteome:up000000625 | 1676 (~38,2%) | 1965(~22,87%) |
| Гидролаза С-С связи | ec:3.7.1*AND organism:"Escherichia coli (strain K12) [83333]" AND proteome:up000000625 | 1 | 2 |
| Оксидоредуктазы (Acting on a heme group of donors) | ec:ec:1.9.* AND organism:"Escherichia coli (strain K12) [83333]" AND proteome:up000000625 | Periplasmic nitrate reductase, EC 1.9.6.1 | Periplasmic nitrate reductase, EC 1.9.6.1 Putative cytochrome c oxidase |
| Heat shock proteins | heat shock proteins AND organism:"Escherichia coli (strain K12) [83333]" AND proteome:up000000625 | 48(1,09%) | 5(0.06%) (2 в Swiss-Prot) |
Таким образом, мы видим что в протеоме Escherichia coli примерно в два раза меньше белков, чем в протеоме Paraburkholderia xenovorans (strain LB400) . При этом Ферментов и трансмембранных белков больше у E.coli относительно размера ее генома. Из этого можно сделать предположение, что Paraburkholderia xenovorans является более примитивным организмом. Paraburkholderia xenovorans получает углерод в процессе деградации бифинильных соединений, в этом метаболическом пути участвует С-С гидролаза, у E.coli также был обнаружен фермент данного класса, который участвует в гидролизе ароматического углевода 3-фенилпропионата. Проанализировав результаты поиска на оксидоредуктазы можно сделать вывал, что обе бактери метаболизирую азот, а использование кислорода и наличие дыхательной цепи характерно только дл яParaburkholderia xenovorans, таким образом, эта бактерия аэробна. У E.coli обнаружено больше белков теплого шока, значит она может перенгсить более высокие температуры, что не удивительно, исходя из места обитания организма.
Выводы
С помощью Uniprot Можно получить информацию о белке, протеоме организма, найти схожие последовательности. На основе баз данных можно находить определенные эволюционные закономерности, консервативные участки генома, определять особенности жизнидеятельности разных организмов. Информация, представленная в Uniprot, на сегодня дает много материалов для различных исследований.Список литературы и ресурсов
1. Егорова Д. О. Новые физиологические и молекулярно-биологические свойства бактерий-деструкторов (хлор) ароматических соединений //Вестник Пермского федерального исследовательского центра. – 2014. – №. 2.
2. Parales R. E., Ju K. S. Rieske-type dioxygenases: key enzymes in the degradation of aromatic hydrocarbons. – 2011.
3. https://bacdive.dsmz.de/strain/1965
4. https://www.uniprot.org/docs/userman.htm#FT_line rcsb.org/structure/2OG1
5. UniProt