С помощью программы fiber пакета 3DNA я построила A-, B- и Z-форму дуплекса ДНК
A-форма
B-форма
Z-форма
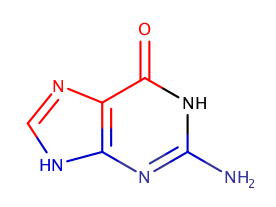
С помощью программы JMol я визуально определила большую и малую бороздки и такие харктеристики, как тип спирали, шаг спирали, число оснований на виток, ширина большой и малой бороздок у A-, B, и Z- форм ДНК. Результаты приведены в таблице. Также я рассмотрела гуанин, с помощью Marvin Sketch выделила красным цветом атомы, смотрящие в сторону большой бороздки, синим - в сторону малой.
В сторону большой бороздки обращены атомы: O6, C6, C5, N7, C8.
В сторону малой бороздки обращены атомы: C2, N2, N3, C4, N9.

| a-форма | b-форма | z-форма | |
| тип спирали | правая | правая | левая |
| шаг спирали |
28.03 | 33.75 | 43.5 |
| число оснований на виток | 11 | 10 | 12 |
| ширина большой бороздки | 17.11 (30:b фосфат) | 20.58 (29:b фосфат) | 11.58 (26:b фосфат) |
| ширина малой борозки | 7.98 (27:b фотсфат) | 13.2 (6:a фосфат) | 7.2 (17:a фосфат) |
Для данного задания была взята выданная тРНК с PDB ID 1ML5 (хотя именно о тРНК корректнее сказать 1ML5_B). Далее с помощью команды find_pair -t 1ml5_old.pdb stdout | analyze были получены файлы с различной информацией, в том числе файл 1ml5_old.out, в котором содержится информация о торсионнных углах.
В таблице ниже я привела значения торсионных углов у заданной тРНК, а также у A-, B- и Z- форм ДНК. Можно сказать, что структура тРНК получилась больше всего похожа на A-форму ДНК.
| alpha | beta | gamma | delta | epsilon | zeta | chi | |
| 1ml5_b | -44.32 | 80.13 | 45.02 | 89.37 | -135.6 | -66.96 | -147.77 |
| a-dna | -51.7 | 174.8 | 41.7 | 79.08 | -147.79 | -75.09 | -157.2 |
| b-dna | -29.9 | 136.34 | 31.14 | 143.34 | -140.8 | -160.5 | -97.99 |
| z-dna | -48.8 | 21.12 | -61.47 | 116.25 | -100.05 | 4.72 | -47.8 |
В том же файле можно найти информацию о водородных связях.
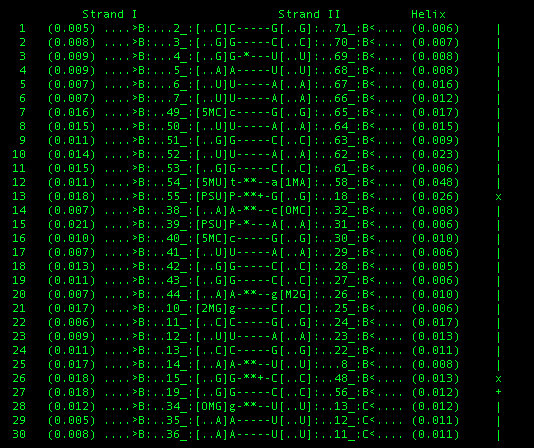
Координаты стеблей: 2-7..71-66, 49-53..65-61, 38-44..32-36, 10-13..25-22
Неканонические пары: G-U, A-c, P-a, A-g
Связи, стабилизирующие третичную структуру: t-a, P-G, A-U, G-C, g-U