Практикум 2. Алгоритмы филогенетической реконструкции
Получение выравнивания цитохромов B
Я решил построить выравниевание цитохромов B на kodomo для выбранных
ранее десяти представителей Teleostei. Был создан файл cyb.list.
С помощью команды seqret @cyb.list cyb.fasta был получен файл с последовательностями
цитохромов B для выбранных мной организмов из банка Swiss-prot. Далее было проведено выравнивание алгоритмом muscle:
muscle -align cyb.fasta -output cyb-alignment.fasta
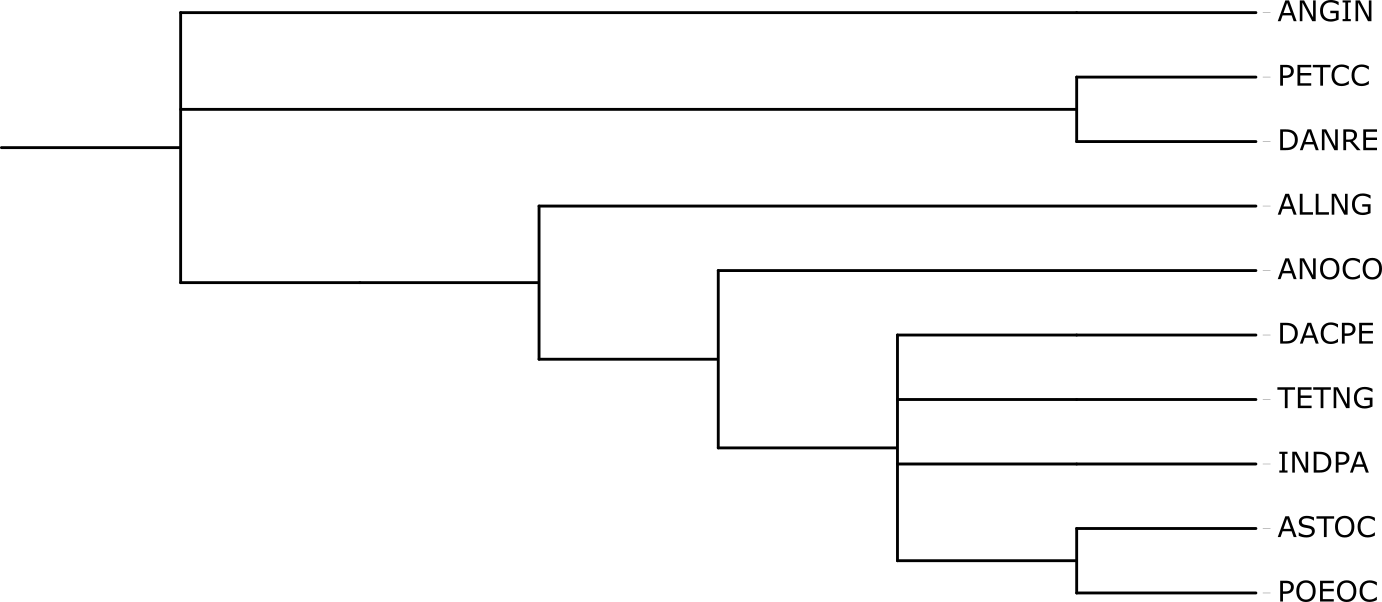
Реконструкция дерева программой FastME
С помощью скрипта Python выравнивание было переведено из формата fasta в phylip-relaxed и записано в файл cyb.phy.
Деревья по моделям p-distance и MtREV были построены соответственно с помощью команд
fastme -i cyb.phy -o pdistance.tre -pp и fastme -i cyb.phy -o mtrev.tre -pM

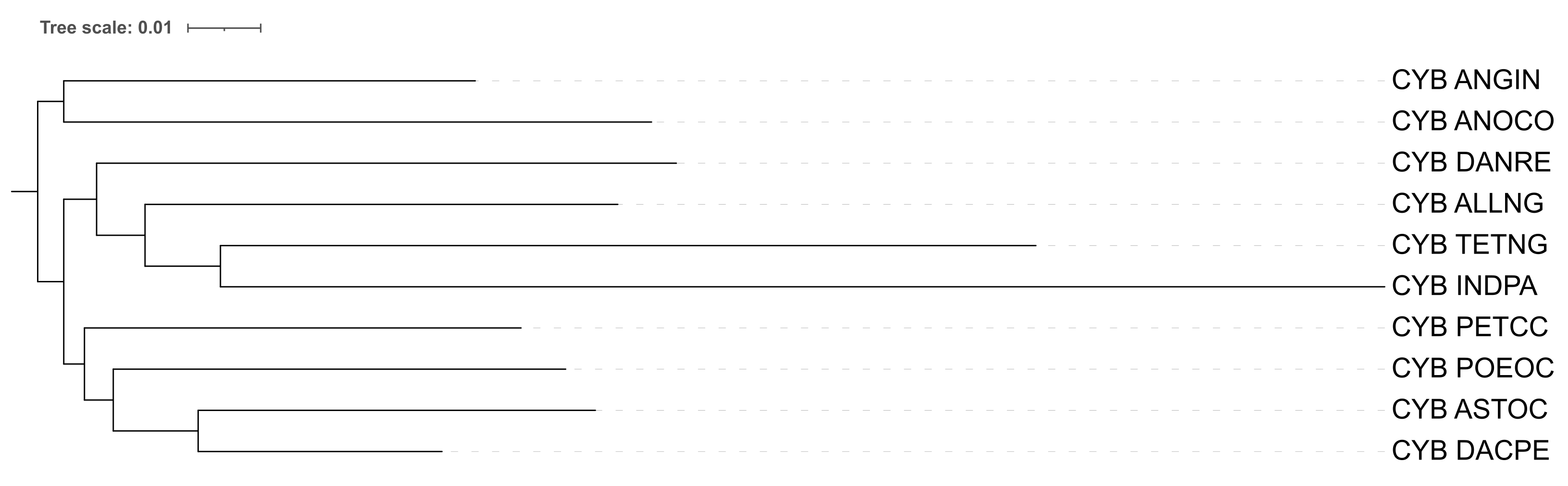
В этом варианте присутствуют заметные различия с исходной филогенией: ANGIN и DANRE отделились в отдельный лист, а у основания другого листа стоит PETCC. Это напоминает реальную систематику, однако отклонение от нее присутствует.
В этом варианте оказалось больше расхождений с реальной систематикой. ANGIN в одном листе с ANOCO (то есть угорь с саблезубым окунем), что не имеет биологического смысла. Остальная топология практически не совпадает, разве что ASTOC, POEOC и DACPE хотя бы находятся в одной ветви.
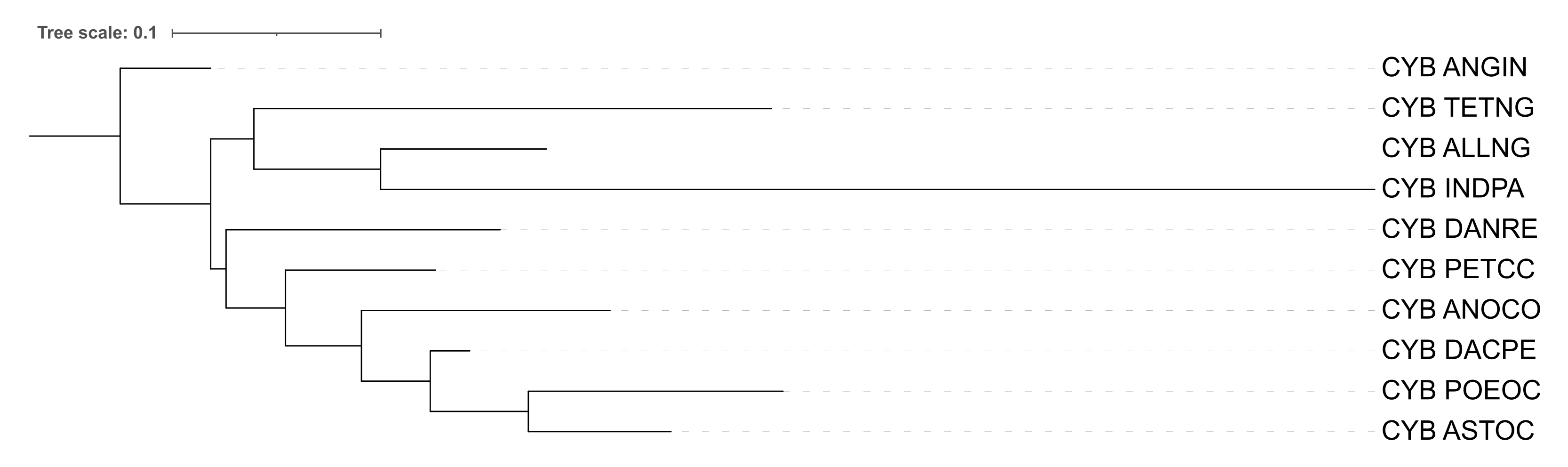
Реконструкция дерева программой IQ-Tree
С помощью команды iqtree -s cyb.phy (с параметрами по умолчанию) дерево было реконструировано. Здесь оно выглядит ближе к систематике, чем деревья, реконструированные программой FastME. ANGIN расположен отдельано, а ASTOC, POEOC и DACPE находятся в отдельной ветви. Остальая топология также варьируется.
Выводы
Хотя полученные деревья частично совпадают с исхоной систематикой, они в целом сомнительно справились с построением деревьев по Цитохрому . Предположительно, это связано с тем, что организмы подобраны неудачно, а также недостаточностью последовательностей всего одного белка для корректного восстановления всей топологии