Сравнивание структур канонических ДНК и стеблей тРНК
Что было сделано:
с помощью пакета 3DNA были получены молекулы A-, B- и Z-форм ДНК
с помощью программы JMol были визуализированы молекулы A-, B- и Z-форм ДНК
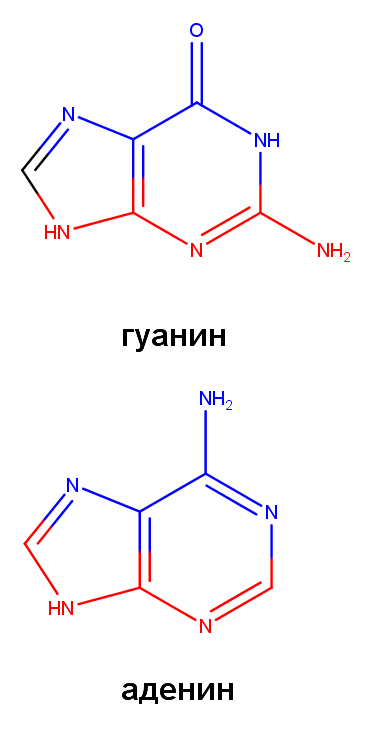
с помощью программы MarvinSketch были визуализированы нуклеотидные основания
с помощью пакета 3DNA были получены данные о структуре тРНК 2dlc
gatc-a:
В сторону большой бороздки направлены атомы G29.N3, G29.C2, G29.C4, G29.N2, G29.N9
В сторону малой бороздки направлены атомы G29.C8, G29.N7, G29.C5, G29.C6, G29.O6
3v9d
В сторону большой бороздки направлены атомы A8.N1, A8.C2, A8.N3, A8.C4, A8.N9
В сторону малой бороздки направлены атомы A8.N6, A8.C6, A8.C5, A8.C8, A8.N7
Примечания:
Скачать файл с последовательностью А-формы можно здесь
Скачать файл с последовательностью В-формы можно здесь
Скачать файл с последовательностью Z-формы можно здесь
Работа с JMol
|
A-форма |
B-форма |
Z-форма |
Тип спирали (правая или левая) |
правозакрученная |
правозакрученная |
левозакрученная |
Шаг спирали (Å) |
5.47 |
33.75 |
43.50 |
Число оснований на виток |
11 |
10 |
12 |
Ширина большой бороздки (Å) |
16.81 |
17.21 |
18.30 |
Ширина малой бороздки (Å) |
7.98 |
11.69 |
9.87 |
тРНК. Работа в Putty с пакетом 3DNA
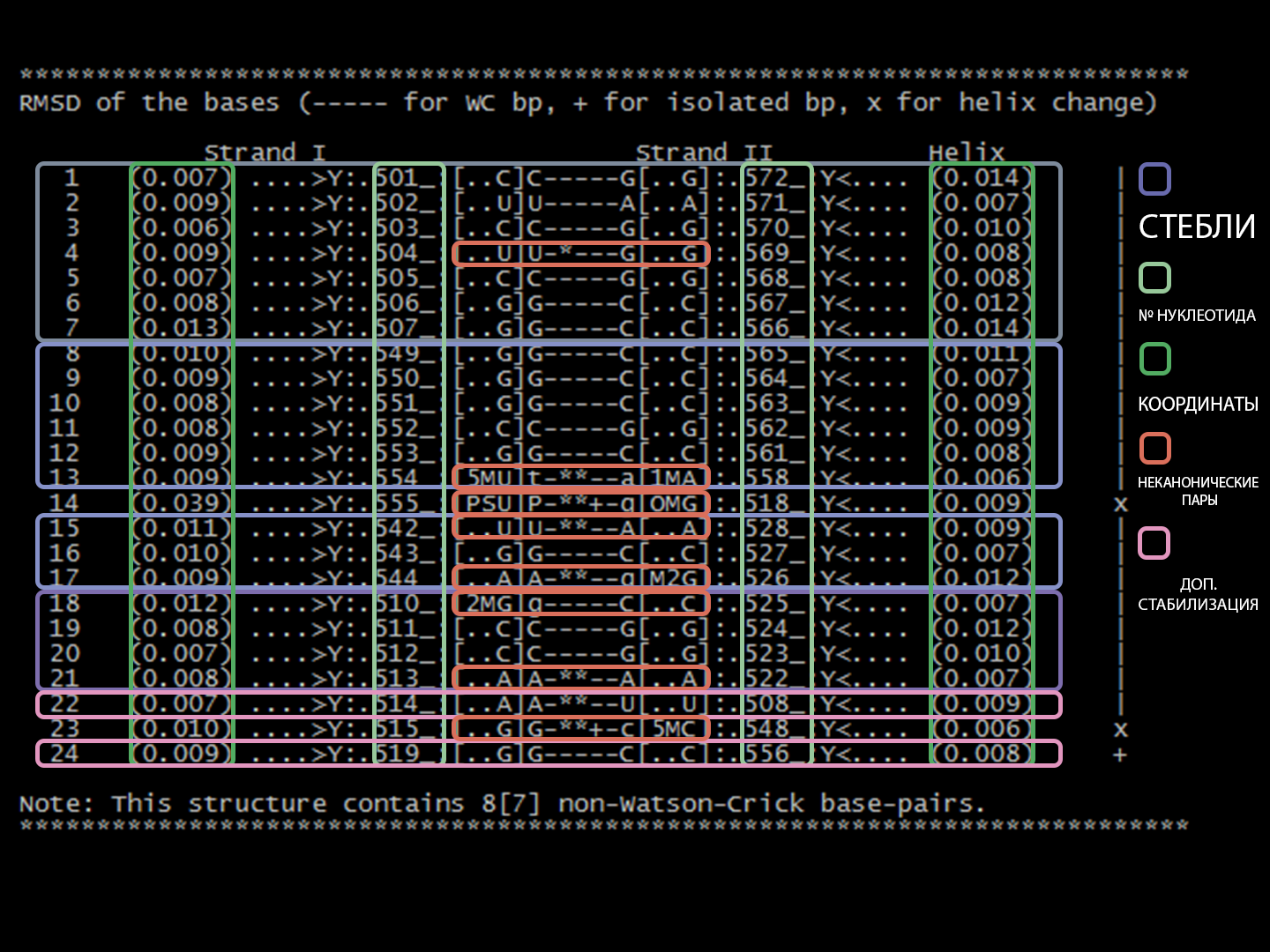
С помощью команд find_pair и analyze был получен файл в формате .out, в котором представлена информация о торсионных углах и водородных связях.
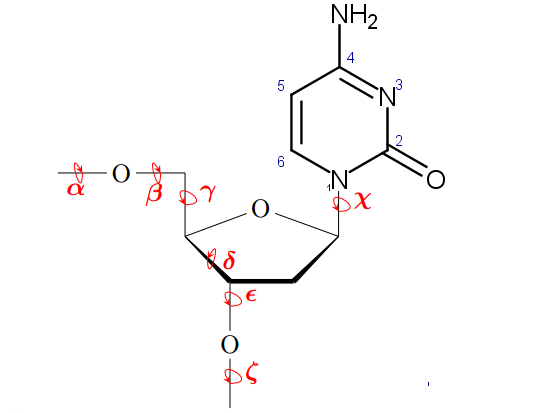
Значения торсионных углов потребовалось усреднить с помощью программы Microsoft Excel.
Если судить по значениям торсионных углов, то данная тРНК (2dlc) больше похожа на А-форму ДНК, т.к. значения торсионных углов
тРНК меньше всего отклоняются от значений торсионных углов А-формы ДНК.
| structure | alpha | beta | gamma | delta | epsilon | zeta | chi |
| A-form | -51.7 | 174.8 | 41.7 | 79.1 | -147.8 | -75.1 | -157.2 |
| B-form | -29.9 | 136.3 | 31.2 | 143.4 | -140.8 | -160.5 | -98.0 |
| tRNA | -52.44 | 69.41 | 49.07 | 88.55 | -129.57 | -63.29 | -159.73 |
С помощью того же файла можно было добыть информацию о водородных связях тРНК. Например, можно обнаружить координаты стеблей, номера нуклеотидов, неканонические пары или пары, обеспечивающие дополнительную прочность структуры. Они представлены на картинке.