Вторичная структура тРНК и контакты ДНК с белком
Что было сделано:
с помощью программы einverted пакета EMBOSS были предсказаны инверсионные участки тРНК 2DLC
с помощью программы RNAfold были предсказаны инверсионные участки тРНК 2DLC и визуализирована структура молекулы
с помощью программы JMol была визуализирована молекула ДНК 1HDD, содержащая контакты с белком
с помощью программы JMol были посчитаны полярные и неполярные связи ДНК с белком
с помощью программы nucplot были получены данные о ДНК-белковых контактах
с помощью программы gsview было получено изображение ДНК-белковых контактов
Предсказание вторичной структуры заданной тРНК
С использованием программы einverted и команды пакета EMBOSS find_pair были найдены (если точнее, не найдены, несмотря на понижение параметра Minimum score treshold до 10) инвертированные участки в тРНК.
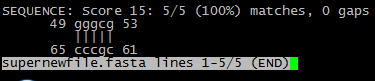
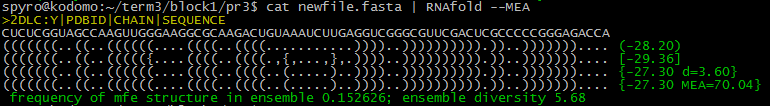
Для нахождения инвертированных участков тРНК была также использована программа RNAfold с опцией --MEA, реализующая алгоритм Зукера.
Она не давала адекватных результатов (судя по описанию наиболее устойчивой структуры, из моей цепи РНК должна была получиться одна длинная шпилька),
поэтому я обратилась к реализации алгоритма Зукера с помощью http://unafold.rna.albany.edu. Он выдал мне несколько вариантов, самым оптимальным из которых был такой:
CUCUCGGUAGCCAAGUUGGGAAGGCGCAAGACUGUAAAUCUUGAGGUCGGGCGUUCGACUCGCCCCCGGGAGACCA
(((((((..(((..........))).(((((.......))))).....(((((.......))))))))))))....
Отмечу, что стандартный параметр"Personal suboptimality" был изменен с 5 на 15.
Ниже представлена картинка с полученным результатом.
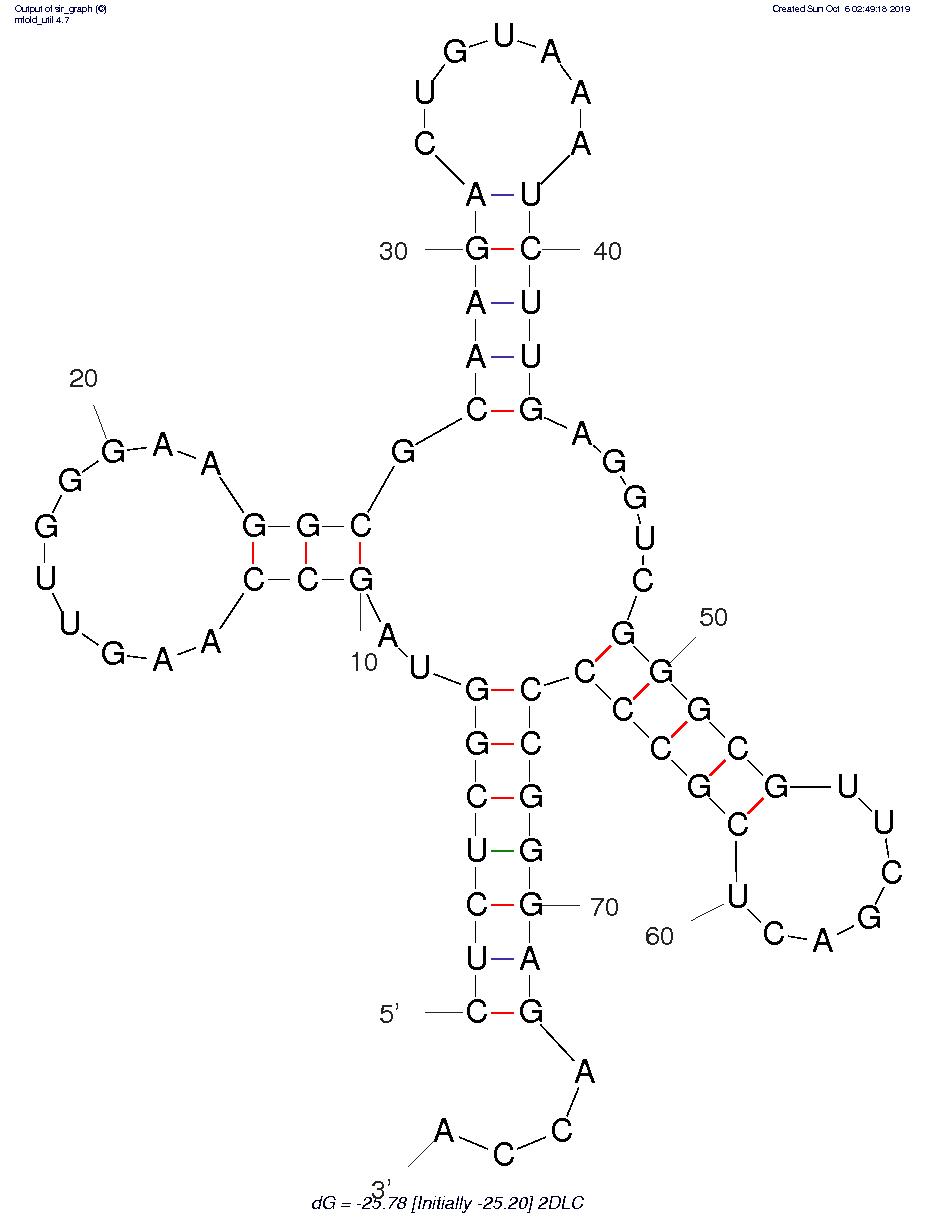
Участок структуры (расшифровку названий см. на рис. 2 в статье О.О.Фаворовой) |
Позиции в структуре (по результатам find_pair) |
Результаты предсказания |
Результаты предсказания по алгоритму Зукера |
Акцепторный стебель |
|
|
|
D-стебель |
|
|
|
T-стебель |
|
|
|
Антикодоновый стебель |
|
предсказано 0 пар из 3 реальных |
|
Общее число канонических пар нуклеотидов |
|
|
|
Поиск ДНК-белковых контактов в заданной структуре
C помощью команд JMol define (с целью задать множества атомов) и select within (<расстояние>,<множество>) были найдены атомы, образующие полярные и неполярные связи атомов ДНК и белка. Полярными считались связи атомов кислорода или азота на расстоянии менее 3.5 ангстрем, а неполярными - связи атомов углерода, фосфора или серы на расстоянии менее 4.5 ангстрем. Результаты подсчета связей представлены в таблице ниже.
Таблица. Контакты разного типа в комплексе 1HHD.pdb
Контакты атомов белка с |
Полярные |
Неполярные |
Всего |
остатками 2'-дезоксирибозы |
7 |
16 |
23 |
остатками фосфорной кислоты |
14 |
10 |
24 |
остатками азотистых оснований со стороны большой бороздки |
5 |
13 |
18 |
остатками азотистых оснований со стороны малой бороздки |
1 |
1 |
2 |
C помощью программы nucplot была получена схема ДНК-белковых контактов. Предварительно файл pdb был переведен в старый формат с помощью команды remediator:
remediator --pdb --old 1hdd.pdb > 1hdd_old.pdb
Результат работы команды nucplot:
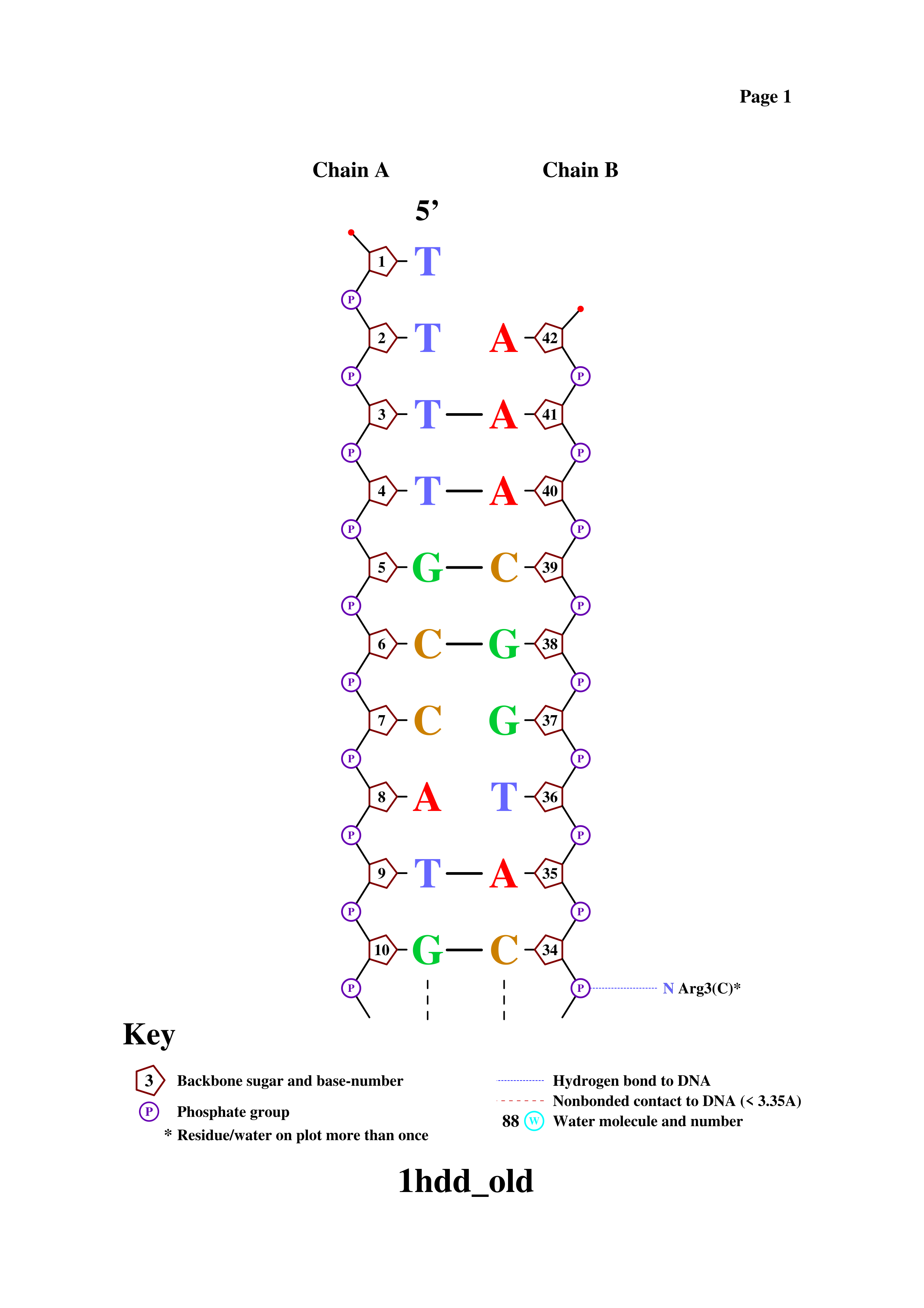
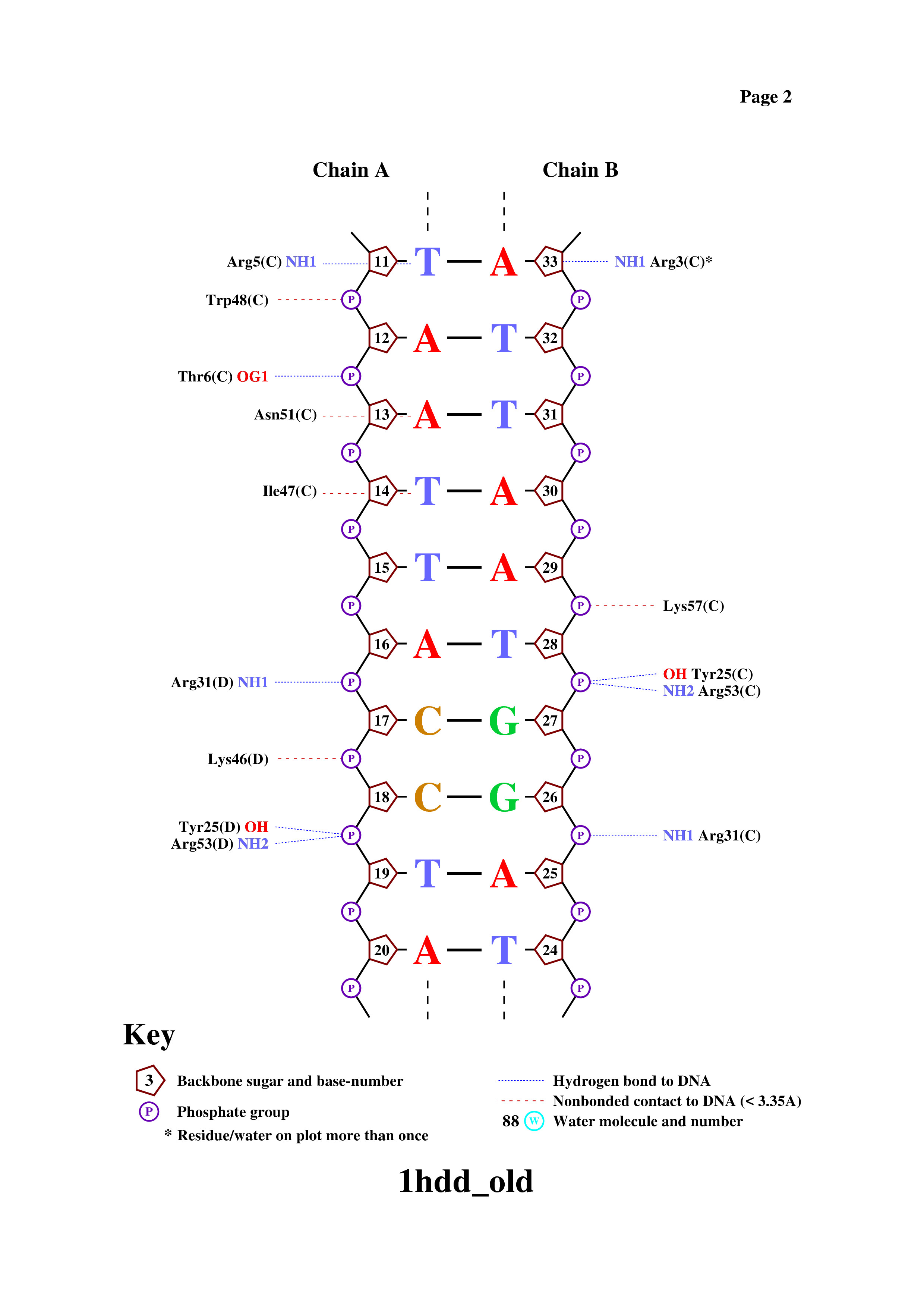
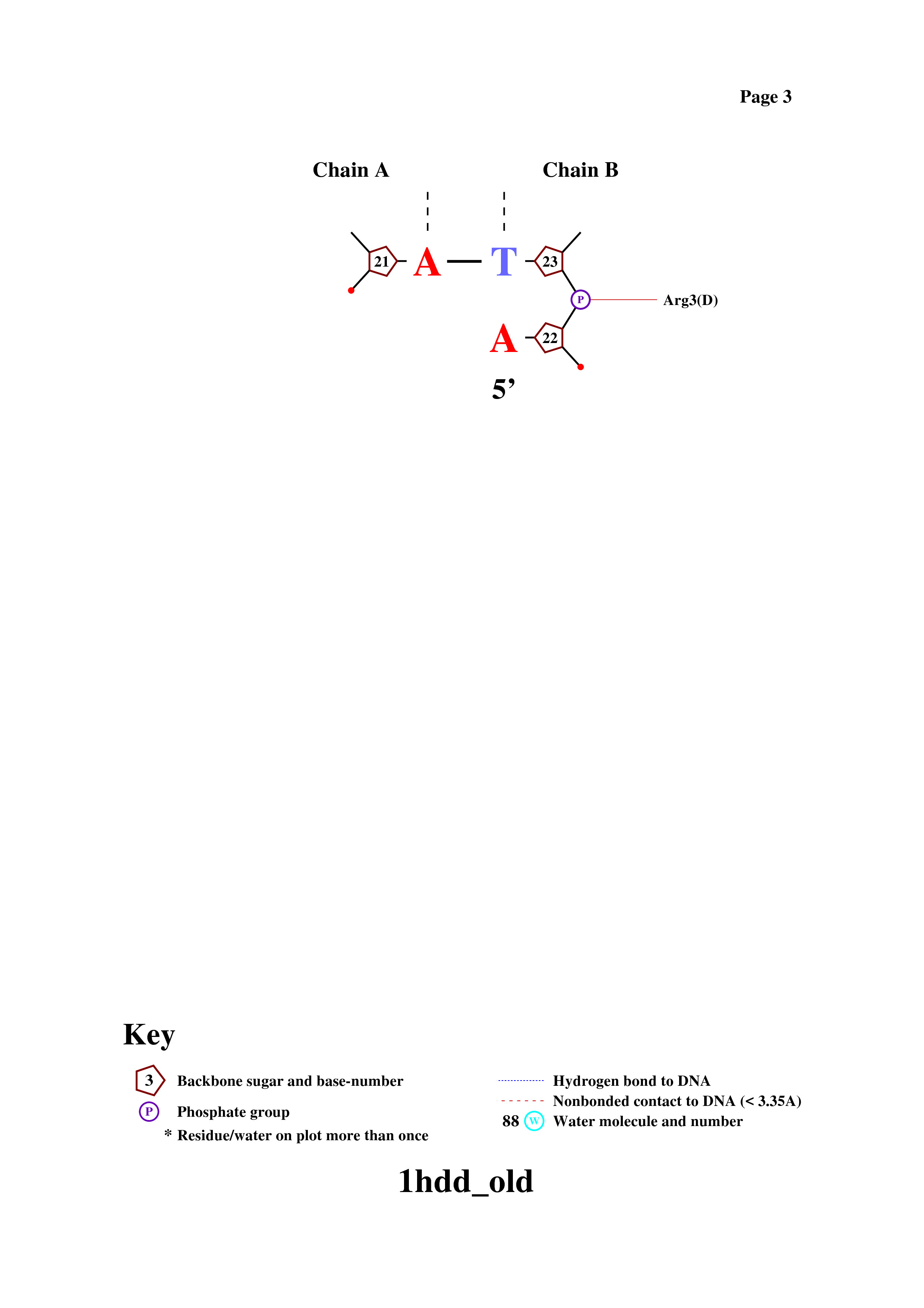
Аминокислотный остаток с наибольшим числом указанных на схеме контактов с ДНК - Arg3 (Имеется 3 водородные связи с ДНК).
Аминокислотный остаток, наиболее важный для распознавания последовательности ДНК тот, который связан не с остовом, а с азотистым основанием. Например, Arg5(C) или Arg3(C)*
На картинке ниже отмечены соединения сразу двух аминокислотных остатков, соединенных с комплементарными азотистыми основаниями цепи А и В.
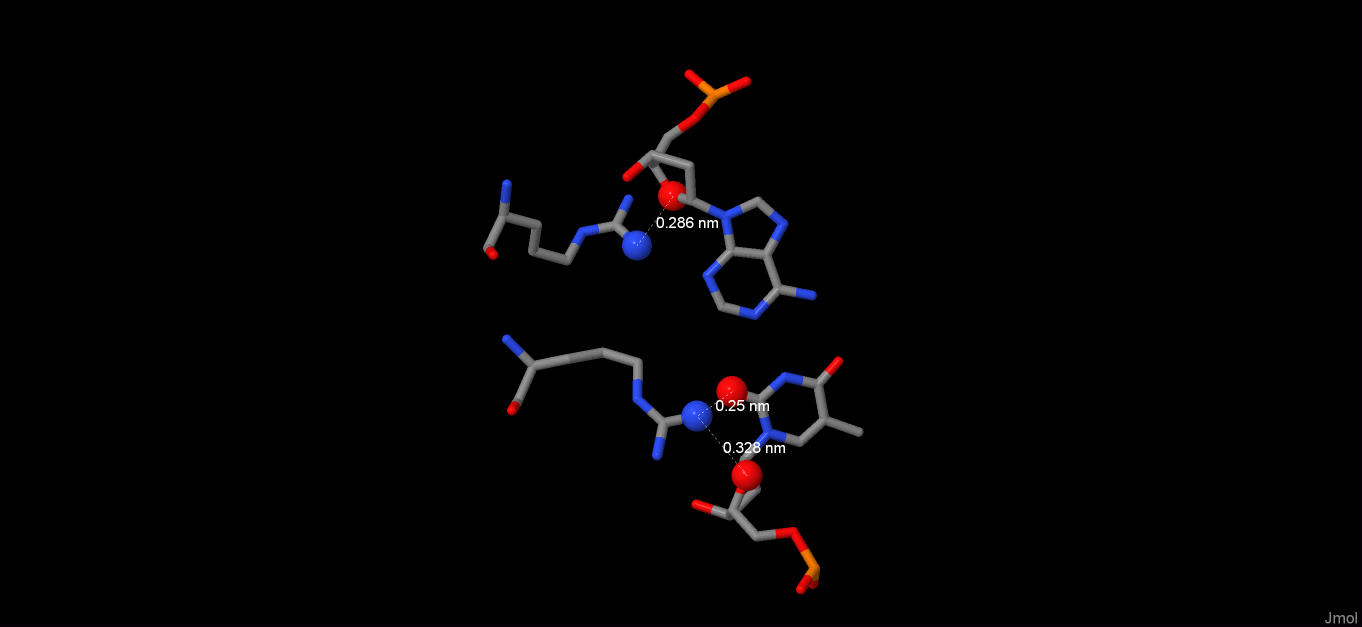
Примечания:
Скачать PDB файл тРНК можно здесь
Скрипт с демонстацией атомов различных множеств, а именно множество атомов кислорода 2'-дезоксирибозы, множество атомов кислорода остатков фосфатов и множество атомов азота нуклеотидных оснований, можно посмотреть здесь

