|
Характеристика сборки генома Ciona intestinalis
Систематическое положение:[1]
- Eukaryota
- Metazoa
- Bilateria
- Chordata
- Olfactores
- Tunicata
- Ascidiacea
- Enterogona
- Phlebobranchia
- Cionidae
- C. intestinalis (Vase tunicate; русское название
не используется)
Описание организма:[1]
Одиночная асцидия с телом до 20 см, покрытым мягкой туникой.
Имеет широкое распостранение и часто является инвазивным видом.
По сути под этим названием описаны несколько родственных видов.
C. intestinales является модельным организмом среди Tunicata,
была одним из первых животных с секвенированным геномом. Используется для
изучения биологии развития Tunicata и эволюции Chordata.
|
|
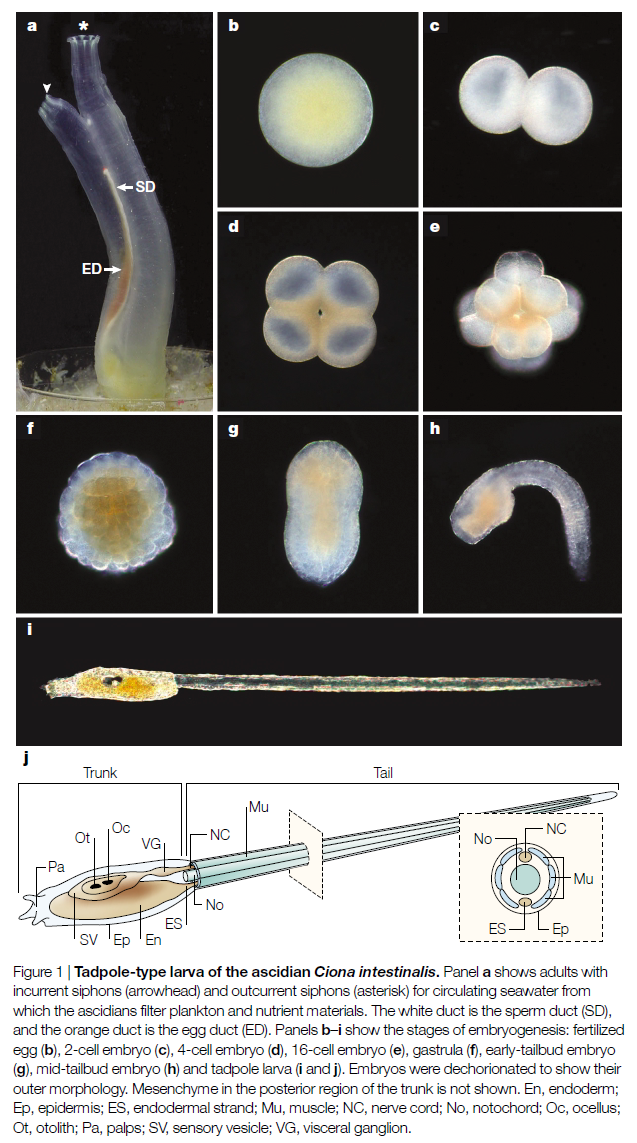
Ciona intestinalis на разных стадиях развития:[2]
|
Информация о сборке генома:
| Название | KH |
| RefSeq AC | GCF_000224145.3 |
| Уровень сборки | Chromosome |
| Общая длина последовательности | 115227301 bp |
| Число контигов | 6381 |
| N50 контигов | 37096 bp |
| L50 контигов | 875 |
| Число скэффолдов | 1280 |
| N50 скэффолдов | 3102162 bp |
| L50 скэффолдов | 12 |
| Число аннотированных белков | 21099 |
| Состав генома |
14 линейных хромосом и 1 кольцевая мтДНК |
| Проект BioProject |
PRJDA65419
|
| Последовательность одного контига из сборки |
Контиг 7
|
Комментарий: В NCBI Genome для вида C. intestinales находятся
2 сборки генома, вторая имеет уровень сборки Scaffold.
В записи BioProject, относящейся к данной сборке, находятся ссылки на 4
публикации, 2 из которых относятся к созданию сборки: Gissi et al. (2004) -
секвенирование и сборка митогенома, Satou et al. (2008) - получение описываемой
версии сборки генома.
Запись Whole Genome Shotgun найдена на странице выбранной сборки в поле
WGS Project, список контигов находится в записи по ссылке в поле WGS.
|
|
CDS прокариотического вируса
Поиск полных геномов Myoviridae длиной 20-30 kbp:
Поиск производился в NCBI Nucleotide. В окне Nucleotide Advanced Search
Builder с помощью билдера был построен запрос:
((Myoviridae[Organism]) AND 20000:30000[Sequence Length]) AND complete genome[Text Word]
По этому запросу найдено 7 записей в GenBank и 5 записей в RefSeq
(отображается в поле Source databases).
Информация о геноме Salmonella phage SEN1:
| AC | KT630644 |
| Название вируса | Salmonella phage SEN1 |
| TaxID | 1647455 |
| Тип генома[3] | dsDNA (I класс по Балтимору), кольцевая молекула |
| Хозяин вируса | Бактерия рода Salmonella |
| Последовательности, кодирующие белки |
CDS |
Комментарий: для скачивания CDS на странице записи полного генома жмётся
кнопка Send to:, ставится флажок Coding sequence в окне Formate
FASTA Nucleotide; поскольку файл скачивается только в формате txt,
пришлось переводить его в fasta.
|
Ключи используемые в Feature table
-
Ключ centromere обозначает участок последовательности экспериментально
определённый как центромера - участок хромосомы, на котором собирается
кинетохор и остаётся после профазы когезиновый комплекс, удерживающий
сестринские хромосомы.
Пример из записи полной последовательности центромерного мобильного элемента
подсолнуха Helianthus annuus (GenBank AC LC075745); знаки в поле
Location/Qualifiers означают, что центромерный участок начинается и
заканчивается за пределами последовательности данной записи:
centromere <1..>4149
-
Ключ D-loop обозначает участок последовательности с D-петлёй (displacement
loop) - структуру, характерная для мтДНК и эукариотических теломер, в которой
одна из цепей двуцепочечной ДНК вытесняется третьей
одиночной цепью и образует несвязанную одноцепочечную петлю.
Пример из записи полной последовательности мтДНК паразитиформного
клеща Metaseiulus occidentalis (GenBank AC EF221760):
D-loop 9577..9887
/note="control region"
-
Ключ transit_peptide обозначает участок последовательности, кодирующий
транзитный пептид - N-концевую последовательность белка, обеспечивающую
его транспорт через внешнюю и внутреннюю мембраны митохондрии или пластиды
и отрезающуюся в матриксе соответствующей эндосимбиотической органеллы.
Пример из записи последовательности мРНК митоходриального фермента NAD-малат
дегидрогеназы табака Nicotiana tabacum (GenBank AC AJ006974):
transit_peptide 13..287
-
Ключ mobile_element обозначает участок последовательности, содержащий
мобильный элемент.
Пример из записи полной последовательности F-плазмиды бактерии
Escherichia coli штамма K12 (GenBank AC AP001918); интересно,
что в широком понимании термин "мобильный элемент" включает в себя
так же и сами переносимые плазмиды, но ключ mobile_element, естественно,
их не описывает:
mobile_element 1..1258
/mobile_element_type="insertion sequence:IS3a"
-
Ключ oriT обозначает участок последовательности кон'югационной плазмиды
бактерии, в котором релаксосома делает разрыв во время кон'югации для
переноса одноцепочечной копии плазмиды в клетку бактерии- или
эукариота-реципиента.
Пример из записи последовательности Ti-плазмиды pTiBo542 клубеньковой
бактерии Agrobacterium tumefaciens (RefSeq AC NC_010929):
oriT 213650..213663
/note="origin of transfer"
-
Ключ rep_origin обозначает участок последовательности, на котором происходит
начало репликации нуклеоида, хромосомы или плазмиды.
Пример из записи последовательности полного генома галобактерии
Haloquadratum walsbyi штамма C23 (GenBank AC FR746099):
rep_origin 49..303
/note="repeat-bounded region indicating the replication
origin"
-
Ключ tmRNA обозначает участок последовательности, кодирующей
транспортно-матричную РНК, особую РНК бактерий (имеющуюся также в митохондриях
якобид и оомицетов и часто встречающуюся в пластидах), позволяющую освободить
рибосому, застрявшую на мРНК с утраченным стоп-кодоном, и продолжить трансляцию
белка со своей собственной последовательности, кодирующий пептидный сигнал к
деградации полученного белка.
Пример из записи полной последовательности мтДНК якобиды Jakoba libera
штамма ATCC 50422 (GenBank AC KC353355):
tmRNA complement(67265..67390)
/gene="ssrA"
|
Ссылки
-
Ciona intestinalis - Wikipedia
-
Satoh, N. (2003) The ascidian tadpole larva:
comparative molecular development and genomics
-
ICTV - Myoviridae
|
|
|
