Ниже по ссылкам доступны последовательности РНК, с которой я работал (последовательность получена по идентификатору в PDB):
РНКПо результатам работы программы einverted (команда ! einverted -sequence rna.seq -gap 12 -threshold 10 -match 3 -mismat ch -3 -outfile outfile -outseq seqout) и алгоритму Зукера составлена таблица по определённым участкам структуры моей тРНК:
| Участок структуры | позиции в структуре (find pair) | предсказание einverted | предсказание по Зукеру |
|---|---|---|---|
| акцепторный стебель | 1-7 72-66 |
- | 1-7 72-66 |
| D-стебель | 10-13 25-22 |
- | - |
| T-стебель | 49-53 65-61 |
49-53 65-61 |
- |
| антикодоновый стебель | 40-44 30-26 |
39-48 31-22 |
- |
| общее число канонических пар нуклеотидов | 21 | 15 | 18 |
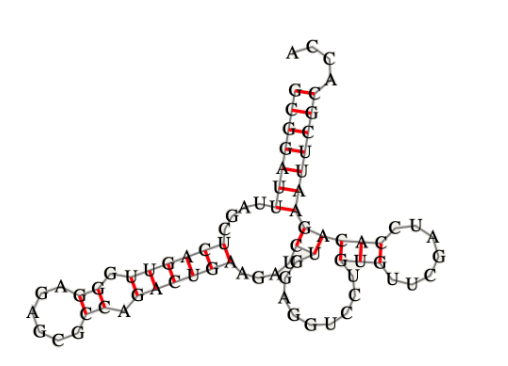
А на рисунке1 изображена структура тРНК, полученная программой ViennaRNA:

Скрипт для опредления множеств
Скрипт с паузами для отображения
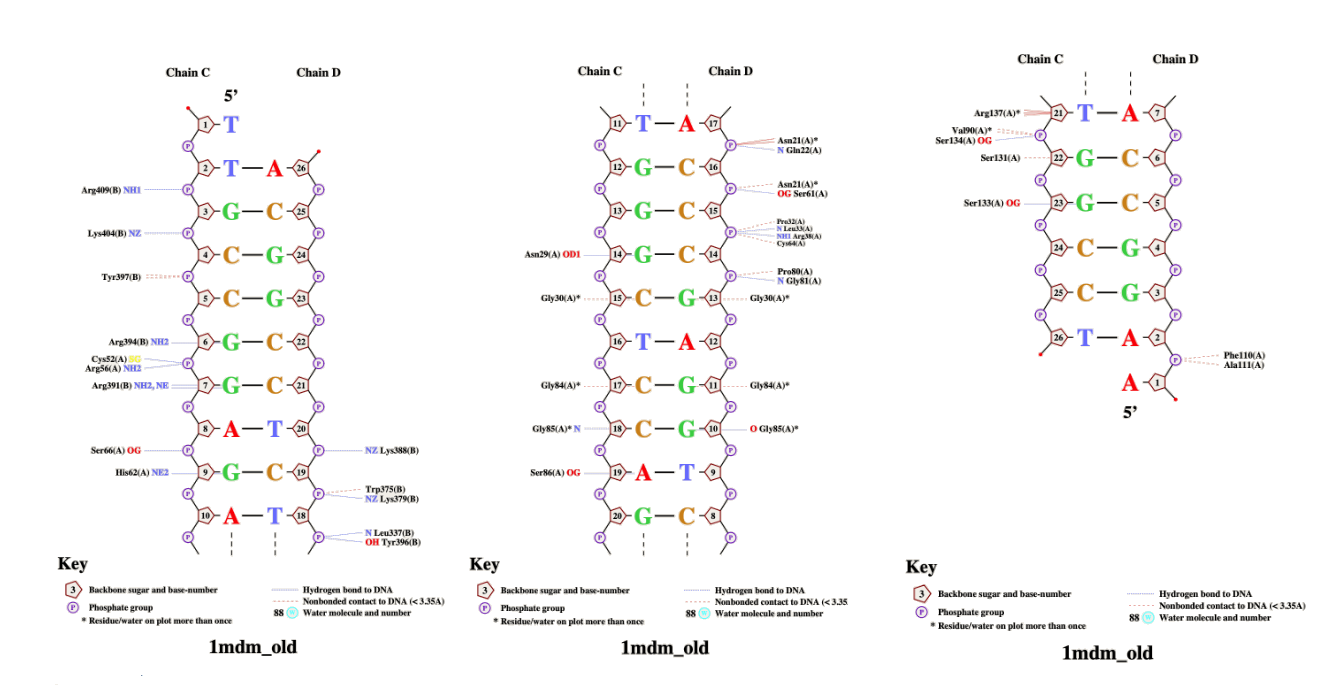
В таблице ниже указана информация об атомах белка, контактирующих с нуклеиновой кислотой (структура 1mdm из PDB):
| С чем контактируют атомы белка | полярные | неполярные | все |
|---|---|---|---|
| остатки 2'-дезоксирибозы | 3 | 13 | 16 |
| фосфаты | 9 | 6 | 15 |
| азотистые основания со стороны большой бороздки | 4 | 10 | 14 |
| азотистые основания со стороны малой бороздки | 0 | 1 | 1 |
Неполярных контактов оказалось значительно больше. Почти нет атомов, контактирующих с НК со стороны малой бороздки.
На рисунке2 показан результат работы программы nucplot для комплекса 1mdm:
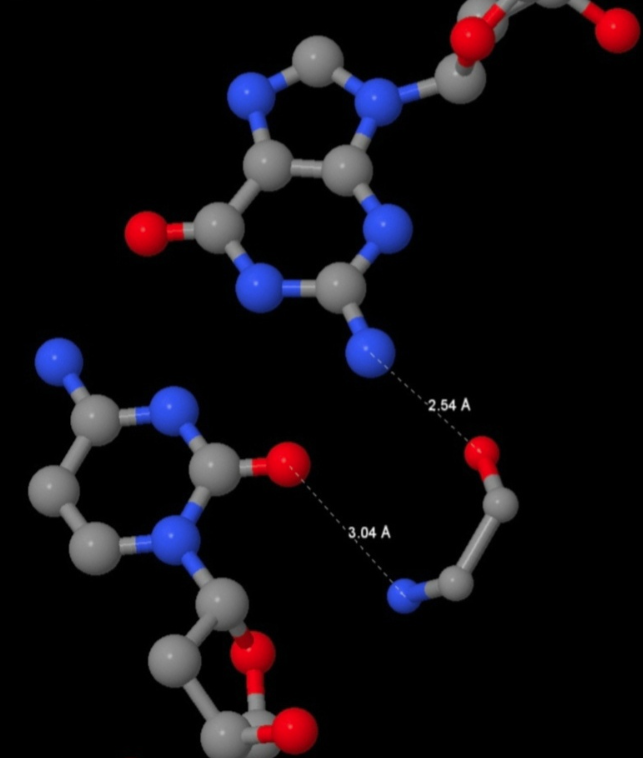
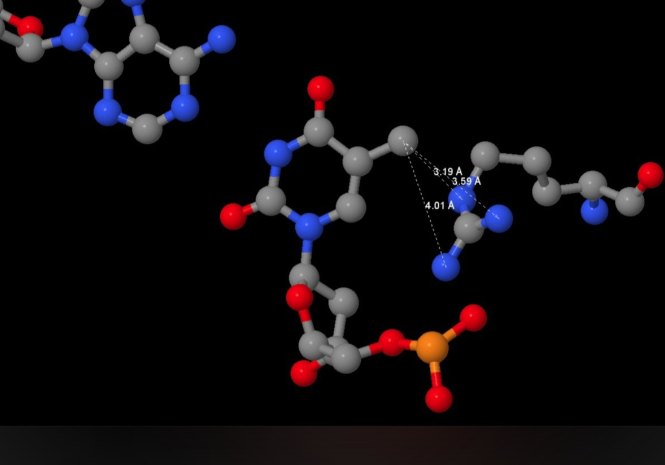
На двух какртинках ниже изображены две структуры, полученные с помощью Jmol для отображения контактов двух аминокислот с НК: