Все ниже описанное можно посмотреть
в файле UPGMA.xls
Для построения дерева для эталонного выравнивания
была получена попарных совпадений последовательностей в этом выравнивании.
На основании этой матрицы была построена матрица "наивных" эволюционных расстояний.
Полученная матрица была использована для построения ультраметрического филогенетического
дерева по методу UPGMA (Unweighted Pair Group Method with Arithmetic Mean). В результате
выполнения алгоритма, предусмотренного этим методом получили правильную скобочную
структуру дерева:
(((HEMN_BRAJA:0.305, HEMN_AQUAE:0.305):0.1235, YQEV_BACSU:0.4275):0.013125, (MOAA_BACSU:0.425, BIOB_YEAST:0.425):0.015625);
Скобочная структура, полученная выше, была визуализована с помощью программ из Online-версии пакета Phylip: drawtree и drawgram. Все параметры были приняты по умолчанию.
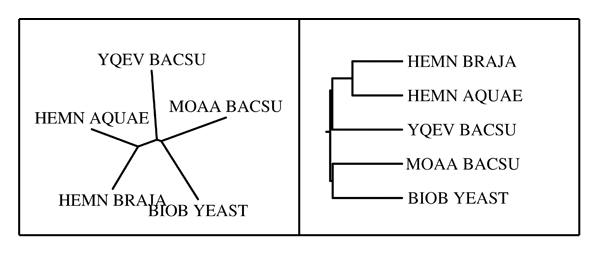
Эталонное выравнивания домена Eps3 перевели в fasta формат, а затем с помощью программы emma (програмный пакет EMBOSS) построили множественное выравнивания. Из файла руководящего дерева взяли правильную скобочную структуру:
((MOAA_BACSU:0.40986,BIOB_YEAST:0.42824):0.02273,(HEMN_BRAJA:0.31194,HEMN_AQUAE:0.29166):0.13981,YQEV_BACSU:0.41227);
Эта скобочная структура была визуализована теми же программами, что и в предыдущем пункте.
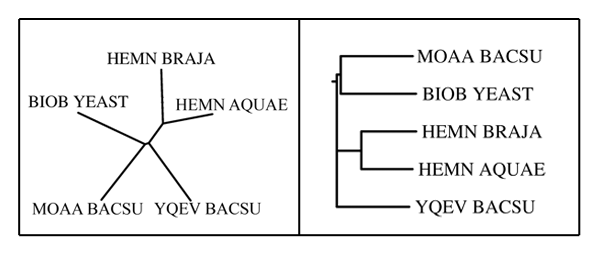
Неукорененное дерево - слева, укорененное - справа.
Итак сравнивания изображения, полученные с помощью разных алгоритмов
следует заметить, что неукоренненые деревья получились
одинаковыми. Укоренненые деревья несколько отличаются. Тем не менее
они отражают почти одинаковый сценарий эволюции.