Банки нуклеотидных последовательностей
1. Нуклеотидная последовательность, секвенированная на ББС
Поиск
Поскольку ставилась цель найти хотя бы одну подходящую последовательность, продвинутые возможности поиска использовать не было необходимости, хватило протого текстовго запроса "WSBS MSU" в базе Nucleotide. По этому запросу находится 170 записей, многие из которых содержат информацию о генах гидромедуз Sarsia и получены в ходе выполнения той же работы, что рассматривается ниже. Однако, хотя по первым страницам поиска и может сложиться обратное впечатление, ими выдача не исчерпывается и содержит также записи минимум о десяти различных родах.
ББС?
В качестве примера выбрана запись с AC в GenBank MN240289. В описании не указано, откуда брались и где секвенировались образцы, но эту информацию можно найти в статье, ссылка на которую находится в поле reference.
Andrey A Prudkovsky, Irina A Ekimova, Tatiana V Neretina. A case of nascent speciation: unique polymorphism of gonophores within hydrozoan Sarsia lovenii, Sci Rep. 2019; 9: 15567. doi: 10.1038/s41598-019-52026-7 [PMC], раздел "Материалы и методы":
Medusae and hydroids of Sarsia spp. (39 specimens) were collected near the White Sea Biological Station (WSBS) in Kandalaksha Bay (66°34′N, 33°08′E).
(...)
Additional material (13 specimens) was collected at WSBS from a flow-in aquarium system with free input of water from the sea or from a closed aquarium system.
(...)
The products were resuspended in 12 μL of formamide and subjected to electrophoresis in an ABI Prism 3500 Genetic Analyzer (Applied Biosystems) at the N.K. Koltsov Institute of Developmental Biology (Moscow, Russia) or the N.A. Pertsov White Sea Biological Station MSU (Primorsky, Russia).
Конечно, по этим цитатам нельзя понять, была ли данная последовательность отсеквенирована именно на ББС, а не в ИБР РАН, но, думаю, это не имеет решающего значения для данного задания.
Описание последовательности
Это последовательность ДНК, секвенированный участок имеет длину 503 нуклеотида и содержит: участок первого внутреннего транскрибируемого спейсера (ITS), полностью ген 5.8S рРНК и второй транскрибируемый спейсер, участок рРНК большой субъединицы (28S).
Добавлена 24.04.2020, автор записи Prudkovsky,A.
Последовательность в формате fasta.
Гидроидная медуза Sarsia lovenii, которой принадлежит этот фрагмент ДНК, обитает в Белом море.
В статье изучался полиморфизм ITS1, ITS2, а также некоторых митохондриальных генов, и было показано, что этот генетический полиморфизм связан с фенотипическим - двумя видами гонофоров: свободно плавающие медузы или прикреплённые медузоиды. Хотя эти два гаплотипа свободно скрещиваются в экспериментальных условиях, в природе такие скрещивания происходят редко и найденные авторами различия могут быть интерпретированы как зарождение двух отдельных видов.
2. Качество сборки генома эукариотического организма
Рассматривался геном трихоплакса, Trichoplax adhaerens.
Трихоплакс является самым известным представителем типа Placozoa, одним из двух кандидатов (наравне с губками) на звание самого примитивного типа многоклеточных животных. Однако данные генома заставляют предположить, что это вторичное упрощение.
Представляет собой трёхслойную пластинку из клеток четырёх типов. Питается водрослями, цианобактериями и другими пищевыми частицами, поглощая наиболее мелкие из них путём фагоцитоза, а крупные переваривая внеклеточно, сформировав поверхностью тела своеобразный замкнутый карман вокруг пищи. Обитает на мелководьях теплых морей. Может размножаться фрагментацией пластинки и почкованием, половое размножение предполагается, но достоверного описания нет.
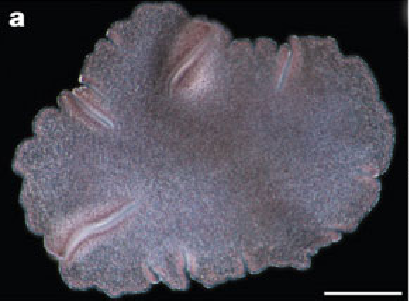
| "уровень сборки" | Scaffold |
|---|---|
| общая длина | 105,631,681 |
| контигов | 3,217 |
| скэффолдов | 1,414 |
| N50 (скэффолды) | 5,978,658 |
| L50 (скэффолды) | 6 |
| N50 (контиги) | 204,191 |
| L50 (контиги) | 132 |
| аннотированных белков | не указано |
В NCBI Genome находятся две сборки генома трихоплакса, лучшая из них - с RefSeq ID GCF_000150275.1. Характеристики указаны в таблице слева.
Статья: Srivastava,M., Begovic,E. et al. The Trichoplax genome and the nature of placozoans, Nature 454 (7207), 955-960 (2008) [PubMed ]
Последовательность одного контига в формате fasta. Для нахождения этой последовательности я перешла по ссылке WDS в описании сборки, перешла к разделу с контигами и скачала первый из них.
3. Список полных геномов SARS-CoV-2
Поисковой запрос: "SARS-CoV-2" (и выбор выпадающего организма) в поле Virus базы NCBI Viruses.
Находок с полным геномом 18870 (таблица). Из них в RefSeq только одна, она и была выбрана для следующего задания.
4. Последовательности CDS одного генома коронавируса
| AC | NC_045512 |
|---|---|
| название вида | Severe acute respiratory syndrome coronavirus 2 |
| TaxID | 2697049 |
| тип генома | линейная одноцепочечная РНК |
| хозяин вируса | Homo sapiens |
Fasta-файл с CDS.
Получение: на страницу генома в Nucleotide > Send to > Coding Sequences > Format = FASTA Nucleotide > Create file