
|
|
|
|
Занятие 5. Ферменты и метаболические пути. База данных KEGG. Для выполнения задания я выбрала метаболизм инозитолфосфата(ссылка на карту метаболического пути), реакцию R09827 (отщеления остатка фосфорной кислоты от одного из участников метаболического пути). Ее катализует 2 ортологических ряда белков:
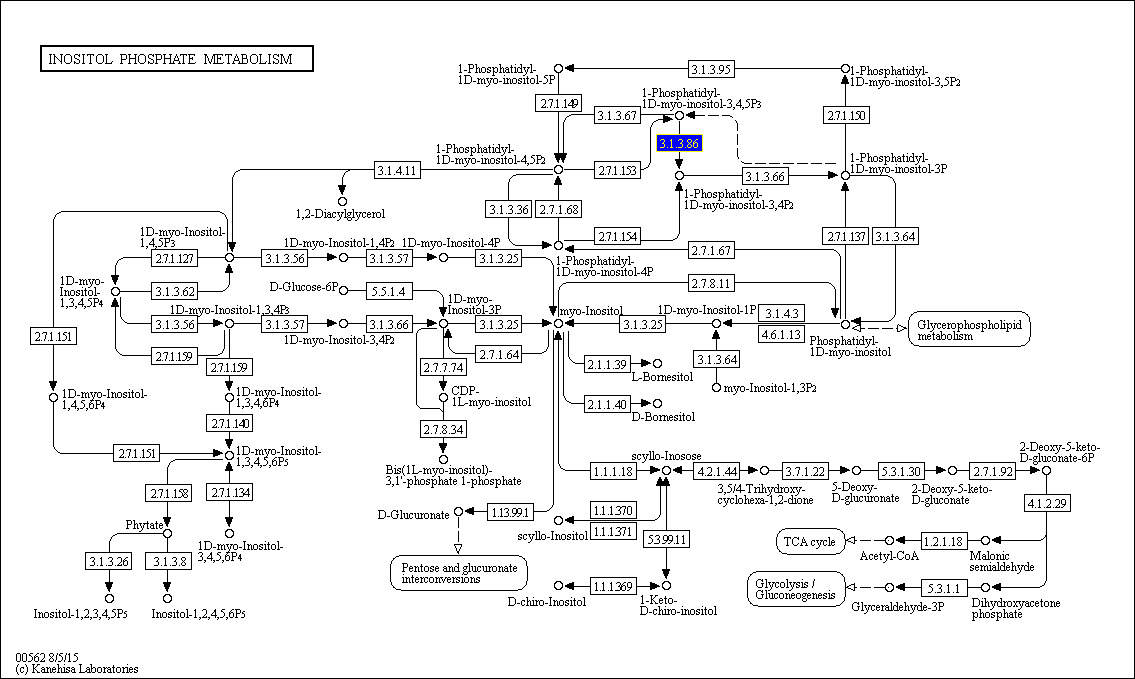
Рисунок 1. Карта метаболического пути инозитолфосфата Из базы Uniprot я получила последвательности всех белков по двум ортологическим рядам(использовала сервис Retrieve/ID mapping), и построила выравнивание с помощью программы muscle, установленной на kodomo(с настройками по умолчанию): файл с выравниванием. Чтобы проанализировать гомологичность белков в выравнивании, я открыла файл в программе Jalview(файл с проектом*, раскраска атомов Clustalx). *окошко v1 в проекте соответсвует исходному выравниванию, v2 - выравниванию с удаленными лишними последовательностями. Гомологичность белков в выравнивании Итак, выровнены ли между собой последовательности? По моему мнению, да, множественное выравнивание существует. Заметны большие блоки по всей "высоте" выравнивания. Участок с 622 по 900 выровнялся несколько лучше других, концевой участок хуже(можно предположить, что конец отвечает не за выполнение общих для этих ортологов функций, а более специфичен для разных групп организмов). Некоторые белки заметно короче других, и выровнялись только по отдельным блокам. Далее я привожу более подробный анализ выравнивания. Проверка выравнивания Некоторые белки в выравнивании, как я уже говорила, короче других. Рассмотрим белок W7XCC6_TETTS из ортологического ряда K03084. Длина этого белка - 510 аминокислотных остатков, а остальных белков, в среднем, раза в два больше. Начиная с 950 позиции в выравнивании, строчка этого белка - один сплошной гэп. Я думаю, его можно удалить. Еще один плохой белок - T1FTN2_HELRO из ряда K15909 длиной 472 а.о. Белок A0A067CTV9_SAPPC(582 а.о.) из того же ряда хотя и имеет меньше гэпов в центральных блоках, но все равно выровнялся плохо, удаляю. Очень сложно сказать, насколько плохими должны быть белки, ведь они могут иметь гэпы в начале и конце выравнивания, но хорошо попадать в блоки, отвечающие, похоже, центральным доменам. Все-таки удаляю еще белки F4Q584_DICFS из K03084 и L8H4T3_ACACA, L8HGG6_ACACA из К15909. Они совсем плохо выровнялись на участках до приблизительно 350 а.о. и с 1100 а.о. и имеют маленькую длину. Теперь можно строить дерево. 
Рис.2 Дерево, построенное прогарммой MEGA по выравниванию белков из разных ортологических рядов Дерево разделяется на клады, соответствующие отдельным ортологическим рядам. У ветви, отделяющей две клады друг от друга бутстрэп-поддержка равна 100% - очевидно, что ветвь достоверна. По длине заметно выделяются ветви F2UGC2_SALR5|K15909 и L8H092_ACACA|K15909. Последняя из них мне не нравилась еще при удалении последовательностей - очень большие гэпы в выравнивании до 362 позиции. Ветвь SALR5 не выглядит сильно отличающейся от остальных, на мой взгляд. |
|
© Шугаева Т.Е. 2016