Практикум 3
1. Реконструкция дерева по нуклеотидным последовательностям
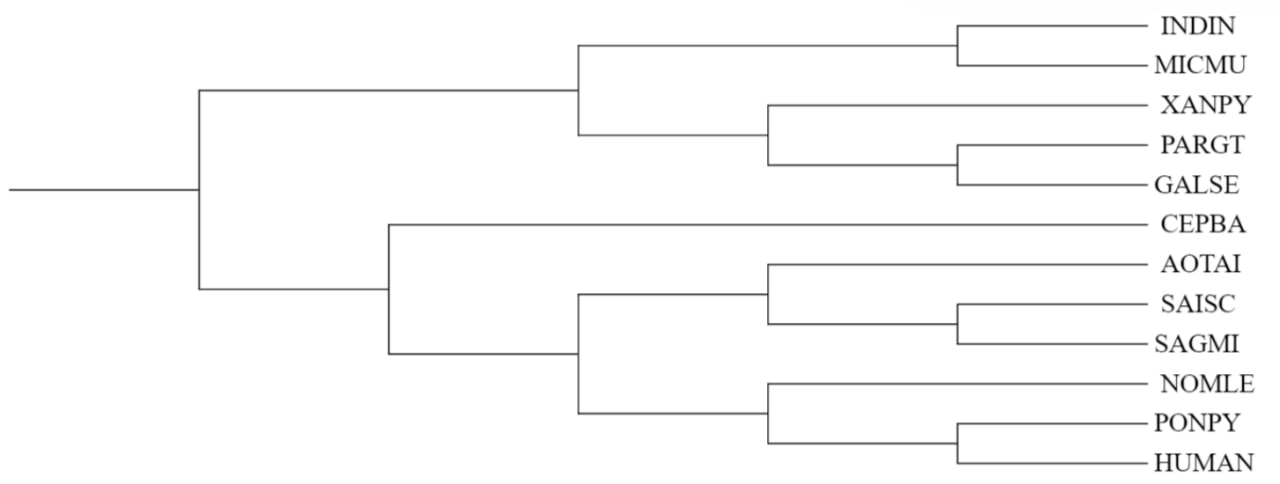

К сожалению, у двух обезьян (CEBPA PARGT) не было последовательностей митохондриального генома или отдельно 12S, поэтому они из дерева исключились. В отличие от дерева на рисунке 1, AOTAI сестринская для SAISC, а не для клады SAGMI+SAISC, забавно, что в дереве построенном по цитохрому В (см. прак 2) AOTAI сестринская для SAGMI.
2. Укоренение во внешнюю группу

В качестве аутгруппы была взята кошка (Felis catus), дерево было построено по последовательностям цитохрома В.
В отличие от дерева на рисунке 1, AOTAI сестринская для SAGMI, а не для клады SAGMI+SAISC (как и на деревьях из практикума 2). Также переместилась группа CEPBA, стала базальной для всех остальных обезьян.
3. Бутстреп
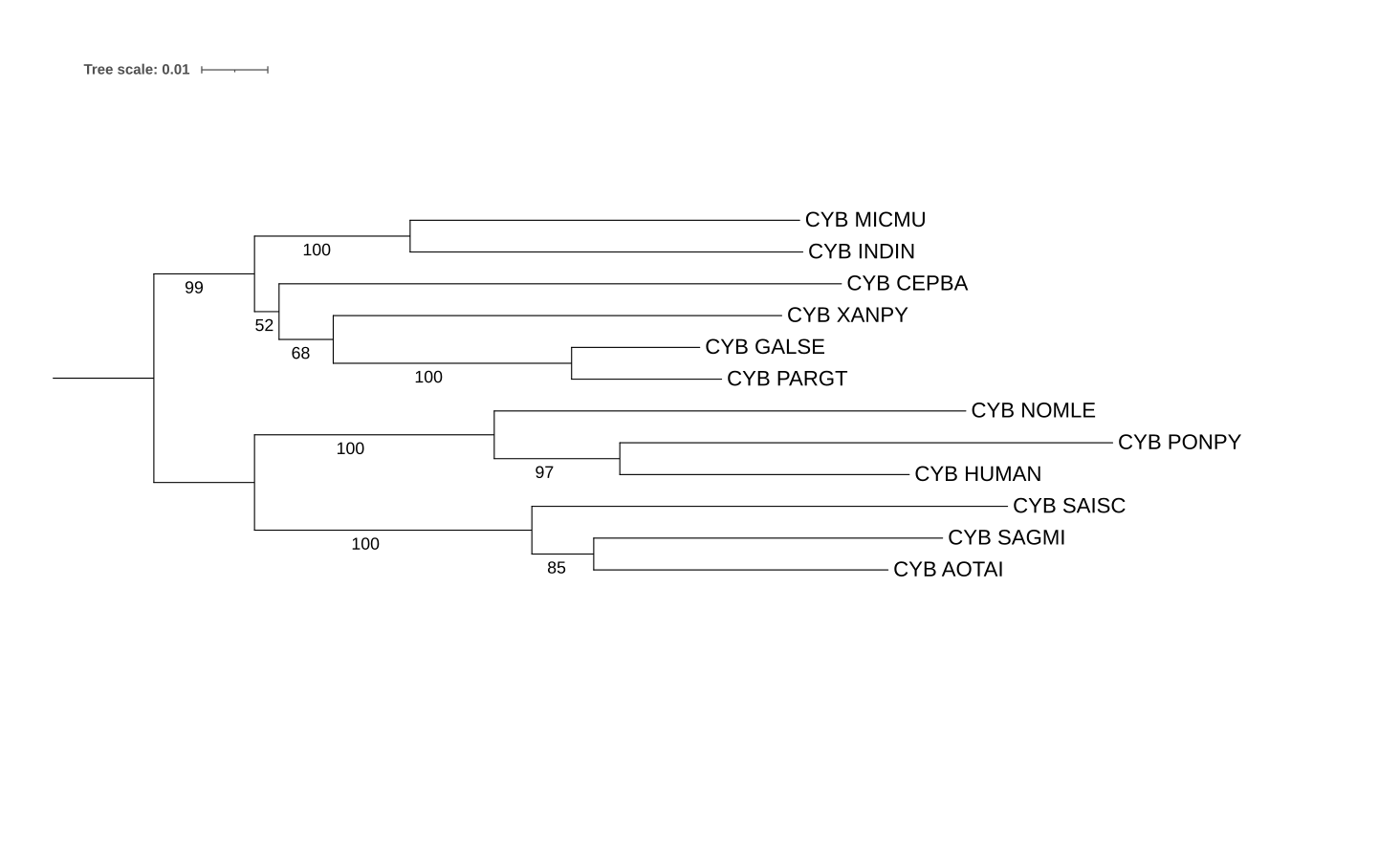
Cамое число поддержки имеет ветвь, несущая клады CEPBA и ((GALSE, PARGT),XANPY), это логично, так как группа CEPBA на разных предыдущих деревьях оказывалась в разных местах (учитывая, что у данного таксона нет секвенированного полного митохондриального генома, возможно не хватает данных для полного понимания нахождения этого таксона на филогенетическом дереве).
Также небольшое число поддержки имеет клада ((GALSE, PARGT),XANPY), чего я не могу объяснить, так как на всех деревьях, включая дерево по таксономии, эта клада воспроизводится.
Клада (SAGMI, AOTAI) имеет число поддержки 85, что так соотносится с разным положением этих групп на других деревьях (на дереве по таксономии клада имеет вид: ((SAISC,SAGMI),AOTAI).)