|
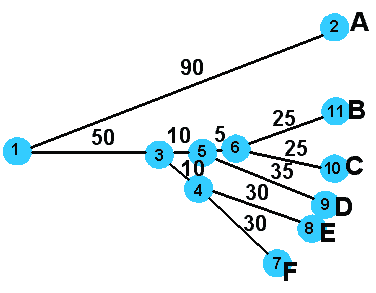
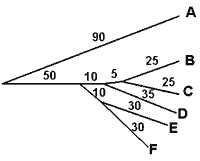
Скобочная структура дерева (число мутаций на 100 п.н.) |
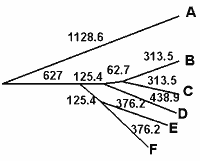
Скобочная структура дерева (число мутаций на всю последовательность) |
|
( A:90, ( ((B:25,C:25):10, D:35):5, (E:30, F:30):10):50 ); |
( A:1128.6, ( ((B:313.5,C:313.5):125.4, D:438.9):62.7, (E:376.2, F:376.2):125.4):627 ); |
| Соответствующее дерево | Соответствующее дерево |
 |
 |