Практикум 8.
Задание1
Из БД Pfam был выбран домен PF05187, его выравнивание seed содержит 38 последовательностей. По ссылке можно скачать это выравнивание.
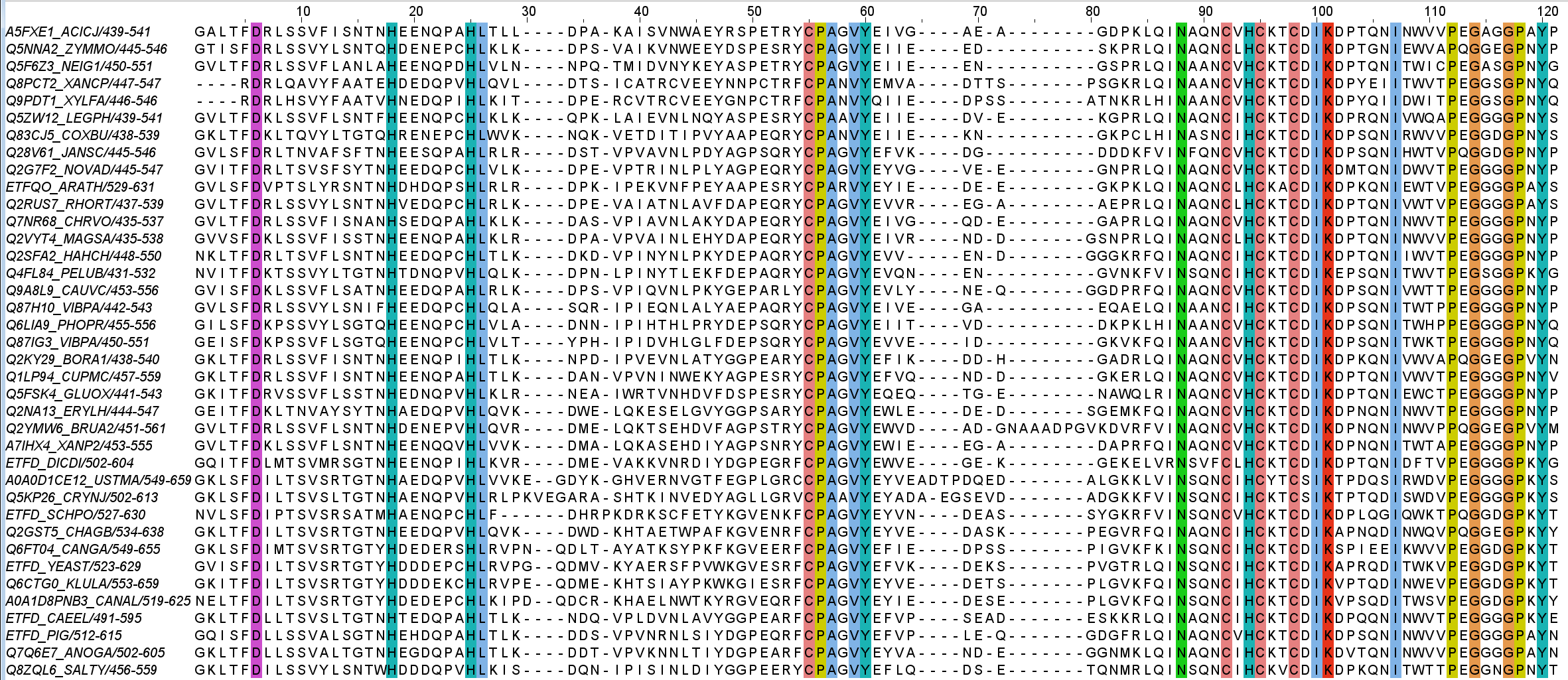
При пороге Identity Treshold, равном 100%, нашлось несколько консервативных мотивов, я выбрала один из них(Рис.1). Был cостававлен паттерн, описывающий этот мотив: CPA.VY.
(в выравнивании по нему нашлось 38 последовательностей).
Поиск по этому мотиву в базе данных SwissProt на сайте MyHits выдал 31 находку, при чем все они из они семейства.
Результаты выполнения задания также можно увидеть в файле.
Задание 2
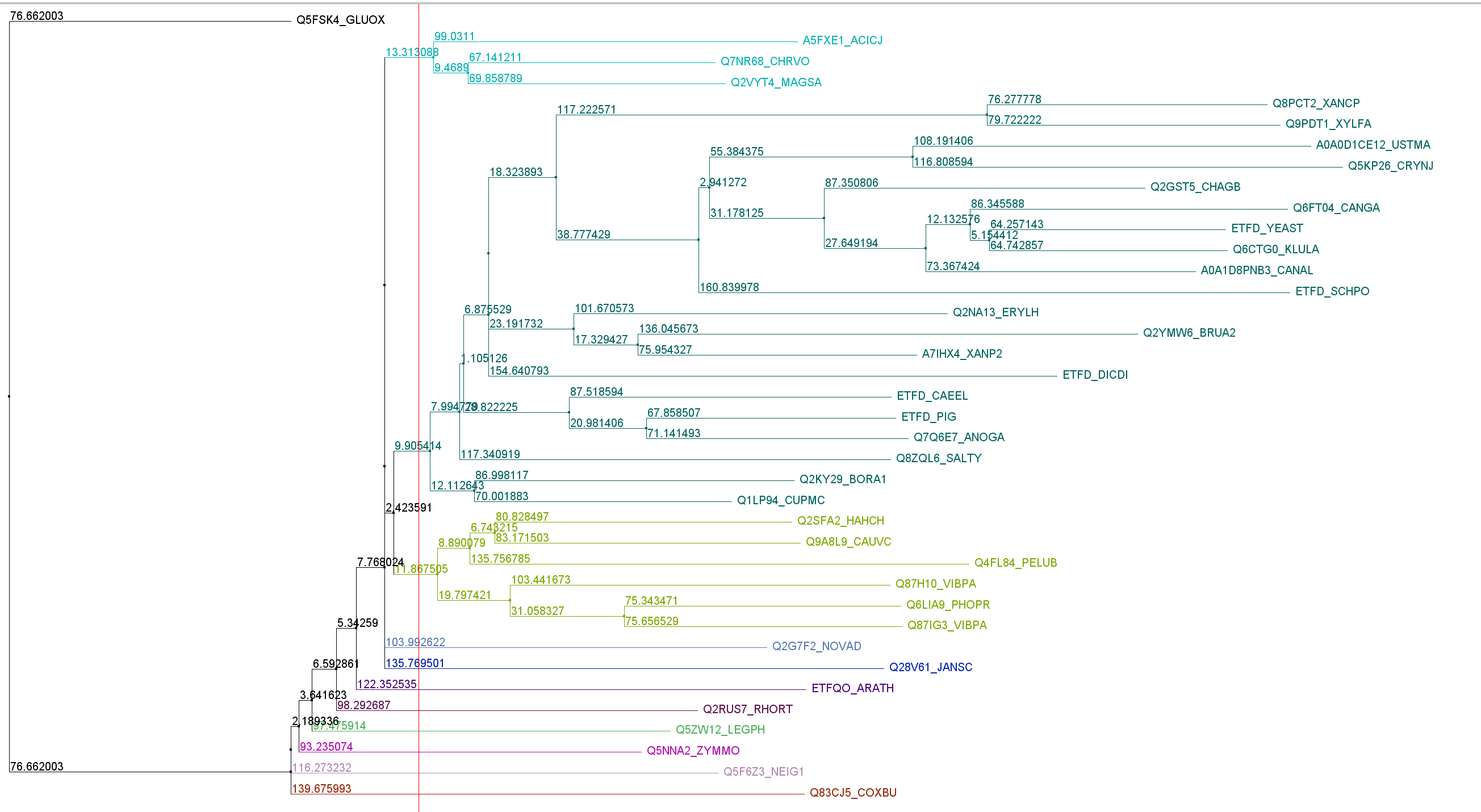
В Jalview было построено филогенетическое дерево методом NJ(Рис.2). Была выбрана клада (на рисунке обозначена голубым цветом), ее выравнивание было перенесено в отдельное окно. Был найден консервативный мотив в этой кладе( его паттерн: Y.{2}PE.RYCPAGVYEIV), во всем выравнивание он встречается 3 раза(как раз таки вся эта выбранная клада). Следовательно, данный мотив встречается лишь в рамках выбранной группы, что говорит о его специфичности для выбранной клады.
Задание 3
Был выбран белок Q7VDL2. Он находится бактерии Prochlorococcus marinus и является ингибитором клеточного деления.
| Идентификатор белка | Q7VDL2 | ||||
|---|---|---|---|---|---|
| Номер итерации | Число находок выше порога (0,005) | Идентификатор худшей находки выше порога | E-value этой находки | Идентификатор лучшей находки ниже порога | E-value этой находки |
| 1 | 146 | Q9AG20.1 | 0.005 | A8GFG7.1 | 0.005 |
| 2 | 188 | B6JKX0.1 | 7e-08 | - | - |
| 3 | 188 | Q9ZM51.1 | 2,00E-12 | A7H8E6.1 | 0.014 |
После третьей итерации число находок, проходящее порог в 0.005 E-VALUE, перестало меняться.Это говорит о высоком сходстве белков выбранного семейства.
Задание 4
Для выполнения задания был выбран геном бактерии Staphylococcus hominis(strain FDAARGOS_575), ее хромосома с локусом CP033732 и длиной 2220494 нуклеотидов. Ожидаемое число TA в геноме равно 259333.14866736863. Реальное число TA в геноме равно 224913. P-value 0.101, это скорее всего является статистичеси занчимым