Обзор особенностей генома бактерии
Listeria innocua Clip11262
АННОТАЦИЯ
В данном обзоре представлен анализ организации генома бактерии Listeria innocua Clip11262. В работе проанализированы такие характеристики генома, как распределение длин кодируемых белков, расстояний между CDS, а также типов генов и их распределения по цепям ДНК на хромосоме и плазмиде.
ВВЕДЕНИЕ
Listeria innocua Clip11262 - грамположительная, факультативно-анаэробная бактерия, выделенная из пищевых продуктов и окружающей среды [1]. Как и для всего рода Listeria, для Listeria innocua характерна устойчивость к ряду неблагоприятных условий, включая способность расти при низких температурах (до 0°C), высоких концентрациях соли и широком диапазоне pH [2]. Ключевой особенностью Listeria innocua Clip11262 является ее тесная генетическая связь с патогенным видом Listeria monocytogenes , при этом сам штамм Clip11262 считается непатогенным, поэтому его используют для сравнительных геномных исследований с целью выявления факторов вирулентности у патогенных видов рода Listeria [3].
Систематическое положение Listeria innocua Clip11262 [4]:
Домен : Bacteria
Царство : Bacillati
Домен : Bacteria
Тип : Bacillota
Класс : Bacilli
Порядок : Bacillales
Семейство : Listeriaceae
Род : Listeria
Вид : Listeria innocua
РЕЗУЛЬТАТЫ И ОБСУЖДЕНИЕ
Длины белков, закодированных в геноме Listeria innocua Clip11262
Распределение длин белков, закодированных в геноме бактерии Listeria inoccua Clip11262 представлено на гистограмме (рис.1.)
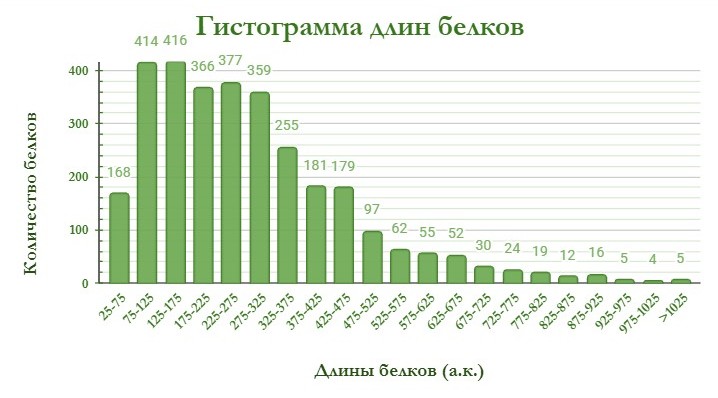
Белки с длинами в интервалах 75-125 а.к. и 125-175 а.к. встречаются с приблизительно равной частотой. Также в области 175-325 а.к. три столбца демонстрируют сопоставимые значения частоты. Далее с увеличением длины белков постепенно уменьшается их количество. 75% белков имеют длину 102-486 а.к. Минимальная длина белка - 25 а.к. Максимальная длина белка - 2167 а.к. Средняя длина белка - 294 а.к.
Анализ расстояний между последовательностями (CDS)
На рисунке 2 представлена гистограмма расстояний между кодирующими последовательностями на плюс-цепи самой большой хромосомы.
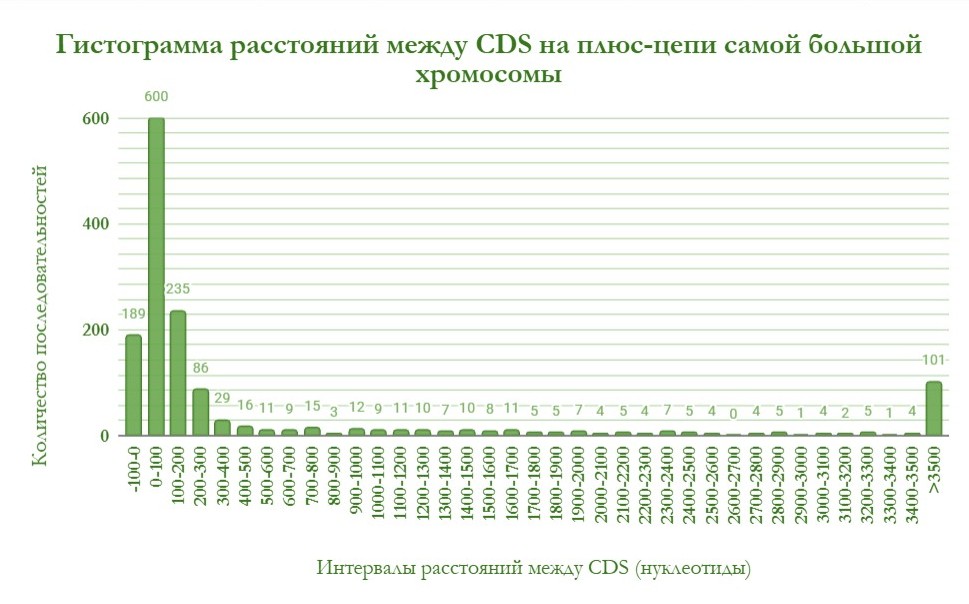
Наибольшее количество участков между генами имеет длину 0-100 нуклеотидов. Также расстояние между некоторыми последовательностями отрицательное, что свидетельствует о перекрывании их рамок считывания.
Анализ структурной организации генома
На рисунках 3 и 4 представлены диаграммы генов, кодирующих белки и разные типы РНК, на хромосоме и плазмиде соответственно.
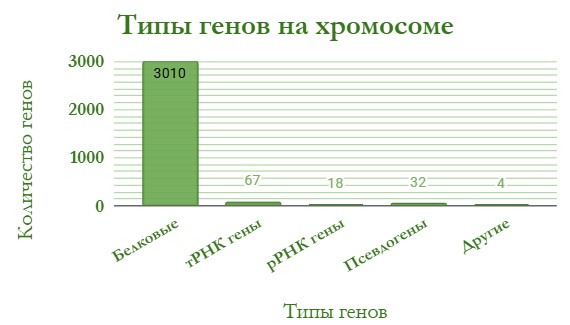
Наблюдается преобладание генов, кодирующих белки, что свидетельствует о том, что основная генетическая функция данной хромосомы заключается в хранении информации для синтеза полипептидов. В значительно меньших количествах представлены гены, кодирующие тРНК, рРНК и псевдогены.
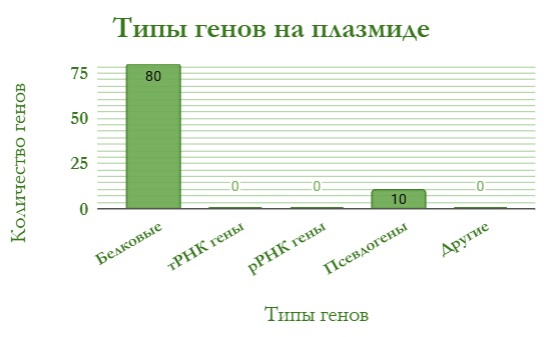
Общее количество генов в плазмиде на 3041 меньше, чем в хромосоме. Также, как и в хромосоме, наблюдается преобладание белок-кодирующих генов, присутствуют псевдогены. При этом в плазмиде отсутствуют гены, кодирующие тРНК и рРНК.
На рисунках 5 и 6 представлены диаграммы распределения генов на “+” и “-” цепи хромосомы и плазмиды соответственно.
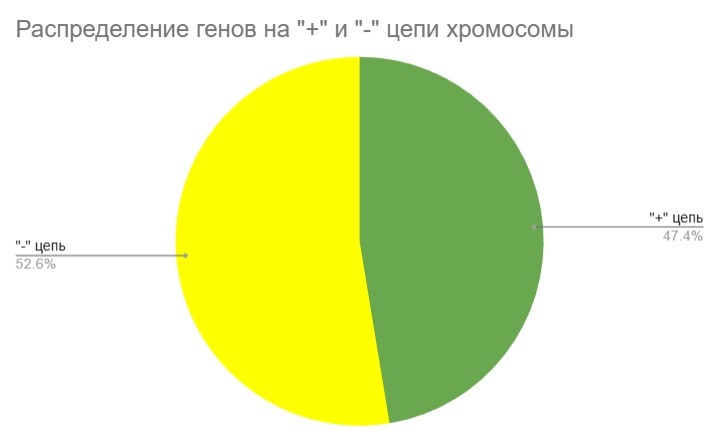
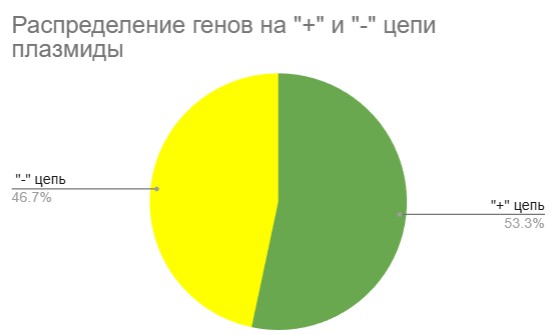
В обоих случаях распределение близко к равномерному, что указывает на то, что механизм транскрипции не отдает явного предпочтения ни "+", ни "-" цепи как матричной. При этом гены на хромосоме немного смещены в сторону "-" цепи (52.6% против 47.4%), а на плазмиде наблюдается обратная картина распределения: преобладают гены на “+” цепи (53.3% против 46.7%).
МАТЕРИАЛЫ И МЕТОДЫ
Для работы использовались геномная и протеомная последовательности исследуемой бактерии, полученные из базы данных Национального центра биотехнологической информации (NCBI) [4]. Статистический анализ и визуализация данных выполнялись с использованием электронных таблиц Google Sheets.
Для построения гистограммы длин белков использовалась таблица CDS from genome of Listeria innocua Clip11262 (см. таблицу S1 сопроводительных материалов, листы prot_lengths и prot_lengths_hist).
Для анализа расстояний между последовательностями (CDS) и структурной организации генома использовалась таблица Genomic features of Listeria innocua Clip11262 (см. таблицу S2 сопроводительных материалов, листы inter_cds_intervals-hist и genome )
ВОЗМОЖНЫЕ ДАЛЬНЕЙШИЕ ИССЛЕДОВАНИЯ
Перспективным направлением дальнейших исследований является сравнительный геномный анализ непатогенной бактерии Listeria innocua Clip11262 и патогенной Listeria monocytogenes . Например, можно выявить гены, присутствующие у патогена и отсутствующие у непатогенного вида.
СПИСОК ЛИТЕРАТУРЫ
1. Moura A. et al. Atypical hemolytic Listeria innocua isolates are virulent, albeit less than Listeria monocytogenes //Infection and immunity. – 2019. – Т. 87. – №. 4. – С. 10.1128/iai. 00758-18.
2. Orsi R. H., Wiedmann M. Characteristics and distribution of Listeria spp., including Listeria species newly described since 2009 //Applied microbiology and biotechnology. – 2016. – Т. 100. – №. 12. – С. 5273-5287.
3. Glaser P. et al. Comparative genomics of Listeria species //Science. – 2001. – Т. 294. – №. 5543. – С. 849-852.
4. NCBI Taxonomy: Listeria innocua Clip11262. NCBI:txid272626