Филогенетическая реконструкция
Подготовка последовательностей
Целью данного практикума является построение филогенетического дерева для сем. Оленевые (Cervidae),
основываясь на схожести аминокислотных последовательностей цитохрома B.
Для этого мы сперва подготовили текстовый файл cyb.list с идентификаторами последовательностей. Потом с помощью функционала EMBOSS скачали
записи из банка Swiss-Prot
seqret @cyb.list cyb.fasta
Далее выровняли полученные записи с помощью программы для множественного выравнивания muscle:
muscle -align cyb.fasta -output cyb-alignment.fasta
Использование программы FastME
Программа FastME работает только с выравниваниями в формате phylip-relaxed, поэтому был написан код для перевода данных в этот формат:
#!/usr/bin/env python3
from Bio import AlignIO
inh = open("cyb-alignment.fasta", "r")
outh = open("cyb.phy", "w")
alignment = AlignIO.parse(inh, "fasta")
AlignIO.write(alignment, outh, "phylip-relaxed")
inh.close()
outh.close()
После применения программы получили файл cyb.phy, который подали на вход программе fastme.
fastme -i cyb.phy -o cyb_p-dist_tree -pp
fastme -i cyb.phy -o cyb_MtREV_tree -pM
где: -i - название файла, подающегося на вход
-o - название файла, получаемого на выход
-pp - модель p-distance
-pM - модель MtREV

Рис. 1. Дерево, построенное программой fastme по аминокислотным последовательностям CYB, с помощью метода ME, оценивающее эволюционное расстояние с помощью модели p-distane, укорененное в Munmu
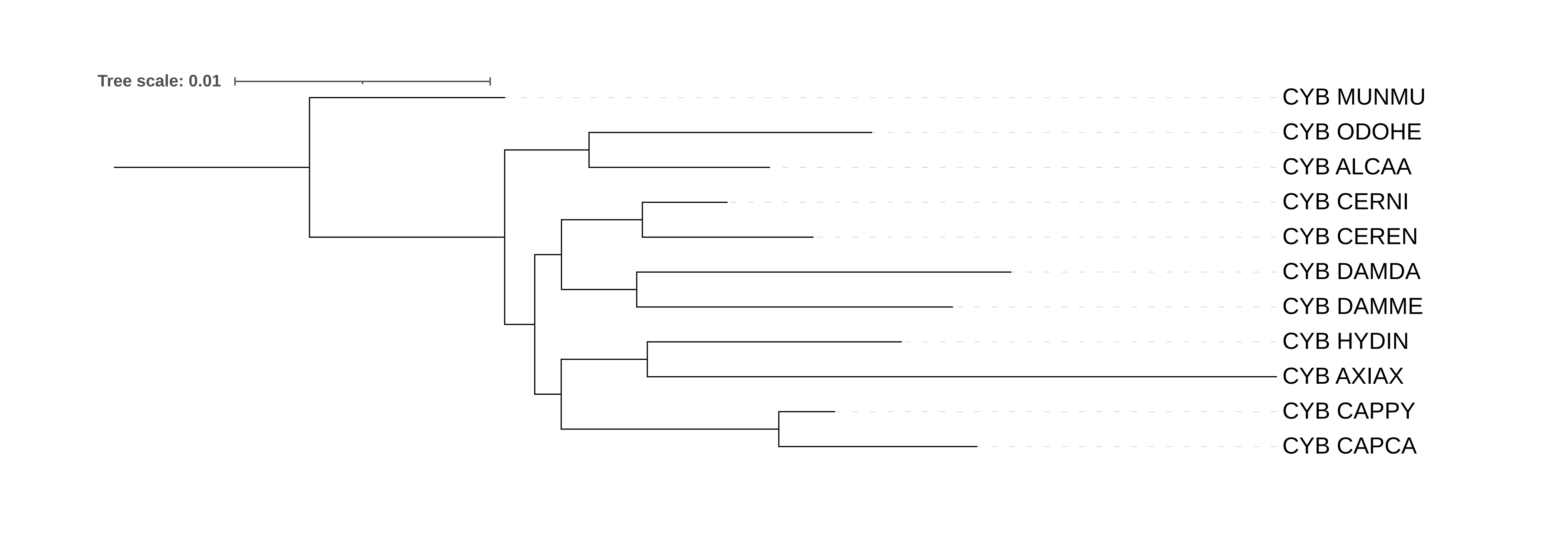
Рис. 2. Дерево, построенное программой fastme по аминокислотным последовательностям CYB, с помощью метода ME, оценивающее эволюционное расстояние с помощью модели MtREV, укорененное в Munmu
Использование программы IQ-Tree
Программа IQ-Tree была запущена с помощью кода:
iqtree -s cyb.phy
На выход получили много файлов, но дерево будем строить по файлу cyb.phy.treefile

Рис. 3. Дерево, построенное программой IQ-Tree по аминокислотным последовательностям CYB, с помощью метода ML, укорененное в Munmu
Сравнение деревьев
В качестве организма для укоренение дерева был выбран Muntiacus muntjak, так как эволюционно эти животные считаются наиболее древними среди сем. Оленевые[1].
Несложно заметить, что приведенные деревья, построенные разными методами (рис. 1 и 2 - дистанционным методом ME, рис.3 - символьным методом ML) практически идентичные, и виды животных на них сгруппированы одинаково.
Ошибочно на деревьях расположен вид Hydropotes inermis (HYDIN), который систематически принадлежит отдельному подсемейству Hydropotinae, а в нашем случае сгруппирован с Axis axis из другого подсемейства. Помимо этого ошибочно расположен род Capreolus (CAPCA, CAPPY),
который формирует вместе с ODOHE и ALCAA подсемейство Odocoileinae. В остальном виды сгруппировались по систематике, однако клад в нашей реконструкции получилось больше,
что связано с неразрешенностью систематического дерева из прошлого практикума.