Нахождение паралогов и ортологов
Составление списка гомологичных белков
Из отдела Pseudomonadota были выбраны 7 представителей AGRFC - Agrobacterium fabrum, ACICJ - Acidiphilium cryptum, BRUSU - Brucella suis, BARHE - Bartonella henselae, BURMA - Burkholderia mallei, BORPE - Bordetella pertussis, AROAE - Aromatoleum aromaticum (Далее будут использоваться только буквенные сокращения).
Из их протеомов была составлена библиотека, в которой мы потом с помощью blastp искали гомологи белка CLPX_ECOL (ATP-dependent Clp protease ATP-binding subunit ClpX).
Для поиска использовались следующие команды:
blastp -db bacteria_db -query proteom.fasta -out results.txt -outfmt 7 -evalue 1e-4
Получили следующие находки: results
Построение дерева
Для полученных находок были скачаны fasta последовательности, объеденены в один файл и выровнены с помощью программы muscle. Далее полученное выравнивание с помощью написанной программы было переведено в формат phylip-relaxed, после чего было построено дерево с помощью программы fastme:
fastme -p -i input.phy -o output -b 100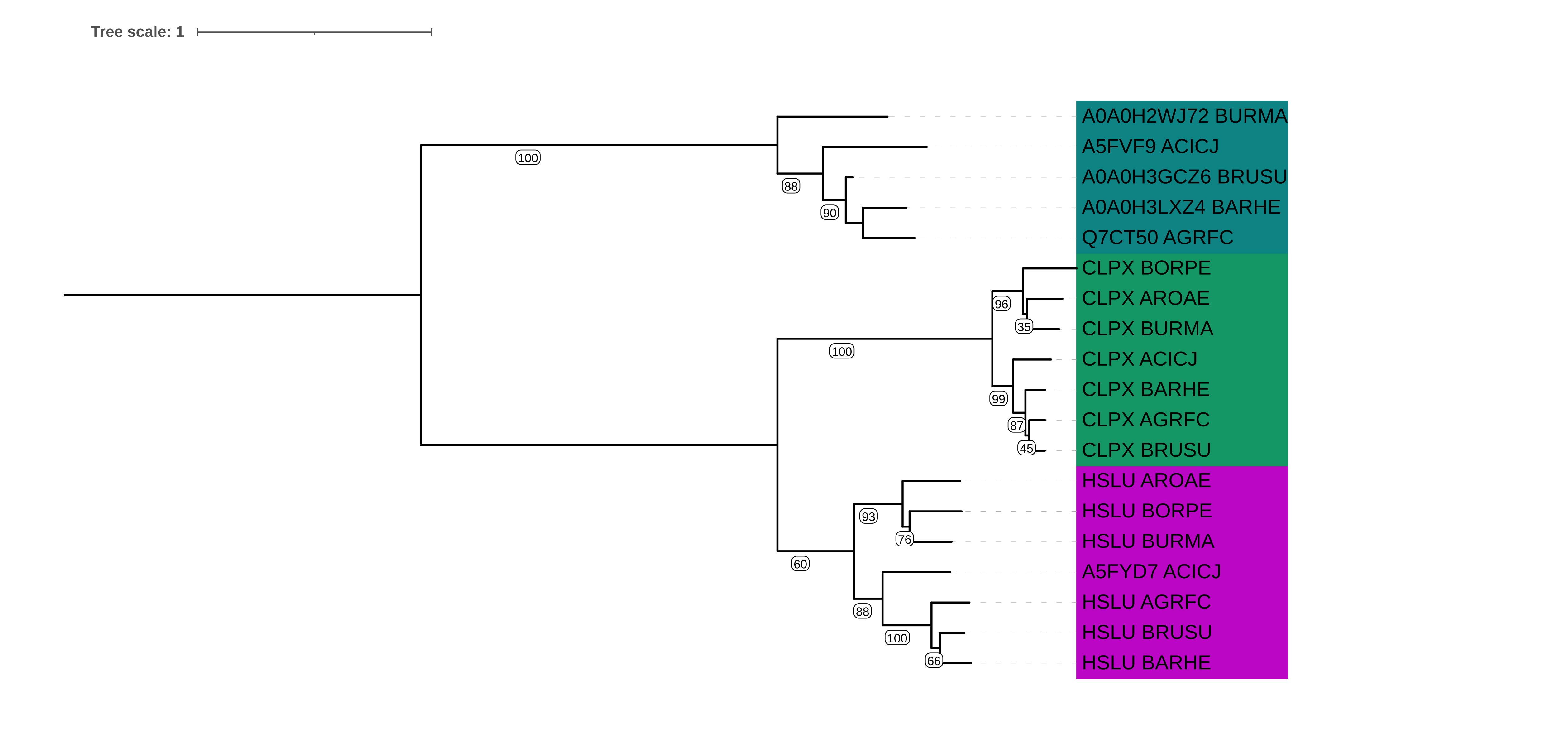
Рис. 1. Дерево построенное по аминокислотной последовательности гомлогов белка CLPX_ECOL, с помощью программы fastme, использующей метод ME, оценивающее эволюционное расстояние с помощью модели LG, укорененное в среднюю ветвь и с бутстрепом 100, разными цветами выделены белки ортологи
По данному построению можно к примеру выделить пары паралогов: CLPX_BURMA - HSLU_BURMA, Q7CT50_AGRFC - CLPX_AGRFC и HSLU_AROAE - CLPX_AROAE,
а также пары ортологов:
CLPX_BORPE - CLPX_AROAE, HSLU_BRUSU - HSLU_BARHE и CLPX_BARHE - CLPX_AGRFC.
Формула Newick для рис. 1. : Newick
Далее проводился анализ, насколько корректно группы ортологов отражают филогению выбранных видов
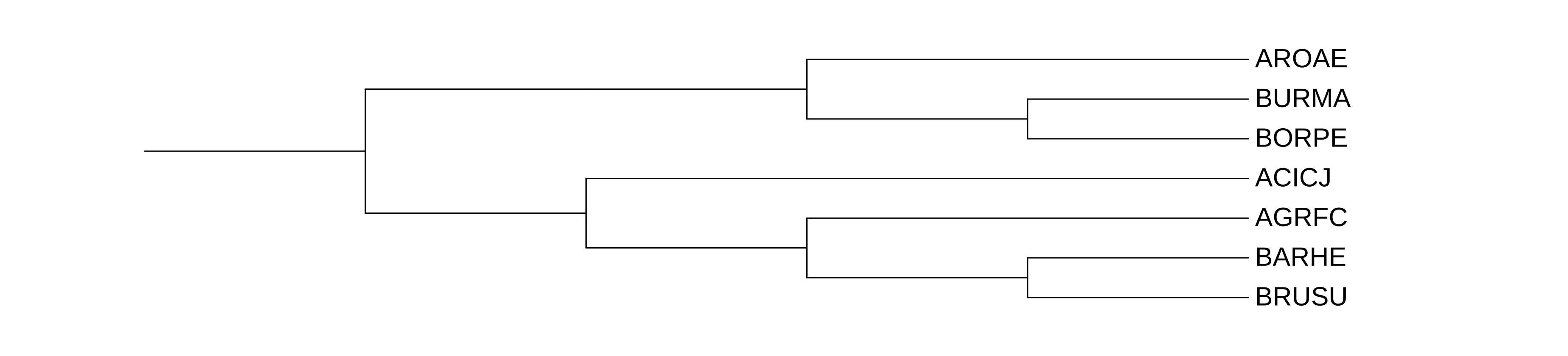
Рис. 2. Верная филогения для выбранных видов
 Рис. 3. Дерево как и на рис. 1., но с свернутыми ветвями. В группе CLPX (ATP-dependent Clp protease ATP-binding subunit ClpX) и HSLU (ATP-dependent protease ATPase subunit HslU) представлены все выбранные виды, в группе темно-бирюзового цветы, отвечающей ортологом белка (ATP-dependent zinc metalloprotease FtsH) отсутвуют виды AROAE и BORPE
Рис. 3. Дерево как и на рис. 1., но с свернутыми ветвями. В группе CLPX (ATP-dependent Clp protease ATP-binding subunit ClpX) и HSLU (ATP-dependent protease ATPase subunit HslU) представлены все выбранные виды, в группе темно-бирюзового цветы, отвечающей ортологом белка (ATP-dependent zinc metalloprotease FtsH) отсутвуют виды AROAE и BORPE
Если сравнить рис. 1. и рис. 2., то можно заметить, что группы белков HSLU точно отражает филогинию бактерий, группа CLPX схожа с филогенией, однако вид AGRFC ближе к BRUSU, чем вид BARHE, что неверно. Помимо этого AROAE поменялся местами с BORPE, что тоже неверно. Третья группа совпадает с филогенией, за исключением отсутсвия в ней белков, пренадлежащих двум отсутствующим видам.
Подводя итог, можно сделать вывод, что в целом группы ортологов с неплохой точностью описывают филогению бактерий, некоторые расхождения можно связать с ходом эволюции конкретно выбранных белков. Не ясным остается отсутствие белков ATP-dependent zinc metalloprotease FtsH у видов AROAE и BORPE, что может быть связано с вторичной утратой этих белков, либо с последующим горизонтальным переносам этого гена виду BURMA от родственных видов.